Изобретение относится к медицинской микробиологии, в частности к молекулярному типированию средневекового биовара основного подвида штаммов Yersinia pestis из природных очагов Прикаспия и сопредельных очагов чумы, и может быть использовано в научно-исследовательских и практических учреждениях Роспотребнадзора.
Бактерия Y. pestis является возбудителем зоонозной природно-очаговой особо опасной инфекционной болезни с трансмиссивным механизмом передачи возбудителя -чумы, до сих представляющей угрозу в области общественного здравоохранения. К основному подвиду Y. pestis, вирулентному для человека, относят четыре биовара: античный, средневековый, восточный и интермедиум. Масштабные молекулярно-генетические исследования показали, что на территории Российской Федерации и других стран СНГ наибольшее распространение имеет средневековый биовар основного подвида Y. pestis. Он циркулирует в 7 из 11 природных очагов чумы на территории РФ и в большинстве очагов стран СНГ, и занимает 93,3% от общей территории этих природных очагов. Также он встречается в природных очагах чумы Китая, Монголии, Ирана и Индии. Эти штаммы отличаются экологической пластичностью и существуют в очагах различного типа: пустынных, полупустынных, горных, высокогорных, равнинных, в том числе и с высокой степенью аридности, где не циркулируют другие биовары и подвиды Y. pestis. Штаммы средневекового биовара являются высоко вирулентными и эпидемически значимыми.
Наибольший ареал распространения получила ветвь 2.MED1 средневекового биовара. Она циркулирует в 33 автономных природных очагах: площадь природных очагов чумы сусликового типа составляет 221347 км2; песчаночьего типа - 1728676 км2; сурочьего типа - 18442 км2. В начале XX века в очагах Северного и Северо-Западного Прикаспия ветвь 2.MED1 циркулировала совместно с генетически близкой ветвью средневекового биовара 2.MED4. Установлено, что штаммы этих двух филогенетических линий Y. pestis средневекового биовара - 2.MED1 и 2.MED4, являлись этиологическими агентами вспышек чумы в северной части Прикаспия.
Высокая вирулентность и широкая распространенность средневекового биовара основного подвида возбудителя чумы требуют изучения геномного портрета его штаммов для разработки эффективных методов генотипирования и повышения эффективности молекулярно-эпидемиологического мониторинга очагов чумы. Также отмечено сохранение в текущем десятилетии разнонаправленной тенденции в динамике эпизоотической активности природных очагов стран СНГ с циркуляцией штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1. Решение проблемы дифференциации штаммов средневекового биовара от штаммов других биоваров и подвидов, а также внутрибиоварной дифференциации средневековых штаммов важно прежде всего с практической точки зрения. Разделение штаммов, отличающихся по вирулентности, по географическому региону и очагу происхождения, необходимо для проведения молекулярной экспертизы вспышек или отдельных случаев чумы. В отношении генетически мономорфного средневекового биовара эффективным методом является генотипирование по уникальным единичным полиморфным нуклеотидам (SNPs), которые являются распространенными генетическими маркерами в бактериальном геноме. Метод SNP-генотипирования позволяет выявлять однонуклеотидные полиморфизмы, характеризующиеся эволюционной стабильностью, что делает их кандидатными маркерами для молекулярного типирования и паспортизации природных очагов высоковирулентного средневекового биовара Y. pestis. Установление SNP-генотипов штаммов средневекового биовара Y. pestis, выделенных более чем за столетний период в очагах Прикаспийского региона, создает предпосылки для создания канонического SNP-профиля (canSNP) для молекулярно-генетической детализации паспортизации очагов, в которых циркулирует этот высоковирулентный биовар. Полученные результаты могут быть использованы при эпидемиологическом расследовании случаев чумы, а также возможных актов биотерроризма.
Выявление маркерного SNP возможно с помощью проведения фрагментного секвенирования полиморфного участка генома. Данный метод обеспечивает глубокий уровень дифференциации исследуемых штаммов, позволяя различить штаммы близкородственных генетических популяций по филогеографическому принципу. Разработка способа идентификации SNP-генотипов возбудителя чумы средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру значительно повысит эффективность молекулярно-эпидемиологического мониторинга, эпидемиологического расследования вспышек и случаев заноса штаммов возбудителя чумы на территорию РФ. Также определение основных генотипов, характерных для территорий Северного и Северо-Западного Прикаспия, необходимо для установления источника и региона происхождения возбудителя, определения путей заноса инфекции, проведения молекулярной экспертизы случаев и вспышек чумы, а также для проведения молекулярно-генетической паспортизации природных очагов этого особо опасного заболевания.
К настоящему времени существуют много способов молекулярно-генетической индикации и идентификации штаммов возбудителя чумы методами ПЦР с электрофоретическим и гибридизационно-флуоресцентным учетом результатов в режиме реального времени (ПЦР-РВ).
Для разделения штаммов Y. pestis средневекового и античного биоваров известен способ, описанный в патенте RU №2496882 (опубл. 27.10.2013, Бюл. №30). Он основан на использовании ПЦР с электрофоретическим учетом результатов. Однако, этот метод не предлагает способа внутрибиоварной дифференциации штаммов средневекового биовара на SNP-генотипы ветвей 2.MED1 и 2.MED4.
Опубликован способ дифференциации биоваров и геновариантов штаммов Y. pestis основного подвида с помощью полимеразной цепной реакции (патент RU №2565554, опубл. 20.10.2015 Бюл. №29). Этот способ предназначен для разделения биоваров основного подвида и отдельных популяций штаммов Y. pestis, но не для дифференциации филогеографических популяций средневекового биовара ветвей 2.MED1 и 2.MED4.
Известен способ проведения внутривидовой дифференциации типичных и атипичных штаммов Y. pestis средневекового биовара методом ПЦР с гибридизационно-флуоресцентным учетом результатов (Патент RU №2550257, опубл. 10.05.2015 Бюл. №13). Способ предназначен для разделения штаммов основного подвида средневекового биовара, но не позволяет разделять штаммы по принадлежности к филогеографическим популяциям средневекового биовара 2.MED1 и 2.MED4 возбудителя чумы из очагов Прикаспия.
Разработан способ подвидовой дифференциации штаммов возбудителя чумы методом полимеразной цепной реакции (патент RU №2552611, опубл. 10.06.2015 Бюл. №16), основанный на использовании метода ПЦР с электрофоретическим учетом результатов. Однако и этот способ не обеспечивает проведение внутривидовой дифференциацию штаммов возбудителя чумы средневекового биовара по их принадлежности к SNP-генотипам.
Известен «Способ детекции чумного микроба и набор реагентов для его осуществления» (патент RU №2796820, опубл. 29.05.2023 Бюл. №16). В нем предложен способ детекции чумного микроба, основанный на магнитоуправляемой сепарации бактерий вида Y. pestis с использованием набора иммуномагнитных частиц magF19, с последующим определением бактерий вида Y. pestis методом петлевой изотермической амплификации. Этот способ не предназначен для проведения дифференциации штаммов Y. pestis средневекового биовара по принадлежности к филогеографическим популяциям очагов чумы Прикаспия.
В патенте RU №2621869 (Опубл. 07.06.2017 Бюл. №16) представлен способ подвидовой дифференциации штаммов возбудителя чумы методом полимеразной цепной реакции с гибридизационно-флуоресцентным учетом результатов в режиме реального времени. Описанный способ позволяет проводить подвидовую дифференциацию штаммов Y. pestis, но не дает возможности разделять штаммы по их принадлежности к средневековому биовару и SNP-генотипам филогенетических ветвей 2.MED1 и 2.MED4.
Известен способ дифференциации штаммов Y. pestis основного и неосновных подвидов методом ПЦР в режиме реального времени (RU 2642273, опубл. 24.01.2018, Бюл. №3). Способ предусматривает выделение хромосомной ДНК из исследуемого материала, постановку ПЦР со специфическими праймерами и аллель-специфическими зондами. Способ обеспечивает разделение Y. pestis основного и неосновных подвидов, но не решает проблемы внутрибиоварной дифференциации чумного микроба и ветвей 2.MED1 и 2.MED4 по принадлежности к SNP-генотипам.
Патентное изобретение RU №2684231 (Опубл. 04.04.2019 Бюл. №10) «Способ дифференциации штаммов Y. pestis средневекового биовара по филогенетической принадлежности методом ПЦР с электрофоретическим учетом результатов» и RU №2705813 (Опубл. 12.11.2019 Бюл. №32) с гибридизационно-флуоресцентным учетом результатов позволяет отнести штаммы средневекового биовара к конкретной филогенетической ветви средневекового биовара (2.MED0, 2.MED1, 2.MED2, 2.MED3), но не позволяет идентифицировать штаммы филогенетической ветви 2.MED4 и SNP-генотипы филогенетических ветвей 2.MED1 и 2.MED4.
Способ внутривидовой дифференциации штаммов возбудителя чумы описан в патенте RU №2737775 (Опубл. 02.12.2020 Бюл. №34). При помощи указанного способа, возможно разделение штаммов Y. pestis и Y. pseudotuberculosis с дальнейшей дифференциацией штаммов Y. pestis по их принадлежности к основному и центральноазиатскому подвидам методом мультиплексной ПЦР. В тоже время этот способ не предусматривает определение принадлежности штаммов Y. pestis к конкретными филогенетическим ветвям и генотипам средневекового биовара.
Зарегистрирован способ индикации и идентификации штаммов возбудителя чумы по их принадлежности к виду Y. pestis, к подвидам, биоварам, филогенетическим ветвям (0.ANT, l.ANT, 2.ANT, 2.MED, 2.MED0, l.ORI, 0.РЕ5, 0.РЕ4) и по наличию генов основных факторов патогенности методом ДНК-чипа (RU №2734636 опубл. 21.10.2020 Бюл. №30). Однако этот способ не позволяет определять принадлежность штаммов к филогенетическим ветвям, таким как 2.MED1 и 2.MED4.
В патенте RU №2767371 (Опубл. 17.03.2022 Бюл. №8) описан способ дифференциации штаммов Y. pestis путем молекулярно-генетического типирования с использованием в качестве генетических маркеров IS-элементов. Данный метод обеспечивает дифференциацию штаммов Y. pestis по их генетическим группам на основные и неосновные подвиды, однако не предусматривает определение принадлежности штаммов к конкретным филогенетическим ветвям и генотипам средневекового биовара.
Разработан «Способ определения филогенетической принадлежности штаммов Yersinia pestis основного подвида методом аллель-специфической ПЦР в режиме реального времени» (RU №2799415 РФ, Опубл. 05.07.2023, Бюл. №19). Способ обеспечивает быструю и надежную идентификацию штаммов Y. pestis по их принадлежности к филогенетическим ветвям основного подвида 0.ANT1, 0.ANT2, 0.ANT3, 0.ANT5, 3.ANT, 4.ANT, 2.MED1, 2.MED2, 2.MED3, 2.MED4, l.ORI1, 1.ORI2, 1.ORI3 методом аллель-специфической ПЦР-РВ, который предусматривает проведение 28 моноплексных аллель-специфических ПЦР-РВ с двумя вариантами прямого праймера с последующей дифференциацией штаммов по наличию и отсутствию сигналов флуоресценции по маркерным SNPs. Но данный метод не предназначен для определения генотипов отдельных филогеографических популяций 2.MED1 и 2.MED4.
Технический результат заключается в обеспечении надежной идентификации SNP-генотипов филогенетических ветвей 2.MED1 и 2.MED4 средневекового биовара, распространенных на территории природных очагов чумы Северного и Северо-Западного Прикаспия.
Технический результат изобретения достигается способом идентификации SNP-генотипов, определяемых полиморфизмом единичных нуклеотидов 24 генов, характерных для штаммов средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4 возбудителя чумы, которые выделялись в различные периоды эпизоотической активности природных очагов на территории Прикаспийского региона методом секвенирования по Сэнгеру, который предусматривает проведение моноплексных полимеразных цепных реакций (ПЦР) для каждой мишени с уникальными праймерами и последующим проведением секвенирования по Сэнгеру и установлением SNP-генотипа исследуемого штамма.
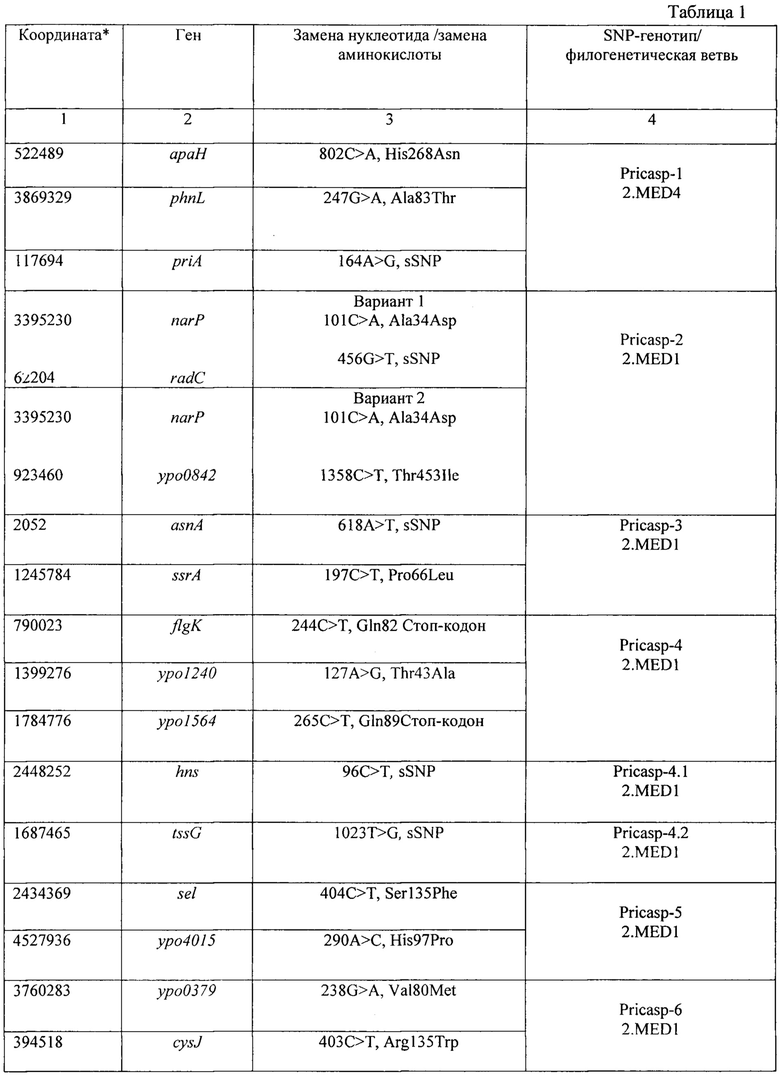
Координаты SNPs мишеней (названия и координаты даны по номенклатуре генома штамма Y. pestis CO92, номер доступа в NCBI GenBank NC_003143), использованных в разработанном способе идентификации SNP-генотипов возбудителя чумы средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру указаны в табл. 1. Заявляемый способ осуществляют следующим образом.
Выделение ДНК исследуемого штамма чумного микроба проводят по стандартной методике в соответствии с МУ 1.3.2569-09 «Организация работ лабораторий, использующих методы амплификации нуклеиновых кислот при работе с материалом, содержащим микроорганизмы I-IV групп патогенности».
Полимеразную цепную реакцию проводят с использованием сконструированных праймеров (SEQ ID NO: 1-24) в 24 моноплексных ПЦР в отдельных пробирках. Олигонуклеотидные праймеры, применяемые для амплификации полиморфного участка в ПЦР, рассчитаны на основе нуклеотидных последовательностей штаммов Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143.1) и KIM10 (номер доступа в NCBI GenBank NC_004088.1). С помощью указанных праймеров в ПЦР проводят амплификацию 24 ДНК-мишеней, по которым определяют принадлежность к девяти SNP-генотипам, характерным для штаммов средневекового биовара основного подвида Y. pestis из очагов Северного и Северо-Западного Прикаспия: «Pricasp-1» (араН, phnL, priA), «Pricasp-2» (narP, radC, ypo0842), «Pricasp-3» (asnA, ssrA), «Pricasp-4» (flgK, ypo1240, ypo1564), «Pricasp-4.1» (hns), «Pricasp-4.2» (tssG), «Pricasp-5» (sel, ypo4015), «Pricasp-6» (ypo0379, cysJ, gltB), «Pricasp-7» (YPO_RS18685, YPO_RS21620), «Pricasp-8» (уро0033, ptsP, selenide), «Pricasp-9» (YPO_RS09555).
Для проведения ПЦР применяют следующие условия реакции:
для мишеней генотипа «Pricasp-3», «Pricasp-4», «Pricasp-4.1», «Pricasp-4.2», «Pricasp-5» - денатурация - 95°C - 10 мин; циклирование (40 циклов) - 95°С - 20 с, 59°С - 40 с, 72°С - 25 с, финальная элонгация 1 мин.
для мишеней «Pricasp-1», «Pricasp-2», «Pricasp-5», «Pricasp-6», «Pricasp-9»: денатурация - 95°C - 10 мин; циклирование (40 циклов) - 95°С - 20 с, 60°С - 30 с, 72°С - 20 с, финальная элонгация 1 мин.
для мишеней «Pricasp-7», «Pricasp-8»: денатурация - 95°С - 10 мин; циклирование (40 циклов) - 95°С - 15 с, 58°С - 35 с, 72°С - 20 с, финальная элонгация 1 мин.
Продукты, полученные в ПЦР, визуализируют методом электрофореза в 1,5% агарозном геле, приготовленном на 1xTAE с добавлением 0,5 мкг/мл бромида этидия, и последующего просмотра в УФ-свете при длине волны 310 нм. К 5 мкл полученного амплификата добавляют 1 мкл красителя, вносят в лунки геля и задают напряжение 10-15 В/см. Электрофоретическое разделение продолжают до прохождения красителем около 4/5 длины геля. При просмотре в УФ-свете фрагменты анализируемой ДНК проявляются в виде оранжево-красных полос, размеры которых должны соответствовать фрагментам (100-300 пн.). Наличие этого этапа желательно для подтверждения качества ампликона, полученного на этапе ПЦР амплификации.
Далее оставшуюся ПЦР-смесь с ампликонами подготавливают для проведения автоматического секвенирования. На первом этапе проводят очистку продуктов ПЦР с помощью ферментов - Exonuclease I (Escherichia coli) и щелочная фосфатаза SAP. Готовят смесь реагентов на один ПЦР-образец: 11,7 мкл деионизованной воды, 2 мкл буфера для ПЦР (10Х, рН 8-8,5), 1 мкл фосфотазы и 0,3 мкл экзонуклеазы. Полученную смесь перемешивают, центрифугируют для осаждения капель со стенок пробирок и инкубируют при 37°С в течение 30 мин, а затем - при 85°С в течение 10 мин. Очищенные таким образом амликоны готовы к проведению следующего этапа. Для получения меченых ампликонов с использованием реакционной смеси Brilliant Dye Terminator V 3.1 готовят реакционную смесь. Состав смеси зависит от длины ампликона. Если длина фрагмента от 100 до 300 н.п., то состав смеси будет таким: 0,3 мкл Brilliant Dye Terminator V 3.1, 2,0 мкл 5× буфера для секвенирования, праймер до концентрации 2-3 пкмоль/мкл, 1 мкл очищенного ампликона и деионизованной воды до конечного объема 10 мкл.
Амплификацию проводят в течение 35 циклов, каждый из которых состоит из трех этапов и одноразовой предварительной денатурации ампликонов:
3 мин при 96°С (одноразовая предварительная денатурация ампликонов),
Далее циклический процесс из трех этапов:
30 с при 96°С (денатурация ампликонов),
10 с при 45-58°С (отжиг праймеров),
2 мин при 60°С (синтез комплементарной цепи).
Для очистки к 10 мкл ПЦР-продукта добавляют 40 мкл смеси следующего состава: 1,5 мкл 3М ацетата натрия, 31,3 мкл 96% этанола и 7,2 мкл деионизованной воды. Смесь перемешивают и инкубируют при температуре +4°С в течение 40-60 мин.
Образцы центрифугируют с охлаждением (+4°С) в течение 15 мин при 4000 g. Супернатант удаляют. К осадку (он обычно не видим) добавляют 200 мкл 70% этанола, перемешивают и центрифугируют с охлаждением (+4°С) в течение 10 мин при 4000 g. Супернатант удаляют, осадок высушивают при температуре 50-55°С в течение 10-15 мин до полного испарения спирта. В пробирки с очищенными образцами добавляют по 14 мкл формамида, перемешивают, инкубируют 3-4 мин при 95-100°С, после чего сразу помещают на ледяную баню на 2-3 мин.
Далее подготовленные образцы секвенируют на платформе «ABI PRISM 3500XL» (Applied Biosystems, США), используя полимер РОР-7 для 3500 /3500xL и капилляры длиной 50 см. (или аналогичной платформе для секвенирования по Сэнгеру). Анализ полученных последовательностей проводят при помощи программы 3500 Series Data Collection Software, оценку гомологии можно проводить с помощью пакета программ Mega X (или UGENE, SeaView 5.0 и т.д.).
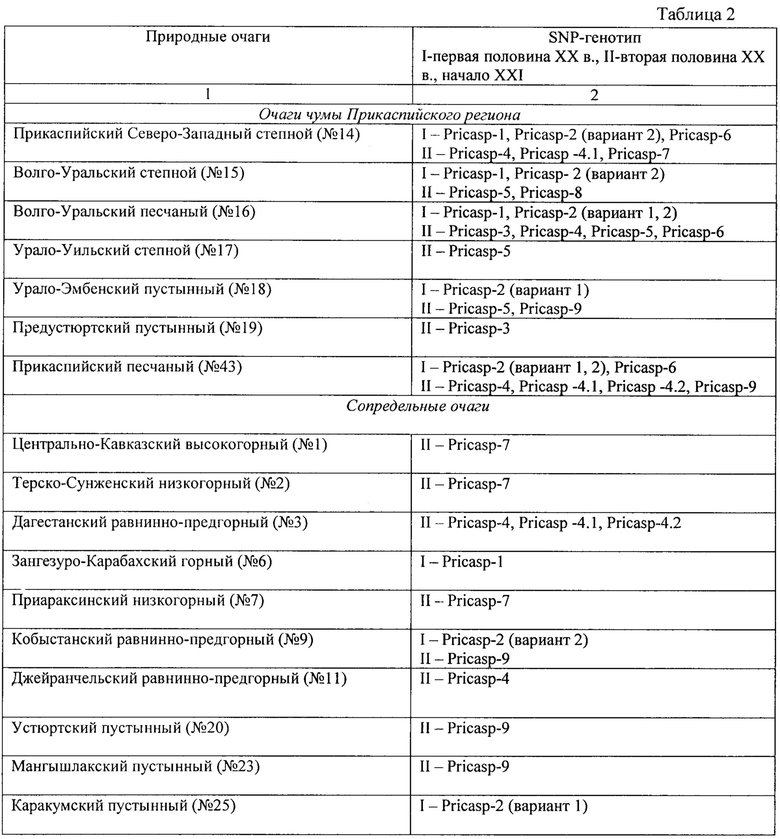
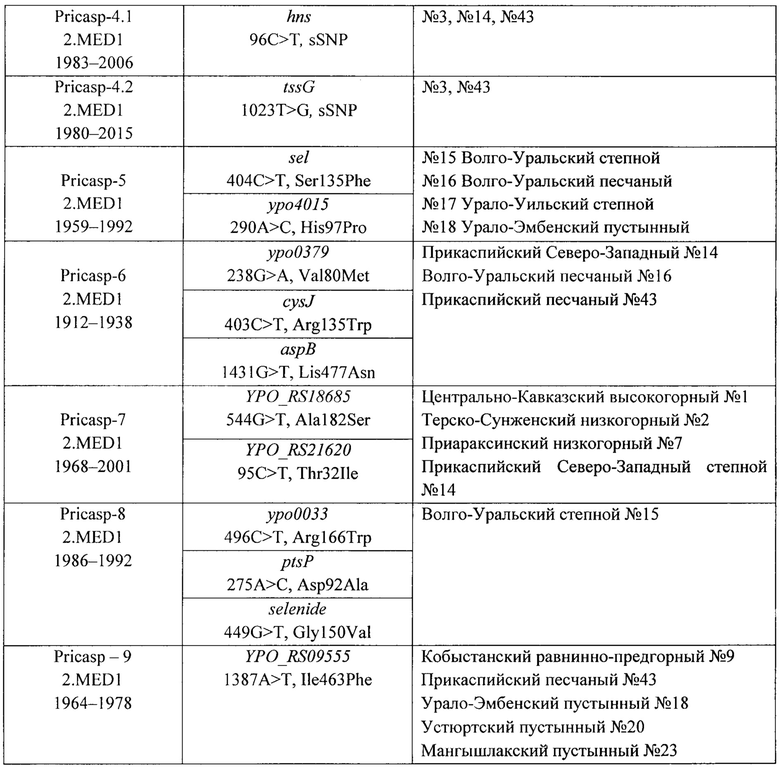
Принадлежность исследуемого штамма чумного микроба из Прикаспийского региона и сопредельных очагов чумы к конкретному геноварианту Pricasp устанавливают по результатам данных фрагментного секвенирования по наличию маркерных SNPs в указанной позиции гена (по эталонному геному CO92, AL590842.1) по табл. 3 учета результатов. Полученный фрагмент локуса анализируют с помощью программы MEGA X (или аналогичной программы, принимающей файлы формата fasta). По наличию маркерного SNP в указанной позиции локуса определяют принадлежность исследуемого штамма Y. pestis к конкретному геноварианту с одновременным определением его филогеографической принадлежности. На фигуре показаны результаты фрагментного секвенирования выборки штаммов Y. pestis филогенетических ветвей 2.MED1 и 2.MED4. Показана маркерная нуклеотидная замена С→Т в позиции 248 в гене flgK генотипа Pricasp-4 (координата по геному референсного штамма Y. pestis CO92 - 790023) филогенетической линии 2.MED1.
Специфичность сконструированных праймеров проверена на выборке из 190 штаммов Y. pestis, выделенных в 1912-2015 гг. от носителей, переносчиков и человека на территории 17-ти природных очагов чумы Прикаспия, Кавказа и Центральной Азии (их филогенетическая принадлежность проверена методом полногеномного SNP-анализа). В качестве контроля также исследовали полногеномные последовательности 8 штаммов Y. pestis других филогенетических ветвей из базы данных NCBI Genbank: Pestoides А (0.РЕ4а, NZ_ACNT00000000), Pestoides F (0.PE2. NC_009381), 620024 (0.PE7, ADPM00000000), CO92 (1.ORI1, AL590842.1), 351001 (2.ANT2, ADPF00000000), 91 (2.MED2, ADPU00000000), CMCC125002 (2.MED3, ADQN00000000), KIM10 (2.MED1, AE009952.1). Специфичность праймеров и подобранных мишеней также оценивалась с помощью алгоритма BLAST по всем имеющимся геномам Y. pestis в базе данных NCBI GenBank.
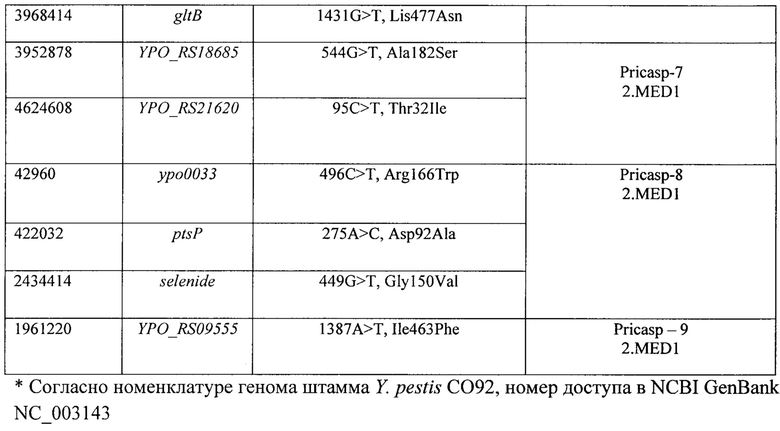
С помощью предлагаемого способа идентификации SNP-генотипов штаммов средневекового биовара основного подвида Y. pestis из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру установлена принадлежность 176 штаммов к SNP-генотипам: Pricasp-1 - 18 шт., Pricasp-2 - 20 шт., Pricasp-3 - 6 шт., Pricasp-4 (включая 4.1+4.2) - 41 шт., Pricasp-5 - 48 шт., Pricasp-6 - 14 шт., Pricasp-7 - 12 шт., Pricasp-8 - 9 шт., Pricasp-9 - 8 шт., и определено распространение филогеографических популяций SNP-генотипов штаммов Y. pestis средневекового биовара основного подвида, указанное в таблице 2 «SNP-профиль, установленный для штаммов Y. pestis средневекового биовара из очагов Северного и Северо-Западного Прикаспия периода 1912-2015 гг.».
Сущность изобретения подтверждается следующими примерами.
Пример 1. Идентификация SNP-генотипа «Pricasp-1» штаммов средневекового биовара филогенетической ветви 2.MED4 Y. pestis из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Экстракцию ДНК исследуемого образца проводят с помощью коммерческих наборов для выделения ДНК. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, идентификация SNP-генотипа «Pricasp-1» (араН, phnL, priA) проводится следующим образом. В мишени «араН» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 802 наблюдается замена нуклеотида С>А (замена аминокислоты His268Asn); в мишени «phnL» в позиции гена 247 наблюдается замена нуклеотида G>A (Ala83Thr); в мишени «priA» в позиции гена 164 наблюдается замена нуклеотида A>G, которая является синонимичной и не приводит к замене аминокислоты. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Наличие всех трех мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-1» филогенетической ветви 2.MED4 основного подвида средневекового биовара Y. pestis. Этот генотип встречался на территории следующих очагов чумы: Прикаспийского Северо-Западного степного (№14), Волго-Уральского степного (№15), Волго-Уральского песчаного (№16), Зангезуро-Карабахского горного (№6) в период 1917-1950 гг.
Пример 2. Идентификация SNP-генотипа «Pricasp-2» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, идентификация SNP-генотипа «Pricasp-2» (narP, radC, уро0842) осуществляется следующим образом. Этот генотип представлен несколькими вариантами комбинации мишеней: общая SNP (narP), вариант 1 (narP+radC), вариант 2 (narP+YPO0842). В общей мишени «narP» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis С092 (номер доступа в NCBI GenBank NC_003143) в позиции гена 101 наблюдается замена нуклеотида С>А (Ala34Asp); в «radC» в позиции гена 456, присутствует синонимичная замена G>T; в мишени «YPO0842» в позиции гена 1358, наблюдается замена нуклеотида С>Т (Thr453Ile). Принадлежность к генотипу «Pricasp-2» определяется по наличию мутации в гене «narP». Далее проводится определение варианта генотипа «Pricasp-2». К варианту 1 относятся штаммы, у которых обнаружены специфические мутации в комбинации генов «narP»+«radC»; для варианта 2 характерны мутации в генах «narP»+«УРО0842». В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Штаммы этого генотипа встречались в период 1930-1954 гг. на территории следующих очагов чумы: Кобыстанском равнинно-предгорном (№9), Прикаспийском Северо-Западном степном (№14), Волго-Уральском степном (№15), Волго-Уральском песчаном (№16), Урало-Эмбенском пустынном (№18), Каракумском пустынном (№25), Прикаспийском песчаном (№43). Вариант 1 (narP+radC) распространен в указанных выше очагах: №16, №18, №25, №43; вариант 2 (narP+YPO0842): №9, №14, №15, №16, №43.
Пример 3. Идентификация SNP-генотипа «Pricasp-3» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, штаммы, относящиеся к SNP-генотипу «Pricasp-3» (asnA, ssrA) должны иметь следующие нуклеотидные замены. В мишени «asnA» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 618, наблюдается замена нуклеотида А>Т (синонимичная, sSNP); в мишени «ssrA» в позиции гена 197 наблюдается замена нуклеотида С>Т (Pro66Leu). Наличие специфических SNPs в генах «asnA» и «ssrA» указывает, что исследуемый штамм относится к генотипу «Pricasp-3» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. В период 1990-2002 гг.штаммы данного генотипа были выделены на территории Волго-Уральского песчаного (№16) и Предустюртского пустынного (№19) очагов чумы.
Пример 4. Идентификация SNP-генотипов «Pricasp-4», «Pricasp-4.1» и «Pricasp-4.2» штаммов Y. pestis филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Внутри генотипа «Pricasp-4» выделено еще два геноварианта «Pricasp-4.1» (hns), «Pricasp-4.2» (tssG), которые характеризуют локальные популяции на территории Северо-Западного Прикаспия. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, штаммы, относящиеся к SNP-генотипам «Pricasp-4» (flgK, уро1240, уро1564), «Pricasp-4.1» (hns), «Pricasp-4.2» (tssG) демонстрируют следующие результаты. По мишени «flgK» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 244 присутствует замена нуклеотида С>Т, приводящая к образованию стоп-кодона (Gln82Стоп-кодон); в мишени «уро1240» в позиции гена 127 наблюдается замена нуклеотида A>G (Thr43Ala); в мишени «уро1564» в позиции гена 265 наблюдается замена нуклеотида С>Т, которая приводит к образованию стоп-кодона (Gln89Стоп-кодон). Наличие всех трех мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-4» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. Далее проводят определение принадлежности к дополнительным геновариантам «Pricasp-4.1» и «Pricasp-4.2». По мишени «hns» в позиции гена 96 присутствует замена нуклеотида С>Т (sSNP), что характерно для штаммов, относящихся к генотипу «Pricasp-4.1». По мишени «tssG» в позиции гена 1023 наблюдается синонимичная замена T>G, характерная для штаммов генотипа «Pricasp-4.2». В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Генотип «Pricasp-4» выделялся в период 1979-2015 гг.в Дагестанском равнинно-предгорном (№3), Джейранчельском равнинно-предгорном (№11), Прикаспийском Северо-Западном (№14), Волго-Уральском песчаном (№16) и Прикаспийском песчаном (№43). Геновариант «Pricasp-4.1» выделялся в очагах №3, №14, №43 в период 1983-2006 гг.; геновариант «Pricasp-4.2» выделялся в очагах №3 и №43 в период 1980-2015 гг.
Пример 5. Идентификация SNP-генотипа «Pricasp-5» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, штаммы, относящиеся к SNP-генотипу «Pricasp-5» (sel, уро4015) имеют следующие результаты. В мишени «sel» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC 003143) в позиции гена 404 наблюдается замена нуклеотида С>Т (Ser135Phe); в мишени «уро4015» в позиции гена 290 наблюдается замена нуклеотида А>С (His97Pro). Наличие этих мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-5» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Генотип «Pricasp-5» встречался в период 1959-1992 в Волго-Уральском степном (№15), Волго-Уральском песчаном (№16), Урало-Уильском степном (№17), Урало-Эмбенском пустынном (№18) очагах чумы.
Пример 6. Идентификация SNP-генотипа «Pricasp-6» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, штаммы, относящиеся к SNP-генотипу «Pricasp-6» (уро0379, cysJ, gltB), показывают следующие результаты. В мишени «уро0379» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 238 наблюдается замена нуклеотида G>A (Val80Met); в мишени «cysJ» в позиции гена 403 наблюдается замена нуклеотида С>Т (Arg135Trp); в мишени «gltB» в позиции гена 1431 наблюдается замена нуклеотида G>T (Lis477Asn). Наличие всех трех мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-6» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Штаммы этого генотипа выделялись в период 1912-1938 гг. в Прикаспийском Северо-Западном степном (№14), Волго-Уральском песчаном (№16) и в Прикаспийском песчаном (№43).
Пример 7. Идентификация SNP-генотипа «Pricasp-7» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, у штаммов, относящихся к SNP-генотипу «Pricasp-7» (YPO_RS18685, YPO_RS21620), имеются следующие нуклеотидные замены. В мишени «YPO_RS18685» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 544 наблюдается замена нуклеотида G>T (Ala182Ser); в мишени «YPO_RS21620» в позиции гена 95 наблюдается замена нуклеотида С>Т (Thr32Ile). Наличие этих мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-7» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Штаммы этого генотипа выделялись в период 1968-2001 гг.в Центрально-Кавказском высокогорном (№1), Терско-Сунженском низкогорном (№2), Приараксинском низкогорном (№7), Прикаспийском Северо-Западном степном (№14) очагах чумы.
Пример 8. Идентификация SNP-генотипа «Pricasp-8» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, у штаммов, относящихся к SNP-генотипу «Pricasp-8» (уро0033, ptsP, selenide), имеются следующие нуклеотидные замены. В мишени «уро0033» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 496 наблюдается замена нуклеотида С>Т (Arg166Trp); в мишени «ptsP» в позиции гена 275 наблюдается замена нуклеотида А>С (Asp92Ala); в мишени «selenide» в позиции гена 449 наблюдается замена нуклеотида G>T (Gly150Val). Наличие всех трех мутаций указывает, что исследуемый штамм относится к генотипу «Pricasp-8» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. В период 1986-1992 гг. этот генотип встречался только у штаммов из Волго-Уральского степного очага чумы (№15).
Пример 9. Идентификация SNP-генотипа «Pricasp-9» штаммов Y. pestis средневекового биовара филогенетической ветви 2.MED1 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру
Исследование штамма Y. pestis проводят аналогично примеру №1. Моноплексные ПЦР осуществляют с праймерами (SEQ ID NO: 1-24), рассчитанными на ДНК мишени, которые составляют девять генотипов «Pricasp-1»-«Pricasp-9». При анализе ампликонов, полученных методом секвенирования по Сэнгеру, штаммы, относящиеся к SNP-генотипу «Pricasp-9» (YPO_RS09555), демонстрируют следующие результаты. В мишени «YPO_RS09555» при выравнивании полученного ампликона на референсную последовательность генома Y. pestis CO92 (номер доступа в NCBI GenBank NC_003143) в позиции гена 1387 наблюдается замена нуклеотида А>Т (Ile463Phe). Наличие данной мутации указывает, что исследуемый штамм относится к генотипу «Pricasp-9» филогенетической ветви 2.MED1 основного подвида средневекового биовара Y. pestis. В остальных ДНК мишенях полиморфные нуклеотиды не выявляются. Данный генотип характерен для штаммов возбудителя для Кобыстанского равнинно-предгорного (№9), Прикаспийского песчаного (№43), Урало-Эмбенского пустынного (№18), Устюртского пустынного (№20) и Мангышлакского пустынного (№23) очагов чумы и выделялся в период 1964-1978 гг.
Таким образом, применение предлагаемого способа идентификации SNP-генотипов штаммов Yersinia pestis средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4 из очагов Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру с использованием мишеней «Pricasp-1» (араН, phnL, priA), «Pricasp-2» (narP, radC, ypo0842), «Pricasp-3» (asnA, ssrA), «Pricasp-4» (flgK, ypo1240, ypo1564), «Pricasp-4.1» (hns), «Pricasp-4.2» (tssG), «Pricasp-5» (sel, ypo4015), «Pricasp-6» (ypo0379, cysJ, gltB), «Pricasp-7» (YPO_RS18685, YPO_RS21620), «Pricasp-8» (уро0033, ptsP, selenide), «Pricasp-9» (YPO_RS09555) обеспечивает определение геновариантов штаммов Y. pestis средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4, распространенных в природных очагах Северного и Северо-Западного Прикаспия, по маркерным полиморфным нуклеотидам SNPs, периоду выделения и географической принадлежности. Получение последовательностей генов с маркерными полиморфными нуклеотидами создает основу для создания канонического SNP-профиля (canSNP) для молекулярно-генетической детализации паспортизации очагов, в которых циркулирует этот высоковирулентный средневековый биовар основного подвида Y. pestis. Предлагаемый способ также может повысить эффективность эпидемиологического отслеживания происхождения геноварианта Y. pestis при проведении молекулярно-эпидемиологического мониторинга, а также будет полезен для создания баз данных генотипов штаммов Y. pestis природных очагов Прикаспия и сопредельных очагов чумы.
--->
<?xml version="1.0" encoding="UTF-8"?>
<!DOCTYPE ST26SequenceListing PUBLIC "-//WIPO//DTD Sequence Listing
1.3//EN" "ST26SequenceListing_V1_3.dtd">
<ST26SequenceListing dtdVersion="V1_3" fileName="Primers.xml"
softwareName="WIPO Sequence" softwareVersion="2.3.0"
productionDate="2023-12-25">
<ApplicationIdentification>
<IPOfficeCode>RU</IPOfficeCode>
<ApplicationNumberText></ApplicationNumberText>
<FilingDate>2023-12-25</FilingDate>
</ApplicationIdentification>
<ApplicantFileReference>1</ApplicantFileReference>
<ApplicantName languageCode="ru">Федеральное казенное учреждение
науки «Российский научно-исследовательский противочумный институт
«Микроб» Федеральной службы по надзору в сфере защиты прав
потребителей и благополучия человека</ApplicantName>
<ApplicantNameLatin>Federal State Institution of Science
"Russian Research Anti-Plague Institute "Microbe" of
the Federal Service for Supervision of Consumer Rights Protection and
Human Welfare</ApplicantNameLatin>
<InventionTitle languageCode="ru">Способ идентификации SNP-генотипов
возбудителя чумы средневекового биовара филогенетических ветвей
2.MED1 и 2.MED4 из очагов Северного и Северо-Западного Прикаспия
методом секвенирования по Сэнгеру</InventionTitle>
<SequenceTotalQuantity>48</SequenceTotalQuantity>
<SequenceData sequenceIDNumber="1">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q2">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gggaccacgggcaactaaa</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="2">
<INSDSeq>
<INSDSeq_length>17</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..17</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q4">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tggctgcctcgatgaat</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="3">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q6">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>acgctgctacgctccctcta</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="4">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q8">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tgactgacccaaccgaca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="5">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q10">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tcagccgttgcagcagtt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="6">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q12">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ggcgttatggattatggg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="7">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q14">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tcgtgttattcgccatgaag</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="8">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q16">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tcacctgcgtcgttatcaaa</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="9">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q18">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cgggggcaaagcattaca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="10">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q20">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cgtattggtgccgtcatcat</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="11">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q22">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>atcgttgacgaccatccg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="12">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q24">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ttttaacgtatccagcccg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="13">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q26">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>agatgctaaaggccgtgaac</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="14">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q28">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>atgtcgccgtttaatccag</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="15">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q30">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ggatggacacgctactgaca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="16">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q32">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>caaacgacgaaaactacgcac</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="17">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q34">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ccggttactcacgccagc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="18">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q36">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tcgcggcactgagagaggaa</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="19">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q38">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tgtcaggcgtcgctcatt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="20">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q40">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tggcgggataggtggtta</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="21">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q42">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ccgctccgctgccctatatca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="22">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q44">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>atcacgtaacggacgcggga</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="23">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q46">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ggtcgttaatgaacgccgcga</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="24">
<INSDSeq>
<INSDSeq_length>23</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..23</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q48">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tcagcggctgtacagtggacatt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="25">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q50">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tctggtgctgttgcgggtct</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="26">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q52">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ccgcagccactgagcaacaa</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="27">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q54">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gctattgctattttggggtgg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="28">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q56">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gggttcaggggcatcaat</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="29">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q58">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gaatgccagccgagcgactt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="30">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q60">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gctgtgcggtgtggtattga</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="31">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q62">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tggtgtctctcgcaatca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="32">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q64">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>agacggcaagcaggtgtt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="33">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q66">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cccatcaacttcacgctgt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="34">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q68">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tgggtgtggtgcgctatga</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="35">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q70">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gccgaaacagacaacgatct</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="36">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q72">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cgttgctgtaaccaaactgc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="37">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q74">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>taacggtgtgtataaagcggg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="38">
<INSDSeq>
<INSDSeq_length>22</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..22</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q76">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gcgtagtccataaccgtaaatc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="39">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q78">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tacgcggctttatctgtgtg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="40">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q80">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>caaatgctgctgtgatccg</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="41">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q82">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>taccggcattcaacacca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="42">
<INSDSeq>
<INSDSeq_length>19</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..19</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q84">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cgaacgattggaaacagct</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="43">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q86">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>gtgggagatggcaagagcgt</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="44">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q88">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tgcaagtgggctaacgaggc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="45">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q90">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ctattgctattttggggtggc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="46">
<INSDSeq>
<INSDSeq_length>18</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..18</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q92">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aagatgccaatgcccaat</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="47">
<INSDSeq>
<INSDSeq_length>21</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..21</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q94">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>acggctagctgtaccaccgtc</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="48">
<INSDSeq>
<INSDSeq_length>20</INSDSeq_length>
<INSDSeq_moltype>DNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..20</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>genomic DNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier id="q96">
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>Yersinia pestis</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>tgaggcgaataccagcggca</INSDSeq_sequence>
</INSDSeq>
</SequenceData>
</ST26SequenceListing>
<---
| название | год | авторы | номер документа |
|---|---|---|---|
| Способ определения филогенетической принадлежности штаммов Yersinia pestis основного подвида методом аллель-специфической ПЦР в режиме реального времени | 2022 |
|
RU2799415C1 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ ШТАММОВ Yersinia pestis СРЕДНЕВЕКОВОГО БИОВАРА ПО ФИЛОГЕНЕТИЧЕСКОЙ ПРИНАДЛЕЖНОСТИ МЕТОДОМ ПЦР С ЭЛЕКТРОФОРЕТИЧЕСКИМ УЧЕТОМ РЕЗУЛЬТАТОВ | 2018 |
|
RU2684231C1 |
| СПОСОБ ИДЕНТИФИКАЦИИ ШТАММОВ YERSINIA PESTIS СРЕДНЕВЕКОВОГО БИОВАРА С ПОСЛЕДУЮЩЕЙ ДИФФЕРЕНЦИАЦИЕЙ ПО ФИЛОГЕНЕТИЧЕСКОЙ ПРИНАДЛЕЖНОСТИ МЕТОДОМ ПОЛИМЕРАЗНОЙ ЦЕПНОЙ РЕАКЦИИ С ГИБРИДИЗАЦИОННО-ФЛУОРЕСЦЕНТНЫМ УЧЕТОМ РЕЗУЛЬТАТОВ | 2018 |
|
RU2705813C1 |
| СПОСОБ ОПРЕДЕЛЕНИЯ ГЕНОВАРИАНТОВ ШТАММОВ ВОЗБУДИТЕЛЯ ЧУМЫ МЕТОДОМ МУЛЬТИЛОКУСНОГО СЕКВЕНИРОВАНИЯ | 2014 |
|
RU2561469C1 |
| СПОСОБ ИНДИКАЦИИ И ИДЕНТИФИКАЦИИ ШТАММОВ ВОЗБУДИТЕЛЯ ЧУМЫ ПО ИХ ПРИНАДЛЕЖНОСТИ К ВИДУ YERSINIA PESTIS, К ПОДВИДАМ, БИОВАРАМ, ФИЛОГЕНЕТИЧЕСКИМ ВЕТВЯМ И ПО НАЛИЧИЮ ГЕНОВ ОСНОВНЫХ ФАКТОРОВ ПАТОГЕННОСТИ МЕТОДОМ ДНК-ЧИПА | 2020 |
|
RU2734636C1 |
| СПОСОБ ИДЕНТИФИКАЦИИ YERSINIA PESTIS И YERSINIA PSEUDOTUBERCULOSIS И ОДНОВРЕМЕННОЙ ДИФФЕРЕНЦИАЦИИ YERSINIA PESTIS ОСНОВНОГО И ЦЕНТРАЛЬНОАЗИАТСКОГО ПОДВИДОВ МЕТОДОМ МУЛЬТИПЛЕКСНОЙ ПЦР | 2020 |
|
RU2737775C1 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ ШТАММОВ YERSINIA PESTIS РАЗЛИЧНЫХ ПОДВИДОВ И БИОВАРОВ МЕТОДАМИ ПОЛИМЕРАЗНОЙ ЦЕПНОЙ РЕАКЦИИ И МУЛЬТИЛОКУСНОГО СИКВЕНС-ТИПИРОВАНИЯ | 2011 |
|
RU2471872C1 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ ШТАММОВ ВОЗБУДИТЕЛЯ ЧУМЫ ОСНОВНОГО ПОДВИДА СРЕДНЕВЕКОВОГО И АНТИЧНОГО БИОВАРОВ МЕТОДОМ ПОЛИМЕРАЗНОЙ ЦЕПНОЙ РЕАКЦИИ | 2012 |
|
RU2496882C2 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ ТИПИЧНЫХ И АТИПИЧНЫХ ШТАММОВ Yersinia pestis СРЕДНЕВЕКОВОГО БИОВАРА МЕТОДОМ ПЦР С ГИБРИДИЗАЦИОННО-ФЛУОРЕСЦЕНТНЫМ УЧЕТОМ РЕЗУЛЬТАТОВ | 2014 |
|
RU2550257C2 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ БИОВАРОВ И ГЕНОВАРИАНТОВ ШТАММОВ Yersinia pestis ОСНОВНОГО ПОДВИДА С ПОМОЩЬЮ ПОЛИМЕРАЗНОЙ ЦЕПНОЙ РЕАКЦИИ | 2014 |
|
RU2565554C2 |

Изобретение относится к области биотехнологии, в частности к молекулярному типированию средневекового биовара основного подвида Yersinia pestis из очагов Северного и Северо-Западного Прикаспия. Изобретение обеспечивает идентификацию геновариантов штаммов Y. pestis средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4, распространенных в природных очагах Северного и Северо-Западного Прикаспия, по маркерным полиморфным нуклеотидам SNPs. Получение последовательностей генов с маркерными полиморфными нуклеотидами создает основу для создания канонического SNP-профиля штаммов для молекулярно-генетической детализации паспортизации очагов, в которых циркулирует высоковирулентный средневековый биовар основного подвида Y. pestis. Предлагаемый способ повысит эффективность эпидемиологического отслеживания происхождения геноварианта средневекового биовара при проведении молекулярно-эпидемиологического мониторинга, а также будет использован для создания баз данных генотипов штаммов Y. pestis природных очагов Прикаспия и сопредельных очагов чумы. 1 ил., 3 табл., 9 пр.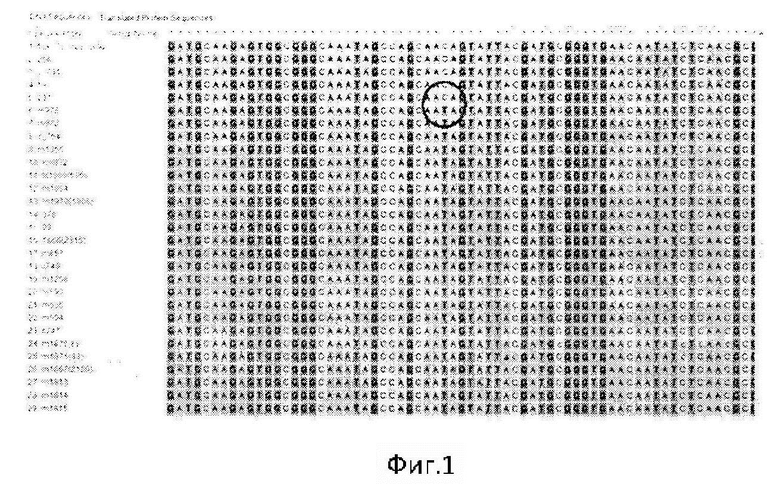
Способ идентификации SNP-генотипов возбудителя чумы средневекового биовара филогенетических ветвей 2.MED1 и 2.MED4 из природных очагов чумы Северного и Северо-Западного Прикаспия методом секвенирования по Сэнгеру, включающий выделение ДНК штамма, проведение моноплексных ПЦР с комплектом из 24 сконструированных пар праймеров: SEQ ID NO: 1-6 на ДНК-мишени генотипа «Pricasp-1» араН, phnL, priA; SEQ ID NO: 7-12 на ДНК-мишени генотипа «Pricasp-2» narP, radC, ypo0842; SEQ ID NO: 13-16 на ДНК-мишени генотипа «Pricasp-3» asnA, ssrA; SEQ ID NO: 17-22 на ДНК-мишени генотипа «Pricasp-4» flgK, ypo1240, ypo1564; SEQ ID NO: 23-24 на ДНК-мишень генотипа «Pricasp-4.1» hns; SEQ ID NO: 25-26 на ДНК-мишень генотипа «Pricasp-4.2» tssG; SEQ ID NO: 27-30 на ДНК-мишени генотипа «Pricasp-5» sel, ypo4015; SEQ ID NO: 31-36 на ДНК-мишени генотипа «Pricasp-6» ypo0379, cysJ, gltB; SEQ ID NO: 37-40 на ДНК-мишени генотипа «Pricasp-7» YPO_RS18685, YPO_RS21620; SEQ ID NO: 41-46 на ДНК-мишени генотипа «Pricasp-8» уро0033, ptsP, selenide; SEQ ID NO: 47-48 на ДНК-мишени генотипа «Pricasp-9» YPO_RS09555, получение ПЦР продуктов амплификации, их фрагментное секвенирование по Сэнгеру и проведение анализа нуклеотидной последовательности, при выравнивании с последовательностью референсного генома штамма Y. pestis С092 по файлу формата *.ƒasta для выявления полиморфного SNP по наличию маркерного нуклеотида SNP в ДНК-мишени устанавливают принадлежность исследуемого штамма к конкретному SNP-генотипу в соответствии с таблицей
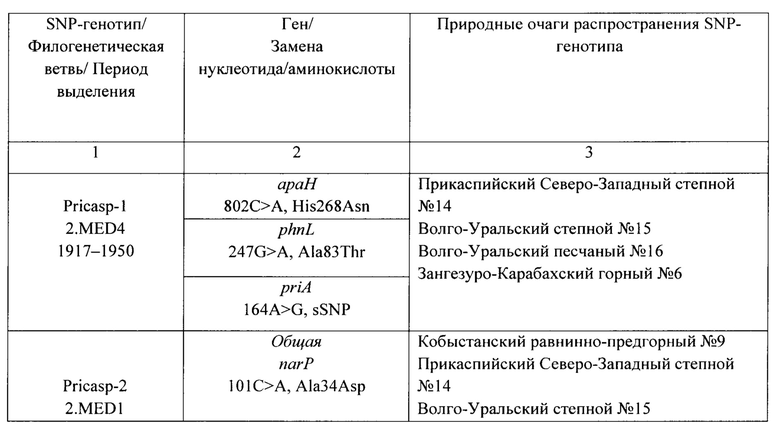
| БАЛЫКОВА А.Н | |||
| и др | |||
| SNP-профили штаммов Yersinia pestis средневекового биовара из очагов чумы Прикаспия, Проблемы особо опасных инфекций, 2022, Номер 4, стр | |||
| Механический грохот | 1922 |
|
SU41A1 |
| Способ определения филогенетической принадлежности штаммов Yersinia pestis основного подвида методом аллель-специфической ПЦР в режиме реального времени | 2022 |
|
RU2799415C1 |
| СПОСОБ ДИФФЕРЕНЦИАЦИИ ШТАММОВ Yersinia pestis СРЕДНЕВЕКОВОГО БИОВАРА ПО ФИЛОГЕНЕТИЧЕСКОЙ ПРИНАДЛЕЖНОСТИ МЕТОДОМ ПЦР С ЭЛЕКТРОФОРЕТИЧЕСКИМ УЧЕТОМ РЕЗУЛЬТАТОВ | 2018 |
|
RU2684231C1 |
| CN 110592245 A, 20.12.2019 | |||
| VOGLER A.J | |||
| et al | |||
| A review of methods for subtyping Yersinia pestis: From phenotypes to whole genome | |||
Авторы
Даты
2024-12-04—Публикация
2024-01-09—Подача