Изобретение относится к области генной инженерии и биотехнологии, а именно к числу средств направляющих РНК, которые могут быть использованы в системах CRISPR-Cas12 в составе рибонуклеопротеиновых комплексов для выявления (обнаружения, детекции) гена антибиотикоустойчивости bla-ТЕМ-1В, а также к диагностическим способам и наборам.
Изобретение позволяет in vitro выявлять единичные копии гена антибиотикоустойчивости bla-TEM-1В.
Направляющие РНК, описанные в настоящей заявке, могут быть использованы для детекции гена антибиотикоустойчивости bla-ТЕМ-1В после проведения специфической амплификации фрагментов гена антибиотикоустойчивости bla-ТЕМ-1В. Амплификация при этом может быть проведена различными способами, среди которых полимеразная цепная реакция (PCR); петлевая изотермическая амплификация (LAMP); геликаза-зависимая амплификация (HDA); рекомбиназа-опосредованная амплификация (RPA); амплификация со смещением цепи (SDA); амплификация, основанная на последовательности нуклеиновых кислот (NASBA); опосредованная транскрипцией амплификация (ТМА); амплификация, опосредованная никирующим ферментом (NEAR); круговая амплификация (RCA) и многие другие виды амплификации.
Направляющие РНК, описанные в настоящей заявке, могут быть использованы для разработки высокочувствительных и высокотехнологичных диагностических систем нового поколения на основе CRISPR технологий для совершенствования методов диагностики инфекционных заболеваний.
Для решения эпидемиологических задач по расшифровке вспышек инфекционных болезней, выявления и идентификации возбудителя, а также детекции специфических бактериальных генов необходимы разработка и внедрение в практику работы надзорных и мониторинговых служб современных технологий молекулярной эпидемиологии. Одной из таких технологий является использование элементов генетического редактирования системы CRISPR-Cas. Данная технология развивается достаточно эффективно в отношении создания средств лечения некоторых болезней, несмотря на ряд трудностей, связанных с возникновением непредвиденных мутаций. При углубленных исследованиях в области применения CRISPR-Cas системы, было выяснено, что она может быть использована для тонких диагностических процедур при выявлении возбудителя/ей инфекции у человека, а также их генотипирования.
В 2018 году было показано, что один из ферментов CRISPR системы - Cas12 после распознавания своей целевой ДНК-мишени начинает неспецифически гидролизовать одноцепочечную, а также двухцепочечную ДНК. Такое свойство Cas12 можно использовать в качестве индикатора присутствия определенной мишени, например, генома вируса или бактерии. Исследователи использовали это открытие для создания технологической платформы обнаружения нуклеиновых кислот, известной как DETECTR (DNA Endonuclease Targeted CRISPR Trans Reporter - ДНК-нацеленная эндонуклеаза CRISPR транс репортер). Впервые DETECTR была использована для выявления и генотипирования вируса папилломы человека (HPV). Предложенная платформа объединяет нуклеазу Cas12a, ее направляющую РНК, специфичную к нуклеиновой кислоте HPV, флуоресцентную репортерную молекулу. Технология DETECTR используется для обнаружения целевой ДНК-мишени после предварительной амплификации [J.S. Chen, Е. Ma, L.B. Harrington, М. Da Costa, X. Tian, J.M. Palefsky, J.A. Doudna, CRISPR-Cas 12a target binding unleashes indiscriminate single-stranded DNase activity, Science 360(6387) (2018) 436-439].
He менее важным приложением системы CRISPR-Cas является идентификация бактериальных патогенов и детекция специфических бактериальных генов. Так, например, с помощью платформы SHERLOCK удалось корректно генотипировать ряд штаммов Escherichia coli и Pseudomonas aeruginosa при низкой перекрестной реактивности. Кроме того, платформа SHERLOCK использована для дифференциации клинических изолятов Klebsiella pneumoniae с двумя различными генами антибиотикоустойчивости, что открывает значительные перспективы к созданию мультиплексных систем для одновременной идентификации бактеральных патогенов и выявления у них генов антибиотикоустойчивости.
В связи с этим крайне актуальной является задача разработки новых эффективных методик выявления генов антибиотикоустойчивости у бактериальных патогенов, основанных на генетических технологиях, таких как CRISPR-Cas.
Из уровня техники известны научные статьи, описывающие обнаружение гена антибиотикоустойчивости bla-ТЕМ-1 В в биологическом материале, содержащем 750 колониеобразующих единиц/мл Klebsiella pneumoniae [Perovic, О., Singh-Moodley, A., Duse, A., Bamford, С, Elliott, G., Swe-Han, К. S., Kularatne, R., Lowman, W., Whitelaw, A., Nana, Т., Wadula, J., Lekalakala, R., Saif, A., Fortuin De-Smit, M., & Marais, E. (2014). National sentinel site surveillance for antimicrobial resistance in Klebsiella pneumoniae isolates in South Africa, 2010 - 2012. South African medical journal=Suid-Afrikaanse tydskrif vir geneeskunde, 104(8), 563-568. https://doi.org/10.7196/samj.76171. Также известны и другие публикации, описывающие выявление гена антибиотикоустойчивости bla-ТЕМ методом ПЦР, однако чувствительность, описанных методов не указана [Monstein, Н. J., Ostholm-Balkhed, А., Nilsson, М. V., Nilsson, М., Dornbusch, К., & Nilsson, L. Е. (2007). Multiplex PCR amplification assay for the detection of blaSHV, blaTEM and blaCTX-M genes in Enterobacteriaceae. APMIS: acta pathologica, microbiologica, et immunologica Scandinavica, 115(12), 1400-1408. https://doi.org/10.1111/j.1600-0463.2007.00722.x; Dallenne, C, Da Costa, A., Deere, D., Favier, C, & Arlet, G. (2010). Development of a set of multiplex PCR assays for the detection of genes encoding important beta-lactamases in Enterobacteriaceae. The Journal of antimicrobial chemotherapy, 65(b), 490-495. https://doi.org/10.1093/jac/dkp498]. Кроме того, были найдены научные статьи, описывающие разработку и получение терапевтических направляющих РНК для элиминации патогенных микроорганизмов семейства Enterobacteriaceae, несущих ген антибиотикоустойчивости Ь1а-ТЕМ-1 В, с помощью технологии CRISPR-Cas [Tagliaferri, Т. L., Guimaraes, N. R., Pereira, M. P. M., Vilela, L. F. F., Horz, H. P., Dos Santos, S. G., & Mendes, Т. A. O. (2020). Exploring the Potential of CRISPR-Cas9 Under Challenging Conditions: Facing High-Copy Plasmids and Counteracting Beta-Lactam Resistance in Clinical Strains of Enterobacteriaceae. Frontiers in microbiology, 11, 578.
https://doi.org/10.3389/fmicb.2020.00578].
До сих пор большинство наборов для обнаружения бета-лактамаз расширенного спектра, к которым в том числе относится бета-лактамаза, кодируемая геном bla-ТЕМ-1В, основаны на методологии диффузионного теста в агаре и определении изоэлектрической точки, которая обычно считается достаточной для идентификации штаммов, продуцирующих бета-лактамазы расширенного спектра. Однако из-за появления большого количества различных бета-лактамаз bla-SHV, bla-TEM и bla-СТХ-М изоэлектрофокусирование, по-видимому, не является подходящим методом для установления фенотипа бета-лактамаз расширенного спектра. Кроме того, описанные методы требуют продолжительного времени, специализированного оборудования, а также квалифицированного персонала (микробиология).
Ближайшими аналогами заявляемого решения являются изобретения по патентам: RU 2743861 (дата приоритета 15.04.2020), RU 2734520 (дата приоритета 15.04.2020), RU 2745637 (дата приоритета 15.04.2020), направленные на получение направляющих РНК, предназначенных для разработки высокочувствительных и высокотехнологичных диагностических систем нового поколения для выявления гена антибиотикоустойчивости blaVIM-2 (металло-бета-лактамаза класс В VIM-2) Pseudomonas aeruginosa; RU 2782314 (дата приоритета 27.12.2021), RU 2782588 (дата приоритета 27.12.2021), RU 2782315 (дата приоритета 27.12.2021), раскрывающие техническую возможность получения направляющих РНК, предназначенных для разработки высокочувствительных и высокотехнологичных диагностических систем нового поколения для выявления гена антибиотикоустойчивости mecA Staphylococcus aureus на основе CRISPR технологий; RU 2791879 (дата приоритета 27.12.2021), RU 2791880 (дата приоритета 27.12.2021), RU 2782739 (дата приоритета 27.12.2021), раскрывающие возможность получения направляющих РНК, предназначенных для разработки высокочувствительных и высокотехнологичных диагностических систем нового поколения для выявления exoU, кодирующего экзотоксин системы секреции третьего типа, Pseudomonas aeruginosa на основе CRISPR технологий. Однако, для расширения спектра подобных диагностических систем и совершенствования методов диагностики инфекционных заболеваний, эпидемиологического надзора и контроля за распространением антибиотикоустойчивых микроорганизмов необходимо разрабатывать новые методы для выявления генов антибиотикоустойчивости патогенных микроорганизмов.
Исходя из вышеизложенного, возникает техническая проблема, заключающаяся в необходимости разработки и получения направляющих РНК для выявления единичных копий гена антибиотикоустойчивости bla-ТЕМ-1 В, in vitro.
Предложенная технология перспективна для разнообразных применений, включая количественное определение ДНК/РНК, быструю мультиплексную детекцию экспрессии, другие виды чувствительной детекции, например, выявление загрязнения образцов нуклеиновыми кислотами. Технология основанная на CRISPR-Cas является многофункциональной, устойчивой к ошибкам технологией детекции ДНК, пригодной для быстрой постановки диагнозов, включая инфекционные заболевания, и генотипирования инфекционных агентов и выявление генов антибиотикоустойчивости и генов, кодирующих экзотоксины, бактериальных патогенов.
Применение предложенной технологии делает возможным создание диагностических систем нового поколения, которые будут обладать следующими свойствами:
• высокая чувствительность;
• возможность проведения диагностики у постели больного;
• возможность проведения диагностики в полевых условиях без применения специализированного высокотехнологичного оборудования;
• скорость и простота анализа;
• сниженная стоимость анализа;
• отсутствие необходимости оснащения диагностической лаборатории дорогостоящим оборудованием;
• отсутствие необходимости проведения выделения нуклеиновых кислот возбудителя.
Изобретение относится к новым средствам направляющим РНК, которые могут быть использованы в системах CRISPR-Cas 12 для ультрачувствительного выявления, идентификации, обнаружения или детекции гена антибиотикоустойчивости bla-ТЕМ-1В в биологических образцах.
Технической задачей предложенного изобретения является разработка новых средств - направляющих РНК, которые могут быть использованы в системах CRISPR-Cas12 с белками Cas12, такими как белок LbCpfl из Lachnospiraceae, для ультрачувствительного выявления гена антибиотикоустойчивости bla-ТЕМ-1В.
При осуществлении настоящего изобретения, согласно приведенной в формуле изобретения совокупности существенных признаков, достигается неожиданный технический результат возможность ультрачувствительного выявления гена антибиотикоустойчивости bla-ТЕМ-1В до единичных копий гена антибиотикоустойчивости bla-ТЕМ-1В в одной реакции. Изобретение обеспечивает повышение эффективности выявления гена антибиотикоустойчивости bla-ТЕМ-1В до 1,5 раз.
Технический результат достигается за счет:
• разработки молекул направляющих РНК, которые могут быть использованы в системах CRISPR-Cas 12 для ультра чувствительного выявления гена антибиотикоустойчивости bla-ТЕМ-1 В, где указанные направляющие РНК выбраны из последовательностей SEQIDNO:l-6, способны связываться с целевыми высоко консервативными участками гена антибиотикоустойчивости bla-ТЕМ-1В, содержат РНК-шпильку, которая распознается РНК-направляемой ДНК-эндонуклеазой LbCpfl из Lachnospiraceae, с обеспечением выявления единичных копий гена антибиотикоустойчивости bla-TEM- 1В.
• применения РНК-направляемой ДНК-эндонуклеазы LbCpfl из Lachnospiraceae, полученных согласно способу, разработанному авторами ранее (Патент RU №2707542, дата приоритета 28.03.2019), для создания рибонуклеопротеиновых комплексов (РПК) системы CRISPR-Cas, пригодных для детекции гена антибиотикоустойчивости bla-TEM- 1В в ультра низких концентрациях (единичные копии).
• разработки набора специфических олигонуклеотидов, выбранных из SEQ ID NO: 7, 8, для предварительной амплификации фрагмента гена антибиотикоустойчивости bla-TEM-1В.
• оптимизации условий проведения предварительной амплификации фрагмента гена антибиотикоустойчивости bla-TEM-1В.
• определения условий проведения ультрачувствительной детекции гена антибиотикоустойчивости bla-TEM-1В и установления последовательности стадий метода.
Направляющие РНК согласно настоящему изобретению соответствуют высоко консервативным фрагментам гена антибиотикоустойчивости bla-TEM-1В. Наиболее предпочтительны направляющие РНК, распознающиеся РНК-направляемой ДНК-эндонуклеазой LbCpf1 из Lachnospiraceae, характеризующиеся, имеющие или содержащие нуклеотидную последовательность, выбранную из:
• SEQIDNO:l;
• SEQ ID NO: 2;
• SEQ ID NO: 3;
• SEQ ID NO: 4;
• SEQ ID NO: 5;
• SEQ ID NO: 6;
• или идентичной любой из них по меньшей мере на 80%, 81%, 82%, 83%, 84%, 85%, 86%, 87%, 88%, 89%, 90%, 91%, 92%, 93%, 94%, 95%, 96%, 97%, 98% или 99%,
• или комплементарной любой из них,
• или гибридизующейся с любой из них в строгих условиях.
Набор специфических олигонуклеотидов для проведения предварительной амплификации фрагмента гена антибиотикоустойчивости bla-TEM-1В согласно настоящему изобретению соответствуют высоко консервативному участку гена антибиотикоустойчивости bla-TEM-1В. Наиболее предпочтительны олигонуклеотиды, характеризующиеся, имеющие или содержащие нуклеотидную последовательность, выбранную из:
• SEQ ID NO: 7;
• SEQ ID NO: 8;
• или идентичной любой из них по меньшей мере на 80%, 81%, 82%, 83%, 84%, 85%, 86%, 87%, 88%, 89%, 90%, 91%, 92%, 93%, 94%, 95%, 96%, 97%, 98% или 99%,
• или комплементарной любой из них,
• или гибридизующейся с любой из них в строгих условиях.
Согласно предложенному изобретению получают рибонуклеопротеиновые комплексы (РПК), состоящие из по меньшей мере одной направляющей РНК и РНК-направляемой ДНК-нуклеазы системы CRISPR-Cas LbCpfl из Lachnospiraceae, пригодные для использования для выявления гена антибиотикоустойчивости bla-TEM-1В в ультранизких концентрациях (единичные копии).
Препараты РПК представляют собой растворы, содержащие направляющую РНК, выбранную из SEQ ID NO: 1-6, объединенную с белком системы CRISPR-Cas (LbCpfl из Lachnospiraceae) или лиофильно высушенные РПК.
Полученные направляющие РНК могут быть использованы в составе набора для обнаружения гена антибиотикоустойчивости bla-TEM-1В с инструкцией по применению.
Способ обнаружения гена антибиотикоустойчивости bla-TEM-1В предусматривает:
i) проведение предварительной амплификации материала образца от пациента, предположительно содержащего ген антибиотикоустойчивости bla-TEM-1В с использованием одного или нескольких специфических олигонуклеотидов, выбранных из SEQ ID NO: 7, 8, с целью получения мишени - предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В,
ii) приготовление реакционной смеси для детекции, содержащей мишень, полученную на стадии (i); рибонуклеопротеиновый комплекс системы CRISPR-Cas, сформированный из РНК-направляемой ДНК-эндонуклеазы LbCpfl из Lachnospiraceae, и по меньшей мере одной направляющей РНК с SEQ ID NO: 1-6; флюоресцентный зонд и буфер для детекции,
iii) проведение 30-60 циклов детекции в реакционной смеси, полученной на стадии (ii), в амплификаторе, с обнаружением таким образом гена антибиотикоустойчивости bla-TEM-1В.
Предварительно амплифицированный фрагмент гена антибиотикоустойчивости bla-TEM-1В согласно предложенному способу может быть представлен фрагментом размером 618 п. о. гена антибиотикоустойчивости bla-TEM-1В.
Предложенный способ обеспечивает выявление гена антибиотикоустойчивости bla-TEM-1В в ультранизких концентрациях, вплоть до единичных копий.
Специфический олигонуклеотид для использования в способе выбирается из группы SEQ ID NO: 7, 8 и используется для предварительной амплификации высококонсервативного фрагмента гена антибиотикоустойчивости bla-TEM-1В, который распознается рибонуклеопротеиновым комплексом.
Набор для использования в способе обнаружения гена антибиотикоустойчивости bla-TEM-1В содержит рибонуклеопротеиновый комплекс системы CRISPR-Cas, сформированный из РНК-направляемой ДНК-эндонуклеазы LbCpfl из Lachnospiraceae, и по меньшей мере одной направляющей РНК с SEQ ID NO: 1-6; флюоресцентный зонд, буфер для детекции и инструкцию по применению.
Набор может дополнительно включать компоненты для проведения предварительной амплификации высококонсервативного фрагмента гена антибиотикоустойчивости bla-TEM-1В, в том числе один или несколько специфических олигонуклеотидов, выбранных из SEQ ID NO: 7, 8.
При этом по меньшей мере одна направляющая РНК в составе набора может находиться в комплексе с белком системы CRISPR-Cas (LbCpfl из Lachnospiraceae) в одном контейнере или отдельно в разных контейнерах.
Предложенная технология позволяет определить единичные копии гена антибиотикоустойчивости bla-TEM-1В в биологических образцах пациента, выбранных из жидкости и/или ткани, предположительно содержащих ген антибиотикоустойчивости bla-TEM-1В. Биологическим образцом может быть образец крови, сыворотки или плазмы крови, клеток крови, слюны, мокроты, лимфоидных тканей, тканей кроветворных органов и других биологических материалов от пациента, которые могут быть использованы для анализа на наличие гена антибиотикоустойчивости bla-TEM-1В.
Краткое описание чертежей
Фиг. 1. Визуализация амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В (размером 618 п. о.) после предварительной амплификации с использованием олигонуклеотидов bla-TEM-1В 59 и bla-TEM-1B 65 при помощи электрофореза в агарозном геле, где буквами a-h обозначены:
а - Продукт, полученный в ходе амплификации 2,56х10б копий модельной матрицы pGEM-T-bla-TEM-1В;
b - Продукт, полученный в ходе амплификации 2,56х105 копий модельной матрицы pGEM-T-bla-TEM-1В;
с Продукт, полученный в ходе амплификации 2,56х104 копий модельной матрицы pGEM-T-bla-TEM-1В;
d - Продукт, полученный в ходе амплификации 2560 копий модельной матрицы pGEM-T-bla-TEM-1В;
е Продукт, полученный в ходе амплификации 256 копий модельной матрицы pGEM-T-bla-TEM-1В;
f - Продукт, полученный в ходе амплификации 25,6 копии модельной матрицы pGEM-T-bla-TEM-1В;
g - Продукт, полученный в ходе амплификации 2,56 копии модельной матрицы pGEM-T-bla-TEM-1В;
h отрицательный контроль, не содержащий модельной матрицы pGEM-T-bla-TEM-1В;
М - стандарты молекулярных масс: снизу вверх 100, 200, 300, 400, 500, 600, 700, 800, 900, 1000, 1200, 1500, 2000, 3000 пар нуклеотидов (GeneRuler 100 bp Plus, Thermo Fisher Scientific, США).
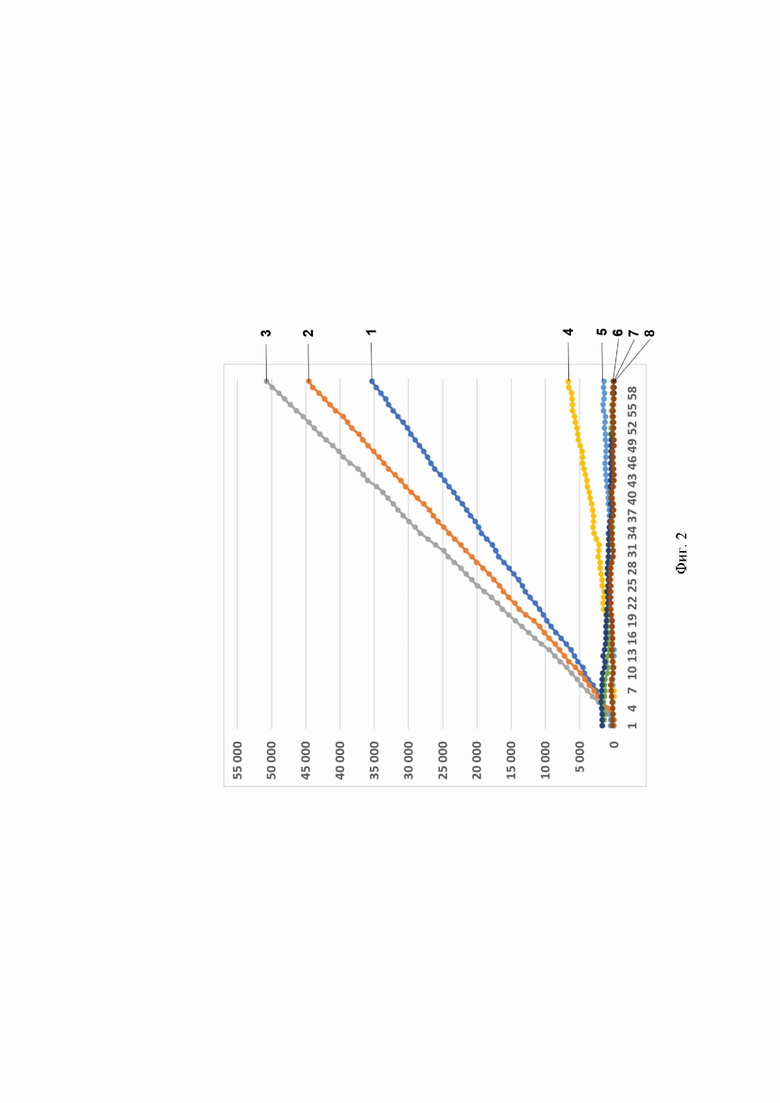
Фиг. 2. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-TEM-1В №56 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-TEM-1В №56, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 1-8 показано количество копий нуклеиновой кислоты на реакцию, а именно:
1 -2 560 000 копий/реакция;
2 256 000 копий/реакция;
3 25 600 копий/реакция;
4-2560 копий/реакция; 5-256 копий/реакция; 6-25,6 копий/реакция; 7-2,56 копий/реакция;
8К - (отрицательный контроль).
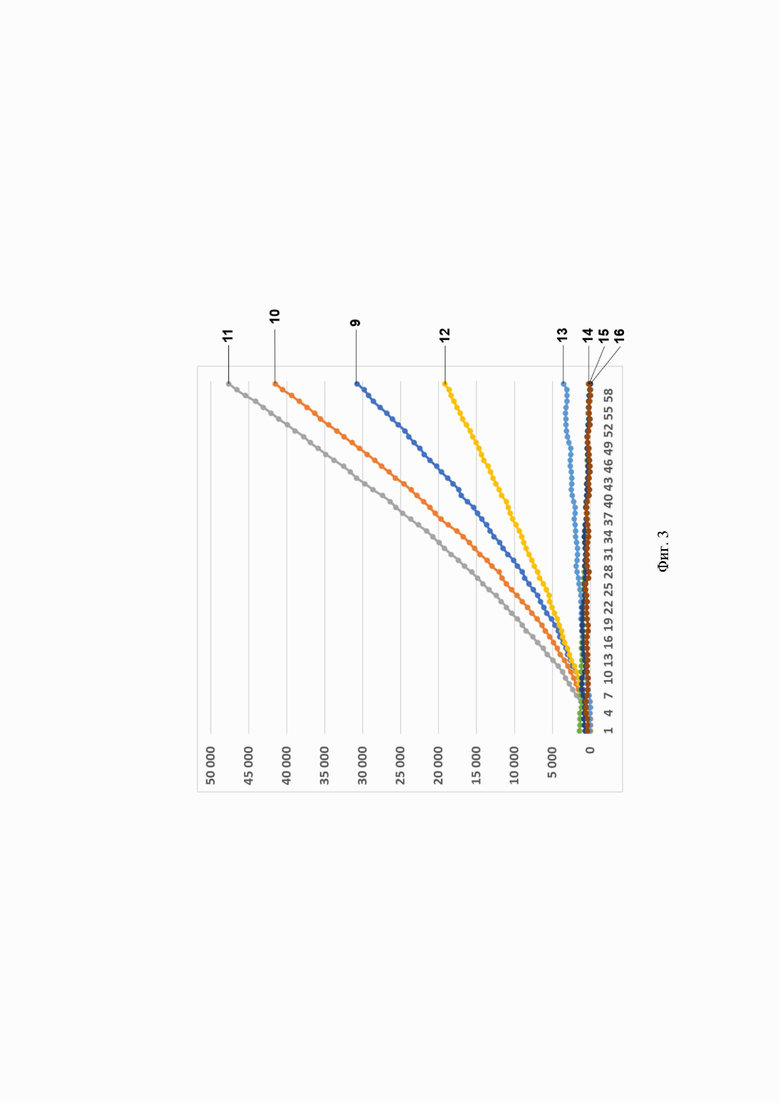
Фиг. 3. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-TEM-1В №166 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-ТЕМ-1В №166, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 9-16 показано количество копий нуклеиновой кислоты на реакцию, а именно:
9 2 560 000 копий/реакция;
10 256 000 копий/реакция;
11 -25 600 копий/реакция;
12 - 2560 копий/реакция;
13 256 копий/реакция;
14 25,6 копий/реакция;
15-2,56 копий/реакция;
16К - (отрицательный контроль).
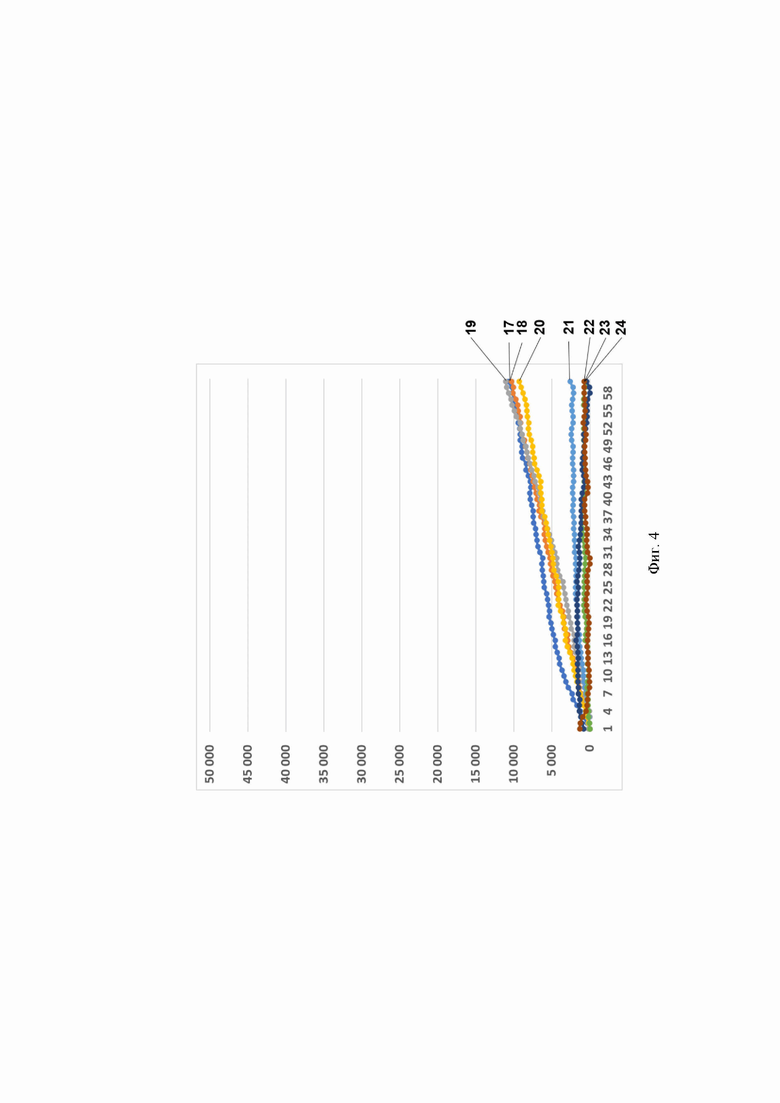
Фиг. 4. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-ТЕМ-1В №329 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-TEM-1В №329, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 17-24 показано количество копий нуклеиновой кислоты на реакцию, а именно:
17-2 560 000 копий/реакция;
18 256 000 копий/реакция;
19 25 600 копий/реакция;
20 - 2560 копий/реакция;
21 - 256 копий/реакция;
22 25,6 копий/реакция;
23 2,56 копий/реакция;
24 - К- (отрицательный контроль).
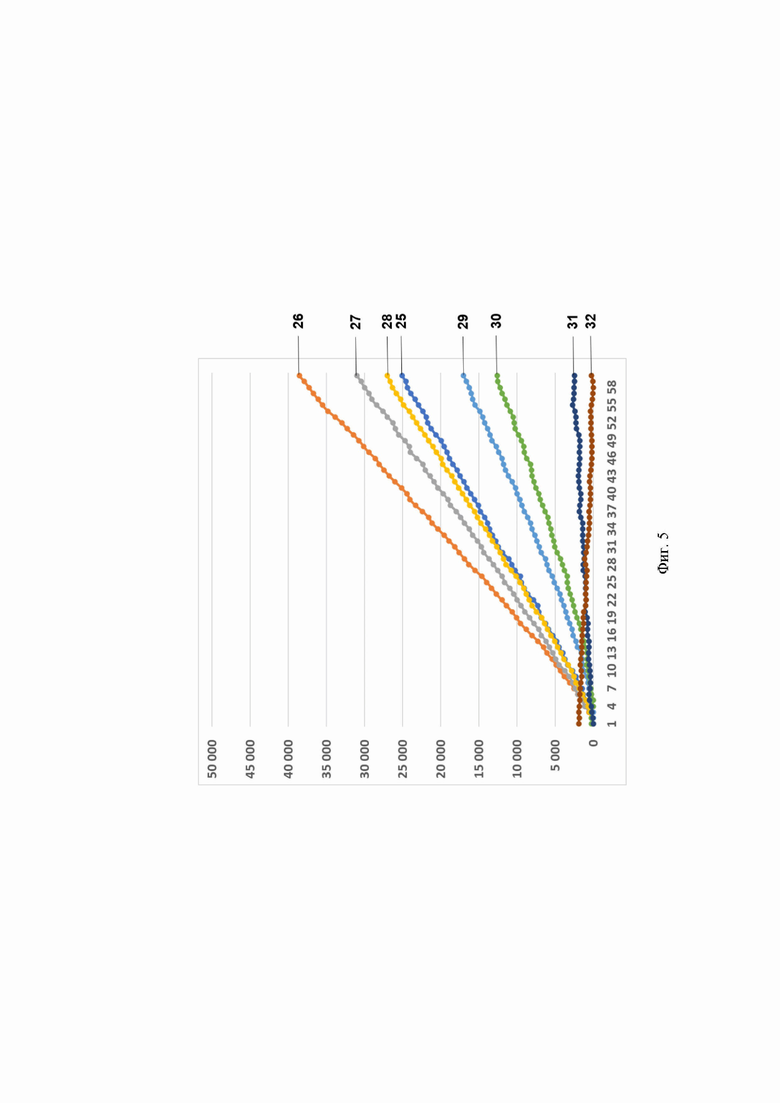
Фиг. 5. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-TEM-1В №410 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-TEM-1В №410, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 25-32 показано количество копий нуклеиновой кислоты на реакцию, а именно:
25- 2 560 000 копий/реакция;
26- 256 000 копий/реакция;
27 - 25 600 копий/реакция;
28 2560 копий/реакция;
29- 256 копий/реакция;
30- 25,6 копий/реакция;
31 2,56 копий/реакция;
32 К- (отрицательный контроль).
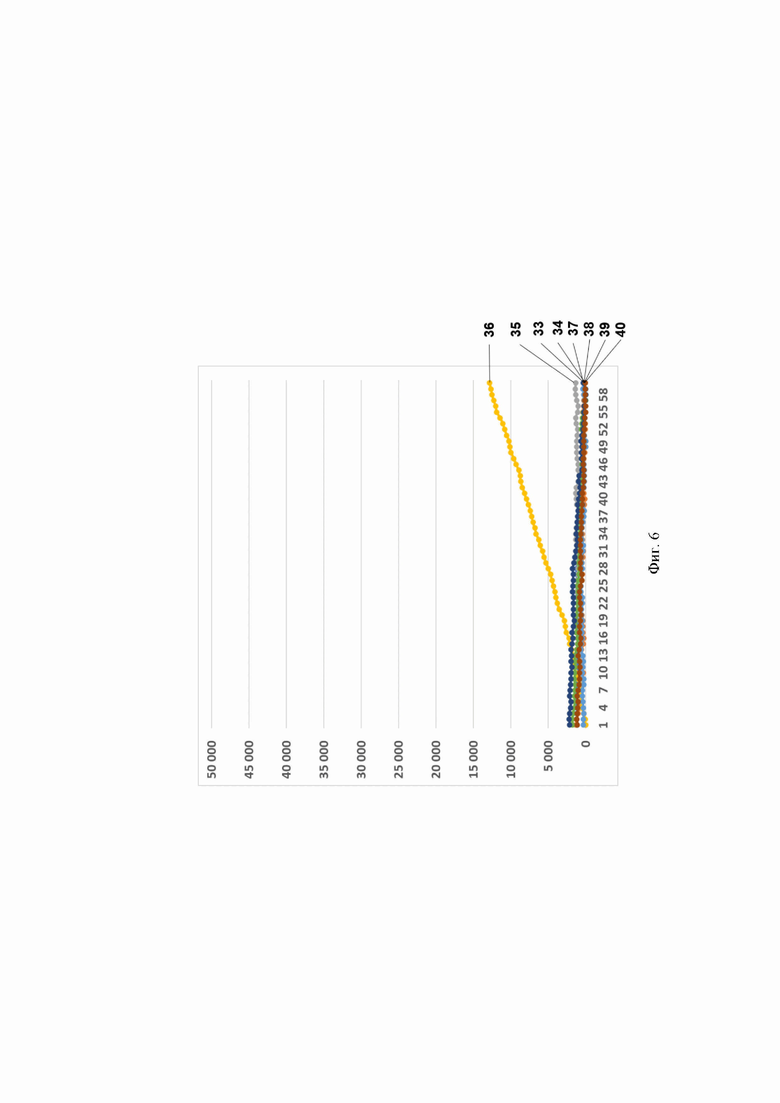
Фиг. 6. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-TEM-1В №479 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-TEM-1В №479, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 33 - 40 показано количество копий нуклеиновой кислоты на реакцию, а именно:
33 - 2 560 000 копий/реакция;
34 - 256 000 копий/реакция;
35 - 25 600 копий/реакция;
36 - 2560 копий/реакция;
37 - 256 копий/реакция;
38-25,6 копий/реакция;
39 2,56 копий/реакция;
40 К- (отрицательный контроль).
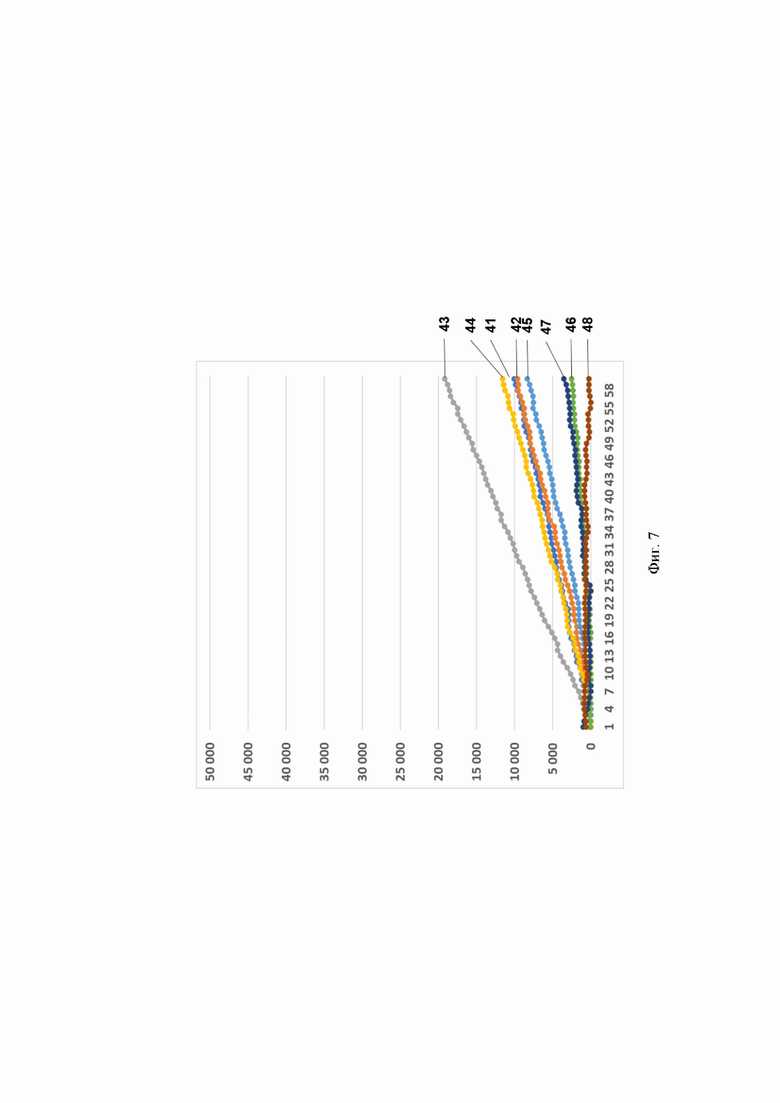
Фиг. 7. Профиль флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновым комплексом, содержащим направляющую РНК crRNA bla-ТЕМ-1В №536 и белок LbCpfl, на котором посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющую РНК crRNA bla-TEM-1В №536, где:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано время флуоресценции, в минутах;
- на кривых 41-48 показано количество копий нуклеиновой кислоты на реакцию, а именно:
41 - 2 560 000 копий/реакция;
42 256 000 копий/реакция;
43 25 600 копий/реакция;
44 - 2560 копий/реакция; 45-256 копий/реакция;
46 25,6 копий/реакция;
47 2,56 копий/реакция;
48 - К- (отрицательный контроль).
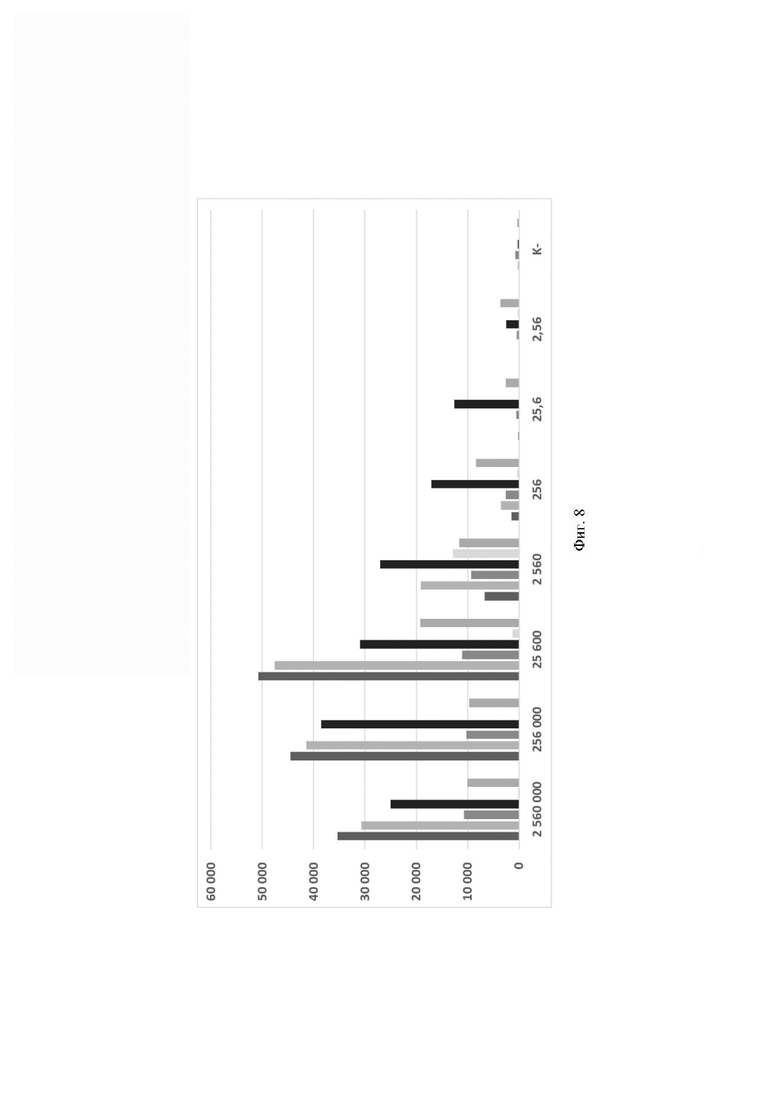
Фиг. 8. Значения флуоресценции в конечной точке (60 цикл анализа, 60 минут) для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-ТЕМ-1В, обработанного рибонуклеопортеиновыми комплексами, содержащим направляющие РНК crRNA bla-TEM-1В №56, crRNA bla-TEM-1B №166, crRNA bla-TEM-1B №329, crRNA bla-TEM-1B №410, crRNA bla-TEM-1B №479 и crRNA bla-TEM-1B №536, где посредством графика визуализировано выявление фрагмента модельной матрицы pGEM-T-bla-TEM-1B с помощью рибонуклеопротеиновых комплексов LbCpf1 из Lachnospiraceae, при этом:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указано количество копий модельной матрицы в реакции;
- столбцом  визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №56;
визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №56;
- столбцом визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №166;
- столбцом  визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №329;
визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №329;
- столбцом  визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №410;
визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №410;
- столбцом визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №479;
- столбцом визуализирована эффективность выявления единичных копий фрагмента модельной матрицы pGEM-T-bla-TEM-1B с использованием crRNA bla-TEM-1В №536.
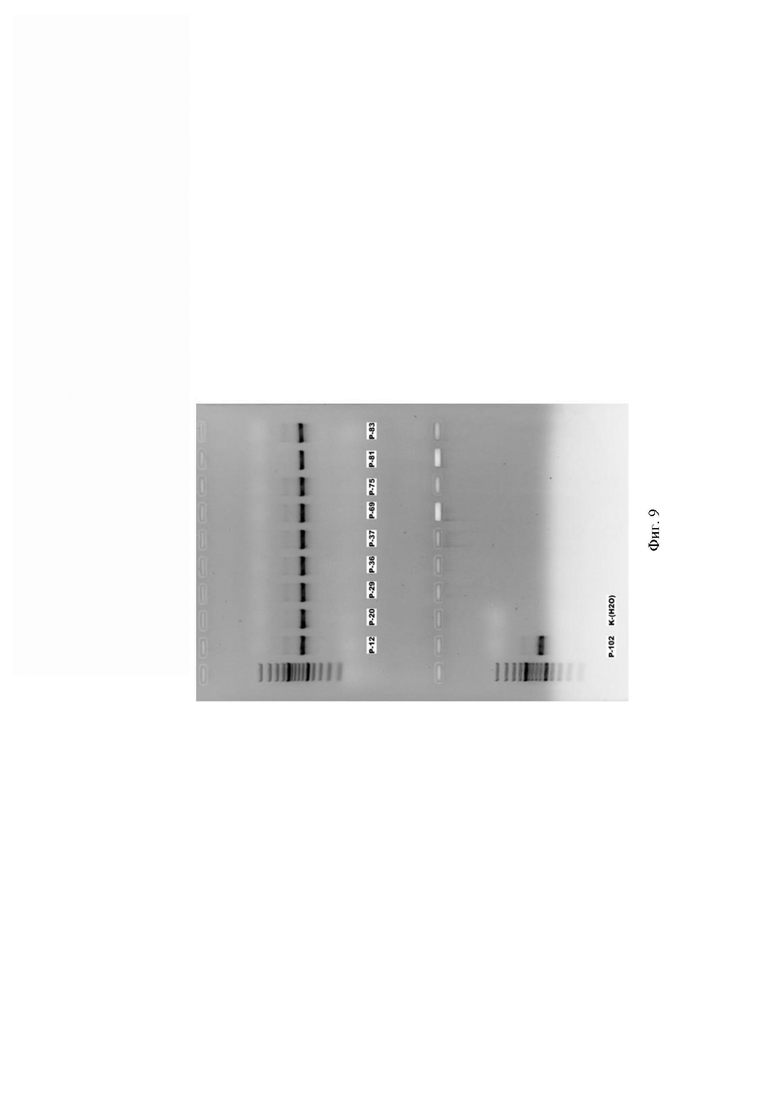
Фиг. 9. Визуализация амплифицированного с клинических образцов фрагмента гена антибиотикоустойчивости bla-TEM-1В (размером 618 п. о.) после предварительной амплификации с использованием олигонуклеотидов bla-TEM-1В 59 и bla-TEM-1В 65 при помощи электрофореза в агарозном геле.
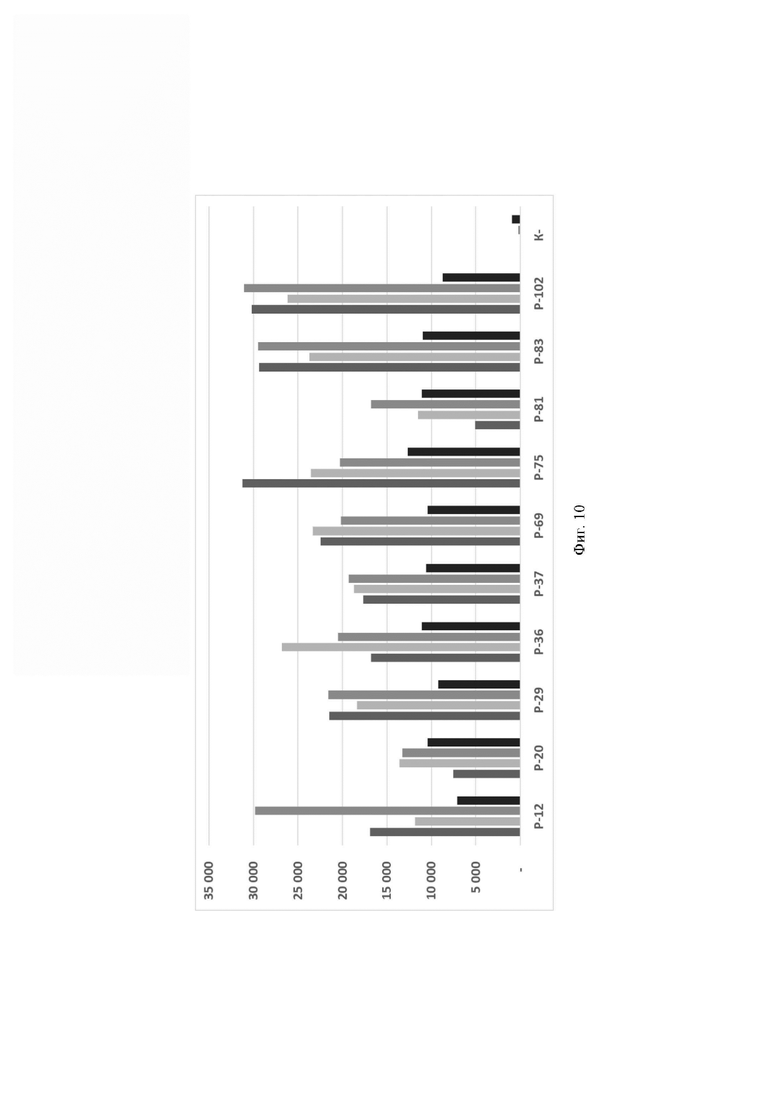
Фиг. 10. Значения флуоресценции в конечной точке (60 цикл анализа, 60 минут) для предварительно амплифицированного с клинических образцов фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновыми комплексами, содержащим направляющие РНК crRNA bla-TEM-1В №56, crRNA bla-ТЕМ-IB №166, crRNA bla-TEM-1B №410 и crRNA bla-TEM-1B №536, где посредством графика визуализировано выявление фрагмента гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов LbCpf1 из Lachnospiraceae на ограниченной панели клинических образцов, при этом:
- по вертикали указаны значения нормализированного флуоресцентного сигнала, создаваемого красителем;
- по горизонтали указаны идентификаторы образца;
- столбцом  показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №56;
показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №56;
столбцом показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-ТЕМ-1B №166;
- столбцом  показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №410;
показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №410;
- столбцом  показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №536. Примеры осуществления изобретения
показана эффективность выявления фрагмента гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов, выделенных из клинических образцов, с использованием crRNA bla-TEM-1В №536. Примеры осуществления изобретения
ПРИМЕР 1: ПОДБОР ПОСЛЕДОВАТЕЛЬНОСТЕЙ-МИШЕНЕЙ В ГЕНЕ АНТИБИОТИКОУСТОЙЧИВОСТИ BLA-TEM- 1 В ДЛЯ СОЗДАНИЯ НАПРАВЛЯЮЩИХ РНК
Для подбора последовательностей-мишеней в гене антибиотикоустойчивости bla-TEM-1В для создания направляющих РНК были использованы современные алгоритмы in silico анализа нуклеотидных последовательностей и программы, находящиеся в открытом доступе, включая Benchling (https://www.benchling.com/molecular-biology/). Был составлен перечень участков гена антибиотикоустойчивости bla-TEM-1В с теоретически рассчитанной вероятностью их расщепления в высоко консервативных участках (Таблица 1). Направляющие РНК, специфически узнающие высоко консервативные участки гена антибиотикоустойчивости bla-TEM-1В, представлены уникальными последовательностями SEQ ID NO: 1-6.

ПРИМЕР 2: ПОДГОТОВКА МАТЕРИАЛА ДЛЯ ОБНАРУЖЕНИЯ ГЕНА АНТИБИОТИКОУСТОЙЧИВОСТИ BLA-TEM-1 В МЕТОДОМ ПРЕДВАРИТЕЛЬНОЙ АМПЛИФИКАЦИИ
Подготовку материала для обнаружения гена антибиотикоустойчивости bla-TEM-1В проводили методом предварительной амплификации. В качестве модельной матрицы, содержащей фрагмент гена антибиотикоустойчивости bla-TEM-1В, использовали плазмидную ДНК pGEM-T-bla-TEM-1B, содержащую в своем составе фрагмент гена антибиотикоустойчивости антибиотикоустойчивости bla-TEM-1В размером 618 п. о.
Предварительную амплификацию участка, соответствующего фрагменту гена антибиотикоустойчивости bla-TEM-1В, проводили с использованием специфических олигонуклеотидов с SEQ ID NO: 7 и SEQ ID NO: 8.
Продукт, кодирующий фрагмент гена антибиотикоустойчивости bla-TEM-1В, получали при проведении ПЦР с использованием специфических олигонуклеотидов bla-TEM-1В59 и bla-TEM-1В 65 (ГенТерра, Россия) и ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия). Размер амплифицированного фрагмента составлял 618 пар нуклеотидов.
Температурный профиль амплификации для получения ПЦР-продуктов фрагментов гена антибиотикоустойчивости bla-TEM-1В:
1. денатурация: 95°С в течение 3 минут;
2. 40 циклов амплификации: 95°С - 15 сек, 55°С - 45 сек, 72°С - 30 сек;
3. финальная элонгация: 72°С в течение 5 минут.
В ходе подготовки материала для обнаружения гена антибиотикоустойчивости bla-TEM-1В методом предварительной амплификации проводили титрование модельной матрицы pGEM-T-bla-TEM-1B путем приготовления серийных разведений (Таблица 2).

Для оценки эффективности предварительной амплификации полученный фрагмент гена антибиотикоустойчивости bla-TEM-1В визуализировали при помощи электрофореза в агарозном геле (фиг. 1).
Подготовленный описанным способом материал использовали для экспериментов по выявлению гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов LbCpfl из Lachnospiraceae, содержащих направляющие РНК crRNA bla-TEM-1В №56, crRNA bla-TEM-1B №166, crRNA bla-TEM-1B №329, crRNA bla-TEM-1B №410, crRNA bla-TEM-1B №479 и crRNA bla-TEM-1B №536, без предварительной очистки.
ПРИМЕР 3: ПОЛУЧЕНИЕ НАПРАВЛЯЮЩИХ РНК И СОЗДАНИЕ РИБОНУКЛЕОПРОТЕИНОВЫХ КОМПЛЕКСОВ ДЛЯ ОБНАРУЖЕНИЯ ГЕНА АНТИБИОТИКОУСТОЙЧИВОСТИ BLA-TEM-1 В
Для получения направляющих РНК для обнаружения гена антибиотикоустойчивости bla-TEM-1В были разработаны специфические олигонуклеотиды, приведенные в Таблице 3. Получение направляющих РНК проводили в несколько этапов:
1. получение ПЦР-продукта с использованием набора специфических олигонуклеотидов (Таблица 3), кодирующего направляющую РНК, способную связываться с целевым высоко консервативным участком гена антибиотикоустойчивости bla-TEM-1В, содержащую РНК-шпильку, которая распознается РНК-направляемой ДНК-эндонуклеазой LbCpfl из Lachnospiraceae;
2. очистка ПЦР-продукта, кодирующего направляющую РНК, специфичную к фрагменту гена антибиотикоустойчивости bla-TEM-1В;
3. синтез направляющей РНК, специфичной к фрагменту гена антибиотикоустойчивости bla-TEM-1В;
4. очистка направляющей РНК, специфичной к фрагменту гена антибиотикоустойчивости bla-TEM-1В.


ПЦР-продукт, кодирующий направляющую РНК crRNA bla-TEM-1B №56, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №56 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №56, составлял 62 пары нуклеотидов.
ПЦР-продукт, кодирующий направляющую РНК crRNA bla-TEM-1В №166, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №166 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №166, составлял 62 пары нуклеотидов.
ПЦР-продукт, кодирующий направляющую РНК crRNA bla-TEM-1В №329, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №329 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №329, составлял 62 пары нуклеотидов.
ПЦР-продукт, кодирующий направляющую РНК crRNA bla-ТЕМ-1 В №410, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №410 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №410, составлял 62 пары нуклеотидов.
ПЦР-продукт, кодирующий направляющую РНК crRNA bla-TEM-1В №479, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №479 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №479, составлял 62 пары нуклеотидов.
ПЦР-продукт, кодирующий направляющую РНК crRNA bla-TEM-1В №536, получали в реакции амплификации с использованием ПЦР-смеси-2 blue (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) и специфических олигонуклеотидов T7pr и crRNA bla-TEM-1В №536 (ГенТерра, Россия). Размер амплифицированного фрагмента, кодирующего crRNA bla-TEM-1В №536, составлял 62 пары нуклеотидов.
Температурный профиль амплификации для получения ПЦР-продуктов, кодирующих направляющие РНК:
1. денатурация: 95°С в течение 3 минут;
2. 35 циклов амплификации: 95°С - 15 сек, 55°С - 45 сек, 72°С - 30 сек;
3. финальная элонгация: 72°С в течение 5 минут.
ПЦР-продукты, кодирующие направляющие РНК, специфичные к фрагменту гена антибиотикоустойчивости bla-TEM-1В, визуализировали при помощи электрофореза в агарозном геле.
Очистку ПЦР-продуктов, кодирующих направляющие РНК, специфичные к фрагменту гена антибиотикоустойчивости bla-TEM-1В, проводили с использованием коммерчески доступного набора ISOLATE II PCR and Gel Kit (BioLine, США) согласно инструкции производителя. Очищенные ПЦР-продукты, кодирующие направляющие РНК, специфичные к фрагменту гена антибиотикоустойчивости bla-TEM-1В, использовали в качестве матрицы для синтеза направляющих РНК.
Синтез направляющих РНК, специфичных к фрагменту гена антибиотикоустойчивости bla-TEM-1В, осуществляли методом in vitro транскрипции с использованием коммерчески доступных наборов реагентов (HiScribe™ Т7 High Yield RNA Synthesis Kit, NEB, США) согласно инструкции производителя. Продукты реакции in vitro транскрипции переосаждали из реакционной смеси добавлением хлорида натрия до конечной концентрации 400 тМ и равного объема изопропилового спирта. Такие модификации протокола производителя, внесенные авторами, позволяют увеличить выход продукта реакции и получить желаемую концентрацию финального препарата направляющей РНК.
Создание готового рибонуклеопротеинового комплекса, содержащего белок семейства CRISPR-Cas 12 LbCpfl из Lachnospiraceae, и направляющую РНК авторы проводили по стандартному протоколу с некоторыми модификациями [С. Anders, М. Jinek, In vitro enzymology of Cas9, Methods Enzymol. 546 (2014) 1-20, https://doi.org/10.1016/B978-0-12-801185-0.00001-51.
Непосредственно перед объединением с Cas-белком препарат направляющей РНК (в количестве 250 нг) прогревали при 90°С в течение 5 минут и позволяли медленно остыть до комнатной температуры (инкубация при комнатной температуре не менее 10 минут). Такое прогревание необходимо для формирования корректной конформации шпильки, содержащейся в направляющей РНК. Многие производители коммерческих препаратов Cas-белков пропускают данный этап при подготовке рибонуклеопротеинового комплекса.
Для формирования готового рибонуклеопротеинового комплекса 250 нг Cas-белка LbCpfl из Lachnospiraceae и подготовленную направляющую РНК смешивали и инкубировали 15 минут при комнатной температуре. Полученный таким способом рибонуклеопротеиновый комплекс готов для выявления гена антибиотикоустойчивости bla-TEM-1В.
ПРИМЕР 4: ОБНАРУЖЕНИЕ ЕДИНИЧНЫХ КОПИЙ ГЕНА АНТИБИОТИКОУСТОЙЧИВОСТИ BLA-TEM-1 В С ПОМОЩЬЮ
РИБОНУКЛЕОПРОТЕИНОВЫХ КОМПЛЕКСОВ CRTSPR7CAS НА ПРИМЕРЕ МОДЕЛЬНОЙ МАТРИЦЫ
Предварительно амплифицированный материал, полученный способом, описанным в Примере 2, использовали в качестве матрицы для обнаружения гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas, полученных способом, описанным в Примере 3.
Для обнаружения гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas готовили реакционную смесь, содержащую следующие компоненты:
• 10 х буфер (100 тМ TrisHCl рН 8,0, 1 М NaCl);
• 50 mM MgC12 (конечная концентрация в реакционной смеси 10 mM);
• 250 нг рибонуклеопротеинового комплекса (LbCpfl из Lachnospiraceae и направляющие РНК crRNA Ыа-ТЕМ-1 В №56, crRNA bla-TEM-1В №166, crRNA bla-TEM-1B №329, crRNA bla-TEM-1B №410, crRNA bla-TEM-1B №479 и crRNA bla-TEM-1B №536);
• 10 pmol флуоресцентный зонд (6FAM-TTATT-BHQ1);
• Мишень (предварительно амплифицированный фрагмент гена антибиотикоустойчивости bla-TEM-1В);
• вода mQ.
Реакционные смеси, содержащие все необходимые компоненты, помещали в амплификатор QuantStudio 5 (Thermo Fisher Scientific, США) и задавали следующие параметры реакции:
30-60 циклов:
1. 37°С-35 сек,
2. 37°С - 25 сек, съемка флуоресценции.
В первую очередь были проведены эксперименты по обнаружению единичных копий гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas, сформированных на основе LbCpfl из Lachnospiraceae, с использованием в качестве мишени модельной матрицы плазмидной ДНК pGEM-T-bla-ТЕМ-1В, содержащую в своем составе фрагмент гена антибиотикоустойчивости bla-TEM-1В размером 618 п. о.
Было показано, что рибонуклеопротеиновые комплексы CRISPR-Cas обладают способностью выявлять единичные копии гена антибиотикоустойчивости bla-TEM-1В. Типичные результаты анализа приведены на примерах профилей флуоресценции в реальном времени для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В, обработанного рибонуклеопортеиновыми комплексами, содержащими направляющие РНК crRNA bla-TEM-1В №56, crRNA bla-ТЕМ-1B №166, crRNA bla-TEM-1B №329, crRNA bla-TEM-1B №410, crRNA bla-TEM-1B №479 и crRNA bla-TEM-1B №536 и белок LbCpfl, на Фиг. 2, Фиг. 3, Фиг. 4, Фиг. 5, Фиг. 6 и Фиг. 7, соответственно.
Отметим, что комплексы CRISPR-Cas 12 выявляют ген bla-TEM-1В с различной эффективностью. Так, crRNA №536 и crRNA №410 выявляют 2,56 копий гена антибиотикоустойчивости bla-TEM-1В в реакции; crRNA №56 и crRNA №166 - 256 копий в реакции; a crRNA №329 и crRNA №479 - 2560 копий в реакции.
В среднем уже на 47-ом цикле анализа (47 минут) значение сигнала, полученного в ходе детекции единичных копий (2,56 копий/реакция) гена антибиотикоустойчивости bla-TEM-1В, превышало значение «шума» (неспецифической флуоресценции контрольного образца, не содержащего мишени) минимум в пять раз, а к 55-ому циклу (55 минут анализа) - в 10 и более раз. Также отметим, что в среднем уже на 35-ом цикле анализа (35 минут) значение сигнала, полученного в ходе детекции 256 копий гена антибиотикоустойчивости bla-TEM-1В в реакции, превышало значение «шума» (неспецифической флуоресценции контрольного образца, не содержащего мишени) минимум в пять раз, а к 42-ому циклу (42 минуты анализа) - в 10 и более раз. Кроме того, в среднем уже на 13-ом цикле анализа (13 минут) значение сигнала, полученного в ходе детекции 2560 копий гена антибиотикоустойчивости bla-TEM-1В в реакции, превышало значение «шума» (неспецифической флуоресценции контрольного образца, не содержащего мишени) минимум в пять раз, а к 21-ому циклу (21 минута анализа) в 10 и более раз.
В ходе работ была оценена эффективность выявления гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе модельной матрицы, с использованием различных направляющих РНК. Было показано, что рибонуклеопротеиновые комплексы CRISPR-Cas, сформированные на основе LbCpfl из Lachnospiraceae и направляющих РНК, выявляют ген антибиотикоустойчивости Ыа-ТЕМ-1 В с различной эффективностью, и их можно расположить в следующем порядке по уменьшению активности: crRNA №536 ≥crRNA №410>crRNA №56 ≥crRNA №166>crRNA №329 ≥crRNA №479 (Фиг. 8).
ПРИМЕР 5: ОБНАРУЖЕНИЕ ГЕНА АНТИБИОТИКОУСТОЙЧИВОСТИ BLA-TEM-1В С ПОМОЩЬЮ РИБОНУКЛЕОПРОТЕИНОВЫХ КОМПЛЕКСОВ CRISPR/CAS НА ОГРАНИЧЕННОЙ ПАНЕЛИ КЛИНИЧЕСКИХ ОБРАЗЦОВ
Разработанные направляющие РНК были апробированы на ограниченной панели клинических образцов (10 шт. ), содержащих ген антибиотикоустойчивости bla-TEM-1В (ранее подтверждено методом секвенирования следующего поколения).
Для обнаружения гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas была проведена предварительная амплификация фрагмента гена антибиотикоустойчивости bla-TEM-1В. Для проведения предварительной амплификации из клинических образцов 10 пациентов с помощью коммерчески доступного набора «РИБО-преп» (ФБУН ЦНИИ Эпидемиологии Роспотребнадзора, Россия) согласно инструкции производителя были выделены препараты ДНК.
Продукт, кодирующий фрагмент гена антибиотикоустойчивости bla-TEM-1В, получали с помощью ПЦР с использованием специфических олигонуклеотидов bla-TEM-1В 59 и bla-TEM-1В 65 (ГенТерра, Россия) и визуализировали при помощи электрофореза в агарозном геле (Фиг. 9).
Полученный таким способом материал использовали в качестве матрицы для обнаружения гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas, полученных способом, описанным в Примере 3.
Обнаружение гена антибиотикоустойчивости bla-TEM-1В с помощью рибонуклеопротеиновых комплексов CRISPR-Cas проводили способом, описанным в Примере 4.
В ходе проведенного анализа было показано, что рибонуклеопротеиновые комплексы CRISPR-Cas обладают способностью выявлять ген антибиотикоустойчивости bla-TEM-1В в препаратах ДНК, выделенных из клинических образцов. При этом в среднем уже на 20 цикле (20 минут) анализа значение сигнала превышало значение «шума» (неспецифической флуоресценции контрольного образца, не содержащего мишени) более чем в 5 раз, а к 29 циклу (29 минут) анализа - более чем в 10 раз (Таблица 4).
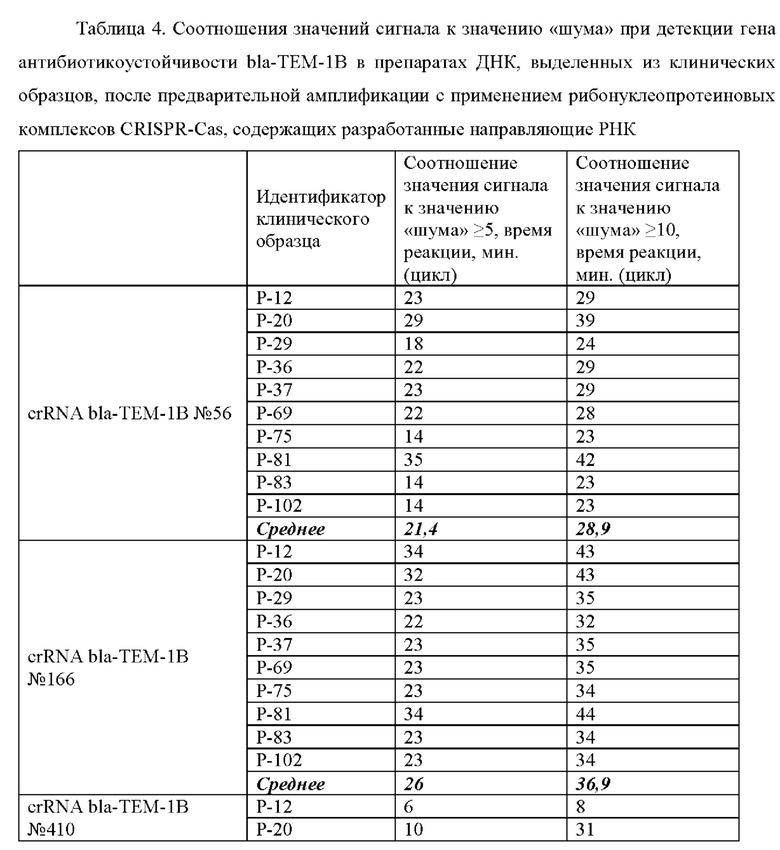
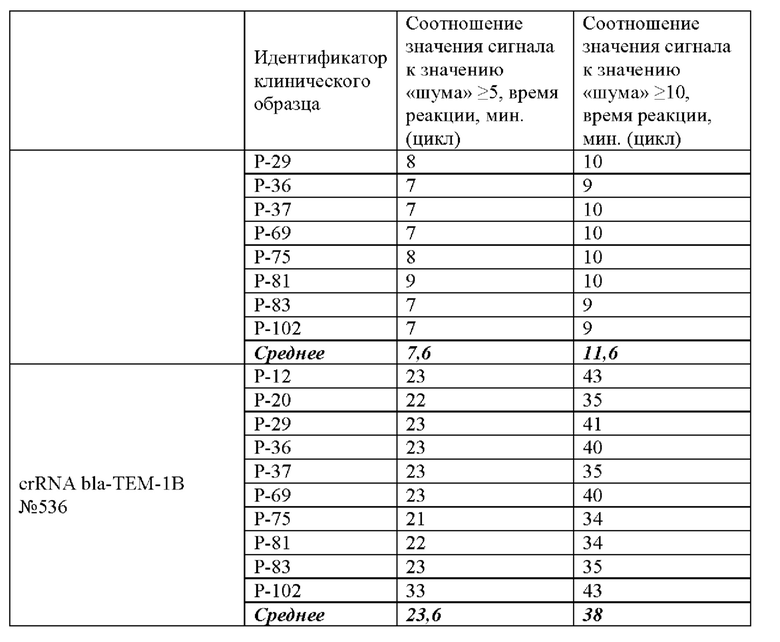
Типичные результаты анализа приведены на примерах значений флуоресценции в конечной точке (60 цикл анализа, 60 минут) для предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1В (10 независимых клинических образцов), обработанных рибонуклеопортеиновыми комплексами, содержащими направляющие РНК crRNA bla-TEM-1В №56, crRNA bla-TEM-1B №166, crRNA bla-TEM-1B №410 и crRNA bla-TEM-1B №536 и белок LbCpfl, на Фиг. 10.
Эффективность выявления гена антибиотикоустойчивости bla-TEM-1В, содержащегося в составе препаратов ДНК, выделенных из клинических образцов, с использованием различных направляющих РНК в составе рибонуклеопротеиновых комплексов CRISPR-Cas, сформированных на основе LbCpfl из Lachnospiraceae, оцененная по соотношению значений сигнала к значению «шума» при детекции, можно представить в следующем порядке по убыванию: crRNA bla-ТЕМ-1B №410>crRNA bla-ТЕМ-1 В №56>crRNA bla-TEM-1B №536 ≥crRNA bla-TEM-1B №166 (Таблица 4).
Таким образом, разработанные направляющие РНК позволяют ультрачувствительно выявлять единичные копии гена антибиотикоустойчивости bla-TEM-1В, и способны обнаруживать его препаратах ДНК, выделенных из клинических образцов, после предварительной амплификации в составе рибонуклеопротеиновых комплексов CRISPR-Cas.
--->
<?xml version="1.0" encoding="UTF-8"?>
<!DOCTYPE ST26SequenceListing PUBLIC "-//WIPO//DTD Sequence Listing
1.2//EN" "ST26SequenceListing_V1_2.dtd">
<ST26SequenceListing dtdVersion="V1_2" fileName="bla-TEM-1B "
softwareName="WIPO Sequence" softwareVersion="1.0.0"
productionDate="2023-12-01">
<ApplicationIdentification>
<IPOfficeCode>RU</IPOfficeCode>
<ApplicationNumberText>b/n</ApplicationNumberText>
<FilingDate>2023-12-01</FilingDate>
</ApplicationIdentification>
<ApplicantFileReference>1</ApplicantFileReference>
<ApplicantName languageCode="ru">ФБУН ЦНИИ Эпидемиологии
Роспотребнадзора</ApplicantName>
<ApplicantNameLatin>FBUN CRIE</ApplicantNameLatin>
<InventionTitle languageCode="ru">Способ обнаружения гена
антибиотикоустойчивости bla-TEM-1B в ультранизких концентрациях и
специфические олигонуклеотиды для использования в
способе</InventionTitle>
<SequenceTotalQuantity>8</SequenceTotalQuantity>
<SequenceData sequenceIDNumber="1">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagatcgccccgaagaacgttttcc</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="2">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagatctgtgactggtgagtactca</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="3">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagatttgcacaacatgggggatca</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="4">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagatcgcaacgttgttgccattgc</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="5">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagattccgcctccatccagtctat</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="6">
<INSDSeq>
<INSDSeq_length>40</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..40</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>aatttctactaagtgtagattcagcaataaaccagccagc</INSDSeq
_sequence>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="7">
<INSDSeq>
<INSDSeq_length>34</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..34</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>ctggatctcaacagcggtaagatccttgagagtt</INSDSeq_seque
nce>
</INSDSeq>
</SequenceData>
<SequenceData sequenceIDNumber="8">
<INSDSeq>
<INSDSeq_length>34</INSDSeq_length>
<INSDSeq_moltype>RNA</INSDSeq_moltype>
<INSDSeq_division>PAT</INSDSeq_division>
<INSDSeq_feature-table>
<INSDFeature>
<INSDFeature_key>source</INSDFeature_key>
<INSDFeature_location>1..34</INSDFeature_location>
<INSDFeature_quals>
<INSDQualifier>
<INSDQualifier_name>mol_type</INSDQualifier_name>
<INSDQualifier_value>other RNA</INSDQualifier_value>
</INSDQualifier>
<INSDQualifier>
<INSDQualifier_name>organism</INSDQualifier_name>
<INSDQualifier_value>bla-TEM-1B</INSDQualifier_value>
</INSDQualifier>
</INSDFeature_quals>
</INSDFeature>
</INSDSeq_feature-table>
<INSDSeq_sequence>cttaccatctggccccagtgctgcaatgataccg</INSDSeq_seque
nce>
</INSDSeq>
</SequenceData>
</ST26SequenceListing>
<---
| название | год | авторы | номер документа |
|---|---|---|---|
| Способ получения препарата рибонуклеопротеинового комплекса CRISPR-Cas и препарат для выявления гена антибиотикоустойчивости bla-TEM-1B в ультранизких концентрациях | 2023 |
|
RU2820307C1 |
| Система CRISPR-Cas12 для выявления гена антибиотикоустойчивости bla-TEM-1B в ультранизких концентрациях | 2023 |
|
RU2829103C1 |
| Набор CRISPR-Cas12 для выявления гена антибиотикоустойчивости bla-NDM-1 в ультранизких концентрациях (варианты) | 2024 |
|
RU2839482C1 |
| Способ обнаружения гена антибиотикоустойчивости bla-OXA-1 в ультранизких концентрациях и специфические олигонуклеотиды для использования в способе | 2024 |
|
RU2841370C1 |
| Система CRISPR-Cas12 для выявления гена антибиотикоустойчивости bla-OXA-1 в ультранизких концентрациях | 2024 |
|
RU2839762C1 |
| Способ получения препарата рибонуклеопротеинового комплекса CRISPR-Cas и препарат для выявления гена антибиотикоустойчивости bla-NDM-1 в ультранизких концентрациях | 2024 |
|
RU2839484C1 |
| Способ обнаружения гена антибиотикоустойчивости bla-NDM-1 в ультранизких концентрациях и специфические олигонуклеотиды для использования в способе | 2024 |
|
RU2841369C1 |
| Система CRISPR-Cas12 для выявления гена антибиотикоустойчивости bla-NDM-1 в ультранизких концентрациях | 2024 |
|
RU2839761C1 |
| Способ получения препарата рибонуклеопротеинового комплекса CRISPR-Cas и препарат для выявления гена антибиотикоустойчивости bla-OXA-1 в ультранизких концентрациях | 2024 |
|
RU2839763C1 |
| Набор CRISPR-Cas12 для выявления гена антибиотикоустойчивости bla-OXA-1 в ультранизких концентрациях (варианты) | 2024 |
|
RU2839486C1 |

Изобретение относится к области биотехнологии. Описана группа изобретений, включающая способ обнаружения гена антибиотикоустойчивости bla-TEM-1B, специфический олигонуклеотид для предварительной амплификации высококонсервативного фрагмента гена антибиотикоустойчивости bla-TEM-1B и набор для использования в способе обнаружения гена антибиотикоустойчивости bla-TEM-1B. В одном варианте реализации способ включает стадии проведения предварительной амплификации материала от образца пациента, предположительно содержащего ген антибиотикоустойчивости bla-TEM-1B, приготовление реакционной смеси для детекции и проведение 30-60 циклов детекции в амплификаторе с обнаружением таким образом гена антибиотикоустойчивости bla-TEM-1B. Изобретение расширяет арсенал средств обнаружения гена антибиотикоустойчивости bla-TEM-1B. 3 н. и 2 з.п. ф-лы, 10 ил., 4 табл., 5 пр.
1. Способ обнаружения гена антибиотикоустойчивости bla-TEM-1B, содержащий:
i) проведение предварительной амплификации материала образца от пациента, предположительно содержащего ген антибиотикоустойчивости bla-TEM-1B, с использованием одного или нескольких специфических олигонуклеотидов, выбранных из SEQ ID NO: 7, 8, с целью получения мишени – предварительно амплифицированного фрагмента гена антибиотикоустойчивости bla-TEM-1B,
ii) приготовление реакционной смеси для детекции, содержащей мишень, полученную на стадии (i); рибонуклеопротеиновый комплекс системы CRISPR-Cas, сформированный из РНК-направляемой ДНК-эндонуклеазы LbCpf1 из Lachnospiraceae, и по меньшей мере одной направляющей РНК c SEQ ID NO: 1-6; флюоресцентный зонд и буфер для детекции,
iii) проведение 30-60 циклов детекции в реакционной смеси, полученной на стадии (ii), в амплификаторе,
с обнаружением таким образом гена антибиотикоустойчивости bla-TEM-1B.
2. Способ по п.1, где предварительно амплифицированный фрагмент гена антибиотикоустойчивости bla-TEM-1B представлен фрагментом размером 618 п.о. гена антибиотикоустойчивости bla-TEM-1B.
3. Способ по п.1 или 2, где способ обеспечивает выявление гена антибиотикоустойчивости bla-TEM-1B в ультранизких концентрациях, вплоть до единичных копий ДНК.
4. Специфический олигонуклеотид, выбранный из SEQ ID NO: 7, 8, для использования в способе по пп.1, 2 или 3 для предварительной амплификации высококонсервативного фрагмента гена антибиотикоустойчивости bla-TEM-1B, который распознается рибонуклеопротеиновым комплексом.
5. Набор для использования в способе обнаружения гена антибиотикоустойчивости bla-TEM-1B по пп.1, 2 или 3, содержащий один или несколько специфических олигонуклеотидов по п.4, рибонуклеопротеиновый комплекс системы CRISPR-Cas, сформированный из РНК-направляемой ДНК-эндонуклеазы LbCpf1 из Lachnospiraceae, и по меньшей мере одной направляющей РНК c SEQ ID NO: 1-6; флюоресцентный зонд, буфер для детекции и инструкцию по применению.
| Способ обнаружения гена антибиотикоустойчивости blaVIM-2 (металло-бета-лактамаза класс B VIM-2) Pseudomonas aeruginosa в ультранизких концентрациях и специфические олигонуклеотиды для использования в способе | 2020 |
|
RU2734520C1 |
| Способ обнаружения гена антибиотикоустойчивости mecA Staphylococcus aureus в ультранизких концентрациях и специфические олигонуклеотиды для использования в способе | 2021 |
|
RU2782588C1 |
| Chen J | |||
| S | |||
| et al | |||
| Способ гальванического снятия позолоты с серебряных изделий без заметного изменения их формы | 1923 |
|
SU12A1 |
| Science, 2018, 360 (6387), p | |||
| СПОСОБ ПОЛУЧЕНИЯ АЗОПИГМЕНТОВ | 1925 |
|
SU436A1 |
| Riano I | |||
| et al | |||
| Detection and characterization of extended-spectrum β-lactamases in Salmonella enterica strains of healthy food animals in Spain | |||
Авторы
Даты
2024-06-03—Публикация
2023-12-05—Подача