Данные родственных заявок
Эта заявка испрашивает приоритет по Предварительной заявки на патент США № 61/779,169, поданной 13 марта 2013 года и Предварительной заявки на патент США № 61/738,355, поданной 17 декабря 2012, каждая из которых включена тем самым здесь ссылкой в их полном виде для всех целей.
Заявление интересов правительства
Данное изобретение было произведено с поддержкой правительства под P50 HG005550, решением Национальных Институтов Здоровья. Правительство имеет определенные права на это изобретение.
Уровень техники
Системы CRISPR бактерий и архебактерий основаны на crРНК в комплексе с белками Cas для направленной деградации комплементарных последовательностей, присутствующих во вторгнувшейся вирусной и плазмидной ДНК (1-3). Недавнее in vitro воссоздание системы CRISPR типа II S. pyogenes продемонстрировало, что crРНК, слитая с нормальной транс-кодируемой tracrРНК, является достаточной для направления белка Cas9 для последовательность-специфического расщепления ДНК-последовательностей-мишеней, соответствующих crРНК (4).
Сущность изобретения
В настоящем описании содержаться ссылки в виде цифр на документы, которые перечислены в конце данного описания изобретения. Документ, соответствующий этой цифре, включен посредством отсылки в это описание изобретения также как если бы он был приведен полностью.
Согласно одному аспекту данного изобретения, эукариотическую клетку трансфицируют двухкомпонентной системой, включающей РНК, комплементарную геномной ДНК, и фермент, который взаимодействует с этой РНК. Эти РНК и фермент экспрессируются клеткой. Затем РНК из комплекса РНК/фермент связывается с комплементарной геномной ДНК. Затем фермент выполняет функцию, такую как расщепление этой геномной ДНК. Данная РНК содержит между приблизительно 10 нуклеотидов – приблизительно 250 нуклеотидов. Например РНК включает приблизительно 20 нуклеотидов – приблизительно 100 нуклеотидов. Согласно некоторым аспектам, фермент может выполнять любую желаемую функцию, для которой он был сконструирован, сайт-специфическим образом. Согласно одному аспекту, этой эукариотической клеткой является клетка дрожжей, клетка растения или клетка млекопитающего. Согласно одному аспекту, фермент расщепляет геномные последовательности, на которые нацелены РНК-последовательности (см. ссылки (4-6)), создавая таким образом эукариотическую клетку с измененным геномом.
Согласно одному аспекту, данное изобретение обеспечивает способ генетического изменения клетки человека включением в геном этой клетки нуклеиновой кислоты, кодирующей РНК, комплементарную геномной ДНК, и нуклеиновой кислоты, кодирующей фермент, который осуществляет желаемое воздействие на геномную ДНК. Согласно одному аспекту, РНК и фермент экспрессируются. Согласно одному аспекту, эта РНК гибридизируются с комплементарной геномной ДНК. Согласно одному аспекту, этот фермент активируется для осуществления желаемой функции, такой как расщепление сайт-специфическим образом, когда РНК гибридизируется с комплементарной геномной ДНК. Согласно одному аспекту, эта РНК и этот фермент являются компонентами бактериальной системы CRISPR Type II.
Согласно одному аспекту, предлагается способ изменения эукариотической клетки, включающий трансфекцию этой эукариотической клетки нуклеиновой кислотой, кодирующей РНК, комплементарную геномной ДНК этой эукариотической клетки, трансфекцию этой эукариотической клетки нуклеиновой кислотой, кодирующей фермент, который взаимодействует с этой РНК и расщепляет эту геномную ДНК сайт-специфическим образом, где эта клетка экспрессирует эти РНК и фермент, где эта РНК связывается с комплементарной геномной ДНК и указанный фермент расщепляет геномную ДНК сайт-специфическим образом. Согласно одному аспекту, ферментом является Cas9 или модифицированный Cas9 или гомолог Cas9. Согласно одному аспекту, эукариотической клеткой является клетка дрожжей, клетка растения или клетка млекопитающего. Согласно одному аспекту, РНК содержит между приблизительно 10 – приблизительно 250 нуклеотидов. Согласно следующему аспекту, РНК содержит между приблизительно 20 – приблизительно 250 нуклеотидов. Согласно еще одному аспекту, РНК содержит между приблизительно 20 до приблизительно 100 нуклеотидов.
Согласно дальнейшему аспекту, предлагается способ изменения клетки человека, включающий трансфекцию клетки человека нуклеиновой кислотой, кодирующей РНК, комплементарную геномной ДНК эукариотической клетки, трансфекцию клетки человека нуклеиновой кислотой, кодирующей фермент, который взаимодействует с РНК и расщепляет геномную ДНК сайт-специфическим образом, где эта клетка человека экспрессирует эти РНК и фермент, где РНК связывается с комплементарной геномной ДНК, а фермент расщепляет эту геномную ДНК сайт-специфическим образом. Согласно одному аспекту, этим ферментом является Cas9 или модифицированный Cas9 или гомолог Cas9. Согласно одному аспекту, РНК содержит между приблизительно 10 – приблизительно 250 нуклеотидов. Согласно следующему аспекту, РНК содержит между приблизительно 20 – приблизительно 100 нуклеотидов.
Согласно другому аспекту, предложен способ изменения эукариотической клетки во множестве сайтов геномной ДНК, включающий трансфекцию эукариотической клетки множеством нуклеиновых кислот, кодирующих РНК, комплементарные различным сайтам геномной ДНК этой эукариотической клетки, трансфекцию этой эукариотической клетки нуклеиновой кислотой, кодирующей фермент, который взаимодействует с этими РНК и расщепляет геномную ДНК сайт-специфическим образом, где эта клетка экспрессирует эти РНК и фермент, где РНК связываются с комплементарными участками геномной ДНК а фермент расщепляет эти геномные ДНК сайт-специфическим образом. Согласно дополнительному аспекту, этим ферментом является Cas9. Согласно еще одному аспекту, этой эукариотической клеткой является клетка дрожжей, клетка растения или клетка млекопитающего. Согласно следующему аспекту, РНК содержит между приблизительно 10 – приблизительно 250 нуклеотидов. Согласно дальнейшему аспекту, эта РНК содержит между приблизительно 20 – приблизительно 100 нуклеотидов.
Подробное описание
Согласно одному аспекту, синтезировали кодон-оптимизированную с учетом использования кодонов у человека версию белка Cas9, содержащую с С-конца сигнал ядерной локализации SV40, и затем клонировали в систему экспрессии млекопитающих (фиг. 1A и фиг. 3A). Соответственно, на фиг. 1 изображено редактирование генома в клетках человека с использованием сконструированной системы CRISPR Type II. Как показано на фиг. 1A, РНК-направляемое нацеливание в клетках человека включает коэкспрессию белка Cas9, несущего с С-конца сигнал ядерной локализации SV40, с одной или несколькими направляющими РНК (гидРНК), которые экспрессировали с использованием промотора U6 полимеразы III. Cas9 раскручивает ДНК-дуплекс и расщепляет обе цепи после узнавания последовательности-мишени гидРНК, но только если на 3’-конце присутствует правильный смежный с протоспейсером мотив (PAM). В принципе, можно нацелить систему на любую геномную последовательность формы GN20GG. Как показано на фиг. 1В, интегрировавшая в геном последовательность, кодирующая GFP, разрушается путем инсерции стоп-кодона и геномного фрагмента в 68 п.н. из локуса AAVS1. Реконструкция этой GFP-последовательности путем гомологичной рекомбинацией (HR) с помощью подходящей донорной последовательностью приводит к получению GFP+-клеток, которые могут быть количественно определены посредством FACS. Последовательности-мишени гидРНК T1 и T2 входят в состав фрагмента AAVS1. Сайты связывания двух половин гетеродимера нуклеазы TAL (TALEN) подчеркнуты. На фиг. 1C приведена столбчатая диаграмма эффективности HR, индуцированной T1, T2 и TALEN-опосредованной нуклеазной активностью в локусе-мишени, что было измерено с использованием FACS. Репрезентативные графики FACS и микроскопические изображения этих клеток-мишеней изображены ниже (шкала столбчатой диаграммы равна 10 микрон). Приведенные данные являются средним +/- SEM (стандартная ошибка среднего (N=3).
Согласно одному аспекту, для направления Cas9 для расщепления представляющих интерес последовательностей, с помощью промотора U6 полимеразы III экспрессируют слитые транскрипты crРНК-tracrРНК, далее называемые как РНК-направляющие (гидРНК). Согласно дополнительному аспекту, гидРНК непосредственно транскрибируются клеткой. Этот аспект имеет то преимущество, что позволяет избежать реконструирование системы процессинга РНК, используемого бактериальными системами CRISPR (фиг. 1A и фиг. 3B) (см. ссылки (4, 7-9)). Согласно еще одному аспекту, предложен способ для изменения геномной ДНК, использующий инициацию транскрипции U6 c G и PAM (смежный с протоспейсером мотив) последовательности-NGG, за которым следует мишень crРНК из 20 п.н. Согласно этому аспекту, геномный сайт-мишень находится в форме GN20GG (см. фиг. 3C).
Согласно следующему аспекту, предложен репортерный анализ GFP (фиг. 1B) в клетках 293T, который подобен описанному ранее анализу (см. ссылку (10)), для тестирования функциональности описанных здесь способов инженерии генома. Согласно этому аспекту, была получена стабильная клеточная линия, содержащая интегрированную в геном последовательность, кодирующую GFP, которая прервана инсерцией стоп-кодона и фрагмента в 68 п.н. из локуса AAVS1, что приводит к тому, что экспрессируемый белковый фрагмент не флуоресцентный. Гомологичная рекомбинация (HR), использующая подходящий репарирующий донор, может восстановить нормальную последовательность GFP, что позволяет специалисту определить количество полученных GFP+-клеток с помощью сортировки клеток с активированной флуоресценцией (FACS).
Согласно следующему аспекту, предложен способ гомологичной рекомбинации (HR). Конструировали две гидРНК, T1 и T2, которые нацелены на промежуточный фрагмент AAVS1 (фиг. 1b). Сравнивали их активность с активностью ранее описанного гетеродимера TAL-эффекторной нуклеазы (TALEN), нацеленного на ту же самую область (см. ссылку (11)). Со всеми тремя нацеливающими реагентами наблюдались успешные события HR, где частота коррекции гена с использованием подхода с T1 и T2 гидРНК, достигала 3% и 8%, соответственно (фиг. 1C). Этот РНК-опосредованный процесс редактирования оказался примечательно быстрым, и первые детектируемые GFP+-клетки появились через ~20 часов после трансфекции, в сравнении с ~40 часами для AAVS1 TALEN. HR наблюдали только после одновременного введения донора репарации, белка Cas9, и гидРНК, что является подтверждением того, что все эти компоненты требуются для редактирования генома (фиг. 4). Хотя явной токсичности, ассоциированной с экспрессией с Cas9/crРНК не отмечали, работа с ZFN и TALEN ранее показала, что разрыв только одной цепи дополнительно уменьшает токсичность. Таким образом, тестировали мутант Cas9D10A, о котором известно, что он функционирует в качестве никазы in vitro, что давало сходную HR (гомологичную рекомбинацию), но более низкую частоту негомологичного соединения концов (NHEJ) (фиг. 5) (см. ссылки (4, 5)). В соответствии с (4), где было показано что белок родственный Cas9 разрезает обе цепи на расстоянии 6 п.н. слева по ходу транскрипции от PAM, данные NHEJ подтвердили, что большинство делеций или инсерций происходит на 3’-конце последовательности-мишени (фиг. 5B). Было также подтверждено, что мутация геномного сайта-мишени предотвращает воздействие гидРНК на HR в этом локусе, демонстрируя, что CRISPR-опосредованное редактирование генома является последовательность-специфическим (фиг. 6). Было показано, что два сайта нацеливания гидРНК в гене GFP, а также три дополнительных фрагмента нацеливания гидРНК из гомологичных районов ДНКметилтрансферазы 3a (DNMT3a) и гена DNMT3b могут последовательность-специфическим образом индуцировать значимую гомологичную рекомбинацию (HR) в сконструированных линиях репортерных клеток (фиг. 7, 8). Вместе эти результаты подтверждают, что РНК-направляемое нацеливание на геном в клетках человека индуцирует сильную гомологичную рекомбинацию (HR) во множественных сайтах-мишенях.
Согласно некоторым аспектам, был модифицирован нативный локус. гидРНК использовали для нацеливания на локус AAVS1, локализованный в гене PPP1R12C на хромосоме 19, который повсеместно экспрессируется в большинстве тканей (фиг. 2A) и в клетках iPS человека 293T, K562 и PGP1 (см. ссылку (12)), и анализировали результаты с помощью next-gen секвенирования локуса мишени. Соответственно фиг. 2 предложена для описания РНК-направляемого редактирование генома в нативном локусе AAVS1 во множестве типов клеток. Как показано на фиг. 2А, T1 (красная) и T2 (зеленая) последовательности-мишени гидРНК находятся в интроне гена PPP1R12C в локусе AAVS1 хромосомы 19. Как показано на фиг. 2B, определены общее количество и локализация делеций, вызываемых NHEJ в клетках iPS 293T, K562 и PGP1 после экспрессии Cas9 и либо T1, либо T2 гидРНК, что было сделано с помощью next-gen секвенирования. Красные и зеленые штрихпунктирные линии обозначают границы сайтов таргетинга T1 и T2 гидРНК. Частота NHEJ для T1 и T2 гидРНК были 10% и 25% и 25% в 293T, 13% и 38% в K562 и 2% и 4% в клетках PGP1 iPS, соответственно. На фиг. 2C изображена схема ДНК-донора для HR в локусе AAVS1, и показаны местоположения секвенирующих праймеров (стрелками) для детектирования успешных событий нацеливания. Как это видно из фиг. 2D, ПЦР-анализ спустя три дня после трансфекции выявил, что только клетки, экспрессирующие донор, Cas9 и T2 гидРНК, показали успешные события HR. Как показано на фиг. 2Е, успешная HR (гомологичная рекомбинация) подтверждалась секвенированием ПЦР-ампликона методом Sanger, показавшем, что ожидаемые ДНК-основания присутствуют на обеих границах геном-донор и донор-вставка. Как показано на фиг. 2F в течение 2 недель с использованием пуромицина отбирали «успешно нацеленные» клоны клеток 293T. Показаны изображения под микроскопом двух репрезентативных GFP+-клонов (масштабная линейка (метка) равна 100 микрон).
В соответствии с результатами для GFP-репортерного анализа, высокую частоту событий NHEJ наблюдали в эндогенном локусе для всех трех типов клеток. Для двух гидРНК T1 и T2 частота NHEJ достигала 10 и 25% в 293T, 13 и 38% в K562 и 2 и 4% в индуцированных плюрипотентных стволовых (iPS) клетках PGP1, соответственно (фиг. 2B). Явная токсичность не наблюдалась от экспрессии Cas9 и crРНК, которая требуется для индукции NHEJ в любом из этих типов клеток (фиг. 9). Как и ожидалось, NHEJ-опосредованные делеции для T1 и T2 сосредоточивались около положений сайта-мишени, что дополнительно подтверждает специфичность к последовательности у этого процесса нацеливания (фиг. 9, 10, 11). Одновременное введение как T1, так и T2 гидРНК приводило к высокоэффективной делеции промежуточного фрагмента 19 п.н. (фиг. 10), демонстрируя, что мультиплексное редактирование геномных локусов выполнимо с использованием этого подхода.
Согласно одному аспекту, HR используют для интеграции либо конструкта дцДНК-донора (см. ссылку (13)), либо олиго-донора в нативный локус AAVS1 (фиг. 2C, фиг. 12). HR-опосредуемую интеграцию подтверждали с использованием как ПЦР (фиг. 2D, фиг. 12) и так и -секвенирования по Sanger (дидезоксисеквенирования) (фиг. 2E). Клоны 293T или iPS легко выделяли из пула модифицированных клеток с использованием селекции на пуромицине на протяжении двух недель (фиг. 2F, фиг. 12). Эти результаты демонстрируют, что Cas9 способен эффективно встраивать чужеродную ДНК в эндогенные локусы в клетках человека. Таким образом, один аспект данного изобретения включает в себя способ интеграции чужеродной ДНК в геном клетки с использованием гомологичной рекомбинации и Cas9.
Согласно одному аспекту, предлагается РНК-направляемая система редактирования генома, которая может быть легко адаптирована для модификации других геномных сайтов путем простой модификации последовательности гидРНК-экспрессирующего вектора, для того чтобы она совпала с совместимой последовательностью в представляющем интерес локусе. Согласно этому аспекту, создавали 190,000 специфически гидРНК-направляющих последовательностей, нацеленных на около 40,5% экзонов генов в геноме человека. Эти последовательности-мишени были включены в формат 200 п.н., совместимый с мультиплексным синтезом на ДНК-эрреях (ранжированных рядах ДНК) (см. ссылку (14)) (фиг. 13). Согласно этому аспекту, обеспечена готовая к использованию система направления на потенциальные сайты-мишени в полноразмерном геноме человека и методология для мультиплексного синтеза гидРНК.
Согласно одному аспекту, предлагаются способы для мультиплексных геномных изменений в клетке с использованием одной или более или множества систем РНК/фермент, описанных здесь, для изменения генома клетки во множестве местоположений. Согласно одному аспекту, сайты-мишени идеально совпадают с последовательностью РАМ NGG и с 8-12 п.о. затравочной последовательности на 3’-конце этой гидРНК. Согласно некоторым аспектам, не требуется абсолютное совпадение для оставшихся 8-12 оснований. Согласно ряду аспектов, Cas9 будет функционировать с отдельными ошибочными спариваниями на 5’-конце. Согласно некоторым определенным аспектам, структура хроматина в локуса-мишени и эпигенетическое состояние могут влиять на эффективность функционирования Cas9. Согласно некоторым аспектам, в качестве пригодных ферментов включены гомологи Cas9, имеющие высокую специфичность. Специалист в данной области будет способен идентифицировать или сконструировать подходящие гомологи Cas9. Согласно одному аспекту, CRISPR-таргетируемые последовательности включают те последовательности, имеющие другие требования PAM (см. ссылку (9)) или направленную эволюцию. Согласно одному аспекту, инактивирование одного из доменов Cas9-нуклеазы увеличивает скорость HR относительно NHEJ и может уменьшать токсичность (фиг. 3А, фиг. 5) (4, 5), тогда как инактивирование обоих доменов может заставить Cas9 функционировать в качестве перенастраиваемого ДНК-связывающего белка. Варианты данного изобретения имеют широкое применения в синтетической биологии (см. ссылки (21, 22)), прямой и мультиплексной перестройке генных сетей (см. ссылки (13, 23)), и направленной ex vivo (см. ссылки (24-26)) и in vivo генотерапии (см. ссылку (27)).
В соответствии с некоторыми аспектами, предложен "переконструированный организм" в качестве модельной системы для биологического открытий и скрининга in vivo. Согласно одному аспекту, создана "переконструированная мышь", несущая индуцируемый трансген Cas9, и локализованную доставку (с использованием аденоассоциированных вирусов, например) библиотек гидРНК, направленных на множество генов или регуляторных элементов, что позволяет проводить скрининг на мутации, которые приводят к появлению опухолей в этом типе ткани-мишени. Применение гомологов Cas9 или вариантов нуклеаза-нуль, несущих эффекторные домены (такие как активаторы), позволяет активировать или подавлять один или многие гены in vivo. Согласно этому аспекту, специалист мог бы проводить скрининг на факторы, которые могут создавать фенотипы, такие как: регенерация ткани, транс-дифференциации и т.д. Согласно некоторым аспектам, (a) применение ДНК-эрреев позволяет выполнять мультиплексный синтез определенных библиотек гидРНК (ссылка на фиг. 13); и (b) поскольку гидРНК имеет малый размер (ссылка на фиг. 3b), их упаковывают и доставляют с использованием множества невирусных или вирусных способов доставки.
Согласно одному аспекту, наблюдались более низкие токсичности когда в геномной инженерии использовались “никазы”, что достигалось инактивированием одного из доменов Cas9-нуклеазы, вырезающем либо цепь ДНК, спарившуюся с РНК, либо вырезающая ее комплемент. Инактивирование обоих доменов позволяет Cas9 функционировать в качестве перенацеливаемого ДНК-связывающего белка. Согласно одному аспекту, этот перенацеленный ДНК-связывающий белок Cas9 присоединяют(a) к доменам активации или репрессии транскрипции для модуляции экспрессии гена-мишени, включающей в том числе ремоделирование хроматина, модификацию гистонов, сайленсинг, инсуляции, прямых взаимодействий с аппаратом транскрипции;
(b) к доменам нуклеазы, таким как FokI, для возможности обеспечения «высоко специфического» контингента редактирования генома после димеризации смежных комплексов гидРНК-Cas9;
(c) к флуоресцентным белкам для визуализации геномных локусов и динамики хромосом; или
(d) к другим флуоресцентным молекулам, таким как связывающиеся с белками или нуклеиновыми кислотами органические флуорофоры, квантовые точки, молекулярные маяки и эхо-зонды или заменители молекулярных маяков;
(e) с мультивалентным лиганд-связывающим доменам белков, что делает возможной программируемую манипуляцию с 3D-архитектурой генома.
Согласно еще одному аспекту, компоненты транскрипционной активации и репрессии могут использовать системы CRISPR, которые природно или синтетически ортогональны, так что гидРНК связываются только с активатором или репрессором класса Cas. Это позволяет иметь большой набор гидРНК для настраивания множества мишеней.
Согласно некоторым аспектам, применение гидРНК дает больше возможность мультиплексирования по сравнению с мРНК, частично вследствие меньшего размера -- 100 против. 2000 нуклеотидной длины, соответственно. Это является особенно ценным, с учетом того, что доставка нуклеиновой кислоты ограничена размером, например в случае упаковки в вирус. Это позволяет получить множественные случаи расщепления, никинга, активации или репрессии – или их комбинации. Эта способность легко нацеливаться на множественные регуляторные мишени позволяет грубо или тонкое настраивать систему или регуляторные сети не ограничиваясь природными регуляторными циклами, начинающимися с специфических регуляторных факторов (например, 4 мРНК, используемых в перепрограммировании фибробластов в индуцированные полипотентные стволовые клетки (IPSC)). Примеры мультиплексированных применений включают в себя::
1. Установление (главной и минорной) аллелей гистосовместимости, гаплотипов и генотипов для трансплантации ткани/органа у человека (или животного) . Этот аспект обеспечивает, например, гомозиготные линии клеток HLA или гуманизированные породы животных – или - набор гидРНК, способных перекладывать такие аллели HLA для других желаемых линий или пород.
2. Мультиплексные мутации цис-регуляторных элементов (CRE = сигналы для транскрипции, сплайсинга, трансляции, фолдинга, деградации РНК или белка, и т.д.) в одной клетке (или коллекции клеток), что может быть использовано для эффективного исследования сложной совокупности регуляторного взаимодействия, происходящих при нормальном развитии или патологических, синтетических или фармацевтических сценариях. Согласно этому аспекту, данные CRE являются (или могут быть сделаны) несколько ортогональными (т.е. с низкими взаимными помехами), так что многие могут тестироваться в одинаковой обстановке) -- например, в дорогостоящей динамической модели эмбрионов животного. Одним вариантом применения является совместное использование с флуоресцентным секвенированием РНК in situ (FISSeq).
3. Мультиплексные комбинации мутаций CRE и/или эпигенетической активации или репрессии CRE могут быть использованы для изменения или репрограммирования iPSC или ESC или других стволовых клеток или нестволовых клеток в любой тип клеток или комбинацию клеточных типов для использования в органах-на-чипах или других культурах клеток или органов для целей тестирования фармацевтических препаратов (малых молекул, белков, РНК, клеток, клеток животного, растения или микробных клеток, аэрозолей и других способов доставки), стратегий трансплантации, стратегий персонализации и т.д.
4. Получение мультиплексных мутантных клеток человека для использования в диагностическом тестировании (и/или секвенировании ДНК) для медицинской генетики. До той степени, пока хромосомная локализация и окружение аллеля генома человека (или эпигенетической метки) могут влиять на точность клинико-генетического диагноза, скорее важно иметь аллели, присутствующие в правильном местоположении в эталонном геноме, чем в эктопическом (иначе трансгенном) местоположении или в отдельном куске синтетической ДНК. Одним вариантом воплощения является серия независимых клеточных линий по одной на каждый диагностический SNP (однонуклеотидный полиморфизм) человека, или структурный вариант. Альтернативно, один вариант включает в себя мультиплексные наборы аллелей в одной и той же клетке. В некоторых случаях будут желательными мультиплексные изменения в одном гене (или множестве генов), при условии независимого тестирования. В других случаях, конкретные комбинации аллелей-гаплотипы позволяют тестировать методы секвенирования (генотипирования), которые точно устанавливают фазу гаплотипа (т.е. затронута ли одна или обе копии гена в отдельном субъекте или типе соматических клеток).
5. Повторяющиеся элементы или эндогенные вирусные элементы могут быть мишенями сконструированных систем Cas+ гидРНК в клетках микробах, растений, животных или человека для уменьшения вредной транспозиции или способствования секвенированию или других аналитических геномных/транскриптомных/протеомных/диагностических инструментах (в которых почти идентичные копии могут быть проблематическими).
Следующие ссылки, идентифицированные цифрами в предыдущем разделе, включены здесь посредством ссылки в их полном виде.
1. B. Wiedenheft, S. H. Sternberg, J. A. Doudna, Nature 482, 331 (Feb 16, 2012).
2. D. Bhaya, M. Davison, R. Barrangou, Annual review of genetics 45, 273 (2011).
3. M. P. Terns, R. M. Terns, Current opinion in microbiology 14, 321 (Jun, 2011).
4. M. Jinek et al., Science 337, 816 (Aug 17, 2012).
5. G. Gasiunas, R. Barrangou, P. Horvath, V. Siksnys, Proceedings of the National Academy of Sciences of the United States of America 109, E2579 (Sep 25, 2012).
6. R. Sapranauskas et al., Nucleic acids research 39, 9275 (Nov, 2011).
7. T. R. Brummelkamp, R. Bernards, R. Agami, Science 296, 550 (Apr 19, 2002).
8. M. Miyagishi, K. Taira, Nature biotechnology 20, 497 (May, 2002).
9. E. Deltcheva et al., Nature 471, 602 (Mar 31, 2011).
10. J. Zou, P. Mali, X. Huang, S. N. Dowey, L. Cheng, Blood 118, 4599 (Oct 27, 2011).
11. N. E. Sanjana et al., Nature protocols 7, 171 (Jan, 2012).
12. J. H. Lee et al., PLoS Genet 5, e1000718 (Nov, 2009).
13. D. Hockemeyer et al., Nature biotechnology 27, 851 (Sep, 2009).
14. S. Kosuri et al., Nature biotechnology 28, 1295 (Dec, 2010).
15. V. Pattanayak, C. L. Ramirez, J. K. Joung, D. R. Liu, Nature methods 8, 765 (Sep, 2011).
16. N. M. King, O. Cohen-Haguenauer, Molecular therapy : the journal of the American Society of Gene Therapy 16, 432 (Mar, 2008).
17. Y. G. Kim, J. Cha, S. Chandrasegaran, Proceedings of the National Academy of Sciences of the United States of America 93, 1156 (Feb 6, 1996).
18. E. J. Rebar, C. O. Pabo, Science 263, 671 (Feb 4, 1994).
19. J. Boch et al., Science 326, 1509 (Dec 11, 2009).
20. M. J. Moscou, A. J. Bogdanove, Science 326, 1501 (Dec 11, 2009).
21. A. S. Khalil, J. J. Collins, Nature reviews. Genetics 11, 367 (May, 2010).
22. P. E. Purnick, R. Weiss, Nature reviews. Molecular cell biology 10, 410 (Jun, 2009).
23. J. Zou et al., Cell stem cell 5, 97 (Jul 2, 2009).
24. N. Holt et al., Nature biotechnology 28, 839 (Aug, 2010).
25. F. D. Urnov et al., Nature 435, 646 (Jun 2, 2005).
26. A. Lombardo et al., Nature biotechnology 25, 1298 (Nov, 2007).
27. H. Li et al., Nature 475, 217 (Jul 14, 2011).
Следующие примеры представлены в качестве репрезентативных примеров воплощения данного изобретения. Эти примеры не должны пониматься как ограничивающие объем данного изобретения, так как эти и другие эквивалентные варианты воплощения будут очевидными в свете данного описания изобретения, фигур и сопутствующей формулы изобретения.
Пример I
Система CRISPR-Cas Типа II
Согласно одному аспекту, в вариантах воплощения этого изобретения используют короткую РНК для идентификации чужеродных нуклеиновых кислот для действия на них посредством нуклеазы в эукариотической клетке. Согласно некоторому аспекту данного изобретения, эукариотическую клетку изменяют для включения в ее геном нуклеиновых кислот, кодирующие одну или несколько коротких РНК и одну или несколько нуклеаз, которые активируются связыванием короткой РНК с последовательностью ДНК-мишени. Согласно некоторым аспектам, примерные системы короткая РНК / фермент могут быть идентифицированы в бактериях или архебактериях, такие как (CRISPR)/CRISPR-ассоциированные (Cas) системы, которые используют короткую РНК для направленной деградации чужеродных нуклеиновых кислот. Защита CRISPR (“Короткие палиндромные повторы, регулярно расположенные кластерами”) включает в себя приобретение и интеграцию новых нацеливающих “спейсеров” из внедряющихся вирусных и плазмидных ДНК в локус CRISPR, экспрессию и процессинг коротких направляющих CRISPR РНК (crРНК), состоящих из единиц спейсер-повтор, и расщепление нуклеиновых кислот (наиболее часто ДНК) комплементарных этому спейсеру.
Известны три класса систем CRISPR и на них ссылаются как на Тип I, Тип II или Тип III. Согласно одному аспекту, особенно полезным ферментом используемым в соответствии с настоящим изобретением для расщепления дцДНК является одноэффекторный фермент, Cas9, характерный для Типа II. (См. ссылку (1)). В бактериях, эта эффекторная система Tипа II состоит из длинной пре-crРНК, транскрибируемой из спейсер-содержащего локуса CRISPR, мультифункционального белка Cas9 и tracrРНК, важной для процессинга гидРНК. Эти tracrРНК гибридизируются с областями повторов, разделяющими спейсеры pre-crРНК, инициируя расщепление дцРНК эндогенной РНКазой III, за которым следует второе событие расщепления в пределах каждого спейсер посредством Cas9, что в результате дает зрелые crРНК, которые остаются ассоциированными с tracrРНК и Cas9. Согласно одному аспекту, эукариотические клетки данного изобретения конструируют таким образом, чтобы избежать использования РНКазы III и процессинга crРНК в целом. См. ссылку (2).
Согласно одному аспекту, фермент данного описания изобретения, такой как Cas9, раскручивает ДНК-дуплекс и ищет последовательности, соответствующие crРНК, для расщепления. Узнавание мишени осуществляется после детектирования комплементарности между последовательностью “протоспейсера” в ДНК-мишени и сохранившейся спейсерной последовательностью в crРНК. Важно, что Cas9 разрезает ДНК только в том случае, если на 3’-конце присутствует корректный смежный с протоспейсером мотив (РАМ). Согласно некоторым аспектам, может быть использован другой смежный с протоспейсером мотив. Например, система S. pyogenes требует последовательность NGG, где N может быть любым нуклеотидом. Системы S. thermophilus Type II требуют NGGNG (см. ссылку (3)) и NNAGAAW (см. ссылку (4)), соответственно, тогда как другие системы S. mutans допускают NGG или NAAR (см. ссылку (5)). Биоинформатические анализы создали обширные базы данных локусов CRISPR в различных бактериях, которые могут служить для идентификации дополнительных пригодных PAM и расширить набор последовательностей, на которые нацеливается CRISPR (см. ссылки (6, 7)). В S. thermophilus, Cas9 генерирует двухцепочечный разрыв с тупыми концами на расстоянии 3 п.н. перед 3’-концом протоспейсера (см. ссылку (8)), процесс, опосредуемый двумя каталитическими доменами белка Cas9: HNH-доменом, который расщепляет комплементарную цепь ДНК, и RuvC-подобным доменом, который расщепляет не-комплементарную цепь (см. фиг. 1A и фиг. 3). Хотя система S. pyogenes еще не была настолько точно охарактеризована, образование двуцепочечного разрыва также происходит в направлении 3’-конца протоспейсера. Если один из этих двух доменов нуклеазы инактивирован, Cas9 будет функционировать в качестве никазы in vitro (см. ссылку (2)) и в клетках человека (см. фиг. 5).
Согласно одному аспекту, специфичность гидРНК-направляемого расщепления Cas9 используют в качестве механизма геномной инженерии в эукариотической клетке. Согласно одному аспекту, гибридизация гидРНК не должна быть 100-процентной для того, чтобы фермент распознал гибрид гидРНК/ДНК и осуществил расщепление. Может наблюдаться некоторая внецелевая активность. Например, система S. pyogenes допускает нарушение комплементарности в первых 6 основаниях из 20 п.н. зрелой спейсерной последовательности in vitro. Согласно одному аспекту, большая жесткость может быть более выгодной in vivo, когда в эталонном геноме человека имеются потенциальные внецелевые сайты совпадения (последние 14 п.н.) NGG для гидРНК. Результат этого ошибочного спаривания и активность фермента в общем виде описаны в ссылках (9), (2), (10) и (4).
Согласно некоторым аспектам, может быть улучшена специфичность. Когда интерференция является чувствительной к точке плавления гибрида гидРНК-ДНК, AT-обогащенные последовательности могут иметь меньше внецелевых сайтов. Осторожный выбор сайтов-мишеней во избежание псевдосайтов с. совпадающими последовательностями по меньшей мере в 14 п.н. в других местах генома может улучшить специфичность. Применение варианта Cas9, требующего более длинную последовательность РАМ, также может уменьшать частоту внецелевых сайтов. Направленная эволюция может улучшать Cas9-специфичность до уровня, достаточного для полного предотвращения внецелевой активности, в идеале требуя полного совпадения 20 п.н. гидРНК с минимальным PAM. Таким образом, модификация белка Cas9 является репрезентативным вариантом данного изобретения. В связи с этим, предвидится разработка новых способов, обеспечивающих много раундов эволюции в коротком временном интервале (см. ссылку (11). Системы CRISPR, полезные в данном изобретении, описаны в ссылках (12, 13).
Пример II
Конструирование плазмиды
Последовательность гена Cas9 оптимизировали с учетом использования кодонов человека и собирали с использованием Hierarchical fusion PCR assembly из 9 500 п.н. gBlock, полученных от IDT. На фиг. 3A, посвященной сконструированной системе типа II CRISPR для клеток человека, показан формат экспрессии и полная последовательность вставки cas9. Мотивы RuvC-подобный и HNH, и C-конец SV40 NLS соответственно окрашенными синим, коричневым и оранжевым цветом. Подобным образом конструировали и Cas9_D10A. Полученные полноразмерные продукты клонировали в вектор pcDNA3.3-TOPO (Invitrogen). Конструкты для экспрессии желаемой гидРНК- были заказаны в виде отдельных 455 п.н. gBlock в IDT и их либо клонировали в вектор pCR-BluntII-TOPO (Invitrogen), либо ПЦР-амплифицировали. На фиг. 3B приведена схема экспрессии на основе промотора U6 для направляющей РНК и предсказанной вторичной структуры РНК-транскрипта. Использование промотора U6 ведет к тому, что 1-ое положение в этом РНК-транскрипте будет ‘G’, и, следовательно, с использованием этого подхода можно нацелиться на все геномные сайты формы GN20GG. На фиг. 3C показаны используемые 7 гидРНК.
Векторы для репортерного анализа HR, включающего использование разорванного GFP, конструировали слиянием посредством ПЦР-сборки последовательности GFP, несущей стоп-кодон и 68 п.н. фрагмент AAVS1 (или их мутанты; см. фиг. 6), или 58 п.н. фрагменты из геномных локусов DNMT3a и DNMT3b (см. фиг. 8), собранные в лентивектор EGIP из Addgene (плазмида #26777). Затем эти лентивекторы использовали для получения стабильных линий репортера. TALEN, используемые в этом исследовании, конструировали с использованием протоколов, описанных в (14). Все ДНК-реагенты, используемые в этом исследовании, являются доступными в Addgene.
Пример III
Культура клеток
Клетки PGP1 iPS поддерживали на покрытых Matrigel (BD Biosciences)-чашках в mTeSR1 (Stemcell Technologies). Культуры пассировали каждые 5-7 дней с использованием TrypLE Express (Invitrogen). Клетки K562 выращивали и поддерживали в RPMI (Invitrogen), содержащей 15% FBS. Клетки HEK 293T культивировали в модифицированной по способу Дульбекко среде Игла (DMEM, Invitrogen), дополненной высокой концентрацией глюкозы с 10% фетальной бычьей сывороткой (FBS, Invitrogen), пенициллином/стрептомицином (пен/стреп, Invitrogen) и не-незаменимыми аминокислотами (NEAA, Invitrogen). Все клетки поддерживали при 37оС и 5% CO2 в увлажняемом инкубаторе.
Пример IV
Таргетинг генов PGP1 iPS, K562 и 293T
Клетки PGP1 iPS культивировали с ингибитором Rho-киназы (ROCK) (Calbiochem) 2 ч перед нуклеофекцией. Клетки собирали с использованием TrypLE Express (Invitrogen) и 2×106 клеток ресуспендировали в реагенте P3 (Lonza) 1 мкг плазмиды Cas9, 1 мкг гидРНК и/или 1 мкг плазмиды с донором ДНК, и осуществляли нуклеофекцию в соответствии с инструкцией изготовителя (Lonza). Затем клетки высевали на mTeSR1-покрытую чашку, дополненную ингибитором ROCK, в течение первых 24 часов. Для клеток K562, 2×106 клеток ресуспендировали в реагенте SF (Lonza) 1 мкг плазмиды Cas9, 1 мкг гидРНК и/или 1 мкг плазмиды с донором ДНК, и осуществляли нуклеофекцию в соответствии с инструкцией изготовителя (Lonza). Для 293T, 0,1×106 клеток трансфицировали 1 мкг плазмиды Cas9, 1 мкг гидРНК и/или 1 мкг плазмиды с донорной ДНК с использованием Липофектамина 2000 как в протоколах изготовителя. ДНК-доноры, используемые для таргетинга на эндогенный AAVS1 были либо дцДНК-донором (фиг. 2C), либо 90-мерным олигонуклеотидом. Первый имеет фланкирующие короткие гомологичные плечи и SA-2A-пуромицин-CaGGS-eGFP-кассету для обогащения успешно таргетированных клеток.
Эффективность нацеливания оценивали следующим образом. Клетки собирали через 3 дня после нуклеофикации и экстрагировали геномную ДНК ~1 X 106 клеток с использованием prepGEM (ZyGEM). Проводили ПЦР амплификацию района-мишени с геномной ДНК, полученной из этих клеток, и проводили глубокое секвенирование ампликонов с использованием MiSeq Personal Sequencer (Illumina) с покрытием >200000 прочтений. Данные секвенирования анализировали для оценивания эффективностей NHEJ. Этой анализированной эталонной последовательностью AAVS1 является:
CACTTCAGGACAGCATGTTTGCTGCCTCCAGGGATCCTGTGTCCCCGAGCTGGGACCACCTTATATTCCCAGGGCCGGTTAATGTGGCTCTGGTTCTGGGTACTTTTATCTGTCCCCTCCACCCCACAGTGGGGCCACTAGGGACAGGATTGGTGACAGAAAAGCCCCATCCTTAGGCCTCCTCCTTCCTAGTCTCCTGATATTGGGTCTAACCCCCACCTCCTGTTAGGCAGATTCCTTATCTGGTGACACACCCCCATTTCCTGGA
ПЦР-праймерами для амплификации таргетирующих районов в геноме человека являются:
AAVS1-R
CTCGGCATTCCTGCTGAACCGCTCTTCCGATCTacaggaggtgggggttagac
AAVS1-F.1
ACACTCTTTCCCTACACGACGCTCTTCCGATCTCGTGATtatattcccagggccggtta
AAVS1-F.2
ACACTCTTTCCCTACACGACGCTCTTCCGATCTACATCGtatattcccagggccggtta
AAVS1-F.3
ACACTCTTTCCCTACACGACGCTCTTCCGATCTGCCTAAtatattcccagggccggtta
AAVS1-F.4
ACACTCTTTCCCTACACGACGCTCTTCCGATCTTGGTCAtatattcccagggccggtta
AAVS1-F.5
ACACTCTTTCCCTACACGACGCTCTTCCGATCTCACTGTtatattcccagggccggtta
AAVS1-F.6
ACACTCTTTCCCTACACGACGCTCTTCCGATCTATTGGCtatattcccagggccggtta
AAVS1-F.7
ACACTCTTTCCCTACACGACGCTCTTCCGATCTGATCTGtatattcccagggccggtta
AAVS1-F.8
ACACTCTTTCCCTACACGACGCTCTTCCGATCTTCAAGTtatattcccagggccggtta
AAVS1-F.9
ACACTCTTTCCCTACACGACGCTCTTCCGATCTCTGATCtatattcccagggccggtta
AAVS1-F.10
ACACTCTTTCCCTACACGACGCTCTTCCGATCTAAGCTAtatattcccagggccggtta
AAVS1-F.11
ACACTCTTTCCCTACACGACGCTCTTCCGATCTGTAGCCtatattcccagggccggtta
AAVS1-F.12
ACACTCTTTCCCTACACGACGCTCTTCCGATCTTACAAGtatattcccagggccggtta
Для анализа событий гомологической рекомбинации HR с использованием ДНК-донора на фиг. 2С, этими праймерами были:
HR_AAVS1-F CTGCCGTCTCTCTCCTGAGT
HR_Puro-R GTGGGCTTGTACTCGGTCAT
Пример V
Биоинформатический подход для вычисления экзона человека, которые являются мишенями CRISPR и методология для их мультиплексного синтеза.
Набор последовательностей гидРНК, которые в максимальной степени нацелены на специфические местоположения в экзонах человека, но в минимальной степени нацелены на другие местоположения в этом геноме, определяли следующим образом. Согласно одному аспекту, максимально эффективное нацеливание посредством гидРНК достигается использованием 23 нт последовательностей, из которых наиболее близкие к 5’-концу 20 нт являются точным комплементом желаемого местоположения, при этом три наиболее близких к 3’-концу основания должны быть в форме NGG. Дополнительно, наиболее близкий к 5’-концу нуклеотид должен быть G для установления сайта начала транскрипции pol-III. Однако, в соответствии с (2), ошибочное спаривание шести наиболее близких к 5’ нуклеотидов из 20 п.н. гидРНК с ее геномной мишенью не отменяет Cas9-опосредуемое расщепление до тех пор, пока последние 14 нт спарены правильно, но ошибочное спаривание восьми наиболее близкими к 5’-концу нуклеотидов совмещенное со спариванием последних 12 нуклеотидов отменяет расщепления, в то время как случай с ошибочным спариванием семи наиболее близких к 5’-концу нт и 13 парами с 3’-конца не был тестирован. Для того чтобы занизить внецелевые эффекты , было поставлено условие, что этот случай с ошибочным спариванием семи нуклеотидов наиболее близких к 5’-концу, подобно случаю с ошибочным спариванием шести, допускает расщепление, так что спаривание наиболее близких к 3’-концу 13 нт является достаточным для расщепления. Для идентификации сайтов мишени CRISPR в экзонах человека, которые должны быть расщеплены без внецелевых расщеплений, испытывали все последовательности из 23 п.н. формы 5’-GBBBB BBBBB BBBBB BBBBB NGG-3’ (формы 1), где B представляют основания в местоположении экзона, для которых не существует последовательность формы 5’-NNNNN NNBBB BBBBB BBBBB NGG-3’ (формы 2) в любом другом местоположении в геноме человека. Конкретно, загрузили (i) BED-файл местоположений кодирующих районов всех генов RefSeq генома человека GRCh37/hg19 из UCSC Genome Browser (15-17). Местоположения кодирующих экзонов в этом BED-файле содержат набор 346089 номеров доступа RefSeq мРНК для генома hg19. Однако некоторые номера доступа RefSeq-мРНК картировались во множественных геномных местоположений (возможные дупликации генов) и многие номера доступа картировались на субпопуляций того же самого набора местоположений экзонов (множественные изоформы одних и тех же генов). Для различения случаев очевидно дуплицированных генов и объединения множества отсылок на один и тот же геномный экзон, возникших из за наличия множественных номеров доступа RefSeq на различные изоформы, (ii) добавляли уникальные цифровые суффиксы к 705 номерам доступа RefSeq, которые имели множественные геномные местоположения, и (iii) использовали функцию mergeBed в BEDTool (18) (v2.16.2-zip-87e3926) для объединения перекрывающихся местоположений экзонов в слитые района экзонов. Эти стадии уменьшали начальный набор из 346089 местоположений экзонов RefSeq до 192783 различных геномных районов. Последовательность hg19 для всех слитых районов экзонов загружали с использованием UCSC Table Browser, добавляя 20 п.н. материал для заполнения места на каждом конце. (iv) С использованием сustom perl кода, идентифицировали 1657793 случаев form 1 в этой последовательности экзонов. (v) Затем эти последовательности фильтровали на присутствие случаев внецелевых form 2: для каждой мишени form 1 в слитом экзоне, экстрагировали наиболее близкие к 3’ 13 п.н. специфические (B) “коровые последовательности и, для каждого кора генерировали четыре 16 п.н. последовательностей 5’-BBB BBBBB BBBBB NGG-3’ (N = A, C, G и T), и производили поиск по всему геному hg19 на точные совпадения с этими 6631172 последовательностями при помощи Bowtie version 0.12.8 (19) с использованием параметров. Каждый сайт экзона-мишени, для которого было более чем одно совпадение, отбрасывали. Следует обратить внимание на то, что поскольку любая специфическая 13 п.н. последовательность, за которой следует последовательность NGG, дает только 15 п.н. специфичность, должно быть в среднем ~5,6 совпадений с удлиненной коровой последовательностью в рандомизированной последовательности ~3Гб (обеих цепях). Таким образом, большинство из этих первоначально идентифицированных последовательностей отбрасывали; однако 189864 последовательности проходили через этот фильтр. Они содержат набор CRISPR-таргетируемых местоположений в экзонах генома человека. Местоположения мишеней 189864 последовательностей находятся в 78028 слитых районах экзонов (~40,5% из всех 192783 х слитных районов экзонов человека) при численности ~2,4 сайта на район-мишеньэкзона. Для оценивания таргетинга на генном уровне, картирования мРНК RefSeq кластеризовали таким образом, что любые два номера доступа RefSeq (включающие в себя дупликаты генов, различаемых в (ii)), которые перекрываются со слитым районом экзона, считают как один кластер генов, 189864 экзон-специфических сайтов CRISPR направлено на 17104 и мишеней из 18872 генных кластеров (~90,6% от всех генных кластеров) при численности ~11,1 на таргетированный генный кластер. (Обратите внимание, что хотя в этих кластерах генов в единый объект «схлестываются» номера доступа RefSeq мРНК, которые представляют собой множественные изоформы одного транскрибируемого гена, они будут также стягивать перекрывающиеся с ними другие гены, а также гены с антисмысловыми транскриптами. На уровне исходных RefSeq-номеров доступа, эти 189864 последовательности направлены на 30563 района-мишени из общих 43726 (~69,9%) картированных RefSeq-номеров доступа (включающих в себя различаемые дупликаты генов) при численности ~6,2 сайтов на таргетированный картированный номер доступа RefSeq.
Согласно одному аспекту, эта база данных может быть усовершенствована внесением поправок с учетом таких факторов как состав оснований и вторичная структура обеих гидРНК и геномных мишеней (20, 21), и эпигенетическое состояние этих мишеней в линиях клеток человека, для которых эта информация является доступной.
Пример VI
Мультиплексный синтез
Последовательности-мишени включали в формат 200 п.н., который является совместимым с мультиплексным синтезом на ДНК-эрреях(23, 24). Согласно одному аспекту этот способ позволяет отыскивать специфические гидРНК или пул последовательностей гидРНК в олигонуклеотидном пуле ДНК-эррея и быстр клонировать их в одинаковый экспрессирующий вектор (фиг. 13A). Конкретно, синтезировали 12k олигонуклеотидный пул из CustomArray Inc. Кроме того, успешно извлекли выбранные из этой библиотеки гидРНК (фиг. 13B) Авторы наблюдали частоту ошибок ~4 мутаций на 1000 п.н. синтезированной ДНК.
Пример VII
РНК-направляемое редактирование генома требует как Cas9, так и направляющей РНК для успешного нацеливания.
С использованием анализа на основе GFP-репортера, описанного на фиг. 1В, тестировали все возможные комбинации донора для репарации ДНК, белка Cas9 и гидРНК на их способность осуществлять успешную HR (гомологичную рекомбинацию) (в 293T). Как показано на фиг. 4, клетки GAP+ наблюдали только, когда присутствовали все 3 компонента, подтверждая, что эти CRISPR компоненты являются существенными для РНК-направляемого редактирования генома. Данные являются средним +/- стандартная ошибка среднего (SEM) (N=3).
Пример VIII
Анализ опосредованного гидРНК и Cas9 редактирования генома
Процесс CRISPR-опосредованного редактирования генома исследовали с использованием либо (A) описанного ранее анализа с GFP-репортером, результаты которого приведены на фиг. 5А, и (В) глубокого секвенирования локусов-мишенией (в 293T), результаты которого показаны на фиг 5В). В качестве сравнения, тестировали мутант D10A Cas9, который, как было показано в ранних сообщениях, функционирует в качестве никазы в анализах in vitro. Как показано на фиг. 5, как Cas9, так и Cas9D10A могут успешно влиять на HR (гомологичную рекомбинацию) при почти одинаковой частоте. Однако секвенирование подтверждает, что, хотя Cas9 обнаруживает значимо повышенное NHEJ присоединение в локусах-мишенях, мутант D10A имеет значимо сниженную частоту NHEJ (как и могло ожидаться из его предполагаемой способности только разрывать ДНК). Также, в соответствии с известной биохимией белка Cas9, данные NHEJ подтверждают, что большинство делеций или инсерций пар оснований встречаются вблизи 3’-конца последовательности-мишени: этот пик находится на ~3-4 основания слева от сайта PAM, c медианной частотой делеций ~9-10 п.н. Данные показаны как среднее +/- стандартная ошибка среднего SEM (N=3).
Пример IX
РНК-направляемое редактирование генома является специфическим к последовательности-мишени.
Подобно анализу с GFP-репортером, описанному на фиг. 1В, были получены 3 стабильные линии 293T, каждая из которых несет разный конструкт GFP-репортера. Они различаются последовательностью встроенного фрагмента AAVS1 (как указано на фиг. 6). Одна линия содержит фрагмент дикого типа, тогда как две другие линии содержат мутацию в 6 п.н. (показанные красным цветом). Затем каждую из линий таргетировали одним из следующих 4 компонентов: пара GFP-ZFN, которая может нацеливаться на все типы клеток, так как ее последовательность-мишень находится во фрагментах фланкирующих GFP и, следовательно, присутствует у всех клеточных линий; AAVS1 TALEN, который может быть потенциально нацелен только wt-AAVS1-фрагмент, так как из мутаций в других двух линиях TALEN неспособен к связыванию этих сайтов в них; T1 гидРНК, которая может также потенциально быть нацелена только на фрагмент wt-AAVS1, так как ее сайт-мишень также разрушен в этих двух мутантных линиях; и наконец T2 гидРНК, которая должна быть способна нацеливаться на все 3 клеточные линии поскольку, в отличие от T1 гидРНК, ее сайт-мишень является неизмененным среди этих 3 линий. ZFN модифицировал все 3 типа клеток, AAVS1 TALEN и T1 гидРНК нацеливались только на тип клеток wt-AAVS1, и T2 гидРНК успешно нацеливается на все 3 типа клеток. Эти результаты вместе подтверждают, что опосредуемое гид-РНК редактирование, является специфичным в отношении последовательности-мишени. Данные показаны в виде среднего +/- стандартная ошибка среднего (SEM) (N=3).
Пример X
Гид-РНК, нацеленная на последовательность GFP, пригодна для надежного редактирования.
В дополнение к 2 гидРНК, нацеленным на вставку AAVS1, тестировали две дополнительных гидРНК, нацеленные на фланкирующие GFP последовательности репортера, описанного на фиг. 1B (в 293T) Как показано на фиг. 7, эти гидРНК были также воздействовать на частоту HR в этом сконструированном локусе. Данные показаны в виде среднего +/- стандартной ошибки среднего (SEM) (N=3).
Пример XI
РНК-направляемое редактирование генома является специфическим в отношении последовательности-мишени и демонстрирует сходные с ZFNs или TALEN эффективности нацеливания
Сходно с анализом с репортером GFP, описанным на фиг. 1В, создали две стабильные клеточные линии 293T, каждая из которых несет отличающийся конструкт репортера GFP. Они различаются по последовательности фрагмента-вставки (как указано на фиг. 8). Одна линия несет фрагмент в 58 п.н. из гена DNMT3a, тогда как другая линия несет гомологичный ему фрагмент в 58 п.н. из гена DNMT3b. Эти различия последовательности выделены красным цветом. Затем каждую из этих линий таргетировали одним из следующих шести реагентов: GFP-ZFN-пары, которая может нацеливаться на все типы клеток, так как ее последовательность-мишень находится во фланкирующих GFP фрагментах и, следовательно, присутствует у всех линий клеток; пары TALEN, которая потенциально нацелена либо на DNMT3a-, либо на DNMT3b-фрагменты; пары гидРНК, которая может быть потенциально нацелена только на DNMT3a-фрагмент; и, наконец, гидРНК, которая должна потенциально нацеливаться только на DNMT3b-фрагмент. Как показано на фиг. 8, эти ZFN модифицировали все 3 типа клеток, а TALEN и гидРНК только соответствующие им мишени. Кроме того, эффективности нацеливания оказались сравнимыми у 6 нацеливающих реагентов. Эти результаты вместе подтверждают, что РНК-направляемое редактирование является специфическим в отношении последовательности-мишени и демонстрирует сходные с ZFN или TALEN эффективности нацеливания. Данные показаны в виде среднего +/- стандартная ошибка среднего (SEM) (N=3).
Пример XII
РНК-направляемое соединение негомологичных концов (NHEJ) в клетках iPS человека.
В клетки iPS человека (PGP1) посредством нуклеофекции вводили конструкты, указанные на левой панели фиг. 9. Через 4 дня после нуклеофекции частоту NHEJ измеряли путем оценки частоты делеций и инсерций при разрывах двойной цепи (DSB) глубоким секвенированием. Панель 1: Чаcтота делеции, детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта–мишени РНК Т1; зеленые штрихпунктирные линии: граница сайта-мишени РНК Т2. Частоту случаев делеции в каждом положении нуклеотида откладывали на графике в виде черных линий и рассчитывали частоту делеции как процент прочтений, несущих делецию. Панель 2: Частота инсерции детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта-мишени РНК Т1; зеленые штрихпунктирные линии: граница сайта-мишени РНК Т2. Частоту случаев инсерции в геномном местоположении, где детектировалось первое встроенное сочленение откладывали на графике в виде черных линий и частоту инсерции рассчитывали как процент прочтений несущих инсерцию. Панель 3: Распределение по размерам делеций. Частоты делеций различных размеров среди всей популяции NHEJ строили в виде графиков. Панель 4: Распределение размеров инсерций. Частоты различных размеров инсерций всей популяции NHEJ строили в виде графиков. Таргетинг iPS обеими гидРНК является эффективным (2-4%), последовательность-специфическим (как показано смещением в положении распределений делеции NHEJ), и подтверждение результатов фиг. 4, анализ на основе NGS также показывает, что как белок Cas9, так и гидРНК являются существенными для событий NHEJ в локусе-мишени.
Пример XIII
РНК-направляемое NHEJ в клетках K562.
В клетки K562 посредством нуклеофекции вводили конструкты, указанными на левой панели фиг. 10. Через 4 дня после нуклеофекции, частоту NHEJ измеряли оцениванием частоты геномных делеций и инсерций при двуцепочечном разрыве глубоким секвенированием. Панель 1: Частота делеции, детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта-мишени T1 РНК; зеленые штрихпунктирные линии: граница сайта-мишени T2 РНК. Частоту случаев делеции в каждом положении нуклеотида откладывали на графике в виде в черных линий и рассчитывали частоту делеции как процент прочтений, несущих делецию. Панель 2: Частота инсерции детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта-мишени РНК Т1; зеленые штрихпунктирные линии: граница сайта-мишени РНК Т2. Частоту случаев инсерции в геномном местоположении, где обнаруживалось первое встроенное сочленение откладывали на графике в виде в черных линиях и частоту инсерции рассчитывали как процент прочтений, несущих инсерцию. Панель 3: Распределение по размерам делеций. Частоту делеций различных размеров среди всей популяции NHEJ строили в виде графиков. Панель 4: Распределение по размерам инсерций. Частоту инсерций различных размеров по всей популяции строили в виде графиков. Таргетинг на K562 обеими гидРНК является эффективным (13-38%) и последовательность-специфическими (как показано смещением в положении распределений делеции NHEJ). Важно, о чем свидетельствуют пики на гистограмме наблюдаемых частот размеров делеций, одновременное введение как T1, так и T2 гидРНК приводило к высокой эффективности делеции промежуточного фрагмента 19 п.н., демонстрируя, что мультиплексное редактирование геномных локусов также является осуществимым с использованием этого подхода.
Пример XIV
РНК-направляемое NHEJ в клетках 293T.
Клетки 293T трансфицировали конструктами, показанными в левой панели фиг. 11. Через 4 дня после нуклеофекции, частота NHEJ измеряли оценивая частоту геномных делеций и инсерций при DSB глубоким секвенированием. Панель 1: Частота делеции, детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта-мишени T1 РНК; зеленые штрихпунктирные линии: граница сайта-мишени T2 РНК. Частоту случаев делеции в каждом положении нуклеотида откладывали на графике в виде черных линий и рассчитывали частоту делеции как процент прочтений, несущих делеции. Панель 2: Частота инсерций, детектируемая в районе-мишени. Красные штрихпунктирные линии: граница сайта-мишени РНК Т1; зеленые штрихпунктирные линии: граница сайта-мишени РНК Т2. Частоту случаев инсерции в геномном местоположении, где обнаруживалось первое встроенное сочленение откладывали на графике в виде в черных линий и частоту инсерции рассчитывали как процент прочтений, несущих инсерцию. Панель 3: Распределение размеров делеций. Частоты делеций различных размеров среди всей популяции NHEJ строили в виде графиков. Панель 4: Распределение размеров инсерций. Частоты различных размеров инсерций всей популяции строили в виде графиков. Таргетинг 293T обеими гидРНК является эффективным (10-24%) и последовательность-специфическим (как показано смещением в положении распределений NHEJ делеций).
Пример XV
HR в эндогенном локусе AAVS1 с использованием либо донора дцДНК либо короткого олигонуклеотидного донора.
Как показано на фиг. 12A, ПЦР-скрининг (со ссылкой на фиг. 2C) подтвердил, что 21/24 случайно выбранные клоны 293T были успешно таргетированы. Как показано на фиг. 12В, сходный ПЦР-скрининг подтвердил, что 3/7 случайно выбранных клонов PGP1-iPS, были также успешно таргетированными. Как показано на фиг. 12C, короткие 90-мерные олигонуклеотиды могли бы осуществлять эффективное нацеливание в эндогенном локусе AAVS1 (показанное здесь для клеток K562).
Пример XVI
Методология для мультиплексного синтеза, извлечения и клонирования в U6-экспрессирующем векторе направляющих РНК, нацеленных на гены в геноме человека
Создавали источник приблизительно 190k биоинформатически вычисленных уникальных сайтов гидРНК, таргетирующих ~40,5% всех экзонов генов в геноме человека. Как показано на фиг. 13А, эти сайты-мишени гидРНК были включены в формат 200 п.н., который является совместимым с мультиплексным синтезом на ДНК-эрреях. Конкретно, эта конструкция позволяет выполнять (i) нацеленный поиск и выделение определенной мишени или пула мишеней гидРНК из олигонуклеотидного пула ДНК-эррея (посредством 3 последовательных раундов гнездовой ПЦР, как указано на этой фигуре схематически), и (ii) высокую частоту клонирование в используемый экспрессирующий вектор, который после линеаризации с использованием AflII служит в качестве реципиента для опосредуемого сборкой Гибсона включения вставкой фрагмента гидРНК. Как показано на фиг. 13B, этот способ был использован для выполнения нацеленного поиска и выделения 10 уникальных гидРНК из 12к олигонуклеотидного пула, синтезированного CustomArray Inc.
Пример XVII
CRISPR-опосредованная РНК-направляемая активация транскрипции.
Система CRISPR-Cas является адаптивной иммунозащитной системой в бактериях и функционирует для ‘расщепления’ вторгающихся нуклеиновых кислот. Согласно одному аспекту, эта система CRISPR-CAS сконструирована для функционирования в клетках человека и для ‘расщепления’ геномной ДНК. Это достигается короткой гидРНК, направляющей белок Cas9 (который имеет нуклеазную функцию) на последовательность-мишень, комплементарную спейсеру в этой гидРНК. Способность ‘расщеплять’ ДНК позволяет использовать это во множестве приложений, относящихся к редактированию генома, а также направленной регуляции генома. Для этого, белок Cas9 изменяли чтобы сделать его нуклеаза-нуль введением мутаций, которые, как предсказывалось, аннулируют связывание с Mg2+ (который, как известно, является важным для функций доменов RuvC-подобный и HNH-подобный): Конкретно, вводили комбинации мутаций D10A, D839A, H840A и N863A. Затем генерированный таким образом нуклеаза-нуль- белок (как подтверждалось его способностью не разрезать ДНК с использованием анализа секвенирования) и здесь далее называемый Cas9R-H-, связывали с доменом активирования транскрипции, здесь это P64, позволяющий системе CRISPR-cas функционировать в качестве РНК-направляемого фактора транскрипции (см. фиг. 14). Это слияние Cas9R-H-+VP64 делает возможной РНК-направляемую транскрипционную активацию двух показанных репортеров. Конкретно, как FACS-анализ, так и иммунофлуоресцентный анализ демонстрирует, что этот белок позволяет гидРНК-специфическое нацеливание на соответствующие репортеры, и, кроме того, в результате происходит активация транскрипции, что оценивалось анализом экспрессии флуоресцентного белка dTomato, было при уровнях, сходных с уровнями, индуцируемыми стандартным слитым белком TALE-VP64.
Пример XVIII
Гибкость последовательностей гидРНК и ее применения.
Гибкость последовательности каркаса гидРНК для инсерций в целях конструирования последовательностей определяли систематическим анализом для ряда случайных инсерций последовательностей на 5’-, середине и 3’-концах гидРНК: конкретно, ставки 1 п.н., 5 п.н., 10 п.н., 20 п.н. и 40 п.н. выполняли в последовательности гидРНК на 5’-, середине и 3’-концах гидРНК (точные положения инсерций изображены ‘красным цветом’ на фиг. 15. Затем эту гидРНК тестируют на функциональность по ее способности индуцировать HR (гомологичную рекомбинацию) в анализе с репортером GFP (как описано здесь). Очевидно, что гидРНК являются гибкими относительно встраивания последовательностей на 5’- и 3’-концах (как измерено по поддерживаемой индуцирующей HR активности). Таким образом, аспекты данного раскрытия изобретения направлены прикрепление небольших последовательностей, соответствующих РНК-аптамерам, которые могут запускать появление активности гидРНК, или опосредовать визуализацию гидРНК. Дополнительно, аспекты данного изобретения направлены на прикрепление оцДНК-доноров к гидРНК посредством гибридизации, делая таким образом возможными разрезание и немедленную физическую локализацию матрицы репарации, которая может стимулировать частоту гомологичной рекомбинации в сравнении с допускающим ошибки негомологичным соединением концов.
Следующие ссылки, идентифицированные в разделе Примеров цифрами, включены здесь посредством ссылок в их полном объеме для всех целей.
Ссылки
1. K. S. Makarova et al., Evolution and classification of the CRISPR-Cas systems. Nature reviews. Microbiology 9, 467 (Jun, 2011).
2. M. Jinek et al., A programmable dual-RNA-guided DNA endonuclease in adaptive bacterial immunity. Science 337, 816 (Aug 17, 2012).
3. P. Horvath, R. Barrangou, CRISPR/Cas, the immune system of bacteria and archaea. Science 327, 167 (Jan 8, 2010).
4. H. Deveau et al., Phage response to CRISPR-encoded resistance in Streptococcus thermophilus. Journal of bacteriology 190, 1390 (Feb, 2008).
5. J. R. van der Ploeg, Analysis of CRISPR in Streptococcus mutans suggests frequent occurrence of acquired immunity against infection by M102-like bacteriophages. Microbiology 155, 1966 (Jun, 2009).
6. M. Rho, Y. W. Wu, H. Tang, T. G. Doak, Y. Ye, Diverse CRISPRs evolving in human microbiomes. PLoS genetics 8, e1002441 (2012).
7. D. T. Pride et al., Analysis of streptococcal CRISPRs from human saliva reveals substantial sequence diversity within and between subjects over time. Genome research 21, 126 (Jan, 2011).
8. G. Gasiunas, R. Barrangou, P. Horvath, V. Siksnys, Cas9-crRNA ribonucleoprotein complex mediates specific DNA cleavage for adaptive immunity in bacteria. Proceedings of the National Academy of Sciences of the United States of America 109, E2579 (Sep 25, 2012).
9. R. Sapranauskas et al., The Streptococcus thermophilus CRISPR/Cas system provides immunity in Escherichia coli. Nucleic acids research 39, 9275 (Nov, 2011).
10. J. E. Garneau et al., The CRISPR/Cas bacterial immune system cleaves bacteriophage and plasmid DNA. Nature 468, 67 (Nov 4, 2010).
11. K. M. Esvelt, J. C. Carlson, D. R. Liu, A system for the continuous directed evolution of biomolecules. Nature 472, 499 (Apr 28, 2011).
12. R. Barrangou, P. Horvath, CRISPR: new horizons in phage resistance and strain identification. Annual review of food science and technology 3, 143 (2012).
13. B. Wiedenheft, S. H. Sternberg, J. A. Doudna, RNA-guided genetic silencing systems in bacteria and archaea. Nature 482, 331 (Feb 16, 2012).
14. N. E. Sanjana et al., A transcription activator-like effector toolbox for genome engineering. Nature protocols 7, 171 (Jan, 2012).
15. W. J. Kent et al., The human genome browser at UCSC. Genome Res 12, 996 (Jun, 2002).
16. T. R. Dreszer et al., The UCSC Genome Browser database: extensions and updates 2011. Nucleic Acids Res 40, D918 (Jan, 2012).
17. D. Karolchik et al., The UCSC Table Browser data retrieval tool. Nucleic Acids Res 32, D493 (Jan 1, 2004).
18. A. R. Quinlan, I. M. Hall, BEDTools: a flexible suite of utilities for comparing genomic features. Bioinformatics 26, 841 (Mar 15, 2010).
19. B. Langmead, C. Trapnell, M. Pop, S. L. Salzberg, Ultrafast and memory-efficient alignment of short DNA sequences to the human genome. Genome Biol 10, R25 (2009).
20. R. Lorenz et al., ViennaRNA Package 2.0. Algorithms for molecular biology : AMB 6, 26 (2011).
21. D. H. Mathews, J. Sabina, M. Zuker, D. H. Turner, Expanded sequence dependence of thermodynamic parameters improves prediction of RNA secondary structure. Journal of molecular biology 288, 911 (May 21, 1999).
22. R. E. Thurman et al., The accessible chromatin landscape of the human genome. Nature 489, 75 (Sep 6, 2012).
23. S. Kosuri et al., Scalable gene synthesis by selective amplification of DNA pools from high-fidelity microchips. Nature biotechnology 28, 1295 (Dec, 2010).
24. Q. Xu, M. R. Schlabach, G. J. Hannon, S. J. Elledge, Design of 240,000 orthogonal 25mer DNA barcode probes. Proceedings of the National Academy of Sciences of the United States of America 106, 2289 (Feb 17, 2009).
--->
SEQUENCE LISTING
<110> PRESIDENT AND FELLOWS OF HARVARD COLLEGE
<120> RNA-Guided Human Genome Engineering
<130> 010498.01290
<140> PCT/US13/075317
<141> 2013-12-16
<150> US 61/738,355
<151> 2012-12-17
<150> US 61/779,169
<151> 2013-03-13
<160> 46
<170> PatentIn version 3.5
<210> 1
<211> 268
<212> DNA
<213> Homo sapiens
<400> 1
cacttcagga cagcatgttt gctgcctcca gggatcctgt gtccccgagc tgggaccacc 60
ttatattccc agggccggtt aatgtggctc tggttctggg tacttttatc tgtcccctcc 120
accccacagt ggggccacta gggacaggat tggtgacaga aaagccccat ccttaggcct 180
cctccttcct agtctcctga tattgggtct aacccccacc tcctgttagg cagattcctt 240
atctggtgac acacccccat ttcctgga 268
<210> 2
<211> 53
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 2
ctcggcattc ctgctgaacc gctcttccga tctacaggag gtgggggtta gac 53
<210> 3
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 3
acactctttc cctacacgac gctcttccga tctcgtgatt atattcccag ggccggtta 59
<210> 4
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 4
acactctttc cctacacgac gctcttccga tctacatcgt atattcccag ggccggtta 59
<210> 5
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 5
acactctttc cctacacgac gctcttccga tctgcctaat atattcccag ggccggtta 59
<210> 6
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 6
acactctttc cctacacgac gctcttccga tcttggtcat atattcccag ggccggtta 59
<210> 7
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 7
acactctttc cctacacgac gctcttccga tctcactgtt atattcccag ggccggtta 59
<210> 8
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 8
acactctttc cctacacgac gctcttccga tctattggct atattcccag ggccggtta 59
<210> 9
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 9
acactctttc cctacacgac gctcttccga tctgatctgt atattcccag ggccggtta 59
<210> 10
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 10
acactctttc cctacacgac gctcttccga tcttcaagtt atattcccag ggccggtta 59
<210> 11
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 11
acactctttc cctacacgac gctcttccga tctctgatct atattcccag ggccggtta 59
<210> 12
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 12
acactctttc cctacacgac gctcttccga tctaagctat atattcccag ggccggtta 59
<210> 13
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 13
acactctttc cctacacgac gctcttccga tctgtagcct atattcccag ggccggtta 59
<210> 14
<211> 59
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 14
acactctttc cctacacgac gctcttccga tcttacaagt atattcccag ggccggtta 59
<210> 15
<211> 20
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 15
ctgccgtctc tctcctgagt 20
<210> 16
<211> 20
<212> DNA
<213> Artificial
<220>
<223> PCR primer
<400> 16
gtgggcttgt actcggtcat 20
<210> 17
<211> 80
<212> RNA
<213> Artificial
<220>
<223> guide RNA
<400> 17
guuuuagagc uagaaauagc aaguuaaaau aaggcuaguc cguuaucaac uugaaaaagu 60
ggcaccgagu cggugcuuuu 80
<210> 18
<211> 71
<212> DNA
<213> Homo sapiens
<400> 18
taatactttt atcttgtccc ctccacccca cagtggggcc actagggaca ggattggtga 60
cagaaagccc c 71
<210> 19
<211> 52
<212> DNA
<213> Homo sapiens
<400> 19
ttatctgtcc cctccacccc acagtggggc cactagggaa caggattggt ga 52
<210> 20
<211> 22
<212> DNA
<213> Homo sapiens
<400> 20
caggcaggtc ctgctttctc tg 22
<210> 21
<211> 22
<212> DNA
<213> Homo sapiens
<400> 21
cacagtgggg caagcttctg ac 22
<210> 22
<211> 4146
<212> DNA
<213> Homo sapiens
<400> 22
gccaccatgg acaagaagta ctccattggg ctcgatatcg gcacaaacag cgtcggctgg 60
gccgtcatta cggacgagta caaggtgccg agcaaaaaat tcaaagttct gggcaatacc 120
gatcgccaca gcataaagaa gaacctcatt ggcgccctcc tgttcgactc cggggagacg 180
gccgaagcca cgcggctcaa aagaacagca cggcgcagat atacccgcag aaagaatcgg 240
atctgctacc tgcaggagat ctttagtaat gagatggcta aggtggatga ctctttcttc 300
cataggctgg aggagtcctt tttggtggag gaggataaaa agcacgagcg ccacccaatc 360
tttggcaata tcgtggacga ggtggcgtac catgaaaagt acccaaccat atatcatctg 420
aggaagaagc ttgtagacag tactgataag gctgacttgc ggttgatcta tctcgcgctg 480
gcgcatatga tcaaatttcg gggacacttc ctcatcgagg gggacctgaa cccagacaac 540
agcgatgtcg acaaactctt tatccaactg gttcagactt acaatcagct tttcgaagag 600
aacccgatca acgcatccgg agttgacgcc aaagcaatcc tgagcgctag gctgtccaaa 660
tcccggcggc tcgaaaacct catcgcacag ctccctgggg agaagaagaa cggcctgttt 720
ggtaatctta tcgccctgtc actcgggctg acccccaact ttaaatctaa cttcgacctg 780
gccgaagatg ccaagcttca actgagcaaa gacacctacg atgatgatct cgacaatctg 840
ctggcccaga tcggcgacca gtacgcagac ctttttttgg cggcaaagaa cctgtcagac 900
gccattctgc tgagtgatat tctgcgagtg aacacggaga tcaccaaagc tccgctgagc 960
gctagtatga tcaagcgcta tgatgagcac caccaagact tgactttgct gaaggccctt 1020
gtcagacagc aactgcctga gaagtacaag gaaattttct tcgatcagtc taaaaatggc 1080
tacgccggat acattgacgg cggagcaagc caggaggaat tttacaaatt tattaagccc 1140
atcttggaaa aaatggacgg caccgaggag ctgctggtaa agcttaacag agaagatctg 1200
ttgcgcaaac agcgcacttt cgacaatgga agcatccccc accagattca cctgggcgaa 1260
ctgcacgcta tcctcaggcg gcaagaggat ttctacccct ttttgaaaga taacagggaa 1320
aagattgaga aaatcctcac atttcggata ccctactatg taggccccct cgcccgggga 1380
aattccagat tcgcgtggat gactcgcaaa tcagaagaga ccatcactcc ctggaacttc 1440
gaggaagtcg tggataaggg ggcctctgcc cagtccttca tcgaaaggat gactaacttt 1500
gataaaaatc tgcctaacga aaaggtgctt cctaaacact ctctgctgta cgagtacttc 1560
acagtttata acgagctcac caaggtcaaa tacgtcacag aagggatgag aaagccagca 1620
ttcctgtctg gagagcagaa gaaagctatc gtggacctcc tcttcaagac gaaccggaaa 1680
gttaccgtga aacagctcaa agaagactat ttcaaaaaga ttgaatgttt cgactctgtt 1740
gaaatcagcg gagtggagga tcgcttcaac gcatccctgg gaacgtatca cgatctcctg 1800
aaaatcatta aagacaagga cttcctggac aatgaggaga acgaggacat tcttgaggac 1860
attgtcctca cccttacgtt gtttgaagat agggagatga ttgaagaacg cttgaaaact 1920
tacgctcatc tcttcgacga caaagtcatg aaacagctca agaggcgccg atatacagga 1980
tgggggcggc tgtcaagaaa actgatcaat gggatccgag acaagcagag tggaaagaca 2040
atcctggatt ttcttaagtc cgatggattt gccaaccgga acttcatgca gttgatccat 2100
gatgactctc tcacctttaa ggaggacatc cagaaagcac aagtttctgg ccagggggac 2160
agtcttcacg agcacatcgc taatcttgca ggtagcccag ctatcaaaaa gggaatactg 2220
cagaccgtta aggtcgtgga tgaactcgtc aaagtaatgg gaaggcataa gcccgagaat 2280
atcgttatcg agatggcccg agagaaccaa actacccaga agggacagaa gaacagtagg 2340
gaaaggatga agaggattga agagggtata aaagaactgg ggtcccaaat ccttaaggaa 2400
cacccagttg aaaacaccca gcttcagaat gagaagctct acctgtacta cctgcagaac 2460
ggcagggaca tgtacgtgga tcaggaactg gacatcaatc ggctctccga ctacgacgtg 2520
gatcatatcg tgccccagtc ttttctcaaa gatgattcta ttgataataa agtgttgaca 2580
agatccgata aaaatagagg gaagagtgat aacgtcccct cagaagaagt tgtcaagaaa 2640
atgaaaaatt attggcggca gctgctgaac gccaaactga tcacacaacg gaagttcgat 2700
aatctgacta aggctgaacg aggtggcctg tctgagttgg ataaagccgg cttcatcaaa 2760
aggcagcttg ttgagacacg ccagatcacc aagcacgtgg cccaaattct cgattcacgc 2820
atgaacacca agtacgatga aaatgacaaa ctgattcgag aggtgaaagt tattactctg 2880
aagtctaagc tggtctcaga tttcagaaag gactttcagt tttataaggt gagagagatc 2940
aacaattacc accatgcgca tgatgcctac ctgaatgcag tggtaggcac tgcacttatc 3000
aaaaaatatc ccaagcttga atctgaattt gtttacggag actataaagt gtacgatgtt 3060
aggaaaatga tcgcaaagtc tgagcaggaa ataggcaagg ccaccgctaa gtacttcttt 3120
tacagcaata ttatgaattt tttcaagacc gagattacac tggccaatgg agagattcgg 3180
aagcgaccac ttatcgaaac aaacggagaa acaggagaaa tcgtgtggga caagggtagg 3240
gatttcgcga cagtccggaa ggtcctgtcc atgccgcagg tgaacatcgt taaaaagacc 3300
gaagtacaga ccggaggctt ctccaaggaa agtatcctcc cgaaaaggaa cagcgacaag 3360
ctgatcgcac gcaaaaaaga ttgggacccc aagaaatacg gcggattcga ttctcctaca 3420
gtcgcttaca gtgtactggt tgtggccaaa gtggagaaag ggaagtctaa aaaactcaaa 3480
agcgtcaagg aactgctggg catcacaatc atggagcgat caagcttcga aaaaaacccc 3540
atcgactttc tcgaggcgaa aggatataaa gaggtcaaaa aagacctcat cattaagctt 3600
cccaagtact ctctctttga gcttgaaaac ggccggaaac gaatgctcgc tagtgcgggc 3660
gagctgcaga aaggtaacga gctggcactg ccctctaaat acgttaattt cttgtatctg 3720
gccagccact atgaaaagct caaagggtct cccgaagata atgagcagaa gcagctgttc 3780
gtggaacaac acaaacacta ccttgatgag atcatcgagc aaataagcga attctccaaa 3840
agagtgatcc tcgccgacgc taacctcgat aaggtgcttt ctgcttacaa taagcacagg 3900
gataagccca tcagggagca ggcagaaaac attatccact tgtttactct gaccaacttg 3960
ggcgcgcctg cagccttcaa gtacttcgac accaccatag acagaaagcg gtacacctct 4020
acaaaggagg tcctggacgc cacactgatt catcagtcaa ttacggggct ctatgaaaca 4080
agaatcgacc tctctcagct cggtggagac agcagggctg accccaagaa gaagaggaag 4140
gtgtga 4146
<210> 23
<211> 455
<212> DNA
<213> Homo sapiens
<220>
<221> misc_feature
<222> (320)..(338)
<223> n is a, c, g, or t
<400> 23
tgtacaaaaa agcaggcttt aaaggaacca attcagtcga ctggatccgg taccaaggtc 60
gggcaggaag agggcctatt tcccatgatt ccttcatatt tgcatatacg atacaaggct 120
gttagagaga taattagaat taatttgact gtaaacacaa agatattagt acaaaatacg 180
tgacgtagaa agtaataatt tcttgggtag tttgcagttt taaaattatg ttttaaaatg 240
gactatcata tgcttaccgt aacttgaaag tatttcgatt tcttggcttt atatatcttg 300
tggaaaggac gaaacaccgn nnnnnnnnnn nnnnnnnngt tttagagcta gaaatagcaa 360
gttaaaataa ggctagtccg ttatcaactt gaaaaagtgg caccgagtcg gtgctttttt 420
tctagaccca gctttcttgt acaaagttgg catta 455
<210> 24
<211> 99
<212> RNA
<213> Artificial
<220>
<223> guide RNA
<220>
<221> misc_feature
<222> (2)..(20)
<223> wherein N is G, A, C or U
<400> 24
gnnnnnnnnn nnnnnnnnnn guuuuagagc uagaaauagc aaguuaaaag aaggguagug 60
gguuaucaac uugaaaaagc ggcaccgagu caauacuuu 99
<210> 25
<211> 23
<212> DNA
<213> Homo sapiens
<400> 25
gtgaaccgca tcgagctgaa ggg 23
<210> 26
<211> 23
<212> DNA
<213> Homo sapiens
<400> 26
ggagcgcacc atcttcttca agg 23
<210> 27
<211> 23
<212> DNA
<213> Homo sapiens
<400> 27
gtcccctcca ccccacagtg ggg 23
<210> 28
<211> 23
<212> DNA
<213> Homo sapiens
<400> 28
ggggccacta gggacaggat tgg 23
<210> 29
<211> 23
<212> DNA
<213> Homo sapiens
<400> 29
gcatgatgcg cggcccaagg agg 23
<210> 30
<211> 23
<212> DNA
<213> Homo sapiens
<400> 30
gagatgatcg ccccttcttc tgg 23
<210> 31
<211> 23
<212> DNA
<213> Homo sapiens
<400> 31
gaattactca cgccccaagg agg 23
<210> 32
<211> 72
<212> DNA
<213> Homo sapiens
<400> 32
taatactttt atcttgtccc ctccacccca cagtggggcc actagggaca ggattggtga 60
cagaaaagcc cc 72
<210> 33
<211> 70
<212> DNA
<213> Homo sapiens
<400> 33
taatactttt atctgtcaaa aaaaccccac agtggggcca ctaggacagg attggtgaca 60
gaaaagcccc 70
<210> 34
<211> 71
<212> DNA
<213> Homo sapiens
<400> 34
taatactttt atctgtcggg gggaccccac agtggggcca ctagggacag gattggtgac 60
agaaaagccc c 71
<210> 35
<211> 61
<212> DNA
<213> Homo sapiens
<400> 35
taatgcatga tgcgcggccc aaggagggag atgatcgccc cttcttctgg ctctttgaga 60
a 61
<210> 36
<211> 61
<212> DNA
<213> Homo sapiens
<400> 36
taatgaatta ctcacgcccc aaggagggtg atgaccggcc gttcttctgg atgtttgaga 60
a 61
<210> 37
<211> 110
<212> DNA
<213> Homo sapiens
<400> 37
ggtactttta tctgtcccct ccaccccaca gtgggccact cgggacagga ttggtgacag 60
aaaagcccca tccttaggcc tcctccttcc tagtctcctg atattgggtc 110
<210> 38
<211> 90
<212> DNA
<213> Homo sapiens
<400> 38
ttatctgtcc cctccacccc acagtggggc cactagggac aggaaaggtg acagaaaagc 60
cccatcctta ggcctcctcc ttcctagtct 90
<210> 39
<211> 23
<212> DNA
<213> Homo sapiens
<220>
<221> misc_feature
<222> (2)..(21)
<223> wherein N is G, A, T or C
<400> 39
gnnnnnnnnn nnnnnnnnnn ngg 23
<210> 40
<211> 201
<212> DNA
<213> Homo sapiens
<220>
<221> misc_feature
<222> (27)..(51)
<223> wherein N is G, A, T or C
<220>
<221> misc_feature
<222> (93)..(111)
<223> wherein N is G, A, T or C
<220>
<221> misc_feature
<222> (152)..(176)
<223> wherein N is G, A, T or C
<400> 40
tatgaggacg aatctccccg cttatannnn nnnnnnnnnn nnnnnnnnnn nttcttggct 60
ttatatatct tgtggaaagg acgaaaacac cgnnnnnnnn nnnnnnnnnn ngttttagag 120
ctagaaatag caagttaaaa taaggctagt cnnnnnnnnn nnnnnnnnnn nnnnnngtac 180
aagcacacgt ttgtcaagac c 201
<210> 41
<211> 415
<212> DNA
<213> Homo sapiens
<400> 41
attcgccctt tgtacaaaaa agcaggcttt aaaggaacca attcagtcga ctggatccgg 60
taccaaggtc gggcaggaag agggcctatt tcccatgatt ccttcatatt tcatatacga 120
tacaaggctg ttagagagat aataagaatt aatttgactg taaacacaaa gatattagta 180
caaaatacgt gacgtagaaa gtaataattt cttgggtagt ttgcagtttt aaaattatgt 240
tttaaaatgg actatcatat gcttaccgta acttgaaagt atttcgattt cttggcttta 300
tatatcttaa gttaaaataa ggctagtccg ttatcaactt gaaaaagtgg caccgagtcg 360
gtgctttttt tctagaccca gctttcttgt acaaagttgg cattaaaggg cgaat 415
<210> 42
<211> 23
<212> DNA
<213> Artificial
<220>
<223> reporter oligonucleotide
<400> 42
gtcccctcca ccccacagtg ggg 23
<210> 43
<211> 23
<212> DNA
<213> Artificial
<220>
<223> reporter oligonucleotide
<400> 43
ggggccacta gggacaggat tgg 23
<210> 44
<211> 100
<212> DNA
<213> Artificial
<220>
<223> guide RNA
<400> 44
ggggccacta gggacaccat guuuuagagc uagaaauagc aaguuaaaau aaggcuaguc 60
cguuaucaac uucaaaaaca cccacccaga cggugcuuuu 100
<210> 45
<211> 80
<212> DNA
<213> Artificial
<220>
<223> guide RNA scaffold
<400> 45
guuuuagagc uagaaauagc aaguuaaaau aaggcuaguc cguuaucaac uugaaaaagu 60
ggcaccgagu cggugcuuuu 80
<210> 46
<211> 76
<212> DNA
<213> Artificial
<220>
<223> guide RNA scaffold
<400> 46
guuuuagagc uagaaauagc aaguuaaaau aaggcuaguc cguuaucaac uugaaaaagu 60
ggcaccgagu cggugc 76
<---
| название | год | авторы | номер документа |
|---|---|---|---|
| РНК-НАПРАВЛЯЕМАЯ ИНЖЕНЕРИЯ ГЕНОМА ЧЕЛОВЕКА | 2013 |
|
RU2699523C2 |
| ГЕНОМНАЯ ИНЖЕНЕРИЯ | 2014 |
|
RU2764757C2 |
| ГЕНОМНАЯ ИНЖЕНЕРИЯ | 2021 |
|
RU2812848C2 |
| НАПРАВЛЯЕМАЯ РНК РЕГУЛЯЦИЯ ТРАНСКРИПЦИИ | 2014 |
|
RU2756865C2 |
| ГЕНОМНАЯ ИНЖЕНЕРИЯ | 2014 |
|
RU2688462C2 |
| СПОСОБЫ И КОМПОЗИЦИИ ДЛЯ НАЦЕЛЕННОЙ ГЕНЕТИЧЕСКОЙ МОДИФИКАЦИИ С ИСПОЛЬЗОВАНИЕМ ПАРНЫХ ГИДОВЫХ РНК | 2015 |
|
RU2734770C2 |
| НАПРАВЛЯЕМАЯ РНК РЕГУЛЯЦИЯ ТРАНСКРИПЦИИ | 2014 |
|
RU2690935C2 |
| ИСКУССТВЕННАЯ МОДИФИКАЦИЯ ГЕНОМА ДЛЯ РЕГУЛЯЦИИ ЭКСПРЕССИИ ГЕНА | 2018 |
|
RU2767201C2 |
| МОЛЕКУЛА РНК-ПРОВОДНИКА ДЛЯ ГЕНОМНОГО РЕДАКТИРОВАНИЯ ПРОТОМОТОРНОЙ ОБЛАСТИ ГЕНА VRN-A1 ОДНОДОЛЬНЫХ ЗЕРНОВЫХ С ПРИМЕНЕНИЕМ СИСТЕМЫ CRISPR/CAS9 | 2020 |
|
RU2762831C1 |
| СИСТЕМЫ CRISPR-CAS И СПОСОБЫ ИЗМЕНЕНИЯ ЭКСПРЕССИИ ПРОДУКТОВ ГЕНОВ | 2013 |
|
RU2796273C2 |
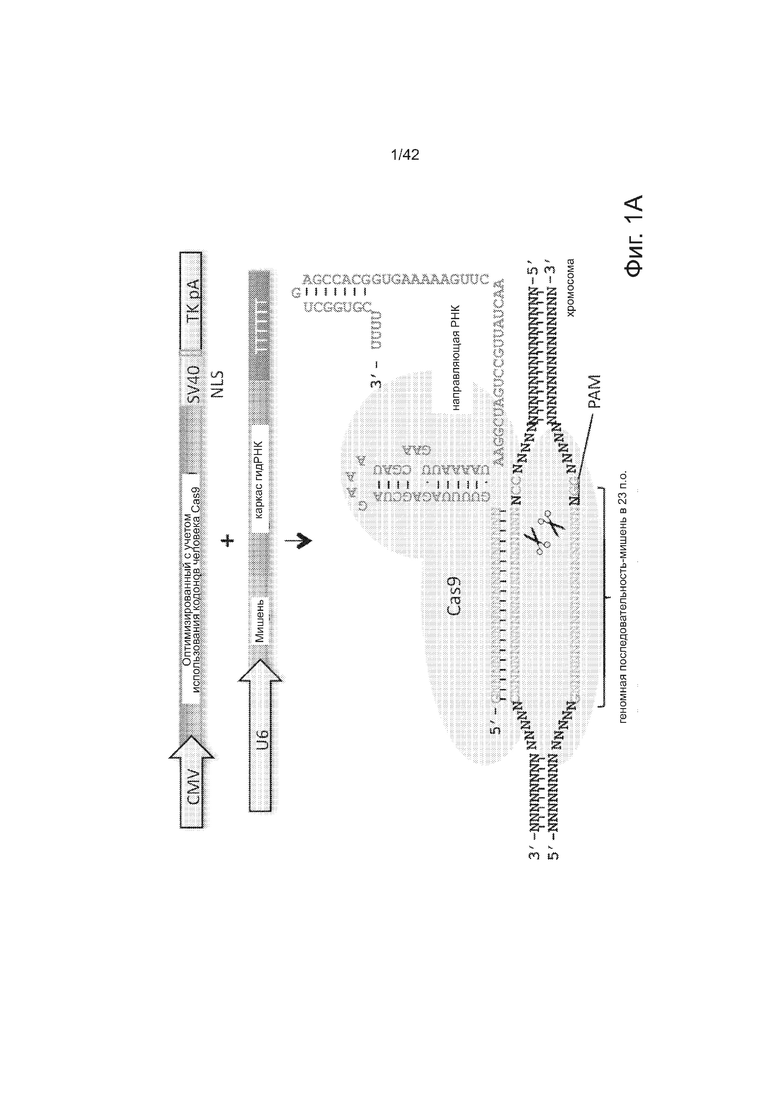
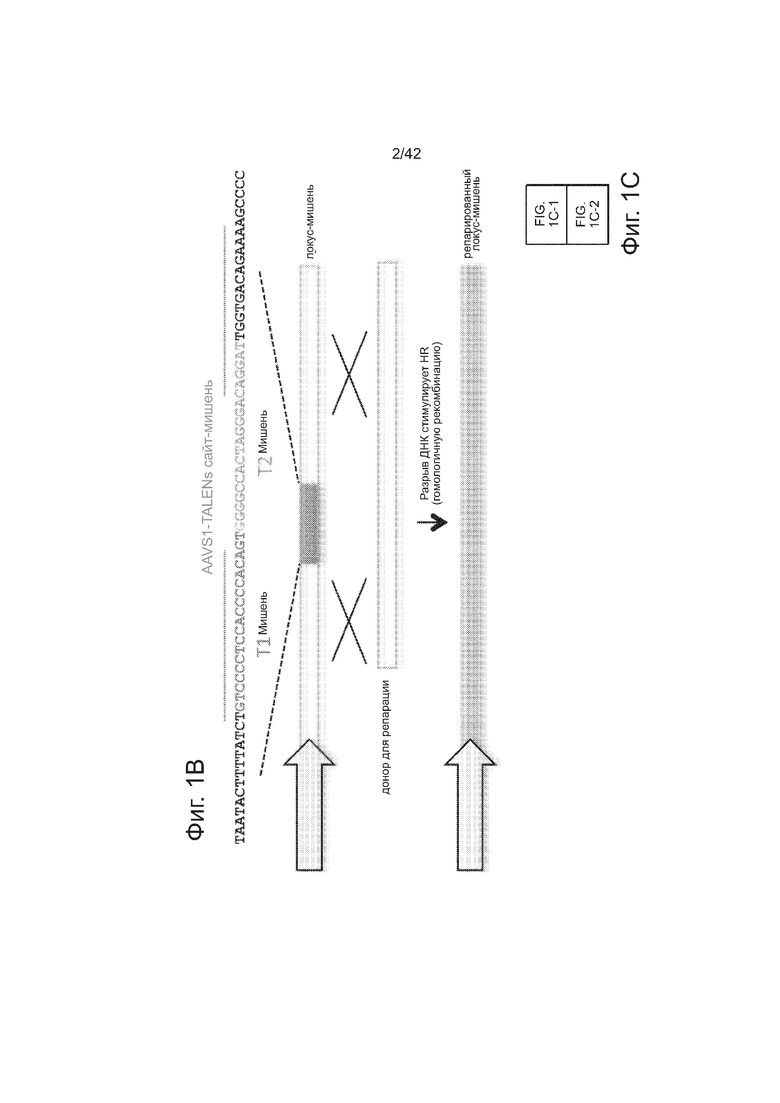
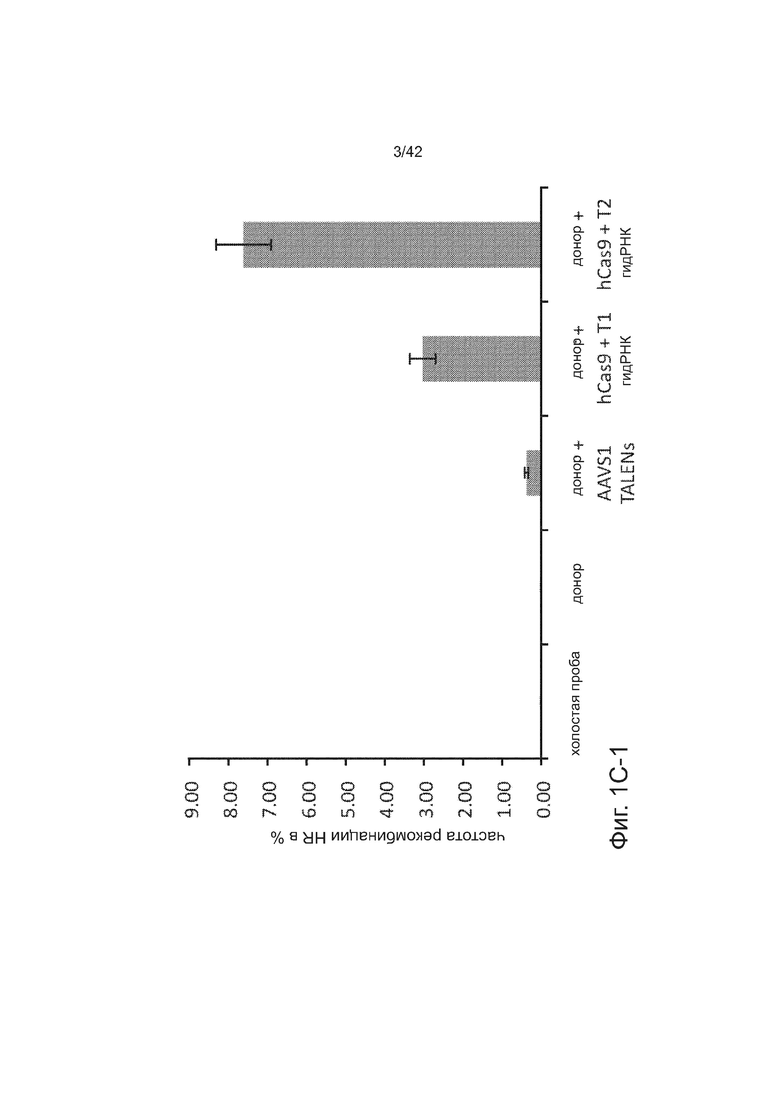


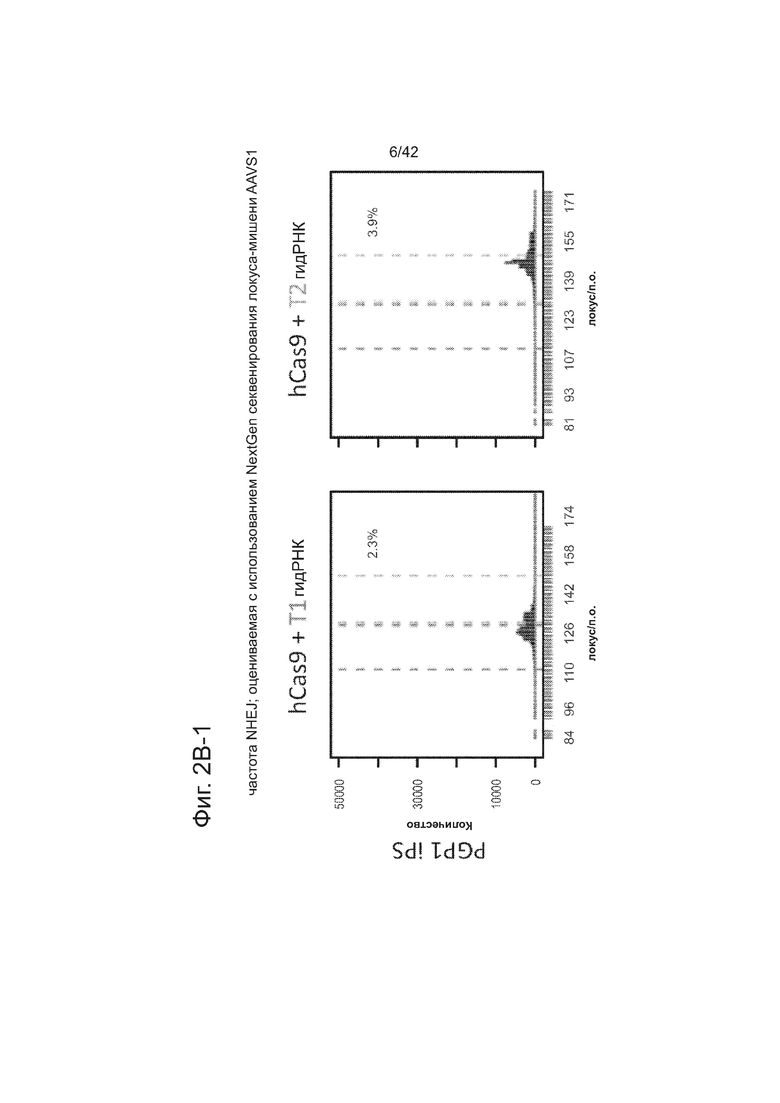
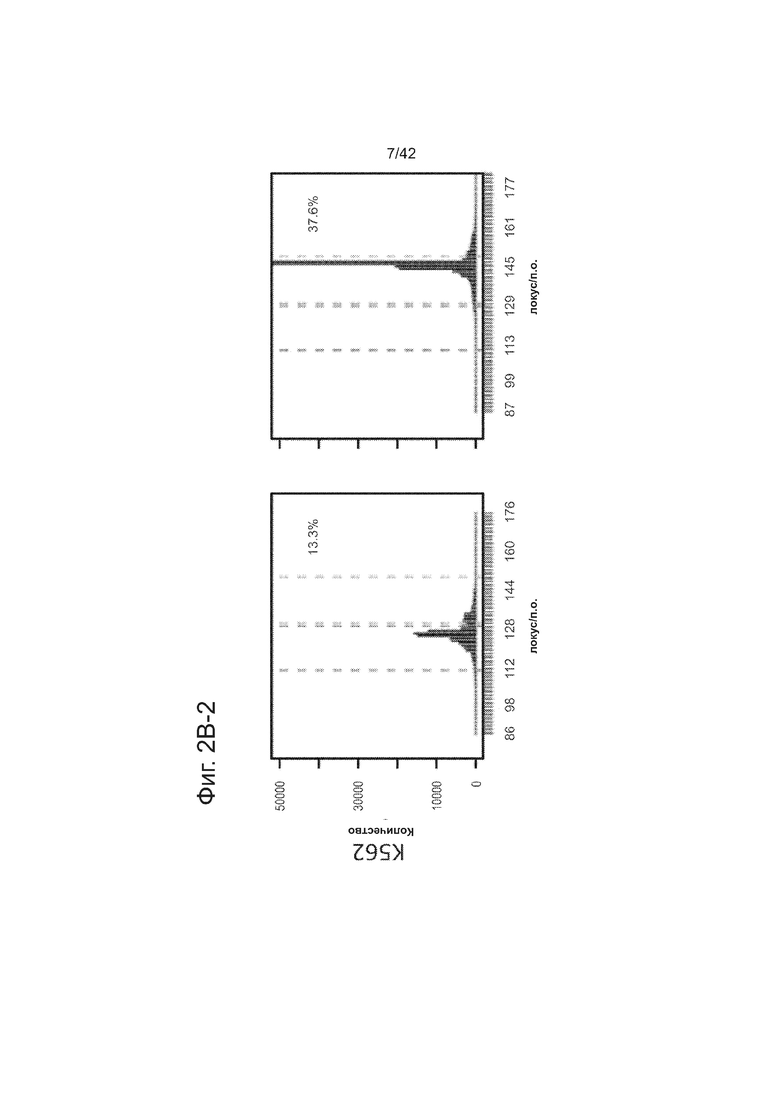
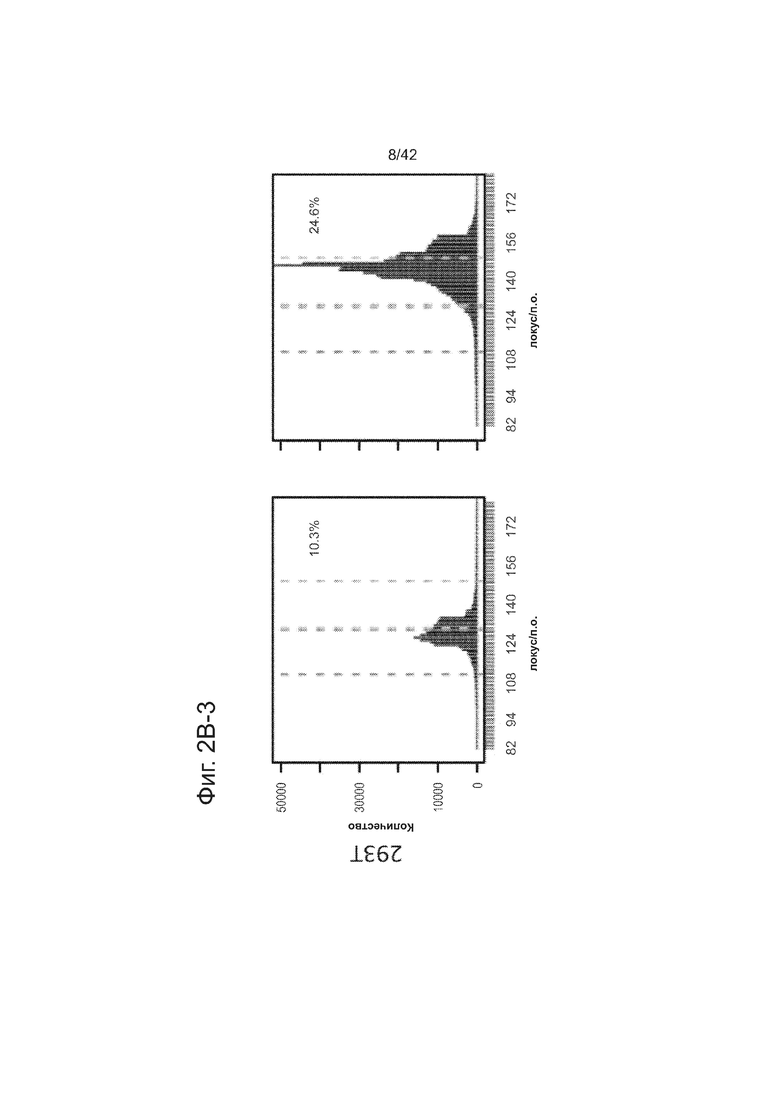
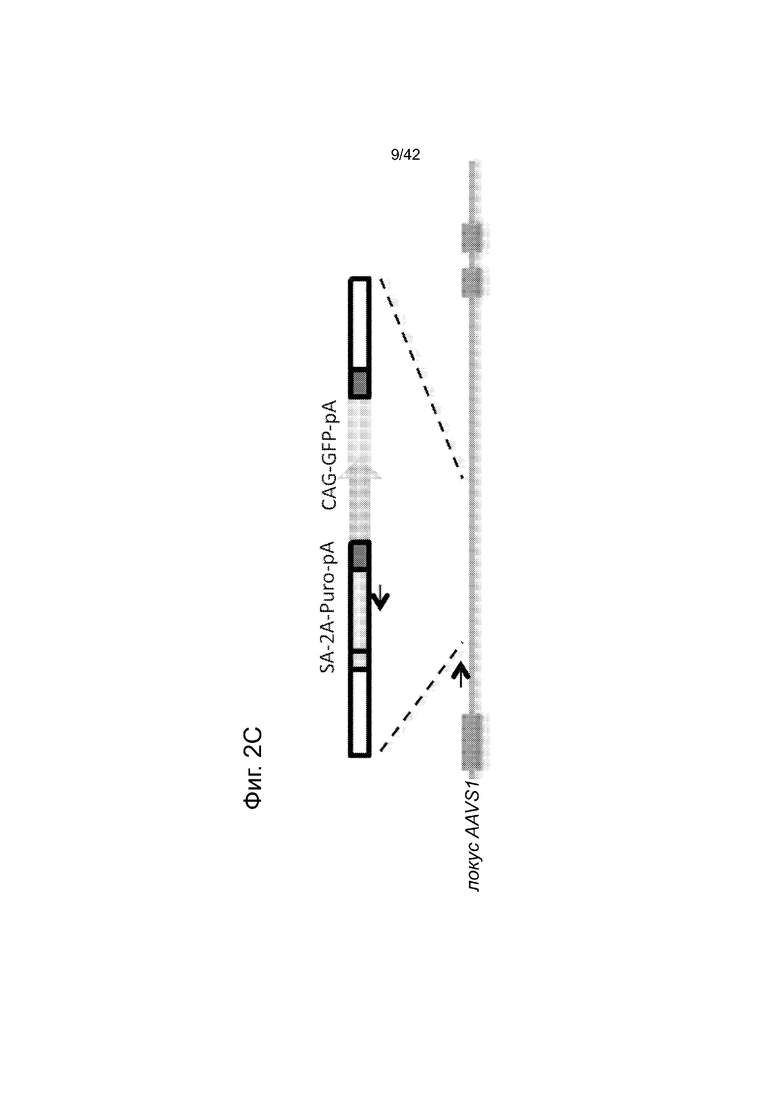

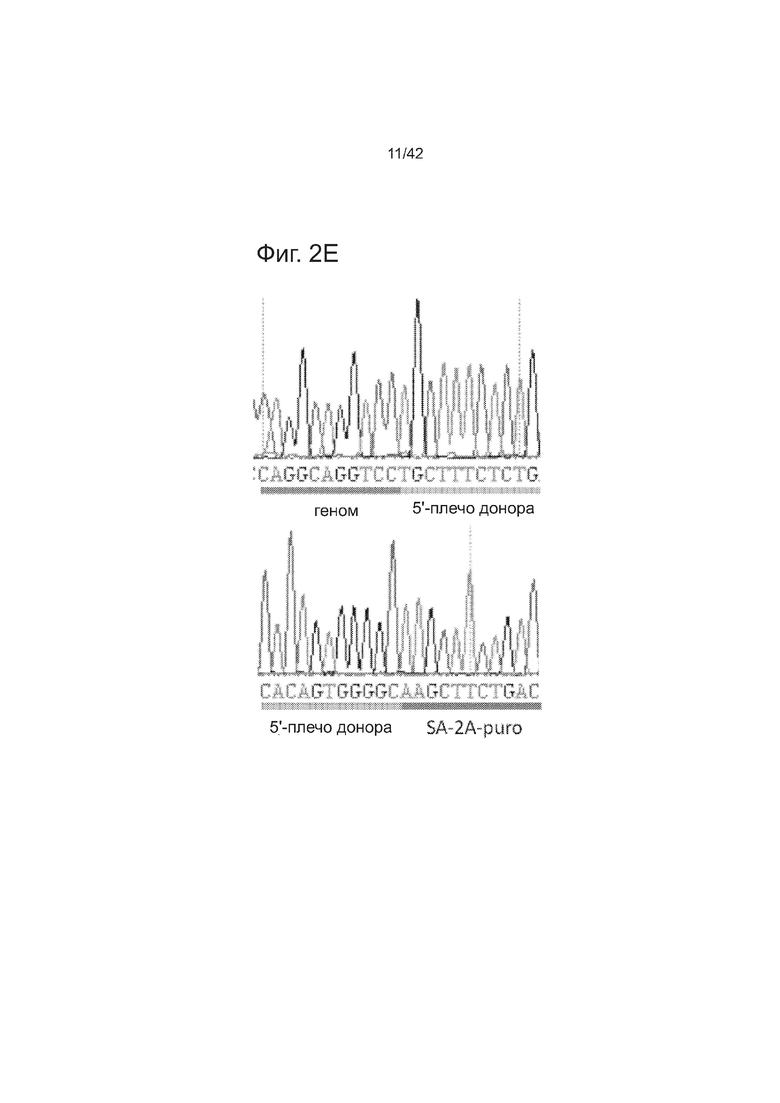
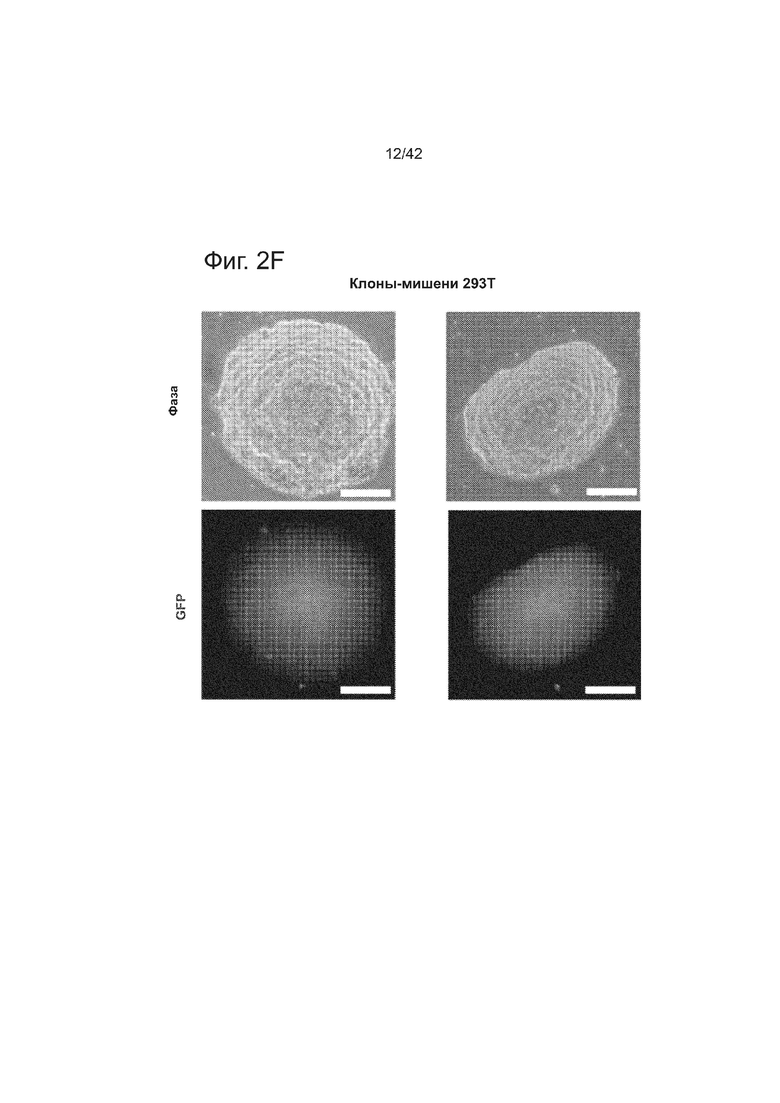





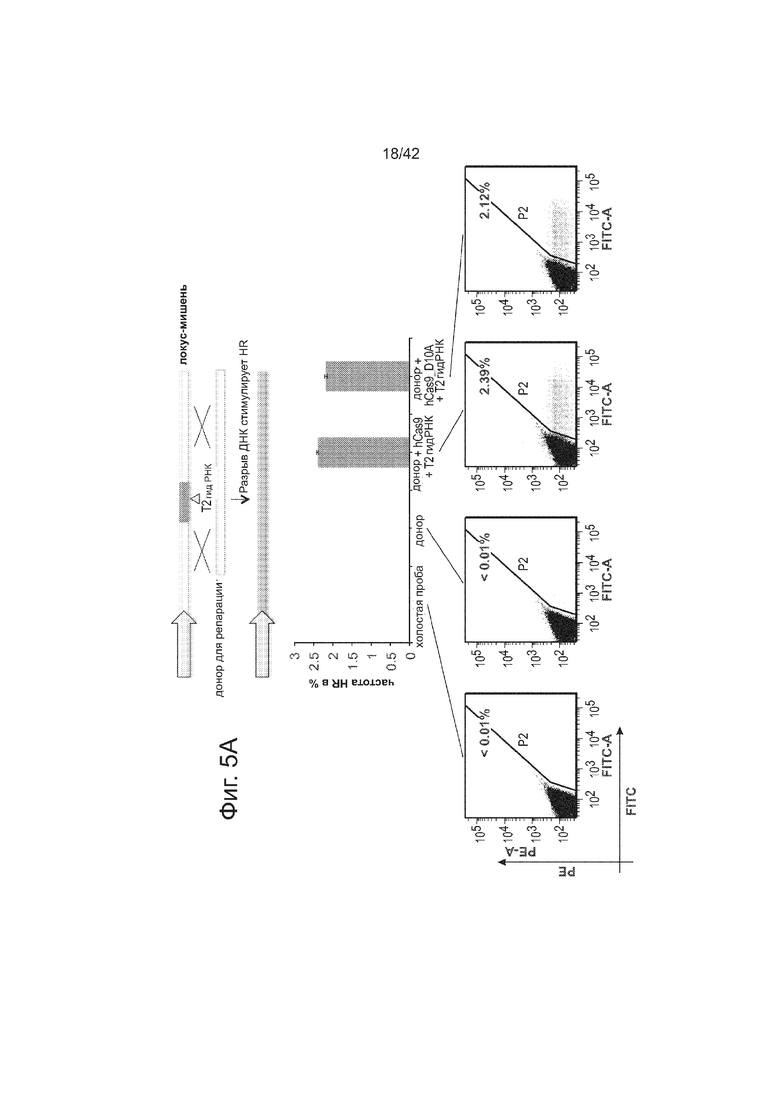
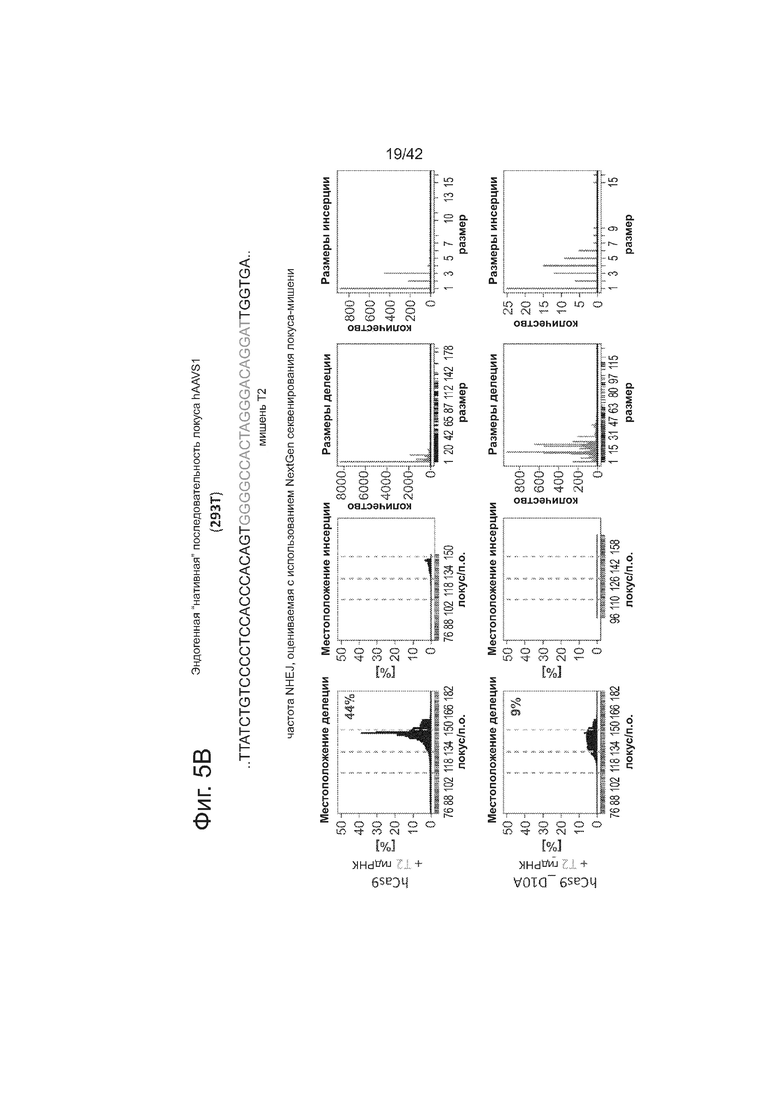
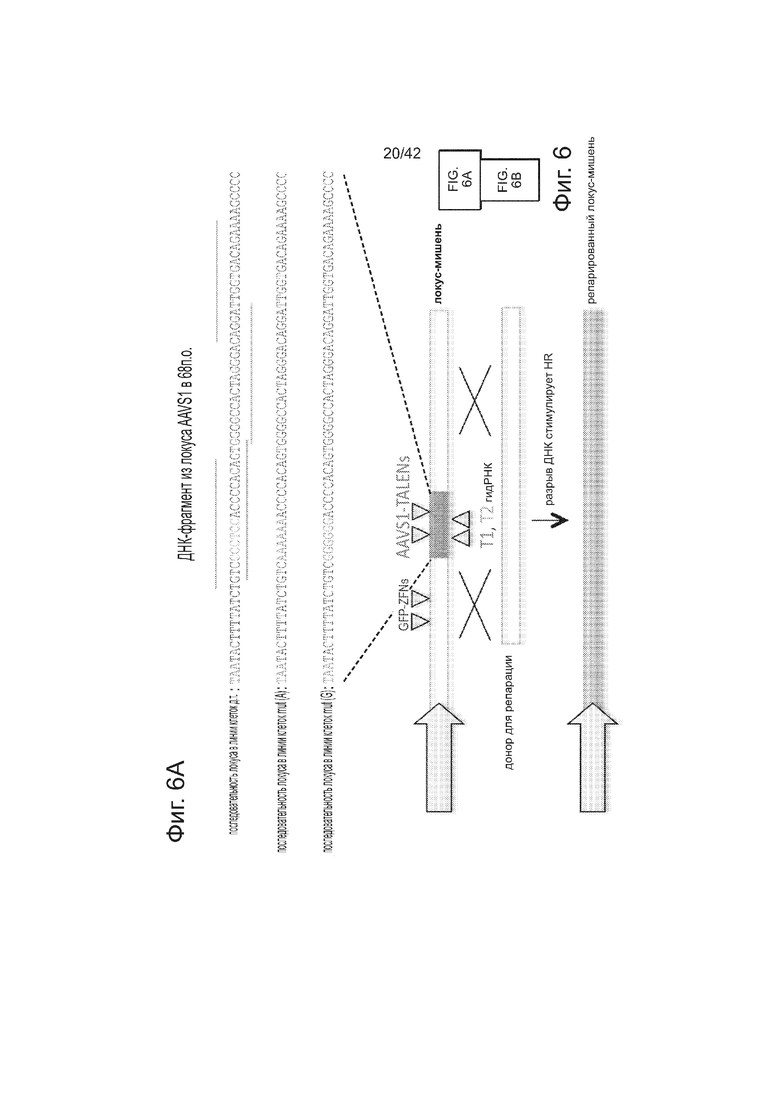
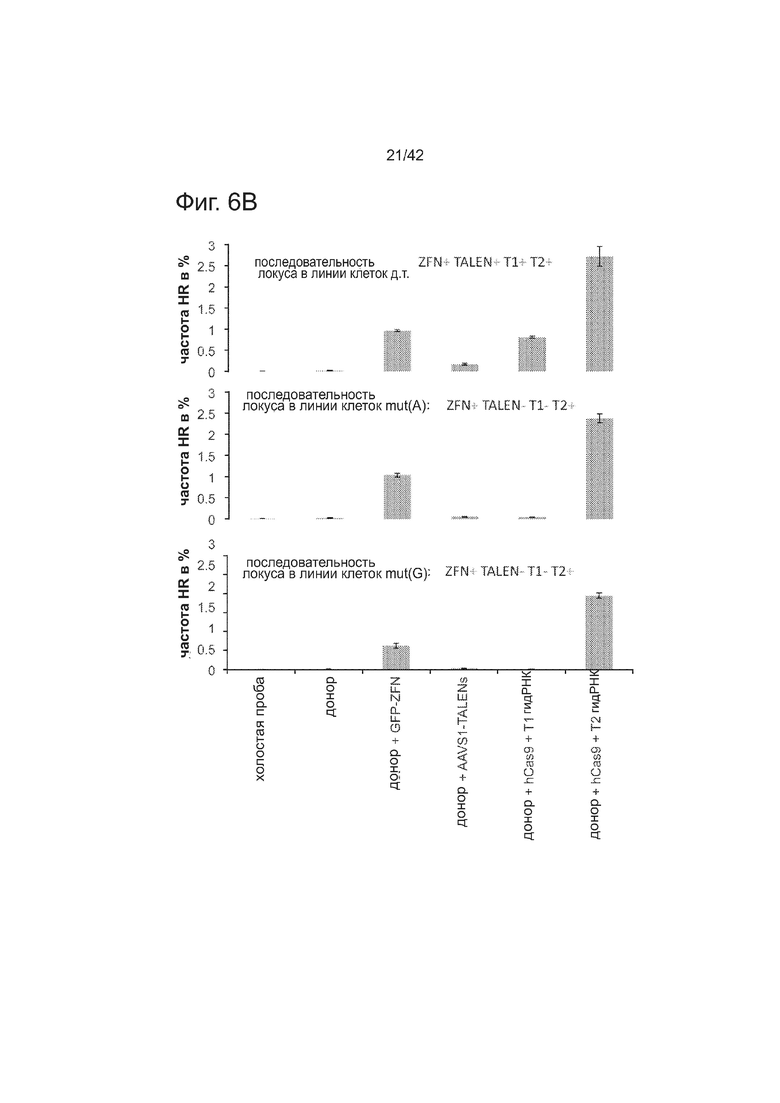
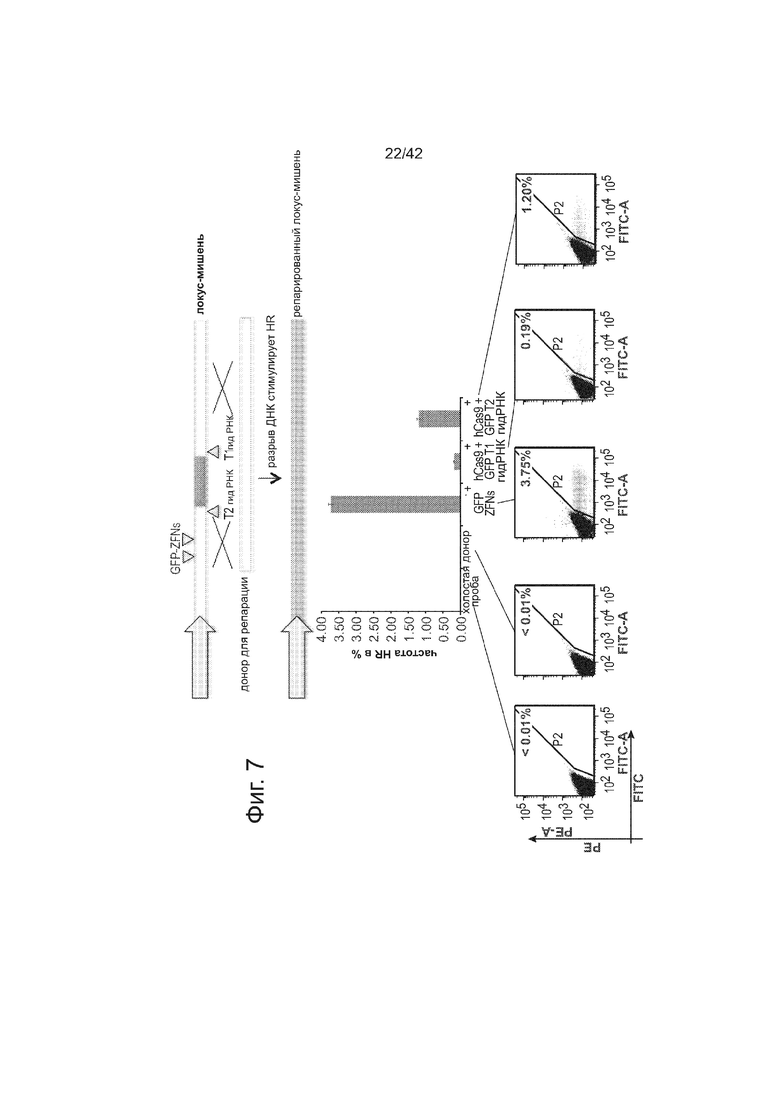
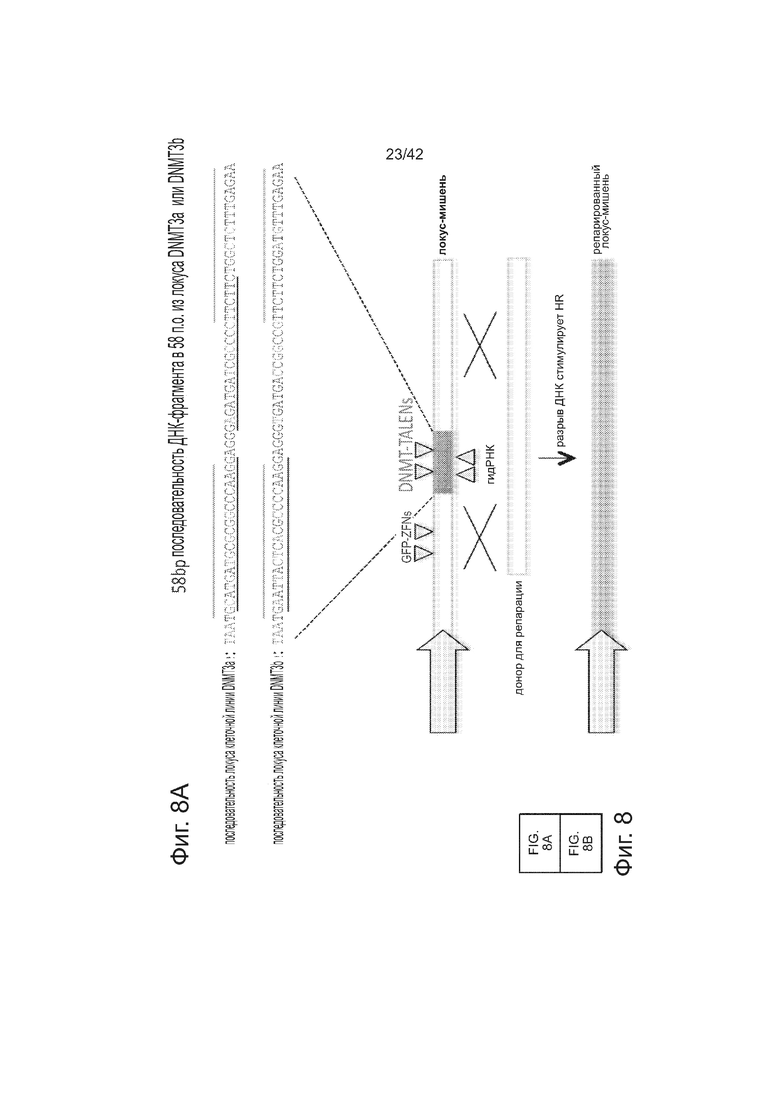

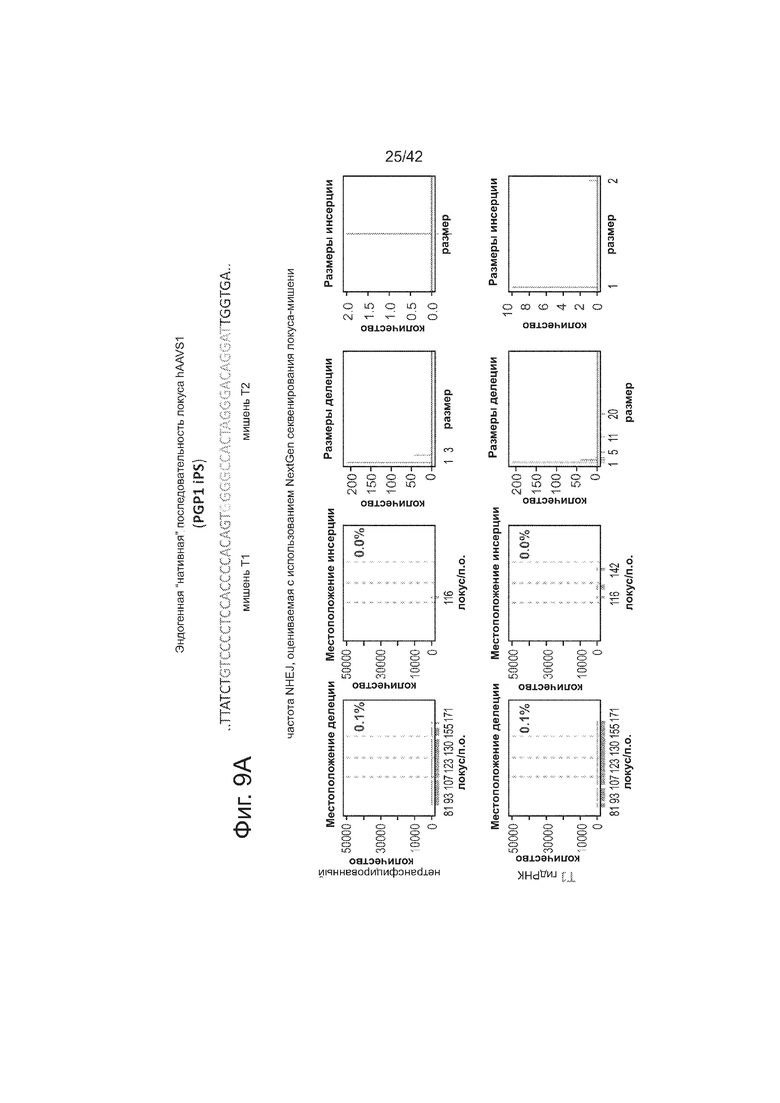
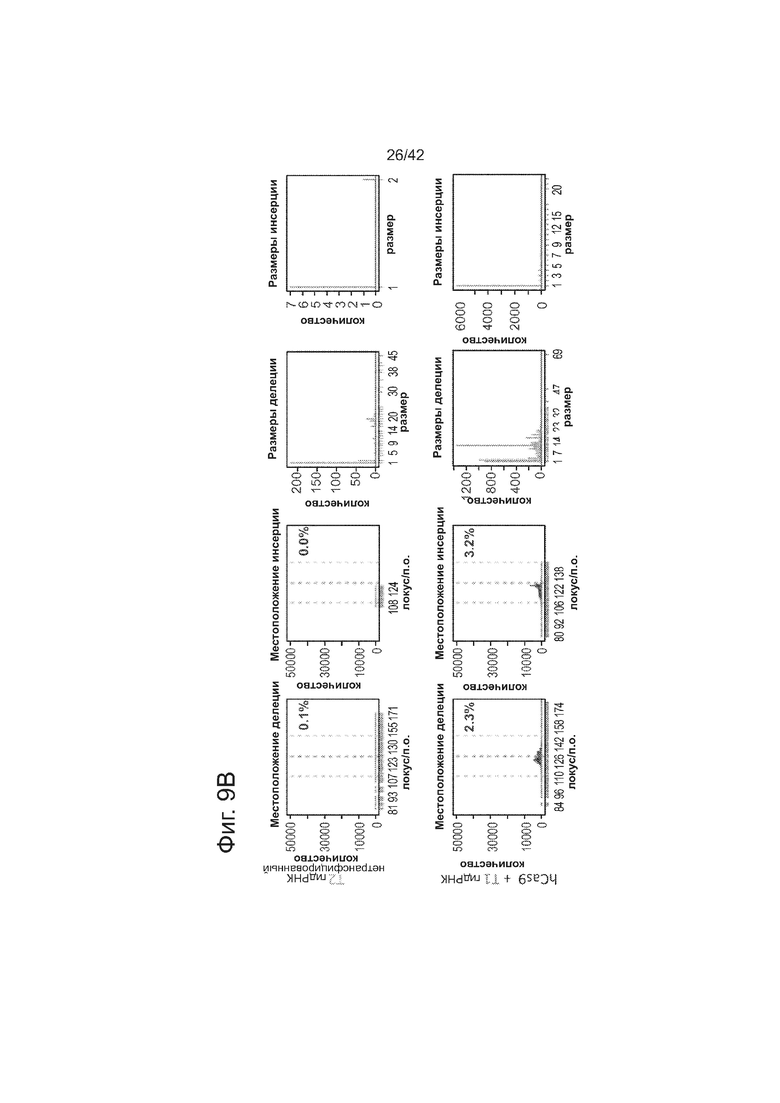
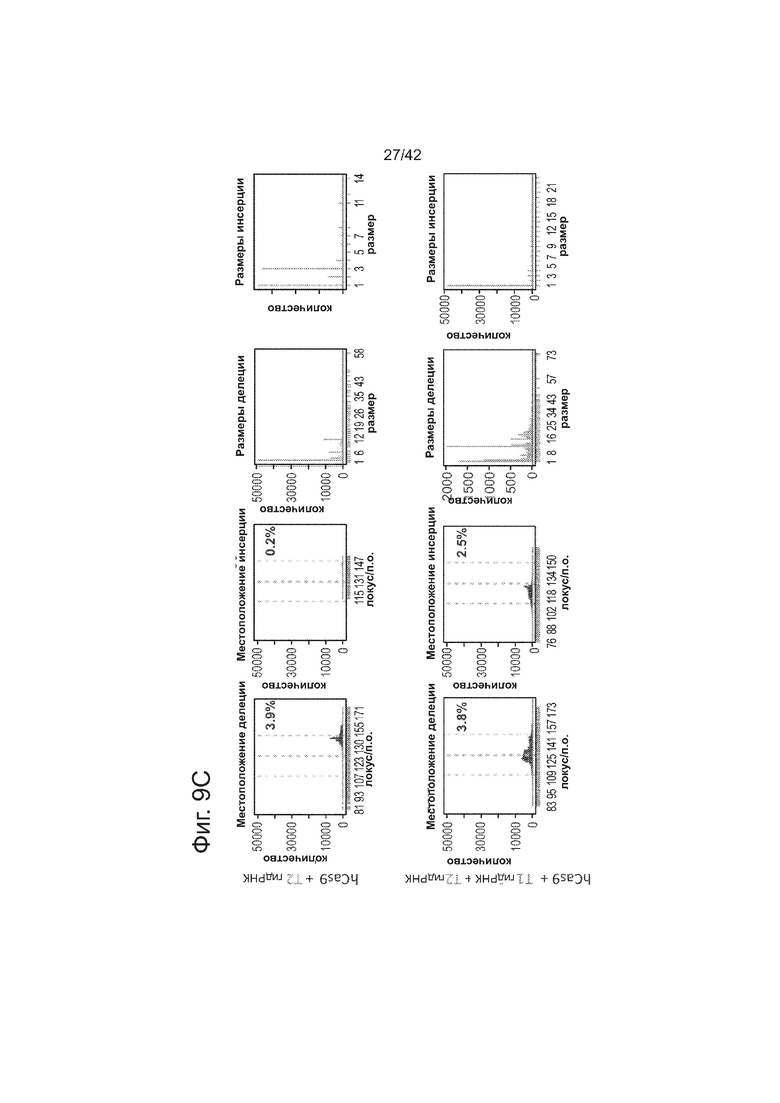
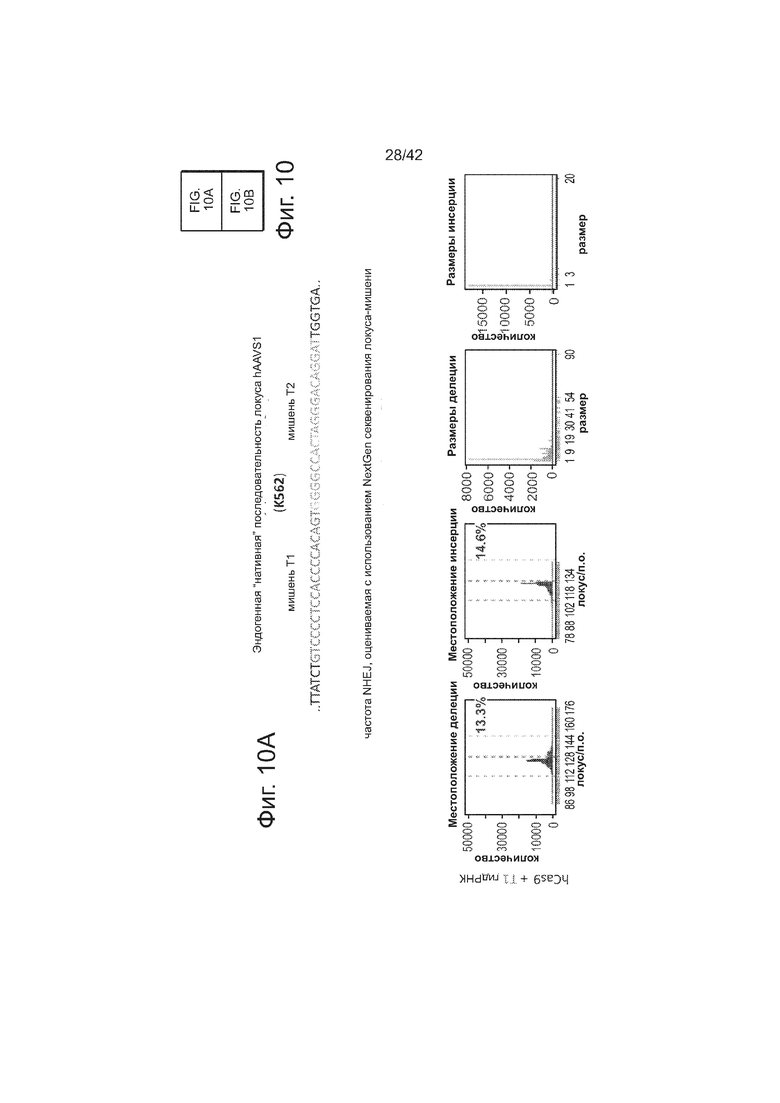
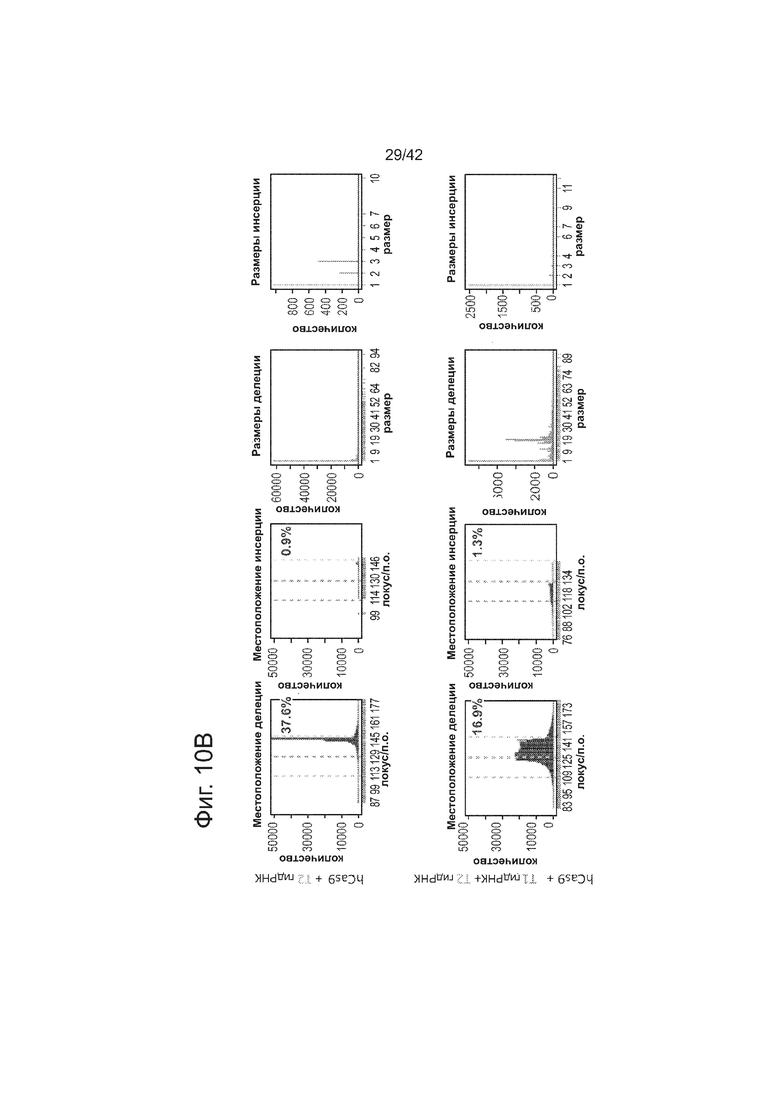
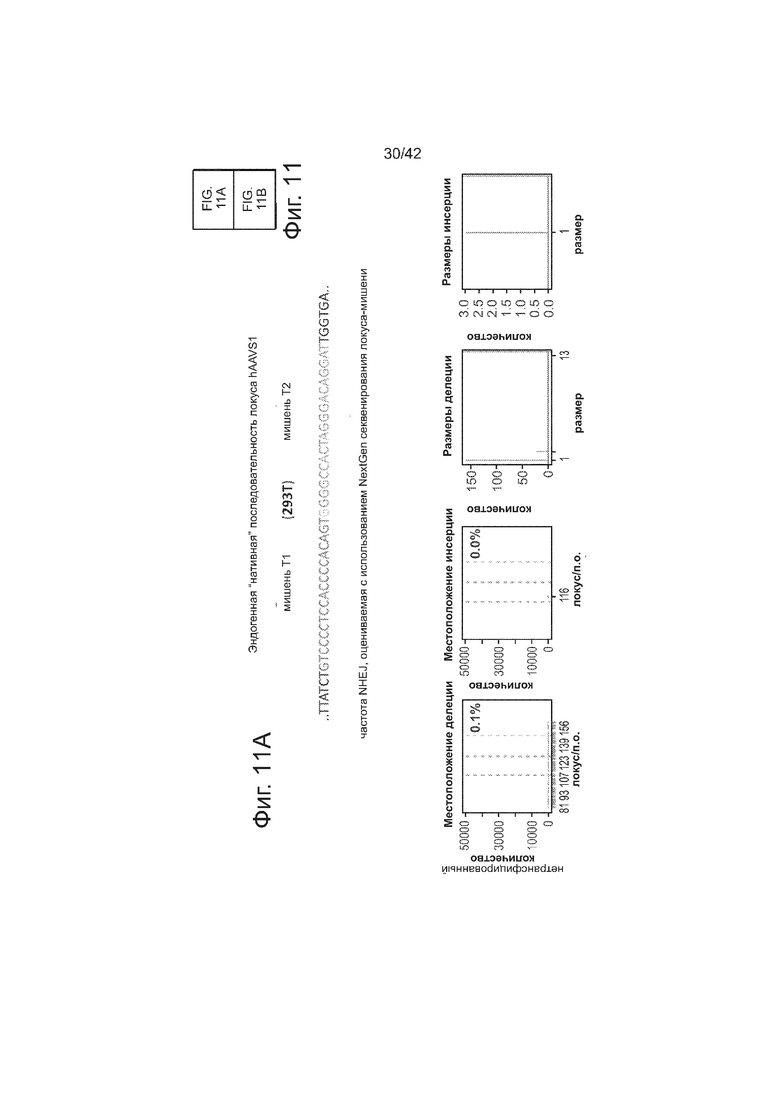
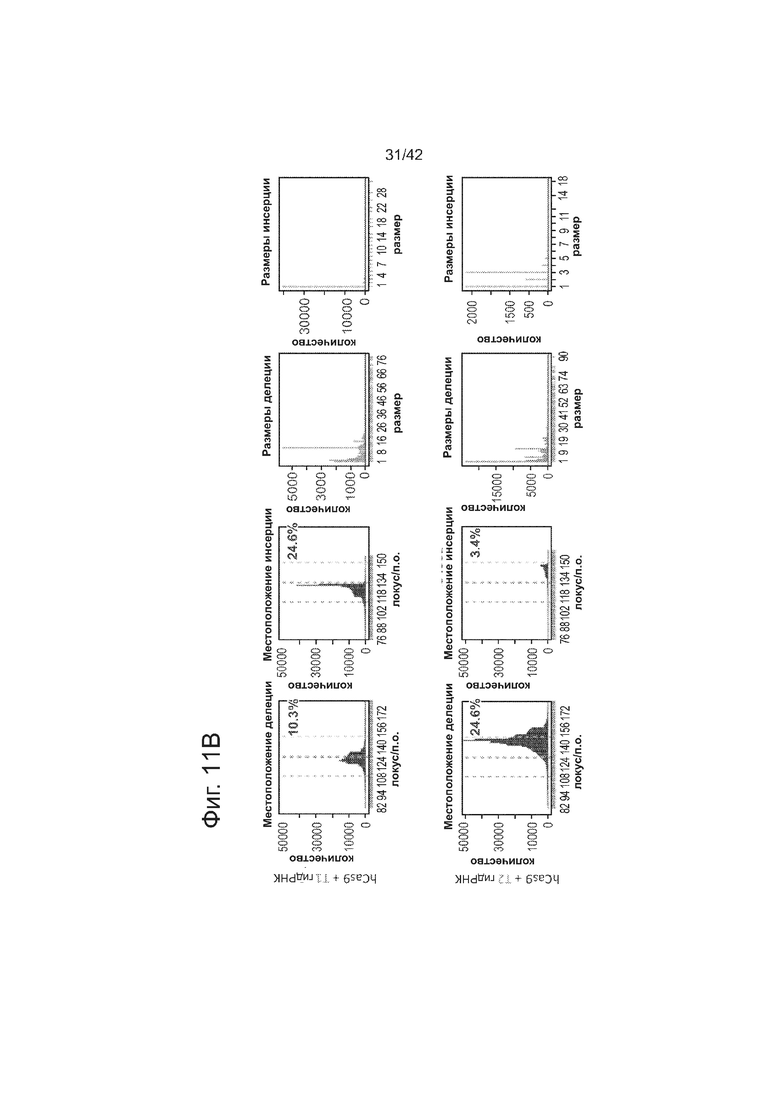

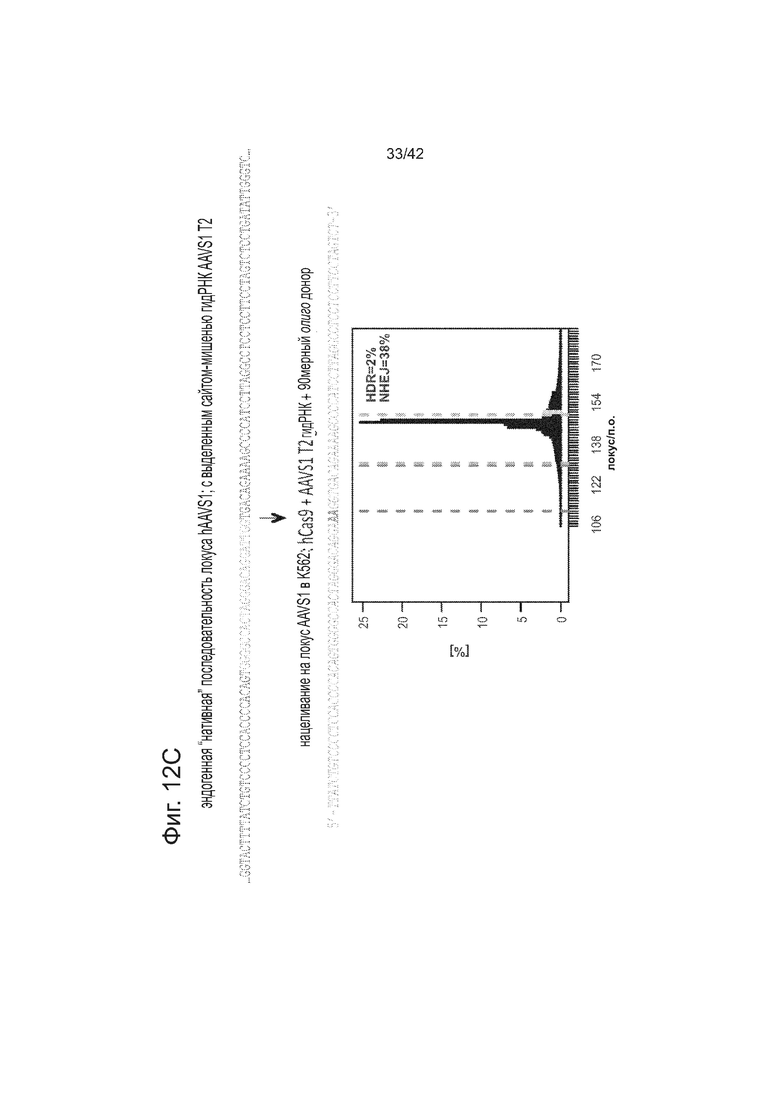

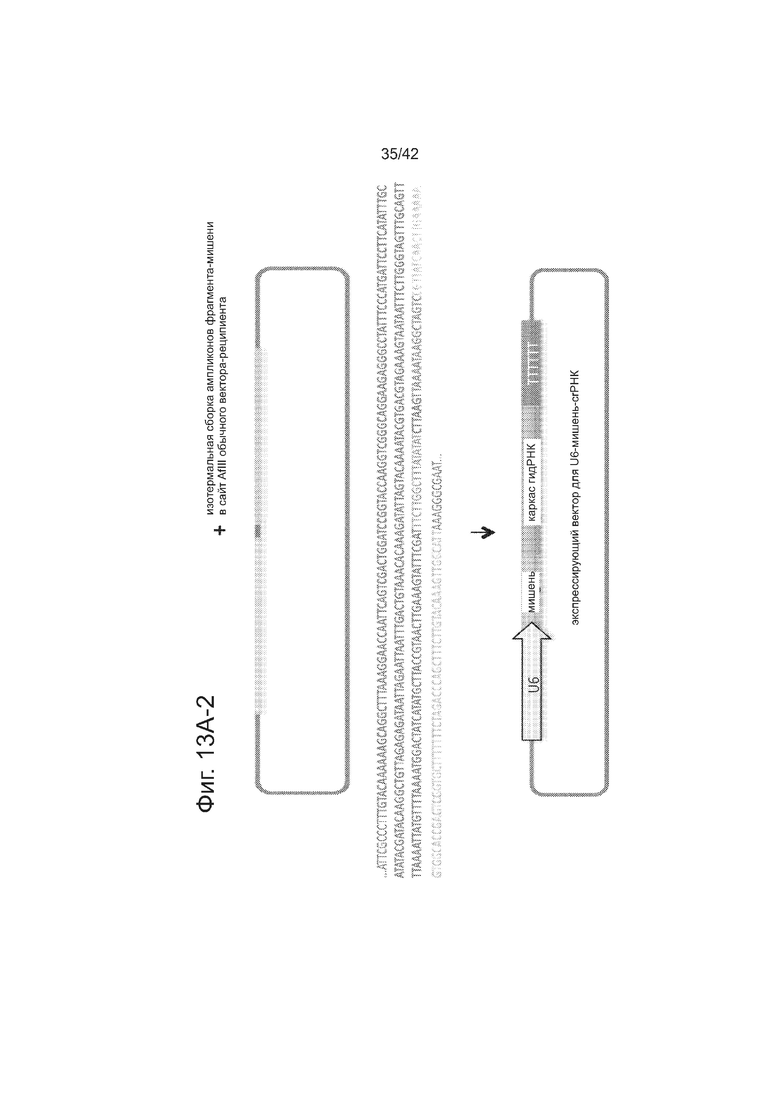
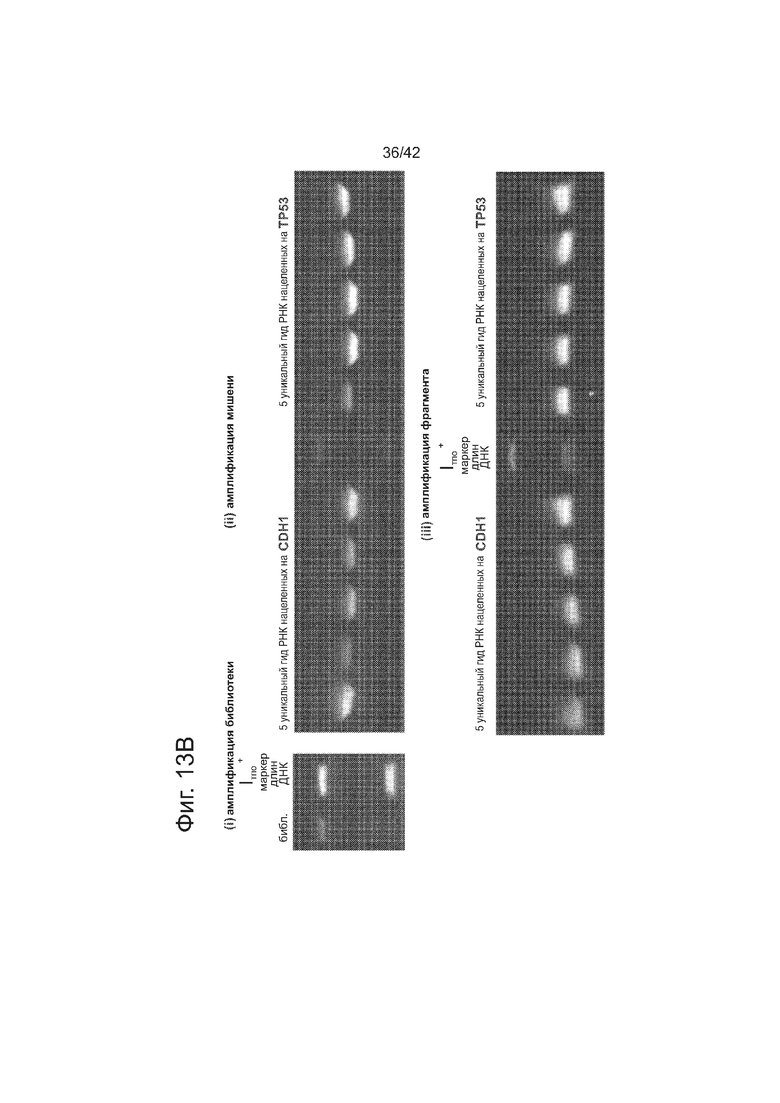
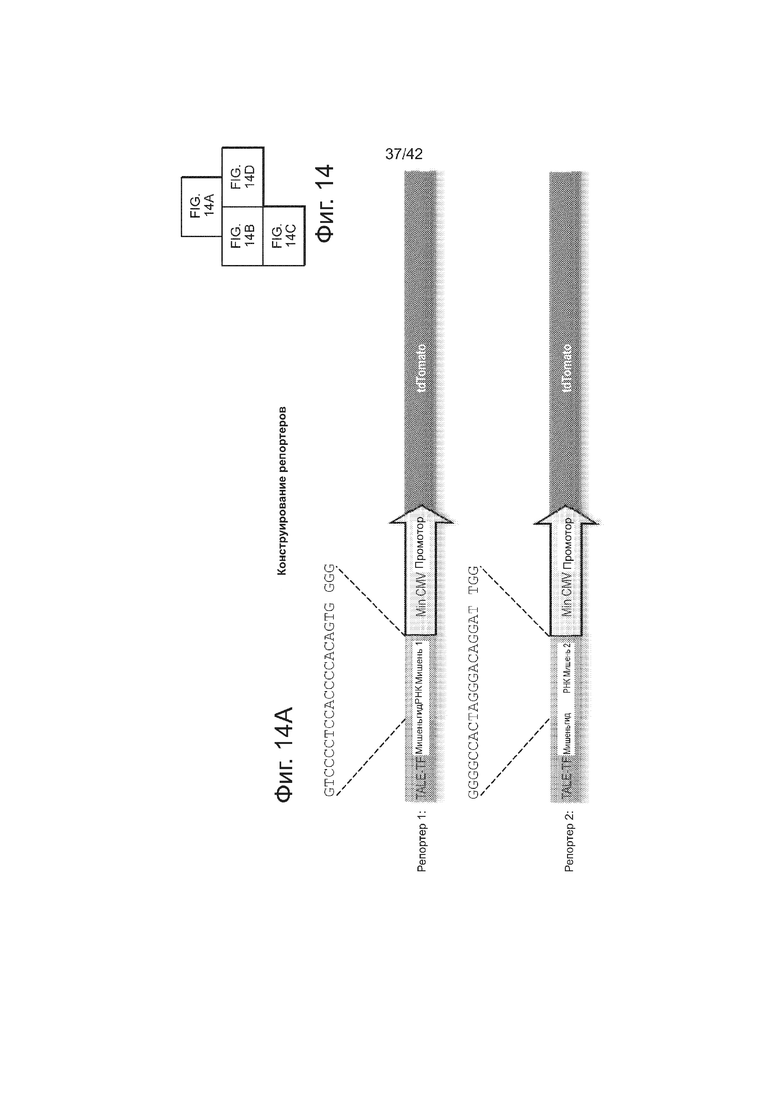
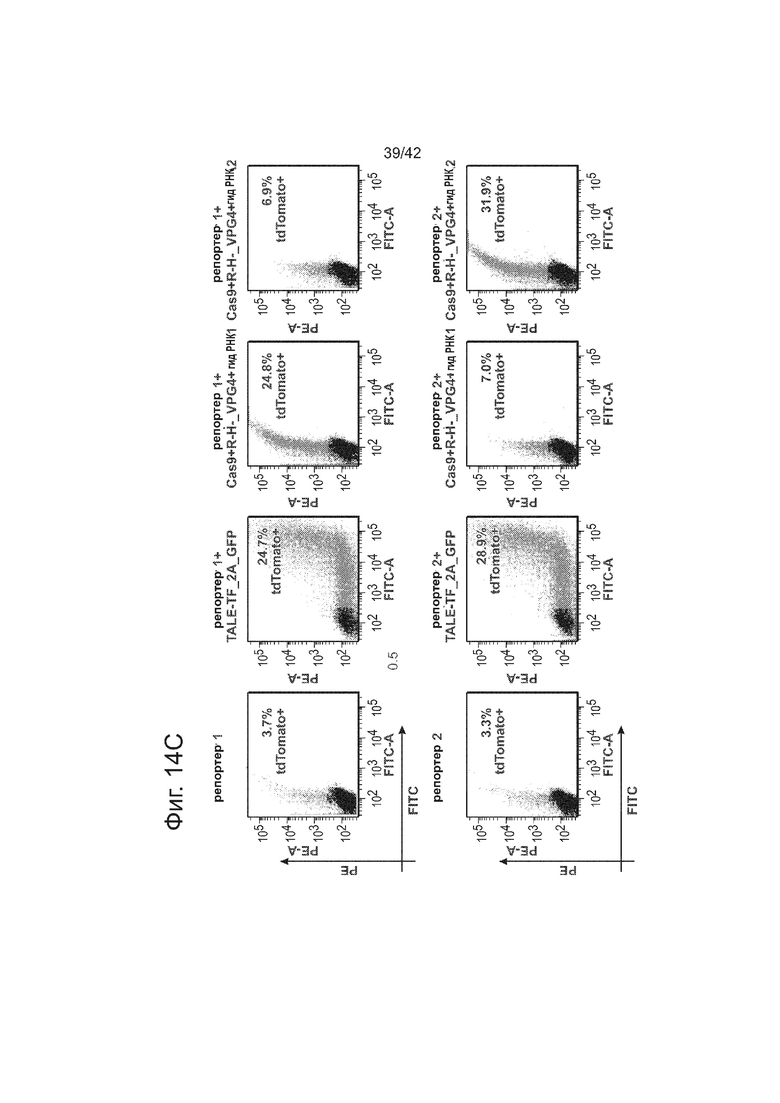

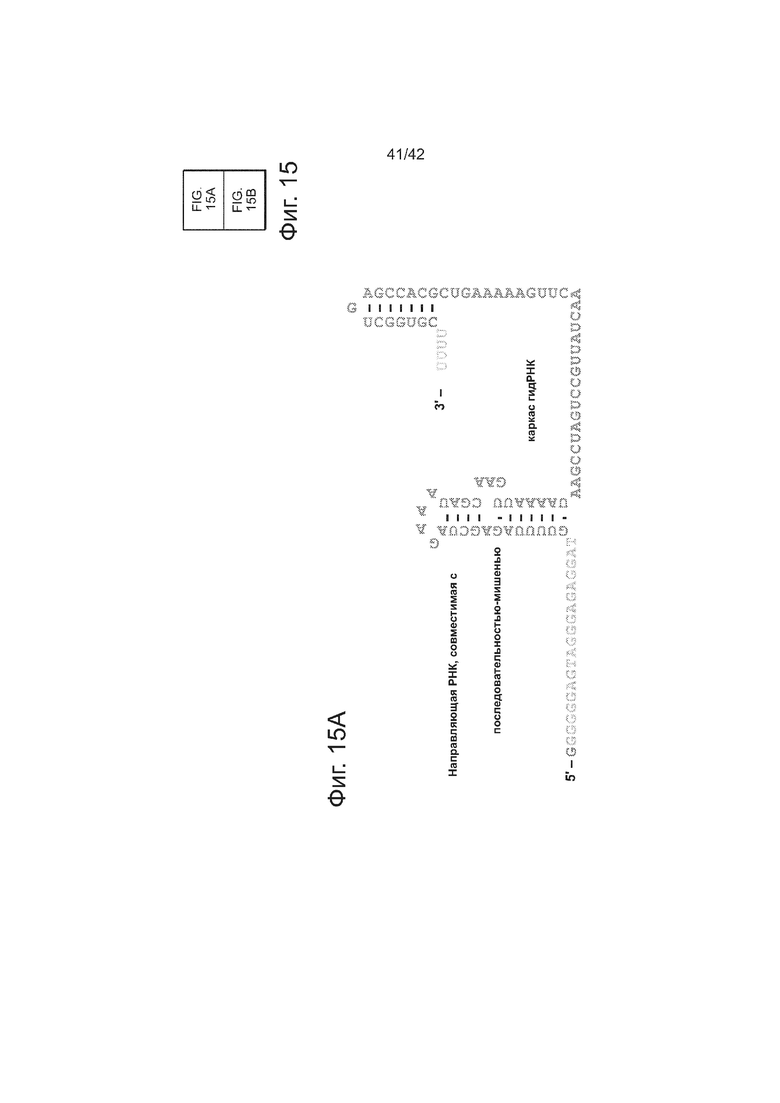
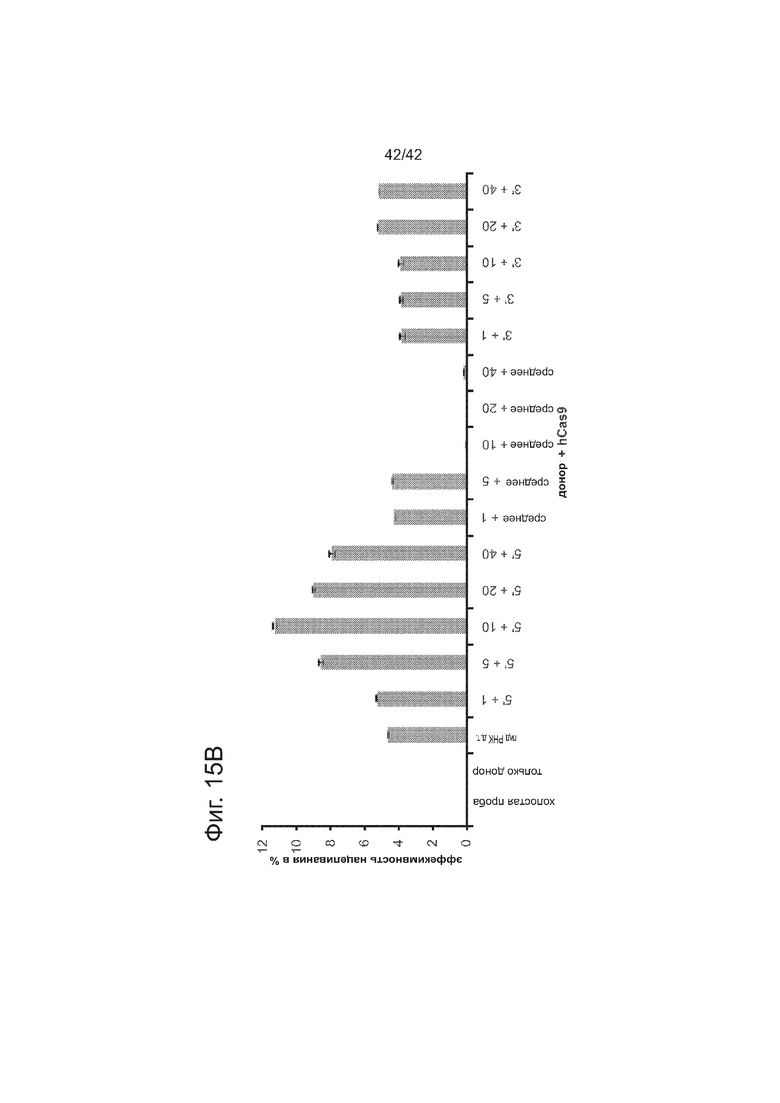
Изобретение относится к области биотехнологии, в частности к направляющей РНК, содержащей спейсер, комплементарный этой целевой нуклеиновой кислоте, и каркас, присоединенный к указанному спейсеру, где каркас связывает белок Cas системы CRISPR типа II, где направляющая РНК содержит от около 100 до около 250 нуклеотидов, а также к содержащей его системе редактирования генома и клетке. Также раскрыта нуклеиновая кислота, кодирующая указанную направляющую РНК, а также содержащие ее конструкция и вирус. Изобретение эффективно в основанном на Cas направляемом РНК редактировании генома эукариотической клетки. 6 н. и 11 з.п. ф-лы, 15 ил., 18 пр.
1. Направляющая РНК для применения в основанном на Cas направляемом РНК редактировании генома эукариотической клетки, содержащей целевую нуклеиновую кислоту, причем направляющая РНК содержит спейсер, комплементарный этой целевой нуклеиновой кислоте, и каркас, присоединенный к указанному спейсеру, где каркас связывает белок Cas системы CRISPR типа II, где направляющая РНК содержит от около 100 до около 250 нуклеотидов и где указанная эукариотическая клетка не является клеткой зародышевой линии клеток человека.
2. Направляющая РНК по п. 1, отличающаяся тем, что направляющая РНК содержит около 100 нуклеотидов.
3. Направляющая РНК по п. 1, отличающаяся тем, что направляющая РНК представляет собой слитый транскрипт crРНК-tracrРНК.
4. Направляющая РНК по п. 1, отличающаяся тем, что направляющая РНК представляет собой слитый транскрипт crРНК-tracrРНК, обладающий вторичной структурой, включающей первую шпильку, соединенную со спейсерной последовательностью, и вторую 3'-шпильку.
5. Направляющая РНК по п. 1, отличающаяся тем, что каркас включает следующую последовательность нуклеиновой кислоты GUUUUAGAGCUAGAAAUAGCAAGUUAAAAUAAGGCUAGUCCGUUAUCAACUUGAAAAAGUGGCACCGAGUCGGUGC (SEQ ID NO:46).
6. Направляющая РНК по п. 1, отличающаяся тем, что к 3'-концу каркаса присоединена последовательность поли-U.
7. Направляющая РНК по п. 1, отличающаяся тем, что последовательность поли-U UUUU присоединена к 3'-концу каркаса.
8. Сконструированная нуклеиновая кислота, кодирующая направляющую РНК по п. 1.
9. Конструкция для экспрессии направляющей РНК, содержащая сконструированную нуклеиновую кислоту по п. 8 и регуляторный элемент, способный к функционированию в эукариотической клетке, функционально связанный со сконструированной нуклеиновой кислотой по п. 8.
10. Конструкция по п. 9, в которой регуляторный элемент представляет собой промотор U6 полимеразы III человека.
11. Система редактирования генома, направляемая РНК, содержащая
(1) направляющую РНК или первую нуклеиновую кислоту, кодирующую эту направляющую РНК, и
(2) фермент Cas, который образует комплекс с направляющей РНК, или вторую нуклеиновую кислоту, кодирующую фермент Cas,
причем направляющая РНК содержит спейсер, комплементарный целевой нуклеиновой кислоте и связывающий эту целевую нуклеиновую кислоту, и где направляющая РНК представляет собой слитый транскрипт crРНК-tracrРНК, содержащий от около 100 до около 250 нуклеотидов,
где фермент Cas является ферментом Cas системы CRISPR типа II,
где указанные первая нуклеиновая кислота и вторая нуклеиновая кислота содержатся в экспрессионных векторах и
где редактирование генома не происходит в клетке зародышевой линии клеток человека.
12. Эукариотическая клетка для получения клетки, содержащей измененную с помощью системы редактирования генома целевую нуклеиновую кислоту, отличающаяся тем, что содержит систему редактирования генома, направляемую РНК, по п.11,
где указанная эукариотическая клетка не является клеткой зародышевой линии клеток человека.
13. Эукариотическая клетка по п.12, которая представляет собой дрожжевую клетку, растительную клетку, клетку млекопитающего или клетку человека.
14. Эукариотическая клетка по п.12, где эукариотическая клетка представляет собой стволовую клетку.
15. Эукариотическая клетка по п.12, где эукариотическая клетка представляет собой iPSC (индуцированную плюрипотентную стволовую клетку) человека.
16. Вирус, включающий нуклеиновую кислоту, кодирующую направляющую РНК, которая содержит спейсер, комплементарный целевой нуклеиновой кислоте, который связывается с целевой нуклеиновой кислотой, где направляющая РНК представляет собой слитый транскрипт crРНК-tracrРНК, включающий от около 100 нуклеотидов до около 250 нуклеотидов, где вирус предназначен для доставки нуклеиновой кислоты, кодирующей направляющую РНК.
17. Вирус по п.16, где вирус представляет собой аденоассоциированный вирус.
| JINEK M | |||
| et al | |||
| A programmable dual-RNA-guided DNA endonuclease in adaptive bacterial immunity, Science, август 2012, 337(6096), pp.816-821 | |||
| GASIUNAS G | |||
| et al | |||
| Разборный с внутренней печью кипятильник | 1922 |
|
SU9A1 |
Авторы
Даты
2022-03-15—Публикация
2013-12-16—Подача