Область техники, к которой относится изобретение
Настоящее изобретение относится к новому слитому белку, включающему IL-12 или его вариант; и антитело против FAP, а также к включающей его противораковой фармацевтической композиции.
Уровень техники
Интерлейкин-12 (IL-12) - типичный воспалительный цитокин, играющий важную роль в эффективной индукции клеточного иммунного ответа. IL-12 связывается и продуцируется активированными макрофагами, моноцитами, дендритными клетками и активированными B-лимфоцитами. IL-12 может усиливать иммунный ответ T-хелперов 1, повышать цитотоксичность клеточных T-лимфоцитов и ингибировать ангиогенез. Как правило, IL-12 активирует продукцию IFN-γ в T-клетках и NK-клетках.
Локальная экспрессия IL-12 делает опухолевые клетки чувствительными к опосредованной T-клетками цитотоксичности, что приводит к ингибированию роста опухоли и запуску гуморального иммунитета. Однако недостатком клинического применения IL-12 является то, что при введении может проявляться системная токсичность, связанная с цитокинами. Эти клинические результаты показывают ограничения IL-12 в качестве монотерапевтического средства для лечения рака.
С другой стороны, белок активации фибробластов альфа (FAP) представляет собой желатиназу, экспрессируемую на активированных фибробластах. Известно, что FAP экспрессируется более чем на 90% связанных с раком фибробластов различных карцином человека, включая рак предстательной железы и рак поджелудочной железы. Таким образом, в последнее время быстро растет интерес к разработке иммунотерапии, направленной на FAP-экспрессирующие клетки (Fang J. et al., Mol. Ther. Oncolytics., 3:16007, 2016).
Подробное описание изобретения
Техническая задача
Таким образом, авторы настоящего изобретения провели исследование с целью разработки нового слитого белка, обладающего противоопухолевым действием. В результате авторы настоящего изобретения обнаружили, что слитый белок, включающий IL-12 и антитело против FAP, обладает повышенной противоопухолевой активностью с одновременным снижением системной токсичности, осуществив тем самым настоящее изобретение.
Решение задачи
В одном аспекте настоящего изобретения предложен слитый белок, включающий первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP.
В еще одном аспекте настоящего изобретения предложена фармацевтическая композиция для предупреждения или лечения рака, включающая слитый белок в качестве активного ингредиента.
В еще одном аспекте настоящего изобретения предложен полинуклеотид, кодирующий первый мономер.
В еще одном аспекте настоящего изобретения предложен полинуклеотид, кодирующий второй мономер.
В еще одном аспекте настоящего изобретения предложен вектор, включающий полинуклеотид.
В еще одном аспекте настоящего изобретения предложена трасформированная клетка, в которую был введен вектор.
В еще одном аспекте настоящего изобретения предложен способ получения слитого белка, включающий: i) культивирование трансформированной клетки; и ii) выделение слитого белка, включающего первый мономер и второй мономер.
В другом аспекте настоящего изобретения предложен способ лечения или предупреждения рака, включающий введение субъекту слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP.
В другом аспекте настоящего изобретения предложено применение слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP, для лечения рака.
В другом аспекте настоящего изобретения предложено применение слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP, для производства лекарственного средства для лечения рака.
Эффекты изобретения
Слитый белок, включающий IL-12 и антигенсвязывающий участок, который специфично связывается с FAP, может проявлять противоопухолевое действие посредством IL-12. Кроме того, было обнаружено, что при реализации антитела против FAP в одном антителе, IL-12 специфично накапливается в опухоли с высокой экспрессией FAP, что снижает системное токсическое действие и демонстрирует опухолеспецифическое противоопухолевое действие. Таким образом, рак можно эффективно лечить путем специфического направленного воздействия на FAP, экспрессируемый на высоком уровне в опухоли, и специфической локализации IL-12 в очаге опухоли.
Краткое описание чертежей
ФИГ. 1 иллюстрирует результат, полученный при идентификации T1.01, T1.02, T1.03, T1.04, T1.05, T1.06 и T1.07 согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 2 иллюстрирует результат, полученный при идентификации T1.08, T1.09, T1.10, T1.11, T1.12, T1.13, T1.14 и T1.15 согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 3 иллюстрирует результат, полученный при идентификации T1.16, T1.17, T1.18, T1.19 и T1.21 согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 4 иллюстрирует результат, полученный при идентификации T1.01m, T1.02m, T1.03m, T1.04m, T1.05m, T1.06m и T1.07m согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 5 иллюстрирует результат, полученный при идентификации T1.08m, T1.09m, T1.10m, T1.11m, T1.12m, T1.13m и T1.15m согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 6 иллюстрирует результат, полученный при идентификации T1.16m, T1.17m, T1.18m, T1.19m, T1.20m, T1.21m и T1.22m согласно одному варианту осуществления с помощью электрофореза в ДСН-ПААГ.
ФИГ. 7 иллюстрирует график, на котором показаны аффинности связывания T1.01 и T1.02 с рекомбинантным человеческим FAP (rhFAP) с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 8 иллюстрирует график, на котором показана аффинность связывания T1.03 с рекомбинантным человеческим FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 9 иллюстрирует график, на котором показаны аффинности связывания T1.04 и T1.05 с рекомбинантным человеческим FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 10 иллюстрирует график, на котором показаны аффинности связывания T1.06 и T1.07 с рекомбинантным человеческим FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 11 иллюстрирует график, на котором показаны аффинности связывания T1.08 и T1.09 с рекомбинантным человеческим FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 12 иллюстрирует график, на котором показаны аффинности связывания T1.10 и T1.11 с рекомбинантным человеческим FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 13 иллюстрирует график, на котором показаны аффинности связывания T1.01m и T1.02m с рекомбинантным мышиным FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 14 иллюстрирует график, на котором показана аффинность связывания T1.03m с рекомбинантным мышиным FAP с помощью метода анализа на основе поверхностного плазмонного резонанса.
ФИГ. 15 иллюстрирует график, на котором показаны аффинности связывания T1.12, T1.01, T1.02 и T1.03 с клетками HEK293-hFAP и клетками HEK293 с помощью проточной цитометрии.
ФИГ. 16 иллюстрирует график, на котором показаны аффинности связывания T1.12m, T1.01m, T1.02m и T1.03m с клетками B16F10-mFAP и клетками B16F10 с помощью проточной цитометрии.
ФИГ. 17 иллюстрирует график, на котором показаны аффинности связывания T1.01, T1.02, T1.03 и T1.12 с бета-1 субъединицей рецептора IL-12 с помощью твердофазного иммуноферментного анализа.
ФИГ. 18 иллюстрирует график, на котором показан результат, полученный при идентификации активности IL-12 T1.01m, T1.02m, T1.03m и T1.12m по оптической плотности в репортерных клетках HEKblue.
ФИГ. 19 иллюстрирует график, на котором показана активность IL-12 T1.01, T1.02, T1.03 и T1.12 по сигнальной способности человеческих T-клеток.
ФИГ. 20 иллюстрирует график, на котором показана активность IL-12 T1.01, T1.02 и T1.03 в присутствии низкомолекулярного гепарина (НМГ) по сигнальной способности человеческих T-клеток.
ФИГ. 21 иллюстрирует график, на котором показан результат, полученный при измерении способности человеческих T-клеток секретировать цитокин IFN-γ при воздействии T1.12, T1.01, T1.02 и T1.03.
ФИГ. 22 иллюстрирует график, на котором показан результат, полученный при измерении способности человеческих NK-клеток секретировать цитокин IFN-γ при воздействии T1.12, T1.01, T1.02 и T1.03.
ФИГ. 23 иллюстрирует график, на котором показана способность ингибировать рост опухоли T1.01m и T1.02m по измерению изменения размера опухоли в модели опухоли на мышах, получавших совместную инъекцию линии мышиных фибробластов NIH-3T3 с оверэкспрессией FAP и линии клеток рака толстой и прямой кишки CT26.
ФИГ. 24 иллюстрирует график, на котором показан результат, полученный при измерении размера опухоли у каждого субъекта с целью идентификации способности ингибировать рост опухоли T1.01m и T1.02m в модели опухоли на мышах, получвших совместную инъекцию линии мышиных фибробластов NIH-3T3 и линии клеток рака толстой и прямой кишки CT26 с оверэкспрессией FAP.
ФИГ. 25 иллюстрирует график, на котором показана способность ингибировать рост опухоли при введении T1.01m и T1.02m для каждой концентрации при измерении изменения размера опухоли у каждого субъекта в модели опухоли на мышах после имплантации линию мышиных клеток рака толстой и прямой кишки CT26 с оверэкспрессией FAP.
ФИГ. 26 иллюстрирует график, на котором показано изменение размера опухоли CT26 после конструирования модели с повторным введением опухоли путем трансплантации клеток CT26 и клеток 4T1 мышам, у которых был достигнут полный ответ при лечении T1.01m в модели опухоли на мышах, получавших совместную инъекцию линии мышиных фибробластов NIH-3T3 и линии клеток рака толстой и прямой кишки CT26 с оверэкспрессией FAP.
ФИГ. 27 иллюстрирует график, на котором показано изменение размера опухоли 4T1 после конструирования модели с повторным введением опухоли путем трансплантации клеток CT26 и клеток 4T1 мышам, у которых был достигнут полный ответ при лечении T1.01m в модели опухоли на мышах, получавших совместную инъекцию линии мышиных фибробластов NIH-3T3 и линии клеток рака толстой и прямой кишки CT26 с оверэкспрессией FAP.
ФИГ. 28 иллюстрирует график, на котором показана способность ингибировать рост опухоли при введении T1.01m, T1.02m и T1.03m у каждого субъекта при измерении размера опухоли для каждого субъекта в модели на мышах с имплантацией мышиных клеток CT26 с оверэкспрессией FAP.
ФИГ. 29 иллюстрирует график, на котором показана способность ингибировать рост опухоли у каждого субъекта при введении T1.03m для каждой концентрации при измерении изменения размера опухоли для каждого субъекта в модели на мышах с имплантацией мышиных клеток CT26 с оверэкспрессией FAP.
ФИГ. 30 иллюстрирует график, на котором показана способность ингибировать рост опухоли при введении T1,03m для каждой концентрации при измерении изменения размера опухоли для каждого субъекта в модели на мышах с имплантацией мышиных клеток B16F10 с оверэкспрессией FAP.
ФИГ. 31 представлен график, на котором показана способность ингибировать рост опухоли при введении T1,03m для каждой концентрации при измерении изменения размера опухоли для каждого субъекта в модели на мышах, получавших совместную инъекцию линии мышиных фибробластов NIH-3T3 и линии клеток рака легкого LLC1 с оверхэкспрессией FAP.
ФИГ. 32 представлен график, на котором показан результат, полученный при измерении размера опухоли через 10 дней после введения T1,16m, T1,17m, T1,03m или комбинации T1,16m и T1,17m в модели на мышах, получавших совместную инъекцию линии мышиных фибробластов NIH-3T3 и линии клеток рака легкого LLC1 с оверхэкспрессией FAP.
ФИГ. 33 представлена схематическая диаграмма слитого белка против FAP/IL-12 (первый слева; на фигуре слева показан мономер против FAP, а справа показан мономер, включающий IL-12), слитого белка против FAP/IL-12, содержащего двойной вариабельный домен (второй), двойного антитела против FAP/IL-12, с которым связан FAP-специфичный одноцепочечный вариабельный фрагмент (scFv) (третий и четвертый), и слитого белка против FAP/IL-12, в котором IL-12 связан с С-концом Fc (пятый).
ФИГ. 34 представлена схематическая диаграмма FAP-специфического Fab/FAP-специфического одноцепочечного вариабельного фрагмента (scFv) и слитого белка IL-12 (слева), димера слитого белка, содержащего FAP-специфический Fab и IL-12 (в центре), и Димер слитого белка, содержащий FAP-специфический одноцепочечный вариабельный фрагмент (scFv) и IL-12 (справа).
Способ осуществления изобретения
Слитый белок, включающий IL-12 и антитело против FAP
В одном аспекте настоящего изобретения предложен слитый белок, включающий IL-12 или его вариант и антигенсвязывающий участок, который специфично связывается с FAP (белком активации фибробластов альфа). В частности, слитый белок может включать Fc-область иммуноглобулина. Кроме того, IL-12 или его вариант может быть вариантом, обладающим низкой гепаринсвязывающей способностью.
В одном варианте осуществления предложен слитый белок, включающий первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP.
В другом варианте осуществления предложен димер слитого белка, включающий IL-12 или его вариант и антигенсвязывающий участок, который специфично связывается с FAP.
IL-12 или его вариант
При использовании в настоящем документе термин "IL-12" относится к гетеродимерному цитокину, состоящему из субъединиц p35 и p40, кодируемых двумя отдельными генами, IL-12A и IL-12B, соответственно. IL-12 продуцируется антигенпрезентирующими клетками, такими как макрофаги, и связывается с рецепторами на клеточной поверхности активированных T-клеток и NK-клеток. IL-12 вызывает пролиферацию T-клеток и NK-клеток, и усиливает цитотоксические эффекты T-клеток, NK-клеток и макрофагов. Кроме того, IL-12 вызывает продукцию IFN-γ, ФНО-α и ГМ-КСФ, и активацию Th1-клеток. С другой стороны, IL-12 связывается с рецептором IL-12, гетеродимерным рецептором, сформированным IL-12Rβ1 и IL-12Rβ2.
При использовании в настоящем документе термин "вариант" IL-12 включает аминокислотную последовательность, имеющую функцию, подобную или идентичную функции белка IL-12 дикого типа. В частности, аминокислотная последовательность субъединиц p35 и p40, из которых состоит IL-12, может иметь замену, вставку или делецию по сравнению с диким типом.
IL-12 или его вариант может включать IL-12A (p35) или его вариант и IL-12B (p40) или его вариант.
Кроме того, IL-12 или его вариант может включать структуру, в которой IL-12A или его вариант; и IL-12B или его вариант связаны пептидным линкером.
В одном варианте осуществления IL-12 или его вариант может быть слитым белком, включающим следующую структурную формулу (I) или (II):
N'-Y-[линкер (1)]o-Z-C' (I)
N'-Z-[линкер (1)]o-Y-C' (II)
в структурных формулах (I) и (II):
N' может быть N-концом слитого белка,
C' может быть C-концом слитого белка,
Y может быть IL-12A или его вариантом,
Z может быть IL-12B или его вариантом,
линкер (1) может быть пептидным линкером, и
o может быть 0 или 1.
Один вариант осуществления IL-12 или его варианта может быть структурой, в которой IL-12B или его вариант, пептидный линкер и IL-12A или его вариант связаны последовательно от N-конца. Кроме того, один вариант осуществления IL-12 или его варианта может быть структурой, в которой IL-12A или его вариант, пептидный линкер и IL-12B или его вариант связаны последовательно от N-конца.
При использовании в настоящем документе термин "IL-12A" относится к субъединице IL-12 массой 35 кДа (p35), которая связывается с субъединицей 40 кДа (p40) IL-12 через дисульфидный мостик с образованием активного цитокина.
Аминокислотная последовательность IL-12A может быть последовательностью, описанной в GenBank AAK84425 (для ознакомления с аминокислотной последовательности p35 мыши, см. GenBank AAA39292). Кроме того, ген IL-12A (p35) является последовательностью, кодирующей субъединицу IL-12A, и может быть нуклеотидной последовательностью, соответствующей кодирующей последовательности (CD), из последовательностей, описанных в GenBank AF404773 (в отношении мышиной последовательности см. GenBank M86672).
При использовании в настоящем документе термин "вариант" IL-12A включает аминокислотную последовательность, которая обладает функцией, подобной или идентичной функции белка дикого типа IL-12A. В частности, это означает, что аминокислот последовательность IL-12A содержит замену, вставку или делецию по сравнению с диким типом. В частности, вариант IL-12A может быть фрагментом IL-12A и может иметь аминокислотную последовательность, в которой с 1-ой по 22-ю аминокислоты SEQ ID NO: 122 удалены. Более конкретно, вариант IL-12A может иметь аминокислотную последовательность SEQ ID NO: 75.
Кроме того, IL-12A, применяемый в одном варианте осуществления настоящего изобретения, может быть аминокислотной последовательностью SEQ ID NO: 75, как человеческий IL-12A. В одном варианте осуществления мышиный IL-12A может быть аминокислотной последовательностью SEQ ID NO: 87.
При использовании в настоящем документе термин "IL-12B" относится к субъединице IL-12 массой 40 кДа (p40), которая связывается с субъединицей IL-12 массой 35 кДа (p35) через дисульфидную связь с образованием IL-12, а также связывается с субъединицей p19 IL-23 с образованием IL-23. С другой стороны, IL-12B также называют стимулирующим естественные киллерные клетки фактором 2.
Аминокислотная последовательность "IL-12B" может быть последовательностью, описанной под номером доступа в GenBank AAD56386 (для ознакомления с аминокислотной последовательностью p40 мыши см. последовательность под номером доступа GenBank AAA39296). Кроме того, ген IL-12B (p40) является последовательностью, кодирующей субъединицу IL-12B, и может быть нуклеотидной последовательностью, соответствующей кодирующей последовательности (CD) из последовательностей, описанных под номером доступа в GenBank AF180563 (для ознакомления с мышиной последовательностью см. последовательность под номером доступа GenBank M86671).
Кроме того, IL-12B, применяемый в одном варианте осуществления настоящего изобретения, может быть человеческим IL-12B, и, в частности, IL-12B может быть аминокислотной последовательностью SEQ ID NO: 74. В одном варианте осуществления мышиный IL-12B может иметь аминокислотную последовательностью SEQ ID NO: 86.
При использовании в настоящем документе термин "вариант" IL-12B включает аминокислотную последовательностью, имеющую функцию, подобную или идентичную функции белка IL-12B дикого типа. В частности, это означает, что аминокислотная последовательность IL-12B содержит замену, вставку или делецию по сравнению с диким типом.
В частности, вариант IL-12B может быть таким, в котором удалены с 1-й по 22-ю аминокислоту SEQ ID NO: 121. Более конкретно, вариант IL-12B может быть таким, в котором 1-8 аминокислот заменены в последовательности SEQ ID NO: 74. Кроме того, вариант IL-12B может быть таким, в котором удалены с 1-й по 22-ю аминокислоту SEQ ID NO: 123. Более конкретно, вариант IL-12B может быть таким, в котором заменены до 1-8 аминокислот в последовательности SEQ ID NO: 86.
Вариант IL-12B (p40) может быть таким, в котором заменена аминокислота, участвующая в связывании гепарина IL-12.
В одном варианте осуществления вариант IL-12B (p40) может быть формой, в которой лизин (K), связывающийся с гепарином в IL-12B, заменен другой аминокислотой. В частности, это может быть форма, в которой 258-й, 260-й, 263-й и 264-й лизины в SEQ ID NO: 74 заменены другими аминокислотами. В частности, вариант IL-12B (p40) может включать аминокислотную последовательность, полученную в результате по меньшей мере одной замены, выбранной из группы, состоящей из K258A, K260A, K263A и K264A, в аминокислотной последовательности SEQ ID NO: 74. В частности, вариант IL-12B (p40) может включать аминокислотную последовательность, полученную при замене K258A и K263A в аминокислотной последовательности SEQ ID NO: 74, или может дополнительно включать мутацию K260A и/или K264A в аминокислотной последовательности SEQ ID NO: 74.
В одном варианте осуществления вариант IL-12B (p40) может быть формой, в которой аргинин (R) или лизин (K), связывающийся с гепарином в IL-12B, заменен другой аминокислотой. В частности, это может быть форма, в которой 254-й аргинин и/или 255-й, 256-й и 260-й лизины в SEQ ID NO: 86 заменены другими аминокислотами. В частности, вариант IL-12B (p40) может включать аминокислотную последовательность, полученную в результате по меньшей мере одной замены, выбранной из группы, состоящей из R254A, K255A, K256A и K260A, в аминокислотной последовательности SEQ ID NO: 86. В частности, вариант IL-12B (p40) может включать аминокислотную последовательность, полученную в результате замены R254A и K260A в аминокислотной последовательности SEQ ID NO: 86, или может дополнительно включать мутацию K255A и/или K256A в последовательности SEQ ID NO: 86.
В одном варианте осуществления вариант IL-12B (p40) может включать аминокислотную последовательность SEQ ID NO: 77, SEQ ID NO: 79, SEQ ID NO: 89 или SEQ ID NO: 91.
В одном варианте осуществления вариант человеческого IL-12B может состоять из следующей структурной формулы A:
[Структурная формула A]
X1-L-X2
где, X1 представляет собой аминокислотную последовательность SEQ ID NO: 125,
X2 представляет собой аминокислотную последовательность SEQ ID NO: 126, и
L представляет собой аминокислотную последовательность, состоящую из V-A1-A2-Q-A3-K*-A4-A5-A6-A7-K*-A8.
A1 представляет собой R или Q, A2 представляет собой V, A или I, A3 представляет собой G или R*, A4 представляет собой S, N или K*, A5 представляет собой K*, N или E, A6 представляет собой R или K, A7 представляет собой E, M или T, и A8 представляет собой K* или E.
По меньшей мере один аминокислотный остаток, отмеченный символом "*", может быть заменен неполярным аминокислотным остатком, выбранным из группы, состоящей из A, G, I, L, M, F, P и V, но не ограничивается этим.
В одном варианте осуществления вариант IL-12B (p40) может включать замену аминокислот, участвующих в связывании гепарина, для уменьшения цитокин-ассоциированного токсического действия IL-12 при сохранении цитотоксического действия в отношении раковых клеток.
FAP и антигенсвязывающий участок, который специфично связывается с FAP
При использовании в настоящем документе термин "FAP (белок активации фибробластов)" относится к белку активации фибробластов, который представляет собой белок, экспрессируемый на поверхности клеток и представленный в окружении опухолевых клеток различных типов опухолей или в опухолевых клетках различных типов опухолей. Известно, что FAP избирательно повышенно экспрессируется на поверхности опухолеассоциированных фибробластов (CAF) в микроокружении опухоли.
Кроме того, FAP представляет собой гомодимер, содержащий две N-гликозилированных субъединицы, имеющих C-концевой внеклеточный домен, в котором расположен ферментный каталитический домен, при этом гликозилированная форма FAP одновременно обладает и пост-пролилдипептидилпептидазной, и желатиназной активностью.
С другой стороны, FAP является пролилэндопептидазой, которая представляет собой мембраносвязанную желатиназу массой приблизительно 170 кДа. Пролилэндопептидаза FAP может распознавать и расщеплять специфическую аминокислотную последовательность. Таким образом, FAP также называют FAPα, сепаразой или циркулирующим антиплазмин-расщепляющим ферментом.
Аминокислотная последовательность FAP может быть последовательностью, описанной под номером в GenBank AAC51668, при этом человеческий FAP первоначально был обнаружен в культивируемых фибробластах с помощью моноклонального антитела (mAb) F19 (см. публикацию Международной заявки на патент WO 93/05804). FAP экспрессируется во многих злокачественных опухолях и применяется в качестве многообещающей антигенной мишени для визуализации, диагностики и лечения различных карцином из-за своей ограниченной экспрессии в нормальных тканях.
FAP включает любые варианты, изоформы и видоспецифические гомологи FAP человека, которые экспрессируются клеткой в естественных условиях, либо экспрессируются в клетке, трансфицированной геном FAP. Антитело согласно настоящему изобретению может связываться с FAP, присутствующим на мембране или клеточной поверхности раковых клеток (опухолевых клеток или клеток стромы опухоли), и может вызывать ADCC или другой эффектор-опосредованный лизис раковых клеток. Кроме того, оно может применяться для блокирования ферментативной активности FAP (например, серинпептидазной, желатиназной, коллагеназной активности), FAP-опосредованного расщепления ECM и FAP-опосредованной инвазии или миграции клеток.
При использовании в настоящем документе термин "специфичное связывание" относится к связыванию, которое в измеримой степени отличается от неспецифичного взаимодействия. Специфичное связывание может быть определено при конкуренции с контрольной молекулой, подобной мишени, которая не обладает связывающей активностью.
При использовании в настоящем документе термин "антигенсвязывающий участок (эпитоп)" относится к детерминанте, которая взаимодействует со специфическим антигенсвязывающим участком в вариабельной области антитела. Антигенсвязывающий участок представляет собой группу молекул, таких как аминокислоты или углеводные боковые цепи, которые обычно обладают специфическими структурными характеристиками, а также специфическими зарядовыми характеристиками. Антигенсвязывающий участок, который специфично связывается с FAP, может быть общим термином для молекул, способных к специфичному связыванию с FAP по типу связывания антигена-антитела.
Кроме того, антитело или его фрагмент может применяться в любой форме, если оно содержит антигенсвязывающий домен, способный специфично связываться с FAP.
Антигенсвязывающий участок может включать другие аминокислоты, не участвующие непосредственно в связывании, или аминокислоты, эффекты которых блокируются аминокислотными остатками в антигенсвязывающем участке.
В частности, антигенсвязывающий участок может быть антителом, которое специфично связывается с FAP или его фрагментом.
При использовании в настоящем документе термин "антитело" относится к молекуле, содержащей антигенсвязывающий участок, а также к иммунологически активному фрагменту молекулы иммуноглобулина, содержащему антигенсвязывающий участок. Молекула иммуноглобулина может быть молекулой иммуноглобулина IgG, IgE, IgM, IgD, IgA, IgY или их сукласса. Антитела включают синтетические антитела, моноклональные антитела, однодоменные антитела, одноцепочечные антитела, рекомбинантные антитела, мультиспецифичные антитела (в том числе биспецифичные антитела), человеческие антитела, гуманизированные антитела, химерные антитела, интратела, scFv (включая, например, моноспецифичные и биспецифичные и т.д.), Fab-фрагмент, F(ab')-фрагмент, дисульфид-связанный Fv (sdFv), антиидиотипические (анти-Id) антитела и антигенсвязывающий фрагмент антител, но не ограничиваются этим.
При использовании в настоящем документе термин "фрагмент антитела" может быть частью антитела, такой как F(ab')2, F(ab)2, Fab', Fab, Fv, scFv. Независимо от структуры фрагмент антитела связывается с таким же антигеном, который распознается интактным антителом.
В одном варианте осуществления антигенсвязывающий участок, который специфично связывается с FAP, может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 96, HCDR2 с SEQ ID NO: 97 и HCDR3 с SEQ ID NO: 98; и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 99, LCDR2 с SEQ ID NO: 100 и LCDR3 с SEQ ID NO: 101. Кроме того, в одном варианте осуществления антигенсвязывающий участок, который специфично связывается с FAP, может иметь вариабельную область тяжелой цепи с SEQ ID NO: 102 и вариабельную область легкой цепи с SEQ ID NO: 103.
Кроме того, в одном варианте осуществления антигенсвязывающий участок, который специфично связывается с FAP, может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 104, HCDR2 с SEQ ID NO: 105 и HCDR3 с SEQ ID NO: 106; и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 107, LCDR2 с SEQ ID NO: 108 и LCDR3 с SEQ ID NO: 109. Кроме того, в одном варианте осуществления антигенсвязывающий участок, который специфично связывается с FAP, может иметь вариабельную область тяжелой цепи с SEQ ID NO: 110 и вариабельную область легкой цепи с SEQ ID NO: 111.
В одном варианте осуществления антигенсвязывающим участком, который специфично связывается с FAP, может быть scFv. Затем scFv может включать вышеописанные CDR-области тяжелой цепи и легкой цепи. В одном варианте осуществления scFv, который специфично связывается с FAP, может иметь аминокислотную последовательность SEQ ID NO: 72 или SEQ ID NO: 84.
Кроме того, антигенсвязывающий участок, который специфично связывается с FAP, может включать известное антитело против FAP или его фрагмент. Антитело против FAP или его фрагмент может относиться к антителу, известному специалистам в данной области, без ограничения.
Антитело против FAP или его фрагмент может включать по меньшей мере одну вариабельную область, выбранную из группы, состоящей из NG-641, AMG-506/MP-0310, 28H1 RG-7827, 4B9 RG-7827, OMTX-705, 3F2, 4G8, 3D9, 4B3, 19G1, 20G8, 5B8, 5F1, 14B3, 16F1, 16F8, O3C9, 29B11, O2D7 и 23C10.
В другом примере в качестве антитела может использоваться антитело против FAP или его фрагмент, раскрытые в публикации заявки на патент Республики Корея KR 20200037826 A, публикации заявки на патент США US 2020-0385488 A1, патенте США US 3,924,445 B2, патенте США US 9,011,847 B2 или публикации заявки на патент США US 2017-007716 A1.
В одном варианте осуществления антитело против FAP может включать вариабельную область NG-641. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 127, HCDR2 с SEQ ID NO: 128 и HCDR3 с SEQ ID NO: 129, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 130, LCDR2 с SEQ ID NO: 131 и LCDR3 с SEQ ID NO: 132. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 248 и вариабельную область легкой цепи с SEQ ID NO: 249.
В одном варианте осуществления антитело против FAP может включать вариабельную область 28H1. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 133, HCDR2 с SEQ ID NO: 134 и HCDR3 с SEQ ID NO: 135, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 136, LCDR2 с SEQ ID NO: 137 и LCDR3 с SEQ ID NO: 138. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 250 и вариабельную область легкой цепи с SEQ ID NO: 251.
В одном варианте осуществления антитело против FAP может включать вариабельную область 4B9. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 139, HCDR2 с SEQ ID NO: 140 и HCDR3 с SEQ ID NO: 141, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 142, LCDR2 с SEQ ID NO: 143 и LCDR3 с SEQ ID NO: 144. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 252 и вариабельную область легкой цепи с SEQ ID NO: 253.
В одном варианте осуществления антитело против FAP может включать вариабельную область OMTX-705. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 145, HCDR2 с SEQ ID NO: 146 и HCDR3 с SEQ ID NO: 147, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 148, LCDR2 с SEQ ID NO: 149 и LCDR3 с SEQ ID NO: 150. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 254 и вариабельную область легкой цепи с SEQ ID NO: 255.
В одном варианте осуществления антитело против FAP может включать вариабельную область 3F2. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 151, HCDR2 с SEQ ID NO: 152 и HCDR3 с SEQ ID NO: 153, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 154, LCDR2 с SEQ ID NO: 155 и LCDR3 с SEQ ID NO: 156. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 256 и вариабельную область легкой цепи с SEQ ID NO: 257.
В одном варианте осуществления антитело против FAP может включать вариабельную область 4G8. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 157, HCDR2 с SEQ ID NO: 158 и HCDR3 с SEQ ID NO: 159, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 160, LCDR2 с SEQ ID NO: 161 и LCDR3 с SEQ ID NO: 162. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 258 и вариабельную область легкой цепи с SEQ ID NO: 259.
В одном варианте осуществления антитело против FAP может включать вариабельную область 3D9. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 163, HCDR2 с SEQ ID NO: 164 и HCDR3 с SEQ ID NO: 165, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 166, LCDR2 с SEQ ID NO: 167 и LCDR3 с SEQ ID NO: 168. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 260 и вариабельную область легкой цепи с SEQ ID NO: 261.
В одном варианте осуществления антитело против FAP может включать вариабельную область 4B3. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 169, HCDR2 с SEQ ID NO: 170 и HCDR3 с SEQ ID NO: 171, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 172, LCDR2 с SEQ ID NO: 173 и LCDR3 с SEQ ID NO: 174. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 262 и вариабельную область легкой цепи с SEQ ID NO: 263.
В одном варианте осуществления антитело против FAP может включать вариабельную область 19G1. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 175, HCDR2 с SEQ ID NO: 176 и HCDR3 с SEQ ID NO: 177, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 178, LCDR2 с SEQ ID NO: 179 и LCDR3 с SEQ ID NO: 180. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 264 и вариабельную область легкой цепи с SEQ ID NO: 265.
В одном варианте осуществления антитело против FAP может включать вариабельную область 20G8. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 181, HCDR2 с SEQ ID NO: 182 и HCDR3 с SEQ ID NO: 183, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 184, LCDR2 с SEQ ID NO: 185 и LCDR3 с SEQ ID NO: 186. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 266 и вариабельную область легкой цепи с SEQ ID NO: 267.
В одном варианте осуществления антитело против FAP может включать вариабельную область 5B8. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 187, HCDR2 с SEQ ID NO: 188 и HCDR3 с SEQ ID NO: 189, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 190, LCDR2 с SEQ ID NO: 191 и LCDR3 с SEQ ID NO: 192. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 268 и вариабельную область легкой цепи с SEQ ID NO: 269.
В одном варианте осуществления антитело против FAP может включать вариабельную область 5F1. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 193, HCDR2 с SEQ ID NO: 194 и HCDR3 с SEQ ID NO: 195, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 196, LCDR2 с SEQ ID NO: 197 и LCDR3 с SEQ ID NO: 198. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 270 и вариабельную область легкой цепи с SEQ ID NO: 271.
В одном варианте осуществления антитело против FAP может включать вариабельную область 14B3. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 199, HCDR2 с SEQ ID NO: 200 и HCDR3 с SEQ ID NO: 201, и вариабельную область легкой цепи, включаю включающую щая LCDR1 с SEQ ID NO: 202, LCDR2 с SEQ ID NO: 203 и LCDR3 с SEQ ID NO: 204. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 272 и вариабельную область легкой цепи с SEQ ID NO: 273.
В одном варианте осуществления антитело против FAP может включать вариабельную область 16F1. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 205, HCDR2 с SEQ ID NO: 206 и HCDR3 с SEQ ID NO: 207, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 208, LCDR2 с SEQ ID NO: 209 и LCDR3 с SEQ ID NO: 210. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 274 и вариабельную область легкой цепи с SEQ ID NO: 275.
В одном варианте осуществления антитело против FAP может включать вариабельную область 16F8. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 211, HCDR2 с SEQ ID NO: 212 и HCDR3 с SEQ ID NO: 213, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 214, LCDR2 с SEQ ID NO: 215 и LCDR3 с SEQ ID NO: 216. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 276 и вариабельную область легкой цепи с SEQ ID NO: 277.
В одном варианте осуществления антитело против FAP может включать вариабельную область O3C9. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 217, HCDR2 с SEQ ID NO: 218 и HCDR3 с SEQ ID NO: 219, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 220, LCDR2 с SEQ ID NO: 221 и LCDR3 с SEQ ID NO: 222. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 278 и вариабельную область легкой цепи с SEQ ID NO: 279.
В одном варианте осуществления антитело против FAP может включать вариабельную область 22A3. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 223, HCDR2 с SEQ ID NO: 224 и HCDR3 с SEQ ID NO: 225, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 226, LCDR2 с SEQ ID NO: 227 и LCDR3 с SEQ ID NO: 228. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 280 и вариабельную область легкой цепи с SEQ ID NO: 281.
В одном варианте осуществления антитело против FAP может включать вариабельную область 29B11. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 229, HCDR2 с SEQ ID NO: 230 и HCDR3 с SEQ ID NO: 231, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 232, LCDR2 с SEQ ID NO: 233 и LCDR3 с SEQ ID NO: 234. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 282 и вариабельную область легкой цепи с SEQ ID NO: 283.
В одном варианте осуществления антитело против FAP может включать вариабельную область O2D7. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 235, HCDR2 с SEQ ID NO: 236 и HCDR3 с SEQ ID NO: 237, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 238, LCDR2 с SEQ ID NO: 239 и LCDR3 с SEQ ID NO: 240. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 284 и вариабельную область легкой цепи с SEQ ID NO: 285.
В одном варианте осуществления антитело против FAP может включать вариабельную область 23C10. В частности, антитело может включать вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 241, HCDR2 с SEQ ID NO: 242 и HCDR3 с SEQ ID NO: 243, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 244, LCDR2 с SEQ ID NO: 245 и LCDR3 с SEQ ID NO: 246. Кроме того, антитело против FAP может включать вариабельную область тяжелой цепи с SEQ ID NO: 286 и вариабельную область легкой цепи с SEQ ID NO: 287.
В одном варианте осуществления антителом против FAP может быть AMG-506/MP-0310. В частности, антитело может включать аминокислотную последовательность SEQ ID NO: 247.
Антитело против FAP специфично связывается с FAP, присутствующим на раковых клетках, при этом может применяться любое антитело при условии, что оно может вызывать гибель раковых клеток.
Структура первого мономера
Первый мономер включает IL-12 или его вариант.
Первый мономер может дополнительно включать антигенсвязывающий участок, который специфично связывается с FAP.
В одном варианте осуществления первый мономер может включать IL-12 или его вариант; и фрагмент Fc-области или его вариант.
В одном варианте осуществления первый мономер может включать IL-12 или его вариант, фрагмент Fc-области или его вариант и антигенсвязывающий участок, который специфично связывается с FAP.
Первый мономер может включать следующую структурную формулу (III) или (IV):
N'-X-[линкер (2)]p-фрагмент Fc-области или его вариант-[линкер (3)]q-(T)r-C' (III)
N'-(T)r-[линкер (2)]q-фрагмент Fc-области или его вариант-[линкер (3)]p-X-C' (IV)
в структурных формулах (III) и (IV),
N' может быть N-концом слитого белка,
C' может быть C-концом слитого белка,
X может быть структурной формулой (I) или (II),
T может быть антигенсвязывающим участком, который специфично связывается с FAP,
линкеры (2) и (3) могут быть пептидными линкерами, и
каждое p, q и r может быть независимо 0 или 1.
В одном варианте осуществления, когда r равно 0, первый мономер может находиться в форме слитого белка, в котором IL-12 или его вариант и фрагмент Fc-области или его вариант соединены пептидным линкером.
Кроме того, первый мономер может включать аминокислотную последовательность SEQ ID NO: 3, SEQ ID NO: 4, SEQ ID NO: 5, SEQ ID NO: 15, SEQ ID NO: 20, SEQ ID NO: 21, SEQ ID NO: 22 или SEQ ID NO: 32.
Кроме того, в структурной формуле (III), когда r равно 1, первый мономер может находиться в форме, в которой мономер антитела против FAP связан с IL-12 или его вариантом.
Кроме того, в структурной формуле (III), когда r равно 1, первый мономер может включать аминокислотную последовательность SEQ ID NO: 292, SEQ ID NO: 293, SEQ ID NO: 296, SEQ ID NO: 297, SEQ ID NO: 298, SEQ ID NO: 299, SEQ ID NO: 302 или SEQ ID NO: 303.
Кроме того, в структурной формуле (IV), когда r равно 1, первый мономер может включать аминокислотную последовательность SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 300 или SEQ ID NO: 301.
В одном варианте осуществления, когда r равно 1, структурная формула (III) может включать следующие структурные формулы (III') и (III"):
N'-X-[линкер (2)]p-фрагмент Fc-области или его вариант-[линкер (3)]q-(T')-C' (III')
N'-(T'')-C' (III'')
в структурных формулах (III') и (III''),
T' представляет собой область тяжелой цепи антитела, которое специфично связывается с FAP, включающую вариабельную область и CH1-область, или область легкой цепи антитела;
T'' представляет собой область легкой цепи антитела, которое специфично связывается с FAP, или областью тяжелой цепи антитела, включающую вариабельную область и CH1-область;
где T' и T'' связываются друг с другом с образованием вариабельной области антитела, где вариабельная область специфично связывается с FAP;
линкеры (2)-(3) представляют собой пептидные линкеры,
каждое p и q независимо равно 0 или 1, и
N', X и C' имеют значение, которое определено выше.
В одном варианте осуществления, когда r равно 1, структурная формула (IV) может включать следующие структурные формулы (IV') и (IV''):
N'-(T')-[линкер (2)]q-фрагмент Fc-области или его вариант-[линкер (3)]p-X-C' (IV'); и
N'-(T'')-C' (IV'')
в структурных формулах (IV') и (IV''),
T' представляет собой область тяжелой цепи антитела, которое специфично связывается с FAP, включающую вариабельную область и CH1-область, или область легкой цепи антитела;
T'' представляет собой область легкой цепи антитела, которое специфично связывается с FAP, или область тяжелой цепи антитела, включающую вариабельную область и CH1-область;
где T' и T'' связываются друг с другом с образованием вариабельной области антитела, где вариабельная область специфично связывается с FAP;
линкеры (2)-(3) являются пептидным линкером,
каждое p и q независимо равно 0 или 1, и
N', X и C' имеют значение, которое определено выше.
Кроме того, первый мономер может включать аминокислотную последовательность SEQ ID NO: 10 и SEQ ID NO: 2; SEQ ID NO: 11 и SEQ ID NO: 2; SEQ ID NO: 27 и SEQ ID NO: 19; SEQ ID NO: 28 и SEQ ID NO: 19; SEQ ID NO: 294 и SEQ ID NO: 2; SEQ ID NO: 295 и SEQ ID NO: 2; SEQ ID NO: 300 и SEQ ID NO: 19; или SEQ ID NO: 301 и SEQ ID NO: 19.
Структура второго мономера
Второй мономер может дополнительно включать антигенсвязывающий участок, который специфично связывается с FAP.
В одном варианте осуществления второй мономер может включать первый FAP-связывающий участок; и второй FAP-связывающий участок.
Антигенсвязывающим участком, который специфично связывается с FAP, может быть Fab, scFv, Fv или их фрагмент. Кроме того, первым FAP-связывающим участком может быть Fab, а вторым FAP-связывающим участком может быть Fv или scFv.
Второй FAP-связывающий участок может быть связан с N-концом или C-концом второго мономера. В частности, второй FAP-связывающий участок может быть дополнительно связан с C-концом тяжелой цепи, C-концом легкой цепи или N-концом вариабельной области.
Второй мономер может включать следующую структурную формулу (V):
N'-(R)s-[линкер (4)]t-Q-[линкер (5)]u-фрагмент Fc-области или его вариант-[линкер (6)]v-(W)a-C' (V)
в структурной формуле (V),
N' может быть N-концом слитого белка,
C' может быть C-концом слитого белка,
R и Q может быть антигенсвязывающим участком, который специфично связывается с FAP,
W может быть scFv, который специфично связывается с FAP; или IL-12 структурной формулы (I) или (II) или его вариантом,
каждый из линкеров (4), (5) и (6) может быть пептидным линкером, и
каждое s, t, u, v и a может быть независимо 0 или 1.
В одном варианте осуществления структурная формула (V) может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 1, SEQ ID NO: 2, SEQ ID NO: 6, SEQ ID NO: 7, SEQ ID NO: 8, SEQ ID NO: 9, SEQ ID NO: 14, SEQ ID NO: 18, SEQ ID NO: 19, SEQ ID NO: 23, SEQ ID NO: 24, SEQ ID NO: 25, SEQ ID NO: 26, SEQ ID NO: 31, SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 300 и SEQ ID NO: 301.
В одном варианте осуществления структурная формула (V) может включать следующие структурные формулы (V') и (V''):
N'-(R')s-[линкер (4)]t-Q'-[линкер (5)]u-фрагмент Fc-области или его вариант-[линкер (6)]p-(W)a-C' (V')
N'-(R'')s-[линкер (4)]t-Q''-[линкер (7)]x-(W)b-C' (V'')
в структурных формулах (V') и (V''),
R' может быть областью тяжелой цепи антитела, которое специфично связывается с FAP, включающей вариабельную область и CH1-область, или областью легкой цепи антитела;
R'' может быть областью легкой цепи антитела, которое специфично связывается с FAP, или областью тяжелой цепи антитела, включающей вариабельную область и CH1-область;
где R' и R'' могут связываться друг с другом с образованием вариабельной области антитела, где вариабельная область специфично связывается с FAP;
Q' может быть областью тяжелой цепи антитела, которое специфично связывается с FAP, включающей вариабельную область и CH1-область, или областью легкой цепи антитела;
Q'' может быть областью легкой цепи антитела, которое специфично связывается с FAP, или областью тяжелой цепи антитела, включающей вариабельную область и CH1-область;
где Q' и Q'' могут связываться друг с другом с образованием вариабельной области антитела, где вариабельная область специфично связывается с FAP,
W может быть scFv, который специфично связывается с FAP; или IL-12 структурной формулы (I) или (II) или его вариантом,
каждый из линкеров (4), (5), (6) и (7) может быть пептидным линкером, и
каждое s, t, u, x, a и b может быть независимо 0 или 1.
В одном варианте осуществления структурная формула (V') может быть SEQ ID NO: 1, SEQ ID NO: 6, SEQ ID NO: 8, SEQ ID NO: 14, SEQ ID NO: 18, SEQ ID NO: 23, SEQ ID NO: 25, SEQ ID NO: 31, SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 300 или SEQ ID NO: 301.
В одном варианте осуществления структурная формула (V'') может быть SEQ ID NO: 2, SEQ ID NO: 7, SEQ ID NO: 9, SEQ ID NO: 19, SEQ ID NO: 24 или SEQ ID NO: 26.
В одном варианте осуществления второй мономер может включать тяжелую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 102, и легкую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 103; или тяжелую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 110, и легкую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 111.
Кроме того, когда W представляет собой scFv, W может иметь аминокислотную последовательность SEQ ID NO: 72 или SEQ ID NO: 84.
Пептидный линкер
При использовании в настоящем документе термин "пептидный линкер" относится к пептиду, используемому для обеспечения физико-химического расстояния или соединения между доменами в слитом белке. Линкер может включать шарнирную область иммуноглобулина.
Пептидные линкеры (1)-(7) относятся к пептидным линкерам, состоящим из аминокислот. В частности, пептидный линкер (2) или (5) может состоять из 5-80 последовательных аминокислот, 7-70 последовательных аминокислот или 10-60 последовательных аминокислот, или 12-50 аминокислот. Пептидный линкер может включать (G4S)n (где n является целым числом от 1 до 10). Таким образом, в (G4S)n n может быть равно 1, 2, 3, 4, 5, 6, 7, 8, 9 или 10.
В одном варианте осуществления пептидный линкер (1) может быть пептидным линкером, состоящим из аминокислотной последовательности SEQ ID NO: 93, SEQ ID NO: 94 или SEQ ID NO: 95.
Пептидный линкер (2) или (5) может состоять из 5-80 последовательных аминокислот, 7-70 последовательных аминокислот или 10-60 последовательных аминокислот, или 12-50 аминокислот. В одном варианте осуществления пептидный линкер (2) может состоять из 30 аминокислот. Кроме того, пептидный линкер (2) может включать по меньшей мере один цистеин. В частности, он может включать один, два или три цистеина. Кроме того, пептидный линкер (2) может быть получен из шарнира иммуноглобулина и может дополнительно включать (G4S)n (где n является целым числом от 1 до 10). В частности, пептидный линкер (2) может включать шарнирную область, состоящую из аминокислотной последовательности любой из SEQ ID NO: 112, SEQ ID NO: 113, SEQ ID NO: 114, SEQ ID NO: 115, SEQ ID NO : 116, SEQ ID NO: 117, SEQ ID NO: 118, SEQ ID NO: 119 и SEQ ID NO: 120.
Кроме того, пептидные линкеры (3), (4), (6) и (7) могут состоять из 1-30 последовательных аминокислот, 5-20 последовательных аминокислот или 10-15 последовательных аминокислот. Пептидный линкер может включать (G4S)n (где n является целым числом от 1 до 10). Таким образом, в (G4S)n n может быть равно 1, 2, 3, 4, 5, 6, 7, 8, 9 или 10.
Кроме того, в частности, пептидный линкер (2), (3) или (5) может включать SEQ ID NO: 93 или SEQ ID NO: 94.
В одном варианте осуществления настоящего изобретения пептидный линкер (2) или (5) может быть пептидным линкером, включающим аминокислотную последовательность SEQ ID NO: 118 или 120.
Fc-область или ее фрагмент
Таким образом, вышеописанный фрагмент иммуноглобулина может быть Fc-областью иммуноглобулина. Fc-область иммуноглобулина может быть как Fc-доменом дикого типа, так и вариантом Fc-домена. Кроме того, Fc-область может быть Fc-областью IgG, IgA, IgE, IgD или IgM. В частности, она может быть получена из IgG1 или IgG2a.
При использовании в настоящем документе термин "вариант Fc-домена" может относиться к форме, которая отличается от Fc-домена дикого типа профилем гликозилирования, имеет высокое гликозилирование по сравнению с Fc-доменом дикого типа, имеет низкое гликозилирование по сравнению с Fc-доменом дикого типа или имеет дегликозилированную форму. Кроме того, это включает агликозилированный Fc-домен. Fc-домен или его вариант могут иметь измененное количество сиаловых кислот, сайтов фукозилирования или гликозилирования в результате подбора условий культивирования или генетической манипуляции хозяина.
Кроме того, гликозилирование Fc-домена иммуноглобулина может быть модифицировано стандартным методами, такими как химические методы, ферментативные методы и методы генной инженерии с использованием микроорганизмов. Кроме того, вариант Fc-домена может находиться в смешанной форме соответствующих Fc-областей иммуноглобулина IgG, IgA, IgE, IgD или IgM. Кроме того, вариант Fc-домена может находиться в форме, в которой некоторые аминокислоты Fc-домена заменены другими аминокислотами.
"Аминокислота", введенная в результате замены и/или добавления, может быть любой аминокислотой, выбранной из группы, состоящей из лизина (K), аланина (A), аргинина (R), аспарагина (N), аспарагиновой кислоты (D), цистеина (C), глутамина (Q), глутаминовой кислоты (E), глицина (G), гистидина (H), изолейцина (I), лейцина (L), метионина (M), фенилаланина (F), пролина (P), серина (S), треонина (T), триптофана (W), тирозина (Y) и валина (V).
Кроме того, Fc-область может включать структуру выступа или структуру впадины.
При использовании в настоящем документе термин "выступ во впадину" является стратегией инженерии при производстве антитела, котрое специфично связывается с разными областями, такого как биспецифичное антитело, мультиспецифичное антитело или гетеродимерное антитело. В целом данный метод включает введение выступа на поверхности контакта первого полипептида (например, первого CH3 домена первой тяжелой цепи антитела) и соответствующей впадины на поверхности контакта второго полипептида (например, второго CH3 домена второй тяжелой цепи антитела), в результате чего выступ может быть помещен во впадину, что способствует образованию гетеродимера и препятствует образованию гомодимера.
'Выступ' конструируют путем замены малых боковых цепей аминокислот на поверхности контакта первого полипептида (например, первого CH3 домена тяжелой цепи первого антитела) более крупными боковыми цепями (например, аргинина, фенилаланина, тирозина или триптофана). Комплементарную 'впадину' такого же или подобного размера, как размер выступа, получают путем замены крупных боковых цепей аминокислот на поверхности контакта второго полипептида (например, второго CH3 домена тяжелой цепи второго антитела) боковыми цепями меньшего размера (например, аланина, серина, валина или треонина). Выступ и впадина могут быть получены путем изменения нуклеиновой кислоты, кодирующей полипептид, например, с помощью сайт-специфического мутагенеза или пептидного синтеза.
В одном варианте осуществления структура выступа в IgG1 может быть SEQ ID NO: 13 или 288, и структура впадины может быть SEQ ID NO: 12 или 289. Структура выступа или структура впадины могут быть формой, в которой 146-я, 148-я и 187-я аминокислота в аминокислотной последовательности SEQ ID NO: 304 заменена другими аминокислотами. В частности, в одном варианте осуществления настоящего изобретения структура выступа или структура впадины может быть формой, в которой аминокислотная последовательность SEQ ID NO: 304 содержит замены T146W, T146S, L148A и Y187A. В частности, структура выступа может содержать замену T146W, и структура впадины может содержать замены T146S, L148A и Y148V.
С другой стороны, в одном варианте осуществления настоящего изобретения структура выступа в IgG2a может быть SEQ ID NO: 30 или 290, и структура впадины может быть SEQ ID NO: 29 или 291. Структура выступа или структура впадины может быть формой, в которой 152-я, 154-я и 193-я аминокислоты в аминокислотной последовательности SEQ ID NO: 305 заменены другими аминокислотами. В частности, в одном варианте осуществления настоящего изобретения структура выступа или структура впадины может быть формой, в которой аминокислотная последовательность SEQ ID NO: 305 содержит замены T152W или T152S, M154A и Y193V. В частности, структура выступа может быть формой, в которой она содержит замену T152W, и структура впадины может быть формой, в которой она содержит замены T152S, M154A и Y193V.
В одном варианте осуществления вариант Fc-домена может включать мутацию DANG или мутацию NG. Таким образом, "мутация DANG" относится к мутации D265A/N297G для устранения эффекторной функции в IgG1 человека или IgG2a мыши.
Эффекторные функции, опосредуемые Fc-областью в молекуле IgG, включают связывание C1q, комплементзависимую цитотоксичность, связывание с Fc-рецептором, антителозависимую клеточно-опосредованную цитотоксичность (ADCC), фагоцитоз, даунрегуляцию рецепторов клеточной поверхности (например, B-клеточного рецептора, BCR) и т.п. Как правило, эти эффекторные функции требуют связывания Fc-области со связывающим доменом (например, вариабельным доменом антитела).
Эффекторная функция может быть изменена путем замены аминокислотной последовательности немутантной Fc-области, при этом Fc-область, в которой изменена эффекторная функция, может быть сконструирована, например, путем модификации связывания с C1q и/или связывания с FcR, что приводит к изменению CDC активности и/или ADCC активности. То есть 'мутация DANG' означает, что эффекторную функцию, опосредуемую Fc-областью, удаляют из молекулы IgG, благодаря чему нежелательная эффекторная функция не появляется во время продукции антитела.
В одном варианте осуществления мутация DANG может быть формой, в которой аминокислота в IgG1 человека с SEQ ID NO: 289 содержит замену D45A/N77G. Кроме того, она может быть формой, в которой аминокислота в IgG2a мыши с SEQ ID NO: 291 содержит замену D51A/N83G.
Структура слитого белка
Слитый белок может быть антителом. В частности, антитело может быть гетеродимерным антителом, включающим структуру выступа во впадину.
Слитый белок может включать структурную формулу (III) и структурную формулу (V); или структурную формулу (IV) и структурную формулу (V).
В частности, один вариант осуществления слитого белка может включать первый мономер согласно (i) или (ii) ниже; и второй мономер согласно (iii), (iv), (v) или (vi) ниже:
Примеры первого мономера:
(i) когда r равно 0, структурная формула (III)
(ii) когда r равно 1, структурная формула (IV)
Примеры второго мономера:
(iii) когда s, a и b равны 0, структурная формула (V') и структурная формула (V'')
(iv) когда s равно 1, и a и b равны 0, структурная формула (V') и структурная формула (V'')
(v) когда s и b равны 0, и a равно 1, структурная формула (V') и структурная формула (V'')
(vi) когда b равно 1, и s и a равны 0, структурная формула (V') и структурная формула (V'').
В одном варианте осуществления слитый белок может включать первый мономер, включающий (i) выше; и второй мономер, включающий (iii) выше (первый слева на ФИГ. 33). Кроме того, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 1, SEQ ID NO: 2, SEQ ID NO: 3, SEQ ID NO: 4, SEQ ID NO: 5, SEQ ID NO: 18, SEQ ID NO: 19, SEQ ID NO: 20, SEQ ID NO: 21 и SEQ ID NO: 22. В частности, слитый белок может включать SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 3; SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 4; SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 5; SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 20; SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 21; или SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 22.
В одном варианте осуществления слитый белок может включать первый мономер, включающий (i) выше; и второй мономер, включающий (iv) выше (второй слева на ФИГ. 33). Кроме того, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 3, SEQ ID NO: 5, SEQ ID NO: 6, SEQ ID NO: 7, SEQ ID NO: 20, SEQ ID NO: 22, SEQ ID NO: 23 и SEQ ID NO: 24. В частности, слитый белок может включать SEQ ID NO: 3, SEQ ID NO: 6 и SEQ ID NO: 7; SEQ ID NO: 5, SEQ ID NO: 6 и SEQ ID NO: 7; SEQ ID NO: 20, SEQ ID NO: 23 и SEQ ID NO: 24; или SEQ ID NO: 22, SEQ ID NO: 23 и SEQ ID NO: 24.
В одном варианте осуществления слитый белок может включать первый мономер, включающий (i) выше; и второй мономер, включающий (v) выше (третий слева на ФИГ. 33). Кроме того, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 2, SEQ ID NO: 3, SEQ ID NO: 5, SEQ ID NO: 8, SEQ ID NO: 19, SEQ ID NO: 20, SEQ ID NO: 22 и SEQ ID NO: 25. В частности, слитый белок может включать SEQ ID NO: 2, SEQ ID NO: 3 и SEQ ID NO: 8; SEQ ID NO: 2, SEQ ID NO: 5 и SEQ ID NO: 8; SEQ ID NO: 19, SEQ ID NO: 20 и SEQ ID NO: 25; или SEQ ID NO: 19, SEQ ID NO: 22 и SEQ ID NO: 25.
В одном варианте осуществления слитый белок может включать первый мономер, включающий (i) выше; и второй мономер, включающий (vi) выше (четвертый слева на ФИГ. 33). Кроме того, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 1, SEQ ID NO: 3, SEQ ID NO: 5, SEQ ID NO: 9, SEQ ID NO: 18, SEQ ID NO: 20, SEQ ID NO: 22 и SEQ ID NO: 26. В частности, слитый белок может включать SEQ ID NO: 1, SEQ ID NO: 3 и SEQ ID NO: 9; SEQ ID NO: 1, SEQ ID NO: 5 и SEQ ID NO: 9; SEQ ID NO: 18, SEQ ID NO: 20 и SEQ ID NO: 26; или SEQ ID NO: 18, SEQ ID NO: 22 и SEQ ID NO: 26.
В одном варианте осуществления слитый белок может включать первый мономер, включающий (ii) выше; и второй мономер, включающий (iii) выше (пятый слева на ФИГ. 33). Кроме того, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 1, SEQ ID NO: 2, SEQ ID NO: 10, SEQ ID NO: 11, SEQ ID NO: 18, SEQ ID NO: 19, SEQ ID NO: 27 и SEQ ID NO: 28. В частности, слитый белок может включать SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 10; SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 11; SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 27; или SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 28.
Кроме того, в одном варианте осуществления, димер слитого белка, включающий IL-12 или его вариант и антигенсвязывающий участок, который специфично связывается с FAP, может быть димером слитого белка, включающим мономер структурной формулы (III) и мономер структурной формулы (V) (слева на ФИГ. 34). Кроме того, в структурной формуле (III) r равно 1, а в структурной формуле (V) s, a и t равны 0. Кроме того, структурная формула (V) может включать (V') и (V''). Кроме того, в (V') и (V'') s, a, t и b равны 0. Кроме того, Fc-область димера содержит структуру выступа во впадину, посредством которой различные слитые белки могут быть связаны друг с другом.
В частности, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 1, SEQ ID NO: 2, SEQ ID NO: 18, SEQ ID NO: 19, SEQ ID NO: 292, SEQ ID NO: 293, SEQ ID NO: 298 и SEQ ID NO: 299. В частности, слитый белок может включать SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 292; SEQ ID NO: 1, SEQ ID NO: 2 и SEQ ID NO: 293; SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 298; или SEQ ID NO: 18, SEQ ID NO: 19 и SEQ ID NO: 299.
Кроме того, димер слитого белка, включающий IL-12 или его вариант и антигенсвязывающий участок, который специфично связывается с FAP, может быть димером слитого белка, включающим структуру структурной формулы (V) (в середине на ФИГ. 34). Кроме того, димер слитого белка может включать (V') и (V''). Кроме того, в структурной формуле (V) s и t равны 0, и a равно 1. Кроме того, в (V') и (V'') s, t и b равны 0, и a равно 1. Кроме того, димер слитого белка может быть димером слитого белка, включающим структуру структурной формулы (IV). Кроме того, в структурной формуле (IV) r равно 1.
В частности, слитый белок может включать по меньшей мере одну аминокислотную последовательность, выбранную из группы, состоящей из SEQ ID NO: 2, SEQ ID NO: 19, SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 300 и SEQ ID NO: 301. В частности, слитый белок может включать SEQ ID NO: 2 и SEQ ID NO: 294; SEQ ID NO: 2 и SEQ ID NO: 295; SEQ ID NO: 19 и SEQ ID NO: 300; или SEQ ID NO: 19 и SEQ ID NO: 301.
В одном варианте осуществления димер слитого белка, включающий IL-12 или его вариант и антигенсвязывающий участок, который специфично связывается с FAP, может быть димером слитого белка, включающим структуру структурной формулы (III) (справа на ФИГ. 34). Кроме того, в структурной формуле (III) r равно 1.
В частности, слитый белок может включать SEQ ID NO: 296, SEQ ID NO: 297, SEQ ID NO: 302 или SEQ ID NO: 303.
Мультиопределенный слитый белок в настоящем документе может быть в химически модифицированной форме. В одном варианте осуществления слитый белок может быть химически модифицирован путем гликозилирования, ацетилирования, пэгилирования, фосфорилирования, амидирования, дериватизации известными защитными/блокирующими группами, протеолитического расщепления и/или связывания с клеточными лигандами или другими белками. Многие из таких химических модификаций могут быть выполнены с помощью известных методов.
Полинуклеотид, кодирующий слитый белок
В другом аспекте настоящего изобретения предложен полинуклеотид, кодирующий первый мономер, или полинуклеотид, кодирующий второй мономер.
В одном варианте осуществления полипептид первого мономера может включать аминокислотную последовательность, обладающую по меньшей мере приблизительно 70%, по меньшей мере приблизительно 75%, по меньшей мере приблизительно 80%, по меньшей мере приблизительно 85%, по меньшей мере приблизительно 86%, по меньшей мере приблизительно 87%, по меньшей мере приблизительно 88%, по меньшей мере приблизительно 89%, по меньшей мере приблизительно 90%, по меньшей мере приблизительно 91%, по меньшей мере приблизительно 92%, по меньшей мере приблизительно 93%, по меньшей мере приблизительно 94%, по меньшей мере приблизительно 95%, по меньшей мере приблизительно 96%, по меньшей мере приблизительно 97%, по меньшей мере приблизительно 98%, по меньшей мере приблизительно 99% или по меньшей мере приблизительно 100% идентичностью с SEQ ID NO: 3, SEQ ID NO: 4, SEQ ID NO: 5, SEQ ID NO: 10, SEQ ID NO: 11, SEQ ID NO: 15, SEQ ID NO: 20, SEQ ID NO: 21, SEQ ID NO: 22, SEQ ID NO: 27, SEQ ID NO: 28, SEQ ID NO: 32, SEQ ID NO: 292, SEQ ID NO: 293, SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 296, SEQ ID NO: 297, SEQ ID NO: 298, SEQ ID NO: 299, SEQ ID NO: 300, SEQ ID NO: 301, SEQ ID NO: 302 или SEQ ID NO: 303.
В одном варианте осуществления полинуклеотид, кодирующий первый мономер, может обладать по меньшей мере приблизительно 70%, по меньшей мере приблизительно 75%, по меньшей мере приблизительно 80%, по меньшей мере приблизительно 85%, по меньшей мере приблизительно 86%, по меньшей мере приблизительно 87%, по меньшей мере приблизительно 88%, по меньшей мере приблизительно 89%, по меньшей мере приблизительно 90%, по меньшей мере приблизительно 91%, по меньшей мере приблизительно 92%, по меньшей мере приблизительно 93%, по меньшей мере приблизительно 94%, по меньшей мере приблизительно 95%, по меньшей мере приблизительно 96%, по меньшей мере приблизительно 97%, по меньшей мере приблизительно 98%, по меньшей мере приблизительно 99% или по меньшей мере приблизительно 100% идентичностью с SEQ ID NO: 38, SEQ ID NO: 39, SEQ ID NO: 40, SEQ ID NO: 45, SEQ ID NO: 46, SEQ ID NO: 50, SEQ ID NO: 55, SEQ ID NO: 56, SEQ ID NO: 57, SEQ ID NO: 62, SEQ ID NO: 63 или SEQ ID NO: 67.
В одном варианте осуществления полипептид второго мономера может включать аминокислотную последовательность, обладающую приблизительно 70%, по меньшей мере приблизительно 75%, по меньшей мере приблизительно 80%, по меньшей мере приблизительно 85%, по меньшей мере приблизительно 86%, по меньшей мере приблизительно 87%, по меньшей мере приблизительно 88%, по меньшей мере приблизительно 89%, по меньшей мере приблизительно 90%, по меньшей мере приблизительно 91%, по меньшей мере приблизительно 92%, по меньшей мере приблизительно 93%, по меньшей мере приблизительно 94%, по меньшей мере приблизительно 95%, по меньшей мере приблизительно 96%, по меньшей мере приблизительно 97%, по меньшей мере приблизительно 98%, по меньшей мере приблизительно 99% или по меньшей мере приблизительно 100% идентичностью с SEQ ID NO: 1, SEQ ID NO: 2, SEQ ID NO: 6, SEQ ID NO: 7, SEQ ID NO: 8, SEQ ID NO: 9, SEQ ID NO: 14, SEQ ID NO: 18, SEQ ID NO: 19, SEQ ID NO: 23, SEQ ID NO: 24, SEQ ID NO: 25, SEQ ID NO: 26, SEQ ID NO: 31, SEQ ID NO: 294, SEQ ID NO: 295, SEQ ID NO: 300 или SEQ ID NO: 301.
В одном варианте осуществления полинуклеотид, кодирующий второй мономер, может обладать по меньшей мере приблизительно 70%, по меньшей мере приблизительно 75%, по меньшей мере приблизительно 80%, по меньшей мере приблизительно 85%, по меньшей мере приблизительно 86%, по меньшей мере приблизительно 87%, по меньшей мере приблизительно 88%, по меньшей мере приблизительно 89%, по меньшей мере приблизительно 90%, по меньшей мере приблизительно 91%, по меньшей мере приблизительно 92%, по меньшей мере приблизительно 93%, по меньшей мере приблизительно 94%, по меньшей мере приблизительно 95%, по меньшей мере приблизительно 96%, по меньшей мере приблизительно 97%, по меньшей мере приблизительно 98%, по меньшей мере приблизительно 99% или по меньшей мере приблизительно 100% идентичностью с SEQ ID NO: 36, SEQ ID NO: 37, SEQ ID NO: 41, SEQ ID NO: 42, SEQ ID NO: 43, SEQ ID NO: 44, SEQ ID NO: 49, SEQ ID NO: 53, SEQ ID NO: 54, SEQ ID NO: 58, SEQ ID NO: 59, SEQ ID NO: 60, SEQ ID NO: 61 или SEQ ID NO: 66.
Полинуклеотид может дополнительно включать нуклеиновую кислоту, кодирующую сигнальную последовательность или лидерную последовательность. При использовании в настоящем документе термин "сигнальная последовательность" относится к сигнальному пептиду, направляющему секрецию целевого белка. Сигнальный пептид транслируется и затем отщепляется в клетке-хозяине. В частности, сигнальная последовательность является аминокислотной последовательностью, инициирующей транспортировку белка через мембрану эндоплазматического ретикулума (ЭПР).
Сигнальные последовательности известны в уровне техники благодаря своим свойствам. Такие сигнальные последовательности обычно содержат от 16 до 30 аминокислотных остатков и могут содержать больше или меньше аминокислотных остатков, чем такие аминокислотные остатки. Типичный сигнальный пептид состоит из трех областей: основной N-концевой области, центральной гидрофобной области и более полярной С-концевой области. Центральная гидрофобная область содержит 4-12 гидрофобных остатков, которые обеспечивают иммобилизацию сигнальной последовательности при транспортировке незрелого полипептида через липидный бислой мембраны.
После инициации сигнальные последовательности отщепляются в просвете ЭПР клеточными ферментами, широко известными как сигнальные пептидазы. Таким образом, сигнальная последовательность может быть секреторной сигнальной последовательностью tPa (активатора тканевого плазминогена), gDs ВПГ (сигнальной последовательностью гликопротеина D вируса простого герпеса) или гормона роста. Предпочтительно может использоваться секреторная сигнальная последовательность, используемая в клетках высших эукариотов, включая млекопитающих и т.п. Кроме того, может использоваться сигнальная последовательность дикого типа или может использоваться сигнальная последовательность, которая содержит замену кодоном, имеющим высокую частоту экспрессии в клетке-хозяине.
Вектор с полинуклеотидом
В другом аспекте настоящего изобретения предложен вектор, включающий полинуклеотид.
Вектор может быть введен в клетку-хозяин для рекомбинации с ней и встроен в геном клетки-хозяина. Или же под вектором подразумевают нуклеиновую кислоту, содержащую полинуклеотидную последовательность, которая может автономно реплицироваться в виде эписомы. Векторы включают линейные нуклеиновые кислоты, плазмиды, фагемиды, космиды, РНК-векторы, вирусные векторы и их аналоги. Примеры вирусного вектора включают, без ограничения ими, ретровирусы, аденовирусы и аденоассоциированные вирусы.
В частности, вектор может включать плазмидную ДНК, фаговую ДНК и т.п.; а также коммерчески разработанные плазмиды (pUC18, pBAD, pIDTSAMRT-AMP и т.п.), плазмиды, полученные из E. coli (pYG601BR322, pBR325, pUC118, pUC119 и подобные), плазмиды, полученные из Bacillus subtilis (pUB110, pTP5 и подобные) дрожжевые плазмиды (YEp13, YEp24, YCp50 и т.п.), фаговую ДНК (Charon4A, Charon21A, EMBL3, EMBL4, λgt10, λgt11, λZAP и т.п.), векторы на основе вирусов животных (ретровирусов, аденовирусов, вируса осповакцины и т.п.), векторы на основе вирусов насекомых (бакуловирусов и т.п.). Поскольку вектор демонстрирует разные уровни экспрессии и модификации белка в зависимости от клетки-хозяина, предпочтительно выбирать и использовать такую клетку-хозяина, которая более всего подходит для этой цели.
При использовании в настоящем документе под термином "экспрессия гена" или "экспрессия" целевого белка подразумевается транскрипция последовательностей ДНК, трансляция мРНК транскриптов и секреция продуктов в виде слитых белков или их фрагментов. Полезным вектором экспрессии может быть RcCMV (Invitrogen, Carlsbad) или его вариант. Векторы экспрессии могут содержать промотор цитомегаловируса человека (ЦМВ), который обеспечивает постоянную транскрипцию целевого гена в клетках млекопитающих, и сигнальную последовательность полиаденилирования из бычьего гормона роста для повышения уровня стабильности РНК после транскрипции.
Трансформированная клетка, экспрессирующая слитый белок
В другом аспекте настоящего изобретения предложена трансформированная клетка, в которую был введен вектор.
Клетки-хозяева для трансформированной клетки могут включать, без ограничения перечисленными, прокариотические клетки, эукариотические клетки и клетки млекопитающих, растений, насекомых, грибов или бактерий. В качестве примера прокариотических клеток может использоваться E. coli. Кроме того, в качестве примера эукариотических клеток могут использоваться дрожжи. Кроме того, в качестве клеток млекопитающих могут использоваться клетки СНО, клетки F2N, клетки CSO, клетки BHK, клетки меланомы Bowes, клетки HeLa, клетки 911, клетки AT1080, клетки A549, клетки HEK 293, клетки HEK293T и т.п. Впрочем, клетки млекопитающих не ограничиваются этим, и могут использоваться любые клетки, которые, как известно специалистам в данной области, можно использовать в качестве клеток-хозяев млекопитающих.
Кроме того, для введения вектора экспрессии в клетку-хозяина можно использовать осаждение с CaCl2, метод Ханахана, эффективность которого была повышена благодаря применению такого восстановителя, как диметилсульфоксид (ДМСО), при осаждении с CaCl2, электропорация, осаждение с фосфатом кальция, слияние протопластов, перемешивание с использованием карбидокремниевого волокна, агробактериальную трансформацию, трансформацию с использованием ПЭГ, декстрансульфата, липофектамина или сухую/опосредованную ингибированием трансформацию и т.п.
Как описано выше, для оптимизации свойств слитого белка в качестве терапевтического средства или для любой другой цели профиль гликозилирования слитого белка (например, сиаловые кислоты, фукозилирование, гликозилирование) можно изменять при манипуляции генами, связанными с гликозилированием, которые несут клетки-хозяева, с применением методов, известных специалистам в данной области.
Способ получения слитого белка
В другом аспекте настоящего изобретения предложен способ получения слитого белка, включающий: i) культивирование трансформированной клетки; и ii) выделение слитого белка, включающего первый мономер и второй мономер.
Способ культивирования трансформированных клеток может быть проведен при использовании методов, хорошо известных в данной области. В частности, культивирование можно вести в периодическом процессе или непрерывно в процессе с подпиткой, или в периодическом процессе с подпиткой.
Применение слитого белка
В другом аспекте настоящего изобретения предложена фармацевтическая композиция для профилактики или лечения рака, включающая слитый белок в качестве активного ингредиента.
Таким образом, рак может быть любым, выбранным из группы, состоящей из рака желудка, рака печени, рака легкого, рака толстой и прямой кишки, рака молочной железы, рака предстательной железы, рака кожи, рака кости, множественной миеломы, глиомы, рака яичника, рака поджелудочной железы, рака шейки матки, рака щитовидной железы, рака гортани, острого миелоидного лейкоза, хронического миелоидного лейкоза, острого лимфобластного лейкоза, хронического лимфобластного лейкоза, опухоли головного мозга, нейробластомы, ретинобластомы, рака головы и шеи, рака слюнных желез и лимфомы.
Предпочтительная доза фармацевтической композиции изменяется в зависимости от состояния и массы тела пациента, тяжести заболевания, формы лекарственного средства, пути и длительности введения и может быть надлежащим образом подобрана специалистом в данной области. В фармацевтической композиции для лечения или профилактики опухоли согласно настоящему изобретению активный ингредиент может содержаться в любом количестве (эффективном количестве) в зависимости от применения, лекарственной формы, цели смешивания и т.п., при условии, что активный ингредиент может проявлять активность при лечении опухоли или, в частности, терапевтическое действие в отношении рака. Его стандартное эффективное количество будут определять в пределах от 0,001% до 20,0% по весу в расчете на общую массу композиции. Таким образом, термин "эффективное количество" относится к количеству активного ингредиента, способного вызывать эффект улучшения или лечения патологического состояния и, в частности, вызывать эффект улучшения или лечения при онкологическом заболевании. Такое эффективное количество может быть определено экспериментально в рамках общих знаний специалистов в данной области.
При использовании в настоящем документе термин "лечение" может использоваться для обозначения как терапевтического, так и профилактического лечения. Таким образом, профилактика может использоваться для обозначения того, что патологическое состояние или заболевание у субъекта облегчается или уменьшается. В одном варианте осуществления термин "лечение" включает применение и любую форму введения для лечения заболевания у млекопитающего, в том числе человека. Кроме того, термин включает ингибирование или замедление прогрессирования заболевания; и включает значения восстановления или улучшения нарушенной или утраченной функции, в результате чего тяжесть заболевания частично или полностью снижается; стимулирование неэффективных процессов; или облегчение серьезного заболевания.
Фармакокинетические параметры, такие как биодоступность, и основные показатели, такие как скорость выведения, также могут влиять на эффективность. Следовательно, "повышенная эффективность" (например, улучшение эффективности) может быть обусловлена улучшением фармакокинеических параметров и повышенной эффективностью, которые можно измерять при сравнении таких параметров, как скорость выведения и лечение или уменьшение опухоли у подопытных животных или людей, участвующих в исследовании.
При использовании в настоящем документе термин "терапевтически эффективное количество" или "фармацевтически эффективное количество" относится к количеству соединения или композиции, эффективному для предупреждения или лечения рассматриваемого заболевания, которое является достаточным для лечения заболевания при разумном соотношении выгоды/риска, которое применимо к терапевтическому лечению и не вызывают побочных эффектов. Уровень эффективного количества может быть определен в зависимости от факторов, включающих состояние здоровья пациента, тип и тяжесть заболевания, активность лекарственного средства, чувствительность пациента к лекарственному средству, способ введения, время введения, путь введения и скорость выведения, длительность лечения, состав или одновременно применяемые лекарственные средства, а также другие факторы, хорошо известные в области медицины. В одном варианте осуществления терапевтически эффективное количество относится к количеству лекарственного средства, эффективному для лечения рака.
Таким образом, фармацевтическая композиция может дополнительно включать фармацевтически приемлемый носитель. Фармацевтически приемлемым носителем может быть любой носитель при условии, что такой носитель является нетоксичным веществом, подходящим для доставки пациенту. В качестве носителя в состав могут входить дистиллированная вода, спирт, жир, воск и инертное твердое вещество. Фармацевтически приемлемый адъювант (буферное вещество, диспергирующее вещество) также может содержаться в фармацевтической композиции.
В частности, при включении фармацевтически приемлемого носителя в дополнение к активному ингредиенту фармацевтическая композиция может быть приготовлена в виде состава для парентерального введения в зависимости от пути введения, с использованием стандартных способов, известных в данной области. Таким образом, термин "фармацевтически приемлемый" означает, что носитель не обладает большей токсичностью, чем может переносить подлежащий введению (назначению) субъект, без ингибирования при этом активности активного ингредиента.
В случае приготовления фармацевтической композиции в виде состава для парентерального введения, она может быть приготовлена в виде препаратов в форме инъекций, трансдермальных пластырей, составов для назальной ингаляции или суппозиториев с подходящими носителями в соответствии со способами, известными в уровне техники. В случае приготовления в виде составов для инъекций в качестве подходящего носителя может использоваться стерильная вода, этанол, многоатомный спирт, такой как глицерин или пропиленгликоль, или их смесь; и предпочтительно может использоваться изотонический раствор, такой как раствор Рингера, фосфатно-солевой буфер (PBS), содержащий триэтаноламин или стерильную воду для инъекций, и 5% декстрозу и т.п. Изготовление фармацевтических композиций известно в уровне техники, при этом можно сделать конкретную ссылку на Remington's Pharmaceutical Sciences (19th ed., 1995) и т.п. Данный документ считается частью настоящего описания.
Предпочтительная доза фармацевтической композиции может составлять от 0,01 мкг/кг до 10 г/кг или от 0,01 мг/кг до 1 г/кг в сутки в зависимости от состояния пациента, массы тела, пола, возраста, тяжести состояния пациента и пути введения. Дозу можно вводить один раз в день или можно разделить на несколько раз в день. Такую дозу не следует считать ограничивающей объем настоящего изобретения в каком-либо аспекте.
Субъектами, которым могут вводить (назначать) фармацевтическую композицию, являются млекопитающие и человек, при этом человек является особенно предпочтительным. В дополнение к активному ингредиенту фармацевтическая композиция согласно настоящей заявке может дополнительно содержать любое соединение или природный экстракт, который, как известно, оказывает терапевтическое воздействие на опухоль.
В другом аспекте настоящего изобретения предложено применение слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP, для лечения рака.
В другом аспекте настоящего изобретения предложено применение слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP, для производства лекарственного средства для лечения рака.
В еще одном аспекте настоящего изобретения предложен способ лечения или профилактики рака, включающий введение субъекту слитого белка, включающего первый мономер, включающий IL-12 или его вариант; и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP.
Таким образом, субъектом может быть субъект, страдающий раком. Кроме того, субъектом может быть млекопитающее, предпочтительно человек.
Путь введения, доза и частота введения слитого белка или димера слитого белка могут изменяться в зависимости от состояния пациента и присутствия или отсутствия побочных эффектов, и, таким образом, слитый белок или димер слитого белка можно вводить субъекту разными способами и в разных количествах. Оптимальный способ введения, доза и частота введения могут быть подобраны в соответствующем диапазоне специалистами в данной области. Кроме того, слитый белок или димер слитого белка можно вводить в комбинации с другими лекарственными средствами или физиологически активными веществами, терапевтическое действие которых известно в отношении заболевания, подлежащего лечению, или они могут быть включены в состав комбинированных препаратов с другими лекарственными средствами.
Далее настоящее изобретение будет описано более подробно посредством следующих примеров. Однако следующие примеры предназначены лишь для иллюстрации настоящего изобретения, и объем настоящего изобретения этим не ограничивается.
Пример получения 1. Обзор человеческого слитого белка против FAP/IL-12 IgG1 DANG
[seq1] состоит из человеческой последовательности вариабельной области тяжелой цепи против FAP и человеческого Fc IgG1, в котором эффекторная функция устранена в результате мутации DANG (D265A, N297G), а структура выступа сформирована в результате мутации T366W.
[seq2] состоит из последовательности человеческой легкой цепи против FAP.
[seq3] состоит из последовательности области p40 (бета) IL-12 человека и линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) интерлейкина-12 человека, линкера GGGGSGGGGS и человеческого Fc IgG1, в котором эффекторная функция устранена в результате мутации DANG (D265A, N297G), и структура впадины сформирована в результате мутаций T366S, L368A и Y407V.
[seq4] состоит из последовательности, в которой лизин (K) в 280-м и 285-м аминокислотных положениях, участвующий в связывании гепарина в области p40 (бета) IL-12 человека, подвергнут мутации с заменой на аланин (A), линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS, и Fc IgG1 человека с выступом и мутациями DANG.
[seq5] состоит из последовательности, в которой лизин (K) в 280-м, 282-м, 285-м и 286-м аминокислотных положениях, участвующий в связывании гепарина в области p40 (бета) IL-12 человека, подвергнут мутации с заменой на аланин (A), линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS, и Fc IgG1 человека с впадиной и мутациями DANG.
[seq6] состоит из человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, и Fc IgG1 человека с выступом и мутациями DANG.
[seq7] состоит из человеческой последовательности вариабельной области легкой цепи против FAP, линкера GGGGSGGGGSGGGGS и человеческой последовательности легкой цепи против FAP.
[seq8] состоит из человеческой последовательности вариабельной области тяжелой цепи против FAP, Fc IgG1 человека с выступом и мутациями DANG, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS, и человеческой последовательности вариабельной области легкой цепи против FAP.
[seq9] состоит из человеческой последовательности легкой цепи против FAP, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS, и человеческой последовательности вариабельной области легкой цепи против FAP.
[seq10] состоит из человеческой последовательности тяжелой цепи против FAP, Fc IgG1 человека с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 человека, линкера GGGGSGGGGSGGGGS, и последовательности области p35 (альфа) IL-12 человека.
[seq11] состоит из человеческой последовательности тяжелой цепи против FAP, Fc IgG1 человека с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, и последовательности области p35 (альфа) IL-12 человека.
[seq12] состоит только из Fc IgG1 человека с впадиной и мутациями DANG.
[seq13] состоит только из Fc IgG1 человека с выступом и мутациями DANG.
[seq14] состоит из человеческой последовательности вариабельной области тяжелой цепи против FAP и Fc IgG1 человека с мутациями DANG.
[seq15] состоит из последовательности области p40 (бета) IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS, и Fc IgG1 человека с мутациями DANG.
[seq16] состоит из последовательности тяжелой цепи человеческого антитела против CD20 и Fc IgG1 человека с выступом и мутациями DANG.
[seq17] является последовательностью легкой цепи человеческого антитела против CD20.
[seq292] состоит из последовательности области p40 (бета) IL-12 человека, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS и Fc IgG1 человека с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и человеческой последовательности вариабельной области легкой цепи против FAP.
[seq293] состоит из последовательности области p40 (бета) IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS и Fc IgG1 человека с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS, и человеческой последовательности вариабельной области легкой цепи против FAP.
[seq294] состоит из человеческой последовательности тяжелой цепи против FAP, Fc IgG1 DANG человека, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 человека, линкера GGGGSGGGGSGGGGS, и последовательности области p35 (альфа) IL-12 человека.
[seq295] состоит из человеческой последовательности тяжелой цепи против FAP, Fc IgG1 DANG человека, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, и последовательности области p35 (альфа) IL-12 человека.
[seq296] состоит из последовательности области p40 (бета) IL-12 человека, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS и Fc IgG1 DANG человека, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и человеческой последовательности вариабельной области легкой цепи против FAP.
[seq297] состоит из последовательности области p40 (бета) IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 человека, линкера GGGGSGGGGS и Fc IgG1 DANG человека, линкера GGGGSGGGGSGGGGS, человеческой последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS, и человеческой последовательности вариабельной области легкой цепи против FAP.
T1.01 (seq1, seq2, seq3) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, направленная против FAP человека, и последовательность IL-12 человека формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.02 (seq1, seq2, seq4) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, направленная против FAP человека, и последовательность IL-12 человека, содержащая мутации (двух) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.03 (seq1, seq2, seq5) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, направленная против FAP человека, и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.04 (seq3, seq6, seq7) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP в форме иммуноглобулина с двойным вариабельным доменом (DVD-Ig) и последовательность IL-12 человека формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.05 (seq5, seq6, seq7) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP в форме DVD-Ig и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.06 (seq2, seq3, seq8) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, в которой одноцепочечный вариабельный фрагмент (scFv) человеческой последовательности против FAP, направленной против FAP человека, соединен с C-концом тяжелой цепи, и последовательность IL-12 человека формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.07 (seq2, seq5, seq8) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, в которой scFv человеческой последовательности против FAP, направленной против FAP человека, соединен с C-концом тяжелой цепи, и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.08 (seq1, seq3, seq9) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP, в которой scFv человеческой последовательности FAP, направленной против FAP человека, соединен с C-концом легкой цепи, и последовательность IL-12 человека, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.09 (seq1, seq5, seq9) представляет собой биспецифичное антитело, в котором человеческая против FAP последовательность, в которой scFv человеческой последовательности против FAP, направленной против FAP человека, соединен с C-концом легкой цепи, и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.10 (seq1, seq2, seq10) представляет собой антитело, в котором человеческая последовательность против FAP, направленная против FAP человека, и человеческая последовательность против FAP, в которой последовательность IL-12 человека соединена с C-концом тяжелой цепи, формируют структуру выступа во впадину.
T1.11 (seq1, seq2, seq11) представляет собой антитело, в котором человеческая последовательность против FAP, направленная против FAP человека, и человеческая последовательность против FAP, в которой последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, соединена с C-концом тяжелой цепи, формируют структуру выступа во впадину.
T1.12 (seq1, seq2, seq12) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только человеческую последовательность против FAP, направленную против FAP человека, устранена.
T1.13 (seq3, seq13) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 человека, устранена.
T1.14 (seq4, seq13) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 человека, содержащую мутации (двух) аминокислот, участвующих в связывании гепарина, устранена.
T1.15 (seq5, seq13) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 человека, содержащую мутации (четырех) аминокислот, участвующих в связывании гепарина, устранена.
T1.16 (seq2, seq14) представляет собой человеческое антитело против FAP, направленное против FAP человека.
T1.17 (seq15) представляет собой Fc-слитый белок, содержащий только последовательность IL-12 человека, содержащую мутации (четырех) аминокислот, участвующих в связывании гепарина.
T1.18 (seq3, seq16, seq17) представляет собой биспецифичное антитело, в котором человеческая последовательность против CD20, направленная против CD20 человека, и последовательность IL-12 человека формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.19 (seq4, seq16, seq17) представляет собой биспецифичное антитело, в котором человеческая последовательность против CD20, направленная против CD20 человека, и последовательность IL-12 человека, содержащая мутации (двух) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.20 (seq5, seq16, seq17) представляет собой биспецифичное антитело, в котором человеческая последовательность против CD20, направленная против CD20 человека, и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.21 (seq12, seq16, seq17) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только человеческую последовательность против CD20, направленную против CD20 человека, устранена.
T1.23 (seq1, seq2, seq292) представляет собой биспецифичное антитело, в котором человеческая последовательность против FAP и последовательность IL-12 человека, в которой scFv человеческой последовательности против FAP соединен с C-концом, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.24 (seq1, seq2, seq293) представляет собой биспецифичное антитело, в котором человеческая последовательность тяжелой цепи против FAP и последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, в которой scFv человеческой последовательности против FAP соединен с C-концом, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.25 (seq2, seq294) представляет собой димер Fc-слитого белка, содержащий человеческую последовательность против FAP, в которой последовательность IL-12 человека соединена с C-концом тяжелой цепи.
T1.26 (seq2, seq295) представляет собой димер Fc-слитого белка, содержащий человеческую последовательность против FAP, в которой последовательность IL-12 человека, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, соединена с C-концом тяжелой цепи.
T1.27 (seq296) представляет собой димер Fc-слитого белка, содержащий последовательность IL-12 человека, в которой scFv человеческой последовательности против FAP соединен с C-концом.
T1.28 (seq297) представляет собой димер Fc-слитого белка, состоящий из последовательности IL-12 человека, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, в котором scFv человеческой последовательности против FAP соединен с C-концом.
[seq1] anti-hu FAP HC hu IgG1 Fc knob DANG
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLWCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq2] anti-hu FAP LC
DIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIKRTVAAPSVFIFPPSDEQLKSGTASVVCLLNNFYPREAKVQWKVDNALQSGNSQESVTEQDSKDSTYSLSSTLTLSKADYEKHKVYACEVTHQGLSSPVTKSFNRGEC
[seq3] hu scIL-12-hu IgG1 Fc hole DANG
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGKSKREKKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq4] hu scIL-12 mut1-hu IgG1 Fc hole DANG
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASKREAKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq5] hu scIL-12 mut2-hu IgG1 Fc hole DANG
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq6] (anti-hu FAP VH)2-hu IgG1 Fc knob DANG
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLWCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq7] (anti-hu FAP VL)2
DIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIKGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIKRTVAAPSVFIFPPSDEQLKSGTASVVCLLNNFYPREAKVQWKVDNALQSGNSQESVTEQDSKDSTYSLSSTLTLSKADYEKHKVYACEVTHQGLSSPVTKSFNRGEC
[seq8] anti-hu FAP HC hu IgG1 Fc knob DANG-anti-hu FAP scFv
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLWCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGKGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
[seq9] anti-hu FAP LC-anti-hu FAP scFv
DIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIKRTVAAPSVFIFPPSDEQLKSGTASVVCLLNNFYPREAKVQWKVDNALQSGNSQESVTEQDSKDSTYSLSSTLTLSKADYEKHKVYACEVTHQGLSSPVTKSFNRGECGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
[seq10] anti-hu FAP HC hu IgG1 Fc hole DANG-hu scIL-12
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSIWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGKSKREKKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNAS
[seq11] anti-hu FAP HC hu IgG1 Fc hole DANG-hu scIL-12 mut2
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSIWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNAS
[seq12] hu IgG1 Fc hole DANG
DKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq13] hu IgG1 Fc knob DANG
DKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLWCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq14] anti-hu FAP HC hu IgG1 Fc DANG
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq15] hu scIL-12 mut2-hu IgG1 Fc DANG
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq16] anti-hu CD20 HC hu IgG1 Fc knob DANG
QVQLQQPGAELVKPGASVKMSCKASGYTFTSYNMHWVKQTPGRGLEWIGAIYPGNGDTSYNQKFKGKATLTADKSSSTAYMQLSSLTSEDSAVYYCARSTYYGGDWYFNVWGAGTTVTVSAASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLWCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGK
[seq17] anti-hu CD20 LC
QIVLSQSPAILSASPGEKVTMTCRASSSVSYIHWFQQKPGSSPKPWIYATSNLASGVPVRFSGSGSGTSYSLTISRVEAEDAATYYCQQWTSNPPTFGGGTKLEIKRTVAAPSVFIFPPSDEQLKSGTASVVCLLNNFYPREAKVQWKVDNALQSGNSQESVTEQDSKDSTYSLSSTLTLSKADYEKHKVYACEVTHQGLSSPVTKSFNRGEC
[seq292] hu scIL-12-hu IgG1 Fc hole DANG-anti-hu FAP scFv
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGKSKREKKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
[seq293] hu scIL-12 mut2-hu IgG1 Fc hole DANG-anti-hu FAP scFv
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLSCAVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLVSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
[seq294] anti-hu FAP HC hu IgG1 Fc DANG-hu scIL-12
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSIWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGKSKREKKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNAS
[seq295] anti-hu FAP HC hu IgG1 Fc DANG-hu scIL-12 mut2
QVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSASTKGPSVFPLAPSSKSTSGGTAALGCLVKDYFPEPVTVSWNSGALTSGVHTFPAVLQSSGLYSLSSVVTVPSSSLGTQTYICNVNHKPSNTKVDKKVEPKSCDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSIWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNAS
[seq296] hu scIL-12-hu IgG1 Fc DANG-anti-hu FAP scFv
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGKSKREKKDRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
[seq297] hu scIL-12 mut2-hu IgG1 Fc DANG-anti-hu FAP scFv
IWELKKDVYVVELDWYPDAPGEMVVLTCDTPEEDGITWTLDQSSEVLGSGKTLTIQVKEFGDAGQYTCHKGGEVLSHSLLLLHKKEDGIWSTDILKDQKEPKNKTFLRCEAKNYSGRFTCWWLTTISTDLTFSVKSSRGSSDPQGVTCGAATLSAERVRGDNKEYEYSVECQEDSACPAAEESLPIEVMVDAVHKLKYENYTSSFFIRDIIKPDPPKNLQLKPLKNSRQVEVSWEYPDTWSTPHSYFSLTFCVQVQGASAREAADRVFTDKTSATVICRKNASISVRAQDRYYSSSWSEWASVPCSGGGGSGGGGSGGGGSRNLPVATPDPGMFPCLHHSQNLLRAVSNMLQKARQTLEFYPCTSEEIDHEDITKDKTSTVEACLPLELTKNESCLNSRETSFITNGSCLASRKTSFMMALCLSSIYEDLKMYQVEFKTMNAKLLMDPKRQIFLDQNMLAVIDELMQALNFNSETVPQKSSLEEPDFYKTKIKLCILLHAFRIRAVTIDRVMSYLNASGGGGSGGGGSDKTHTCPPCPAPELLGGPSVFLFPPKPKDTLMISRTPEVTCVVVAVSHEDPEVKFNWYVDGVEVHNAKTKPREEQYGSTYRVVSVLTVLHQDWLNGKEYKCKVSNKALPAPIEKTISKAKGQPREPQVYTLPPSRDELTKNQVSLTCLVKGFYPSDIAVEWESNGQPENNYKTTPPVLDSDGSFFLYSKLTVDKSRWQQGNVFSCSVMHEALHNHYTQKSLSLSPGGGGGSGGGGSGGGGSQVQLVQSGAEVKKPGASVKVSCKTSRYTFTEYTIHWVRQAPGQRLEWIGGINPNNGIPNYNQKFKGRVTITVDTSASTAYMELSSLRSEDTAVYYCARRRIAYGYDEGHAMDYWGQGTLVTVSSGGGGSGGGGSGGGGSGGGGSDIVMTQSPDSLAVSLGERATINCKSSQSLLYSRNQKNYLAWYQQKPGQPPKLLIFWASTRESGVPDRFSGSGFGTDFTLTISSLQAEDVAVYYCQQYFSYPLTFGQGTKVEIK
Пример получения 2. Обзор anti-FAP/IL-12 IgG2a DANG, мышиного слитого белка
[seq18] состоит из мышиной последовательности вариабельной области тяжелой цепи против FAP и Fc IgG2a мыши, в которой эффекторная функция устранена посредством мутаций DANG (D265A, N297G), и сформирована структура выступа в результате мутации T321W.
[seq19] состоит из мышиной последовательности легкой цепи против FAP.
[seq20] состоит из последовательности области p40 (бета) IL-12 мыши, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши, в которой эффекторная функция устранена посредством мутаций DANG, и сформирована структура впадины в результате мутаций T321S, M323A, Y362V.
[seq21] состоит из последовательности, в которой лизин (K) в 277-м и 282-м аминокислотных положениях, участвующий в связывании гепарина в области p40 (бета) IL-12 мыши, подвергнут мутации с заменой на аланин (A), линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS, и Fc IgG2a мыши с впадиной и мутациями DANG.
[seq22] состоит из последовательности, в которой аргинин (R) в 276-м аминокислотном положении и лизин (K) в 277-м, 278-м и 282-м аминокислотных положениях, участвующие в связывании гепарина в области p40 (бета) IL-12 мыши, подвергнуты мутации с заменой на аланин (A), линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши с впадиной и мутациями DANG.
[seq23] состоит из мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP и Fc IgG2a мыши с выступом и мутациями DANG.
[seq24] состоит из мышиной последовательности вариабельной области легкой цепи против FAP, линкера GGGGSGGGGSGGGGS и мышиной последовательности легкой цепи против FAP.
[seq25] состоит из мыши последовательности вариабельной области тяжелой цепи против FAP, Fc IgG2a мыши с выступом и мутациями DANG, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
[seq26] состоит из мышиной последовательности легкой цепи против FAP, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
[seq27] состоит из мышиной последовательности тяжелой цепи против FAP, Fc IgG2a мыши с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 мыши, линкера GGGGSGGGGSGGGGS и последовательности области p35 (альфа) IL-12 мыши.
[seq28] состоит из мышиной последовательности тяжелой цепи против FAP, Fc IgG2a мыши с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS и последовательности области p35 (альфа) IL-12 мыши.
[seq29] состоит только из Fc IgG2a мыши с впадиной и мутациями DANG.
[seq30] состоит только из Fc IgG2a мыши с выступом и мутациями DANG.
[seq31] состоит из мышиной вариабельной области тяжелой цепи против FAP и Fc IgG2a мыши с мутациями DANG.
[seq32] состоит из последовательности области p40 (бета) IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS, и Fc IgG2a мыши с мутациями DANG.
[seq33] состоит из последовательности вариабельной области тяжелой цепи мышиного антитела против CD20, 18B12, и мышиного IgG2a с выступом и мутациями DANG.
[seq34] состоит из последовательности легкой цепи мышиного антитела против CD20, 18B12.
[seq35] состоит только из Fc IgG2a мыши с мутациями DANG.
[seq298] состоит из последовательности области p40 (бета) IL-12 мыши, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
[seq299] состоит из последовательности области p40 (бета) IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши с впадиной и мутациями DANG, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
[seq300] состоит из мышиной последовательности тяжелой цепи против FAP, Fc IgG2a мыши с мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 мыши, линкера GGGGSGGGGSGGGGS и последовательности области p35 (альфа) IL-12 мыши.
[seq301] состоит из мышиной последовательности тяжелой цепи против FAP, Fc IgG1 мыши с мутациями DANG, линкера GGGGSGGGGSGGGGS, последовательности области p40 (бета) IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS и последовательности области p35 (альфа) IL-12 мыши.
[seq302] состоит из последовательности области p40 (бета) IL-12 мыши, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши с мутациями DANG, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
[seq303] состоит из последовательности области p40 (бета) IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, линкера GGGGSGGGGSGGGGS, последовательности области p35 (альфа) IL-12 мыши, линкера GGGGSGGGGS и Fc IgG2a мыши с мутациями DANG, линкера GGGGSGGGGSGGGGS, мышиной последовательности вариабельной области тяжелой цепи против FAP, линкера GGGGSGGGGSGGGGSGGGGS и мышиной последовательности вариабельной области легкой цепи против FAP.
T1.01m (seq18, seq19, seq20) представляет собой биспецифичное антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, и последовательность IL-12 мыши формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.02m (seq18, seq19, seq21) представляет собой биспецифичное антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, и последовательность IL-12 мыши, содержащая мутации (двух) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.03m (seq18, seq19, seq22) представляет собой биспецифичное антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.04m (seq20, seq23, seq24) представляет собой биспецифичное антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, в форме иммуноглобулина с двойным вариабельным доменом (DVD-Ig) и последовательность IL-12 мыши, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.05m (seq22, seq23, seq24) представляет собой биспецифичное антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, в форме DVD-Ig и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.06m (seq19, seq20, seq25) представляет собой биспецифичное антитело, в котором мышиная последовательность против FAP, в которой одноцепочечный вариабельный фрагмент (scFv) мышиной последовательности против FAP, направленной против FAP мыши, включен на C-конце тяжелой цепи, и последовательность IL-12 мыши, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.07m (seq19, seq22, seq25) представляет собой биспецифичное антитело, в котором мышиная последовательность против FAP, в которой scFv мышиной последовательности против FAP, направленной против FAP мыши, включен на C-конце тяжелой цепи, и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.08m (seq18, seq20, seq26) представляет собой биспецифичное антитело, в котором мышиная последовательность против FAP, в которой scFv мышиной последовательности против FAP, направленной против FAP мыши, включен на C-конце легкой цепи и последовательность IL-12 мыши формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.09m (seq18, seq22, seq26) представляет собой биспецифичное антитело, в котором мышиная последовательность против FAP, в которой scFv мышиной последовательности против FAP, направленной против FAP мыши, включен на C-конце легкой цепи, и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формирует структуру выступа во впадину, и эффекторная функция устранена.
T1.10m (seq18, seq19, seq27) представляет собой антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, и мышиная последовательность против FAP, в которой последовательность IL-12 мыши соединена с C-концом тяжелой цепи, формируют структуру выступа во впадину.
T1.11m (seq18, seq19, seq28) представляет собой антитело, в котором мышиная последовательность FAP, направленная против FAP мыши, и мышиная последовательность против FAP, в которой последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, соединена с C-концом тяжелой цепи, формируют структуру выступа во впадину.
T1.12m (seq18, seq19, seq29) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только мышиную последовательность против FAP, направленную против FAP мыши, устранена.
T1.13m (seq20, seq30) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 мыши, устранена.
T1.14m (seq21, seq30) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 мыши, содержащую мутации (двух) аминокислот, участвующих в связывании гепарина, устранена.
T1.15m (seq22, seq30) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только последовательность IL-12 мыши, содержащую мутации (четырех) аминокислот, участвующих в связывании гепарина, устранена.
T1.16m (seq19, seq31) представляет собой мышиное антитело против FAP, направленное против FAP мыши.
T1.17m (seq32) представляет собой димер Fc-слитого белка, содержащий только последовательность IL-12 мыши, содержащую мутации (четырех) аминокислот, участвующих в связывании гепарина.
T1.18m (seq20, seq33, seq34) представляет собой биспецифичное антитело, в котором мышиная последовательность против CD20 (18B12), направленная против CD20 мыши, и последовательность IL-12 мыши формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.19m (seq21, seq33, seq34) представляет собой биспецифичное антитело, в котором мышиная последовательность против CD20 (18B12), направленная против CD20 мыши, и последовательность IL-12 мыши, содержащая мутации (двух) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.20m (seq22, seq33, seq34) представляет собой биспецифичное антитело, в котором мышиная последовательность против CD20, направленная против CD20 мыши, и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.21m (seq29, seq33, seq34) представляет собой антитело, в котором эффекторная функция структуры выступа во впадину, содержащей только мышиную последовательность против CD20, направленную CD20 мыши, устранена.
T1.22m (seq35) представляет собой белок, содержащий только последовательность Fc мыши, в которой устранена эффекторная функция.
T1.23m (seq18, seq19, seq298) представляет собой биспецифичное антитело, в котором мышиная последовательность против FAP, и последовательность IL-12 мыши, в которой scFv мышиной последовательности против FAP соединена с C-концом, формирует структуру выступа во впадину, и эффекторная функция устранена.
T1.24m (seq18, seq19, seq299) представляет собой биспецифичное антитело, в котором мышиная последовательность тяжелой цепи против FAP и последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, в которой scFv мышиной последовательности против FAP соединен с C-концом, формируют структуру выступа во впадину, и эффекторная функция устранена.
T1.25m (seq19, seq300) представляет собой димер Fc-слитого белка, содержащий мышиную последовательность против FAP, в котором последовательность IL-12 мыши соединена с C-концом тяжелой цепи.
T1.26m (seq19, seq301) представляет собой димер Fc-слитого белка, содержащий мышиную последовательность против FAP, в котором последовательность IL-12 мыши, содержащая мутации (четырех) аминокислот, участвующих в связывании гепарина, соединена с C-концом тяжелой цепи.
T1.27m (seq302) представляет собой димер Fc-слитого белка, содержащий последовательность IL-12 мыши, в котором scFv мышиной последовательности против FAP соединен с C-концом.
T1.28m (seq303) представляет собой димер Fc-слитого белка, состоящий из последовательности IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, в котором scFv мышиной последовательности против FAP соединен с C-концом.
[seq18] anti-mu FAP HC mu IgG2a Fc knob DANG
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLWCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq19] anti-mu FAP LC
QIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIKRADAAPTVSIFPPSSEQLTSGGASVVCFLNNFYPKDINVKWK
IDGSERQNGVLNSWTDQDSKDSTYSMSSTLTLTKDEYERHNSYTCEATHKTSTSPIVKSFNRNEC
[seq20] mu scIL-12-mu IgG2a Fc hole DANG
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRKKEKMKETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq21] mu scIL-12 mut1-mu IgG2a Fc hole DANG
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRAKEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq22] mu scIL-12 mut2-mu IgG2a Fc hole DANG
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq23] (anti-mu FAP VH)2, mu IgG2a Fc knob DANG
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLWCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq24] (anti-mu FAP VL)2
QIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIKGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIKRADAAPTVSIFPPSSEQLTSGGASVVCFLNNFYPKDINVKWKIDGSERQNGVLNSWTDQDSKDSTYSMSSTLTLTKDEYERHNSYTCEATHKTSTSPIVKSFNRNEC
[seq25] anti-mu FAP HC mu IgG2a Fc knob DANG-anti-mu FAP scFv
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLWCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGKGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
[seq26] anti-mu FAP LC-anti-mu FAP scFv
QIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIKRADAAPTVSIFPPSSEQLTSGGASVVCFLNNFYPKDINVKWKIDGSERQNGVLNSWTDQDSKDSTYSMSSTLTLTKDEYERHNSYTCEATHKTSTSPIVKSFNRNECGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
[seq27] anti-mu FAP HC mu IgG2a Fc hole DANG-mu scIL-12
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSMWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRKKEKMKETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSA
[seq28] anti-mu FAP HC mu IgG2a Fc hole DANG-mu scIL-12 mut2
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSMWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSA
[seq29] mu IgG2a Fc hole DANG
EPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq30] mu IgG2a Fc knob DANG
EPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLWCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq31] anti-mu FAP HC mu IgG2a Fc DANG
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq32] mu scIL-12 mut2-mu IgG2a Fc DANG
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq33] anti-mu CD20 HC mu IgG2a Fc knob DANG
QVQLQQPGAELVRPGTSVKLSCKASGYTFTSYWMHWIKQRPGQGLEWIGVIDPSDNYTKYNQKFKGKATLTVDTSSSTAYMQLSSLTSEDSAVYFCAREGYYGSSPWFAYWGQGTLVTVSSAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLWCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq34] anti-mu CD20 LC
QIVMSQSPAILSASPGEKVTMTCRARSSVSYIHWYQQKPGSSPKPWIYATSNLASGVPGRFSGSGSGTSYSLTITRVEAEDAATYYCQQWSSKPPTFGGGTKLEIKRTDAAPTVSIFPPSSEQLTSGGASVVCFLNNFYPKDINVKWKIDGSERQNGVLNSWTDQDSKDSTYSMSSTLTLTKDEYERHNSYTCEATHKTSTSPIVKSFNRNEC
[seq35] mu IgG2a Fc DANG
EPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGK
[seq298] mu scIL-12-mu IgG2a Fc hole DANG-anti-mu FAP scFv
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRKKEKMKETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
[seq299] mu scIL-12 mut2-mu IgG2a Fc hole DANG-anti-mu FAP scFv
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLSCAVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMVSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
[seq300] anti-mu FAP HC mu IgG2a Fc DANG-mu scIL-12
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSMWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRKKEKMKETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSA
[seq301] anti-mu FAP HC mu IgG2a Fc DANG-mu scIL-12 mut2
QVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAAKTTAPSVYPLAPVCGDTTGSSVTLGCLVKGYFPEPVTLTWNSGSLSSGVHTFPAVLQSDLYTLSSSVTVTSSTWPSQSITCNVAHPASSTKVDKKIEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGGSGGGGSGGGGSMWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSA
[seq302] mu scIL-12-mu IgG2a Fc DANG-anti-mu FAP scFv
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQRKKEKMKETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
[seq303] mu scIL-12 mut2-mu IgG2a Fc DANG-anti-mu FAP scFv
MWELEKDVYVVEVDWTPDAPGETVNLTCDTPEEDDITWTSDQRHGVIGSGKTLTITVKEFLDAGQYTCHKGGETLSHSHLLLHKKENGIWSTEILKNFKNKTFLKCEAPNYSGRFTCSWLVQRNMDLKFNIKSSSSSPDSRAVTCGMASLSAEKVTLDQRDYEKYSVSCQEDVTCPTAEETLPIELALEARQQNKYENYSTSFFIRDIIKPDPPKNLQMKPLKNSQVEVSWEYPDSWSTPHSYFSLKFFVRIQAAAEKMAETEEGCNQKGAFLVEKTSTEVQCKGGNVCVQAQDRYYNSSCSKWACVPCRVRSGGGGSGGGGSGGGGSRVIPVSGPARCLSQSRNLLKTTDDMVKTAREKLKHYSCTAEDIDHEDITRDQTSTLKTCLPLELHKNESCLATRETSSTTRGSCLPPQKTSLMMTLCLGSIYEDLKMYQTEFQAINAALQNHNHQQIILDKGMLVAIDELMQSLNHNGETLRQKPPVGEADPYRVKMKLCILLHAFSTRVVTINRVMGYLSSAGGGGSGGGGSEPRGPTIKPCPPCKCPAPNLLGGPSVFIFPPKIKDVLMISLSPIVTCVVVAVSEDDPDVQISWFVNNVEVHTAQTQTHREDYGSTLRVVSALPIQHQDWMSGKEFKCKVNNKDLPAPIERTISKPKGSVRAPQVYVLPPPEEEMTKKQVTLTCMVTDFMPEDIYVEWTNNGKTELNYKNTEPVLDSDGSYFMYSKLRVEKKNWVERNSYSCSVVHEGLHNHHTTKSFSRTPGGGGSGGGGSGGGGSQVQLQQSGAELARPGASVNLSCKASGYTFTNNGINWLKQRTGQGLEWIGEIYPRSTNTLYNEKFKGKATLTADRSSNTAYMELRSLTSEDSAVYFCARTLTAPFAFWGQGTLVTVSAGGGGSGGGGSGGGGSGGGGSQIVLTQSPAIMSASPGEKVTMTCSASSGVNFMHWYQQKSGTSPKRWIFDTSKLASGVPARFSGSGSGTSYSLTISSMEAEDAATYYCQQWSFNPPTFGGGTKLEIK
Пример производства 1. Производство слитых белков
Реагенты и оборудование описаны в Таблицах 3 и 4 ниже.
Синтезированный фрагмент ДНК амплифицировали с помощью ПЦР и очищали ПЦР-продукт из геля. Вектор pTT5 расщепляли рестриктазами EcoRI и BamHI, после чего очищали из геля. Каждый ПЦР-продукт и линейный вектор лигировали с использованием набора In-Fusion. Полученным вектором трансформировали компетентные клетки ECOS101 DH5α и культивировали клетки на чашках с 2xYT агаром, содержащим 100 мкг/мл ампициллина. Все процессы манипуляций выполняли в соответствии со стандартными протоколами трансформации. Положительные рекомбинанты идентифицировали с помощью ПЦР колоний и проверку последовательности рекомбинантной плазмиде проводили с помощью секвенирования. Отбирали одну колонию и инокулировали посевную культуру в 5 мл среды 2xYT, содержащей 100 мкг/мл ампициллина. Ее культивировали со встряхиванием при 37°C в течение 8 часов.
После этого посевную культуру разводили в 200 мл селективной среды 2xYT в соотношении 1:1000. Ее культивировали со встряхиванием при 37°C в течение 16 часов. Бактериальные клетки собирали с помощью центрифугирования при 4°C, 4700 об/мин в течение 10 минут. Бактериальный осадок ресуспендировали в 12 мл буфера RES-EF. После этого добавляли 12 мл буфера LYS-EF и энергично переворачивали закрытую пробирку для тщательного перемешивания, а затем инкубировали в течение 5 минут при комнатной температуре. К лизату добавляли 12 мл буфера NEU-EF и энергично переворачивали для тщательного и быстрого перемешивания.
Перед нанесением лизата на фильтр колонки NucleoBond® Xtra гомогенную суспензию осадка приготавливали путем переворачивания пробирки с лизатом 3 раза, чтобы предотвратить забивание фильтра. После этого фильтр колонки NucleoBond® Xtra и колонку NucleoBond® Xtra промывали 10 мл буфера FIL-EF для промывки фильтра. Фильтр колонки NucleoBond® Xtra извлекали или удаляли путем переворачивания колонки. Колонку NucleoBond® Xtra промывали 90 мл промывочного буфера ENDO.
Колонку NucleoBond® Xtra промывали 45 мл промывочного буфера WASH-EF. Плазмидную ДНК элюировали 15 мл элюирующего буфера ELU. Элюат собирали в центрифужную пробирку объемом 50 мл. Добавляли 10,5 мл изопропанола при комнатной температуре для осаждения элюированной плазмидной ДНК. После встряхивания на вортексе смесь оставляли на 2 минуты.
После этого к осадку добавляли 5 мл 70% этанола. Этанол тщательно и полностью удаляли из пробирки с помощью наконечника пипетки. Осадок сушили при комнатной температуре (20°C). После этого осадок ДНК растворяли в 1000 мкл H2O.
Пример производства 2. Трансфекция клеток и экспрессия белка
Пример производства 2.1. Трансфекция клеток
Используемые материалы и реагенты описаны в Таблице 5 ниже.
Штамм 293F для посева, содержащий полную среду, выдерживали в шейкере-инкубаторе при 130 об/мин, 37°C и 8% CO2. Его культивировали при плотности 0,3-0,4×106 клеток/мл и меняли среду каждые 2-3 дня. За двадцать четыре часа до трансфекции подготавливали новый пассаж клеток 293F при плотности 2,6×106 клеток/мл. Подготовленные клетки культивировали в шейкере-инкубаторе при 130 об/мин, 37°C и 8% CO2. В день трансфекции плотность клеток доводили до плотности 5,0×106 клеток/мл свежей средой. Эту операцию производили в общем объеме 1 л в качалочной колбе объемом 3 л. По 0,4 мг НС и по 0,6 мг LC плазмиды разводили в 50 мл OPTI MEM I и фильтровали через фильтр 0,22 мкм. После этого 2 мг ПЭИ разбавляли в 50 мл OPTI MEM I для приготовления реагента для трансфекции.
Разбавленный ПЭИ добавляли к смеси ДНК и сразу перемешивали. После этого смесь культивировали в течение 15 минут при комнатной температуре. Смесь ДНК-ПЭИ добавляли к клеткам 293F, приготовленным при плотности 2,6×106 клеток/мл. После этого клетки непрерывно культивировали в течение 24 часов в шейкере-инкубаторе при 130 об/мин, 37°C и 8% CO2. Через двадцать четыре часа после трансфекции к 1/20 части культурального раствора добавляли 10% пептона до конечной концентрации 0,5%. После этого клетки непрерывно культивировали в шейкере-инкубаторе при 130 об/мин, 37°C и 8% CO2. Плотность/жизнеспособность клеток измеряли и регистрировали ежедневно в течение 2-5 дней после трансфекции. Клетки собирали для очистки через 7 дней после трансфекции, или когда жизнеспособность клеток составляла меньше 70%.
Пример производства 2.2. Очистка белка
Реагенты, состав буферных растворов, а также оборудование, используемое для очистки белка, описаны в Таблицах 6-8 ниже.
Белки очищали с использованием колонки Mabselect sure. В частности, супернатант собирали центрифугированием при 2000×g, 4°C в течение 20 минут. После этого супернатант фильтровали на фильтре Sartopore 2. На колонку MabSelect Sure объемом 5 мл, уравновешенную Буфером A, наносили осветленный супернатант. После этого колонку промывали Буфером A, пока оптическая плотность А280 не достигала базовой линии. Колонку промывали 10 колоночными объемами (КО) буфера B. Колонку промывали 10 КО Буфера A. Связавшиеся белки элюировали 6 КО Буфера C и добавляли 1/6 объема Буфера D для нейтрализации элюированного вещества. Проводили анализы с помощью электрофореза в ДСН-ПААГ и эВЭЖХ. После этого белки очищали с использованием HIC колонки. Затем белки подвергали диализу против Буфера E при 4°C в течение ночи. На колонку HIC, уравновешенную Буфером E, наносили супернатант. После этого колонку промывали Буфером E, пока оптическая плотность A280 не достигала базовой линии. Связавшиеся белки элюировали в градиенте элюирования (10 КО Буфера F 0%-40%). Связавшиеся белки элюировали в 2 КО 100% Буфера F. Выполняли анализ методом электрофореза в ДСН-ПААГ.
Очищенные белки объединяли в пулы, и затем белки подвергали диализу против конечного буфера при 4°C в течение ночи. После этого проводили анализы с помощью электрофореза в ДСН-ПААГ и эВЭЖХ.
В результате, как показано на ФИГ. 1-6, было обнаружено, что человеческие белки и мышиные белки согласно одному варианту осуществления были очищены.
Пример производства 3. Улучшение производства биспецифичного антитела
Пример производства 3.1. Идентификация улучшения при производстве слитого белка, включающего IL-12 человека
В Таблице 9 ниже представлены изменения продукции человеческого биспецифичного антитела против FAP/IL-12, соответствующего мутации IL-12 человека. Круглые скобки указывают на масштаб производства белка, и единицей измерения являются л. Число перед круглыми скобками указывает продукцию на литр, полученную при делении количества очищенного белка на масштаб производства.
(масштаб производства, л)
Как показано в Таблице 9 выше, при увеличении числа мутаций аминокислот, участвующих в связывании гепарина в области р40 (бета) IL-12 человека, количество белков, очищенных на колонке с белком A (колонка MabSelect Sure), возрастало. Было обнаружено, что биспецифичное антитело Т1.02, в котором лизин (K) в 280-м и 285-м аминокислотных положениях был заменен аланином (A), демонстрирует улучшенную продукцию по сравнению с Т1.01. Было обнаружено, что биспецифичное антитело Т1.03, в котором лизин (K) в 280-м, 282-м, 285-м и 286-м аминокислотных положениях был заменен аланином (A), демонстрирует улучшенную продукцию приблизительно в 2,5 раза по сравнению с Т1.01.
Пример производства 3.2. Идентификация улучшения продукции слитого белка, содержащего IL-12 мыши
В Таблице 10 ниже показаны изменения продукции мышиного биспецифичного антитела против FAP/IL-12, соответствующего мутации IL-12 мыши.
(масштаб производства, л)
Как показано в Таблице 10 выше, по мере увеличения количества мутаций аминокислот, участвующих в связывании гепарина в области p40 (бета) IL-12 мыши, количество белков, очищенных на колонке с белком A (колонка MabSelect Sure), возрастало.
В каждой таблице количество белка после пропускания через колонку с белком A сравнивали путем деления общей продукции белка на масштаб производства. Было обнаружено, что биспецифичное антитело T1.02m, в котором лизин (K) в 277-м и 282-м аминокислотных положениях был заменен аланином (A), и биспецифичное антитело T1.03m, в котором аргинин (R) в 276-м аминокислотном положении был заменен аланином (A), и лизин (K) в 277-м, 278-м и 282-м аминокислотных положениях был заменен аланином (A), демонстрировало постепенное улучшение продукции белка по сравнению с T1.01m и T1.02m. Кроме того, было обнаружено, что продукция T1.03m с использованием линии клеток CHO была улучшена приблизительно в 13 раз по сравнению с продукцией при использовании линии клеток HEK 293.
Пример прозводства 4. Линия клеток и культура линии клеток
Линия клеток HEK-Blue IL-12, трансформированная геном рецептора IL-12 и STAT4-индуцируемым репортерным геном SEAP в клетки HEK293, которые представляют собой эмбриональные фибробласты почек человека, была получена от Invivogen (San Diego, USA). Клетки HEK-Blue IL-12 поддерживали в среде DMEM (GIBCO), содержащей 10% FBS (GIBCO), 100 мкг/мл Нормоцина и 1XHEK-Blue selection.
Клеточная линия эмбриональных фибробластов почек человека HEK293, клеточная линия рака толстой и прямой кишки мыши CT26-WT, клеточная линия меланомы мыши B16F10 и клеточная линия фибробластов мыши NIH3T3 были получены из ATCC (Американской коллекции типовых культур, Manassas, VA, USA). Клетки HEK293, клетки B16F10 и клетки NIH3T3 поддерживали в среде DMEM (GIBCO), содержащей 10% FBS (GIBCO). Линию клеток (HEK293-hFAP) с оверэкспрессией человеческого FAP (белка активации фибробластов альфа) в клетках HEK293 получали с использованием лентивируса, способного доставлять ген FAP человека. Клетки HEK293-hFAP поддерживали в среде DMEM (GIBCO), содержащей 10% FBS (GIBCO) и 5 мкг/мл пуромицина.
Линии клеток (CT26-mFAP, B16F10-mFAP и NIH3T3-mFAP) с оверэкспрессией мышиного FAP (белка активации фибробластов альфа) в клетках CT26-WT, клетках B16F10 и клетках NIH3T3 получали с использованием лентивируса, способного доставлять ген FAP мыши. Клетки CT26-mFAP поддерживали в среде RPMI-1640 (GIBCO), содержащей 10% FBS (GIBCO) и 10 мкг/мл пуромицина. Клетки B16F10-mFAP поддерживали в среде DMEM (GIBCO), содержащей 10% FBS (GIBCO) и 10 мкг/мл пуромицина. Клетки NIH3T3-mFAP поддерживали в среде DMEM (GIBCO), содержащей 10% FBS (GIBCO) и 5 мкг/мл пуромицина.
Пример прозводства 5. Выделение и активация иммунных клеток человека
Контейнер для крови был получен из Красного Креста Республики Корея с одобрения Наблюдательного совета организации (IRB), и мононуклеарные клетки периферической крови (МКПК) были выделены и заморожены. Размороженные МКПК подвергали методу положительной селекции, и человеческие NK-клетки выделяли с использованием набора Easy sep (Stem cell, Vancouver, BC, CA). Выделенные NK-клетки активировали и поддерживали в среде RPMI-1640 (GIBCO) с 10% FBS, содержащей 50 МЕ/мл рекомбинантного человеческого IL-2 (rhIL-2, R&D systems, Minnesota, USA).
Размороженные МКПК подвергали методу отрицательной селекции, и человеческие T-клетки выделяли с использованием набора Easy sep (Stem cell). Человеческие T-клетки культивировали на планшете, покрытом 1 мкг/мл антитела к CD3 (OKT3, Invitrogen), и активировали в течение 72 часов. Человеческие T-клетки поддерживали в среде RPMI-1640 (GIBCO), содержащей 10% FBS (GIBCO).
Пример 1. Определение аффинности связывания слитого белка
Пример 1.1. Идентификация связывания слитого белка с рекомбинантным человеческим FAP
Связывание T1.01, T1.02 и T1.03 с рекомбинантным человеческим FAP идентифицировали с помощью поверхностного плазмонного резонанса (SPR).
В частности, поверхность чипа CM5 активировали смесью 1:1 50 нМ NHS (N-гидроксисукцинимида) и 200 нМ EDC (1-этил-3-(3-диметиламинопропил)карбодиимида) и иммобилизовали 25 мкг/мл антитела против человеческого IgG (Fc) в течение 400 секунд со скоростью 10 мкл/мин. Оставшиеся активные сложноэфирные группы блокировали 1М этаноламином. Т1.01, Т1.02 и Т1.03 разбавляли до 2 мкг/мл и подвергали реакции на чипе СМ5 с иммобилизованным антителом против человеческого IgG (Fc). Рекомбинантный FAP человека разбавляли до 200 нМ в буферном растворе 1×HBS-EP+ и разбавляли методом серийных разведений. Разбавленный рекомбинантный человеческий FAP подвергали реакции со скоростью 30 мкл/мин. Время ассоциации и диссоциации составляло 180 секунд и 400 секунд соответственно. После диссоциации проводили стабилизацию в течение 60 секунд, а затем проводили регенерацию в течение 30 секунд 10 мМ раствором глицина, рН 1,5, со скоростью 30 мкл/мин.
В результате, как показано на ФИГ. 7 и 8, было обнаружено, что T1.01, T1.02 и T1.03 могут специфично связываться с рекомбинантным человеческим FAP.
Связывание T1.04, T1.05, T1.06, T1.07, T1.08, T1.09, T1.10 и T1.11 с рекомбинантным человеческим FAP идентифицировали методом поверхностного плазмонного резонанса (SPR). Поверхность чипа СМ5 активировали смесью 1:1 50 нМ NHS (N-гидроксисукцинимида) и 200 нМ EDC (1-этил-3-(3-диметиламинопропил)карбодиимида) и иммобилизовали 25 мкг/мл антитела против человеческого IgG (Fc) в течение 400 секунд со скоростью 10 мкл/мин. Оставшиеся активные сложноэфирные группы блокировали 1М этаноламином.
В частности, человеческие белки T1.04, T1.05, T1.06, T1.07, T1.08, T1.09, T1.10 и T1.11 разбавляли до 1 мкг/мл, 1 мкг/мл, 1 мкг /мл, 1 мкг/мл, 0,5 мкг/мл, 0,5 мкг/мл, 0,5 мкг/мл и 1 мкг/мл, соответственно, и подвергали реакции на чипе CM5 с иммобилизованным антителом против человеческого IgG (Fc). Рекомбинантный человеческий FAP разбавляли до 25 нМ или 50 нМ в буферном растворе 1xHBS-EP+ и разбавляли методом серийных разведений. Разбавленный рекомбинантный человеческий FAP подвергали реакции со скоростью 30 мкл/мин. Время ассоциации и диссоциации составляло 180 секунд и 400 секунд соответственно. После диссоциации проводили стабилизацию в течение 60 секунд, а затем проводили регенерацию в течение 30 секунд 10 мМ раствором глицина, рН 1,5, со скоростью 30 мкл/мин.
В результате, как показано в Таблице 11 и на ФИГ. 9 и 10, было обнаружено, что T1.04, T1.05, T1.06 и T1.07 могут связываться с рекомбинантным человеческим FAP со специфичным таргетингом FAP. Кроме того, как показано в Таблице 12 и на ФИГ. 11 и 12, было обнаружено, что T1.08, T1.09, T1.10 и T1.11 могут связываться с рекомбинантным человеческим FAP со специфичным таргетингом FAP.
Пример 1.2. Идентификация связывания мышиного белка с рекомбинантным мышиным FAP
Связывание T1.01m, T1.02m и T1.03m с рекомбинантным мышиным FAP идентифицировали с помощью поверхностного плазмонного резонанса (SPR).
Поверхность чипа СМ5 активировали смесью 1:1 50 нМ NHS (N-гидроксисукцинимида) и 200 нМ EDC (1-этил-3-(3-диметиламинопропил)карбодиимида) и иммобилизовали 25 мкг/мл антитела против мышиного IgG (Fc) в течение 400 секунд со скоростью 10 мкл/мин. Оставшиеся активные сложноэфирные группы блокировали 1М этаноламином. T1.01m, T1.02m и T1.03m разбавляли до 2 мкг/мл и подвергали реакции на чипе CM5 с иммобилизованным антителом против мышиного IgG (Fc). Рекомбинантный мышиный FAP разводили до 200 нМ в буферном растворе 1xHBS-EP+ и разбавляли методом серийных разведений. Разбавленный рекомбинантный мышиный FAP подвергали реакции со скоростью 30 мкл/мин. Время ассоциации и диссоциации составляло 180 секунд и 400 секунд соответственно. После диссоциации проводили стабилизацию в течение 60 секунд, а затем проводили регенерацию в течение 30 секунд 10 мМ раствором глицина, рН 1,5, со скоростью 30 мкл/мин.
В результате, как показано на ФИГ. 13 и 14, было обнаружено, что T1.01m, T1.02m и T1.03m могут связываться с рекомбинантным мышиным FAP со специфичным таргетингом FAP.
Пример 1.3. Идентификация связывания с FAP-экспрессирующими клетками
Определяли степень связывания T1.12, T1.01, T1.02 и T1.03 с клетками HEK293 и HEK293-hFAP.
В частности, линию клеток подготавливали путем суспендирования в буферном растворе FACS при плотности 1×105 клеток/100 мкл и обрабатывали 1 мкг каждого из Т1.12, Т1.01, Т1.02 и Т1.03. Клетки два раза промывали буферным раствором FACS. Клетки окрашивали антителом против человеческого IgG (Biolegend). Отрицательный контроль окрашивали только антителом против человеческого IgG (Biolegend). Уровни экспрессии окрашенных клеток измеряли с помощью BD LSR и анализировали с использованием программы FlowJo.
В результате, как показано на ФИГ. 15, было обнаружено, что Т1.12, Т1.01, Т1.02 и Т1.03 связываются с линией клеток человека, экспрессирующих FAP, на 99% или больше. Эти результаты показывают, что слитый белок согласно одному варианту осуществления может связываться с линией клеток человека, экспрессирующих FAP, со специфичным таргетингом FAP.
Кроме того, определяли степень связывания T1.12m, T1.01m, T1.02m и T1.03m с клетками B16F10 и B16F10-mFAP.
В частности, линию клеток подготавливали путем суспендирования в буферном растворе FACS при плотности 1×105 клеток/100 мкл и обрабатывали 1 мкг каждого T1.12m, T1.01m, T1.02m и T1.03m. Клетки два раза промывали буферным раствором FACS. Клетки окрашивали антителом против мышиного IgG2a (Biolegend). Отрицательный контроль окрашивали только антителом против мышиного IgG2a (Biolegend). Скорость экспрессии окрашенных клеток измеряли с помощью BD LSR и анализировали с использованием программы FlowJo.
В результате, как показано на ФИГ. 16, было обнаружено, что T1.12m, T1.01m, T1.02m и T1.03m связываются с линией клеток, экспрессирующих FAP, на 99% или больше. Эти результаты показывают, что слитый белок согласно одному варианту осуществления может связываться с линией клеток мыши, экспрессирующих FAP, со специфичным таргетингом FAP.
Пример 1.4. Идентификация связывания слитого белка с рекомбинантным человеческим рецептором IL-12
С учетом того, что IL-12 в слитом белке должен связываться с рецептором IL-12 для своего действия, было обнаружено, что T1.01, T1.02, T1.03 и T1.12 связываются с рекомбинантным рецептором IL-12 человека.
T1.01, T1.02 и T1.03 иммобилизовали на планшете и связывали рекомбинантный белок рецептора IL-12 человека, конъюгированный с пероксидазой хрена (HRP). В частности, выполняли следующие этапы:
(i) Т1.01, Т1.02, Т1.03 и Т1.12 суспендировали в концентрации 5 мкг/мл и разбавляли методом серийных разведений. Разбавленные Т1.01, Т1.02, Т1.03 и Т1.12 делили на аликвоты в 96-луночном иммунном планшете и обрабатывали в течение 24 часов.
(ii) Лунки промывали промывочным раствором, а затем проводили блокирование в течение 1 часа с использованием 1% раствора BSA (бычьего сывороточного альбумина, Sigma).
(iii) Лунки промывали промывочным раствором, а затем обрабатывали 1 нМ конъюгата рецептора IL-12 бета-1-биотина (IL-12Rβ1-биотин; Acrobiosystems, Newark, USA) в течение 2 часов.
(iv) Лунки промывали промывочным раствором, а затем обрабатывали стрептавидином-HRP в течение 20 минут.
(v) Лунки промывали промывочным раствором, а затем обрабатывали раствором субстрата в течение 20 минут.
(vi) Лунки обрабатывали стоп-раствором и измеряли оптическую плотность при 450 нм.
В результате, как показано на ФИГ. 17, было обнаружено, что T1.01, T1.02 и T1.03 связываются с рекомбинантным белком рецептора IL-12 человека зависимым от концентрации образом. Т1.12 использовали в качестве контроля.
Пример 2. Определение способности слитого белка индуцировать сигнализацию
Пример 2.1. Идентификация сигнальной способности IL-12-распознающих клеток.
С учетом того, что IL-12, как известно, инициирует сигнализацию при индукции фосфорилирования STAT4 (сигнальный трансдуктор и активатор транскрипции 4), медиатора сигнализации, когда IL-12 связывается с рецептором IL-12, оценивали сигнальную способность слитого белка согласно одному варианту осуществления в IL-12-распознающих клетках, экспрессирующих рецептор IL-12.
В частности, линию клеток HEK-Blue IL-12, которые представляют собой IL-12-распознающие клетки, разбавляли до плотности 2,8×105 клеток/мл и вносили по 180 мкл/лунка. Рекомбинантный человеческий IL-12, T1.01m, T1.02m, T1.03m и T1.12m суспендировали при 4 нМ и разбавляли методом серийных разведений. Клетки HEK-Blue IL-12 обрабатывали разведенным рекомбинантным человеческим IL-12, T1.01m, T1.02m, T1.03m и T1.12m. Через 24 часа обработки супернатант клеток собирали и смешивали с раствором QUANTI-Blue (Invivogen) в 96-луночном планшете. Уровень экспрессии репортера измеряли при 620 нм с помощью спектрофотометра (Thermo Fisher).
В результате, как показано на ФИГ. 18, по оптической плотности при 620 нм было определено, что в случае групп обработки IL-12, T1.01m, T1.02m и T1.03m происходило распознавание IL-12, а STAT4 экспрессировал репортерный ген при индукции фосфорилирования. С другой стороны, было установлено, что контроль, T1.12m, не распознавал IL-12 при обработке T1.12m клеток, распознающих IL-12. Эти результаты показывают, что слитый белок согласно одному варианту осуществления специфично связывается с рецептором IL-12, индуцируя сигнализацию.
Пример 2.2. Идентификация сигнальной способности T-клеток человека
Для определения, связывается ли IL-12 с рецептором IL-12 на человечских T-клетках, и инициирует ли IL-12 сигнализацию при индукции фосфорилирования сигнального медиатора STAT4, T-клетки человека, активированные антителом к CD3 (OKT3, Invitrogen), анализировали с использованием набора для анализа AlphaLISA SureFire Ultra p-STAT4 (Tyr693) (PerkinElmer, Massachusetts, USA).
В частности, человеческие белки IL-12, T1.01, T1.02, T1.03 и T1.12 суспендировали в концентрации 100 нг/мл и разбавляли методом серийных разведений. Человеческие T-клетки, активированные антителом к CD3 (OKT3, Invitrogen), обрабатывали разведенным рекомбинантным человеческим IL-12, T1.01, T1.02, T1.03 и T1.12. Через 2 часа обработки клетки лизировали и обрабатывали реагентом (PerkinElmer), который обнаруживает p-STAT4 (фосфорилированный STAT4). p-STAT4 детектировали при длине волны возбуждения 680 нм и длине волны испускания 615 нм с помощью спектрофотометра.
В результате, как показано на ФИГ. 19, было установлено, что полумаксимальная эффективная концентрация (EC50) в группе обработки рекомбинантным человеческим IL-12 составляла 8,945 пМ; EC50 в группе обработки T1.01 составляла 14,48 пМ; EC50 в группе обработки T1.02 составляла 56,51 пМ; и EC50 в группе обработки T1.03 составляла 147,2 пМ. С другой стороны, фосфорилированный STAT4 не был обнаружен в группе обработки T1.12, которая является контролем.
Эти результаты показывают, что мутация IL-12 ослабляет сигнальную способность T-клеток.
Пример 2.3. Идентификация изменения сигнальной способности слитого белка под действием низкомолекулярного гепарина в T-клетках человека
Следующим этапом определение усиления сигнальной способности слитого белка с мутацией IL-12 (IL-12 mut1) под действием низкомолекулярного гепарина проводили с использованием T-клеток человека, активированных антителом к CD3 (OKT3, Invitrogen), и набора для анализа AlphaLISA SureFire Ultra p-STAT4 (Tyr693).
В частности, при наблюдении, ослабляется ли индукция фосфорилирования STAT4, сигнального медиатора, при связывании аттенуированного IL-12 mut2 с рецептором IL-12 T-клеток человека, определяли сигнальную способность в зависимости от присутствия или отсутствия низкомолекулярного гепарина (НМГ) в человеческих T-клетках.
В частности, рекомбинантные человеческие IL-12, T1.01, T1.02 и T1.03 суспендировали в концентрации 100 нг/мл и разбавляли методом серийных разведений. Активированные человеческие T-клетки обрабатывали разбавленным рекомбинантным человеческим IL-12, T1.01, T1.02 и T1.03 в комбинации с низкомолекулярным гепарином. Через 2 часа обработки клетки лизировали и обрабатывали реагентом для обнаружения p-STAT4 (PerkinElmer). p-STAT4 обнаруживали при длине волны возбуждения 680 нм и длине волны испускания 615 нм с помощью спектрофотометра.
В результате, как показано на ФИГ. 20, полумаксимальная эффективная концентрация (EC50) в группе обработки T1.01 и низкомолекулярным гепарином была увеличена в 9,4 раза по сравнению с группой обработки T1.01, полумаксимальная эффективная концентрация (EC50) в группе обработки Т1,02 и низкомолекулярным гепарином увеличилась в 5,5 раза по сравнению с группой обработки Т1,02, и полумаксимальная эффективная концентрация (EC50) в группе обработки Т1,03 и низкомолекулярным гепарином увеличилась в 4 раза по сравнению с группой обработки Т1,03.
Эти результаты показывают, что при добавлении мутации IL-12 (IL-12 mut2) к существующей мутации IL-12 (IL-12 mut1) степень усиления сигнальной способности при добавлении низкомолекулярного гепарина снижалась, и при этом IL-12 был эффективно аттенуирован.
Пример 3. Идентификация способности гибридного белка вызывать секрецию цитокинов
Пример 3.1. Иммуноферментный анализ для измерения цитокинов
Для измерения цитокинов проводили твердофазный иммуноферментный анализ (ИФА, R&D systems) супернатанта, хранившегося при температуре -20°C,включавший следующие этапы:
(i) Антитело для захвата разводили в соответствии с Сертификатом анализа (CoA) и наносили на 96-луночный планшет на 24 часа.
(ii) Лунки промывали промывочным раствором, а затем проводили блокирование в течение 1 часа с использованием 1% раствора BSA (бычьего сывороточного альбумина, Sigma).
(iii) Лунки промывали промывочным раствором, а затем обрабатывали образцы в течение 2 часов.
(iv) Лунки промывали промывочным раствором, затем детектирующее антитело разводили в соответствии с Сертификатом анализа и наносили аликвотами в лунки, после чего лунки обрабатывали им в течение 2 часов.
(v) Лунки промывали промывочным раствором, а затем обрабатывали стрептавидином-HRP в течение 20 минут.
(vi) Лунки промывали промывочным раствором, а затем обрабатывали раствором субстрата в течение 20 минут.
(vii) Лунки обрабатывали стоп-раствором и измеряли оптическую плотность при 450 нм.
Пример 3.2. Определение способности вызывать секрецию цитокинов в T-клетках человека
С учетом того, что секреция IFN-γ (гамма-интерферона), которая имеет решающее значение при иммунном ответе, возникает при обработке T-клеток человека IL-12, способность к секреции IFN-γ оценивали при обработке T-клеток человека рекомбинантным человеческим IL-12, Т1.12, Т1.01, Т1.02 и Т1.03.
В частности, T-клетки человека, активированные антителом к CD3 (OKT3, Invitrogen), разбавляли до плотности 5×105 клеток/мл и наносили в 96-луночный планшет по 200 мкл/лунка. Рекомбинантный человеческий IL-12, T1.12, T1.01, T1.02 и T1.03 разбавляли до 10 нМ и наносили по 20 мкл/лунка. После 48 часов обработки супернатант клеток собирали и хранили образцы при -80°C.
В результате, как показано на ФИГ. 21, было обнаружено, что образец, обработанный рекомбинантным человеческим IL-12, содержал в среднем 1640 пг/мл IFN-γ; образец, обработанный T1.01, содержал в среднем 1115 пг/мл IFN-γ; образец, обработанный T1.02, содержал в среднем 845 пг/мл IFN-γ; и образец, обработанный T1.03, содержал в среднем 607 пг/мл IFN-γ. С другой стороны, было обнаружено, что образец, обработанный T1.12 в качестве контроля, не содержал IFN-γ.
Эти результаты показывают, что Т1.01, Т1.02 и Т1.03 действуют на T-клетки человека, вызывая секрецию IFN-γ.
Пример 3.3. Идентификация способности вызвать секрецию цитокинов в NK-клетках человека
С учетом того, что секреция IFN-γ (интерферона гамма), которая имеет решающее значение при иммунном ответе, происходит при обработке NK-клеток человека IL-12, авторы настоящего изобретения оценивали способность к секреции IFN-γ при обработке активированных рекомбинантным IL-2 (R&D systems) NK-клеток человека рекомбинантным человеческим IL-12, T1.12, T1.01, T1.02 и T1.03.
В частности, человеческие NK-клетки, активированные рекомбинантным человеческим IL-2 (R&D Systems), разбавляли до 5×105 клеток/мл и наносили в 96-луночный планшет по 200 мкл/лунка. Рекомбинантный человеческий IL-12, T1.12, T1.01, T1.02 и T1.03 разбавляли до 10 нМ и наносили по 20 мкл/лунка. После 24 часов обработки супернатант клеток собирали и хранили образцы при -80°С.
В результате, как показано на ФИГ. 22, было обнаружено, что образец, обработанный рекомбинантным человеческим IL-12, содержал в среднем 180 пг/мл IFN-γ; образец, обработанный T1.01, содержал в среднем 205 пг/мл IFN-γ; образец, обработанный T1.02, содержал в среднем 133 пг/мл IFN-γ; и образец, обработанный T1.03, содержал в среднем 80 мкг/мл IFN-γ. С другой стороны, было обнаружено, что образец, обработанный T1.12 в качестве контроля, не содержал IFN-γ. Эти результаты показывают, что T1.01, T1.02 и T1.03 воздействуют на NK-клетки человека, вызывая секрецию IFN-γ.
Пример 4. Оценка противоопухолевой эффективности слитого белка в модели рака толстой и прямой кишки на животных
Пример 4.1. Оценка противоопухолевой эффективности в модели рака толстой и прямой кишки на животных при совместной инъекции FAP-экспрессирующих фибробластов
С учетом того, что слитый белок находится в форме двойного антитела, содержащего структуру последовательности против FAP и структуру последовательности IL-12, а FAP повышенно экспрессируется в фибробластах, присутствующих в микроокружении многих опухолей, после оверэкспрессии мышиного FAP в клетках NIH3T3, клеточной линии мышиных фибробластов, способность ингибировать рост опухоли оценивали в модели опухоли на животных при совместном введении 1:1 CT26, линии клеток рака толстой и прямой кишки мыши.
CT26, клеточную линию рака толстой и прямой кишки мыши, и NIH-3T3, клеточную линию мышиных фибробластов, использовали для получения модели FAP-экспрессирующей опухоли на животных. Затем получали NIH-3T3 в качестве линии FAP-экспрессирующих клеток.
В частности, мышиные клетки NIH-3T3 с оверэкспрессией FAP и клетки CT26 в культуре ресуспендировали в сбалансированном солевом растворе Хэнкса (HBSS, Gibco) в концентрации 1×106 клеток/50 мкл соответственно и смешивали клетки в соотношении 1:1, а затем по 100 мкл на каждую мышь трансплантировали в подкожную область правого бока 6-недельным мышам BALB/c при использовании шприца (25G) объемом 1 см3 с получением FAP-экспрессирующей модели с совместной инъекцией фибробластов на животных. Размер опухоли измеряли с помощью цифрового штангенциркуля, производя измерение по короткой оси и длинной оси опухоли, и размер опухоли измеряли два раза в неделю по формуле расчета (короткая ось, мм)2×(длинная ось, мм)×0,5.
Затем для оценки эффективности лекарственного средства, когда размер опухоли достигал 100 мм3, мышей рандомизировано распределяли по группам. Каждая экспериментальная группа состояла из 10 животных, и в качестве контроля по 100 мкл 50 мкг Т1.24m вводили внутрибрюшинно три раза с интервалом в 3 дня. В тестируемой группе по 100 мкл 10 мкг и 50 мкг T1.02m и 50 мкг T1.01m соответственно вводили внутрибрюшинно три раза с интервалом в 3 дня для оценки ингибирующей способности в отношении роста опухоли.
В результате, как показано на ФИГ. 23, при сравнении размера опухоли на 14-й день было обнаружено, что группы, которым вводили по 10 мкг и 50 мкг T1.02m, обладали превосходной способностью ингибировать рост опухоли на уровне 93,2% и 92,7% соответственно по сравнению с группой, которой вводили 50 мкг T1.24m в качестве контроля. Кроме того, было отмечено, что в группе, в которой вводили 50 мкг T1.01m, наблюдали ингибирование роста опухоли 91,9% по сравнению с группой, в которой вводили 50 мкг T1.24m в качестве контроля.
Кроме того, как показано на ФИГ. 24, на 24-й день после введения в группе, в которой вводили T1,01m и T1,02m, наблюдали субъектов с полным ответом по сравнению с контролем.
Эти результаты показывают, что слитый белок в соответствии с одним вариантом осуществления обладает превосходной противоопухолевой эффективностью в модели рака толстой и прямой кишки на животных.
Пример 4.2. Оценка противоопухолевой эффективности в FAP-экспрессирующей модели рака толстой и прямой кишки на животных
В случае рака толстой и прямой кишки, учитывая высокую экспрессию FAP в самих опухолевых клетках, для оценки противоопухолевого эффекта способность ингибировать рост опухоли оценивали в модели опухоли, в которой оверэкспрессию FAP мыши индуцировали в клетках CT26, т.е. линии клеток рака толстой и прямой кишки мыши.
Для получения модели FAP-экспрессирующей опухоли на мышах, оверэкспрессию FAP индуцировали в CT26, линии клеток рака толстой и прямой кишки мыши. В частности, клетки CT26 с оверэкспрессией FAP в культуре ресуспендировали в сбалансированном солевом растворе Хэнкса (HBSS, Gibco), а затем по 100 мкл 1×106 опухолевых клеток на каждую мышь трансплантировали в подкожную область с левой стороны спины 6-недельных мышей BALB/c при использовании шприца (25G) объемом 1 см3 с получением животной FAP-экспрессирующей модели рака толстой и прямой кишки на мышах. Размер опухоли измеряли с помощью цифрового штангенциркуля, производя измерение по короткой оси и длинной оси опухоли, и размер опухоли измеряли два раза в неделю по формуле расчета (короткая ось, мм)2×(длинная ось, мм)×0,5.
Затем для оценки эффективности лекарственного средства, когда размер опухоли достигал 100 мм3, мышей рандомизированно распределяли по группам. Каждая экспериментальная группа состояла из 8 животных, и в качестве контроля по 100 мкл 50 мкг Т1.24m вводили внутрибрюшинно четыре раза с интервалом в 3 дня. В тестируемой группе по 100 мкл 10 мкг и 100 мкг T1.01m и 2 мкг, 10 мкг и 100 мкг T1.02m соответственно вводили внутрибрюшинно четыре раза с интервалом в 3 дня для оценки ингибирующей способности в отношении роста опухоли.
В результате, как показано на ФИГ. 25, было обнаружено, что группа, в которой вводили 10 мкг и 100 мкг T1.01m, обладала высокой способностью ингибировать рост опухоли на 84,9% и 85,6% соответственно по сравнению с группой, в которой вводили 50 мкг T1.24m в качестве контроля. Кроме того, было отмечено, что группа, в которой вводили T1.02m, обладала высокой способностью ингибировать рост опухоли на 80,1%, 90,5% и 89,8%, соответственно, в зависимости от дозы по сравнению с группой, в которой вводили T1.24m в качестве контроля.
Кроме того, было установлено, что субъекты с полным ответом (CR) присутствовали в каждой группе введения на 30-й день после введения в сочетании с ингибированием роста опухоли, при этом во время исследования не наблюдали изменения массы тела, которое было связано с введением. Эти результаты показывают, что слитый белок согласно одному варианту осуществления обладает превосходной противоопухолевой эффективностью в модели рака толстой и прямой кишки на животных.
Пример 4.3. Оценка ингибирования роста рецидивирующей солидной злокачественной опухоли у мышей с полным ответом при воздействии слитого белка
Чтобы оценить, можно ли ингибировать рецидив опухоли путем индукции долговременного иммунного ответа после лечения слитым белком, повторное введение опухоли проводили у субъектов, у которых полный ответ был достигнут при введении T1.01m в модели опухоли с совместной инъекцией фибробластов NIH-3T3 и клеток CT26. Мышей BALB/c, ранее не подвергавшихся лечению, использовали в качестве контрольных мышей.
Клетки 4T1 вводили подкожно в левый бок, а клетки CT26 вводили подкожно в правый бок контрольным мышам и мышам, у которых полный ответ был достигнут при введении T1.01m, с получением модели рецидива опухоли.
В частности, в модели, в которой совместно вводили фибробласты NIH-3T3 с оверэкспрессией FAP и клетки CT26, модель рецидива опухоли индуцировали у мышей, у которых полный ответ был продемонстрирован при введении T1.01m. Клетки СТ26 и клетки 4Т1 суспендировали в сбалансированном солевом растворе Хенкса (HBSS, Gibco) в концентрации 1×106 клеток/100 мкл соответственно, и клетки СТ26 трансплантировали в подкожную область правого бока мышей при использовании шприца (25G) объемом 1 см3. Формирование и рост опухолей оценивали при подкожной трансплантации клеток 4T1 в левый бок тем же мышам.
В результате, как показано на ФИГ. 26 и 27, было обнаружено, что трансплантированная опухоль 4T1 и опухоль CT26 росли у контрольных мышей без анамнеза лечения, тогда как у мышей, у которых был достигнут полный ответ после введения T1.01m, опухоль 4T1 росла, но рост опухоли CT26 был подавлен. Эти результаты показывают, что слитый белок согласно одному варианту осуществления может ингибировать рецидив опухоли.
Пример 4.4. Оценка снижения активности, соответствующей аминокислотной мутации IL-12 слитого белка
Чтобы уменьшить токсичность in vivo из-за чрезмерной активации иммунной системы под действием IL-12, авторы настоящего изобретения использовали структуру последовательности IL-12, содержащую мутацию в аминокислотной последовательности, связывающейся с гепарином, чтобы вызвать снижение активности в результате блокирования связывания с рецептором IL-12, и это было идентифицировано посредством модели опухоли на животных.
Из антител против FAP, T1.02m и T1.03m, в которых были подвергнуты мутации аминокислоты, участвующие в связывании гепарина, сравнивали с T1.01m, а в качестве контроля использовали фосфатно-солевой буфер (PBS). К тому же, T1.02m содержит структуру последовательности IL-12 мыши, содержащую мутации (двух) аминокислот, участвующих в связывании гепарина, вместе со структурой последовательности против FAP. T1.03m представляет собой слитый белок, содержащий структуру последовательности IL-12, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, вместе со структурой последовательности против FAP.
Для оценки изменения активности IL-12 в зависимости от присутствия и степени аминокислотной мутации, мышиный рак толстой и прямой кишки CT26 с оверэкспрессией FAP получали путем ресуспендирования в PBS в концентрации 5×105 клеток/100 мкл, и способность ингибирования роста опухоли оценивали в модели опухоли на животных, полученной путем трансплантации клеток 5-недельным самкам мышей BALB/c.
В частности, когда размер опухоли в модели достигал 100 мм3, мышей рандомизированно распределяли по группам. Каждая экспериментальная группа состояла из 8 животных, и 100 мкл фосфатно-солевого буфера (PBS) вводили однократно путем инъекции в хвостовую вену в качестве контроля, и каждый из T1.01m, T1.02m и T1.03m вводили внутривенно однократно в дозе 10 мкг.
В результате, как показано на ФИГ. 28, было обнаружено, что все группы введения T1.01m, T1.02m и T1.03m обладали превосходной способностью ингибировать рост опухоли по сравнению с контролем через 15 дней после введения.
Кроме того, было обнаружено, что была снижена способность ингибировать рост опухоли в группе, в которой вводили T1.03m с IL-12, содержащим мутации (четырех) аминокислот, участвующих в связывании гепарина, вместе с мышиной последовательностью против FAP, в сравнении с группой, в которой вводили T1.01m. Эти результаты показывают, что активность IL-12 была снижена в группе, в которой вводили T1.03m, имеющий структуру последовательности IL-12 мыши, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, по сравнению с другими экспериментальными группами и контролем.
Пример 4.5. Оценка противоопухолевой эффективности при однократном введении слитого белка с аминокислотной мутацией IL-12
Для оценки противоопухолевого эффекта слитого белка, имеющего сниженную активность IL-12 из-за структуры последовательности, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, способность ингибировать рост опухоли оценивали в модели опухоли с трансплантацией линии FAP-оверэкспрессирующих клеток рака толстой и прямой кишки мыши CT26.
В частности, опухолевые клетки трансплантировали в правую сторону спины 6-недельным мышам BALB/c, и когда размер опухоли животной модели достигал 70-100 мм3, мышей рандомизированно распределяли по группам и проводили введение. В качестве контроля вводили PBS, а в качестве тестируемой группы однократно внутривенно вводили 100 мкл T1.03m в дозе 2 мкг, 10 мкг и 100 мкг. Размер опухоли измеряли так же, как в Примере 4.1.
В результате, как показано на ФИГ. 29, наблюдали, что группа, в которой вводили 2 мкг, 10 мкг и 100 мкг T1.03m, обладала высокой способностью ингибировать рост опухоли по сравнению с контролем. Изменений массы тела в течение периода исследования не наблюдали. Эти результаты показывают, что T1.03m, у которого снижена активность IL-12 из-за структуры последовательности, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, обладает отличной противоопухолевой эффективностью при некоторой или более высокой концентрации.
Пример 5. Оценка противоопухолевой эффективности слитого белка в модели меланомы на животных
Для обнаружения противоопухолевого эффекта при иммунной активации слитого белка мышиный FAP оверэкспрессировали в линии клеток мышиной меланомы B16F10, которая, как известно, демонстрирует слабую инфильтрацию иммунными клетками, а затем трансплантировали мышам C57BL/6J и оценивали способность ингибирования роста опухоли.
В частности, клетки в культуре ресуспендировали в сбалансированных растворах Хэнкса раствор (HBSS, Gibco), а затем 100 мкл 1×106 опухолевых клеток на каждую мышь трансплантировали в подкожную область с левой боковой стороны спины 6-недельным мышам C57BL/6J.
Затем для оценки эффективности лекарственного средства, когда размер опухоли достигал 70-100 мм3, мышей рандомизированно разделяли по группам. В качестве контроля вводили PBS, а в качестве тестируемой группы однократно внутривенно вводили T1.03m в дозе 10 мкг и 100 мкг.
В результате, как показано на ФИГ. 30, наблюдали, что обе группы, в которых вводили 10 мкг и 100 мкг T1.03m, обладали высокой способностью ингибировать рост опухоли по сравнению с контролем. Изменений массы тела в течение периода исследования не наблюдали. Эти результаты показывают, что T1.03m, который обладает сниженной активностью IL-12 из-за структуры последовательности, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, обладает превосходной противоопухолевой эффективностью даже в модели меланомы на животных.
Пример 6. Оценка противоопухолевой эффективности слитого белка в модели рака легкого на животных
Пример 6.1. Оценка противоопухолевой эффективности слитого белка с аминокислотной мутацией IL-12 в модели рака легкого на животных
С учетом того, что FAP повышенно экспрессируется в фибробластах, присутствующих в микроокружении вокруг опухоли, FAP оверэкспрессировали в NIH-3T3, клеточной линии мышиных фибробластов, а затем совместно вводили с LLC1, линией клеток рака легкого мыши, в соотношении 1:1 с получением модели опухоли на животных, и оценивали способность ингибировать рост опухоли.
В частности, линию клеток NIH-3T3 с оверэкспрессией FAP и клетки LLC1 ресуспендировали в сбалансированном солевом растворе Хэнкса (HBSS, Gibco) в концентрации 1×106 клеток/50 мкл соответственно и смешивали клетки в соотношении 1:1, а затем по 100 мкл на каждую мышь трансплантировали в подкожную область в правый бок 6-недельным мышам C57BL/6J при использовании шприца (25G) объемом 1 см3.
Затем для оценки эффективности лекарственного средства, когда размер опухоли достигал 70-100 мм3, мышей рандомизированно распределяли по группам. В качестве контроля вводили PBS, а в качестве тестируемой группы однократно внутривенно вводили T1.03m в дозе 10 мкг и 100 мкг.
В результате, как показано на ФИГ. 31, наблюдали, что обе группы, в которых вводили 10 мкг или 100 мкг T1.03m, обладали превосходной способностью ингибировать рост опухоли по сравнению с контролем. Изменений массы тела в течение периода исследования не наблюдали. Эти результаты показывают, что T1.03m, который обладает сниженной активностью IL-12 из-за структуры последовательности, содержащей мутации (четырех) аминокислот, участвующих в связывании гепарина, распознает фактор-мишень в микроокружении опухоли и, таким образом, обладает превосходной противоопухолевой эффективностью даже в модель рака легкого на животных.
Пример 6.2. Оценка эффективности направленного воздействия на опухоль в модели рака легкого на животных посредством совместной инъекции слитого белка
Для сравнения противоопухолевой эффективности в соответствии с направленным воздействием на опухоль слитого белка по типу двойного антитела, в котором структура последовательности против FAP и структура последовательности IL-12 образуют структуру "выступа во впадину", была определена способность ингибировать рост опухоли в модели на животных, которым совместно вводили клеточную линию мышиных фибробластов NIH-3T3 с оверэкспрессией FAP и клеточную линию LLC1 рака легкого мыши, в соотношении 1:1.
В частности, для оценки эффективности лекарственного средства, когда размер опухоли достигал 70-100 мм3, мышей рандомизированно распределяли по группам. В качестве контроля два раза в неделю внутрибрюшинно вводили PBS. Группу, в которой вводили только T1.16m или T1.17m, группу, в которой вводили T1.16m и T1.17m в комбинации (T1.16m+T1.17m), и группу, в которой вводили T1.03m, использовали в качестве тестируемых групп для оценки способности ингибирования роста опухоли. T1.16m и T1.17m, которые представляют собой димеры против FAP и IL-12, соответственно, вводили внутрибрюшинно два раза в неделю в дозе 0,01 мкг, и T1.03m, который представляет собой мономерный слитый белок, вводили внутрибрюшинно два раза в неделю в дозе 0,02 мкг для наблюдения способности ингибировать рост опухоли.
В результате, как показано на ФИГ. 32, было отмечено, что группа, в которой вводили T1.03m, обладала превосходной способностью ингибировать рост опухоли через 10 дней после введения по сравнению с контролем. Группу, которой вводили только T1.16m или T1.17m, и каждую группу комбинированного введения сравнивали, и при этом было обнаружено, что группа, в которой вводили только T1.03m, обладала превосходной способностью ингибировать рост опухоли. Эти результаты показывают, что синергетический эффект слитого белка согласно одному варианту осуществления является значимым в сравнении со случаем, когда мишенью является только FAP, или по сравнению с IL-12 без опухоли-мишени.
--->
СПИСОК ПОСЛЕДОВАТЕЛЬНОСТЕЙ
<110> KANAPH THERAPEUTICS INC.
<120> СЛИТЫЙ БЕЛОК, ВКЛЮЧАЮЩИЙ IL-12 И АНТИТЕЛО ПРОТИВ FAP, И ЕГО
ПРИМЕНЕНИЕ
<130> SPO21-021KNP_PCT
<150> KR 10-2020-0100229
<151> 2020-08-11
<160> 305
<170> KoPatentIn 3.0
<210> 1
<211> 454
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc knob DANG
<400> 1
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Trp Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Lys
450
<210> 2
<211> 220
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LC
<400> 2
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
1 5 10 15
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
20 25 30
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
35 40 45
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
50 55 60
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
65 70 75 80
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
85 90 95
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
100 105 110
Lys Arg Thr Val Ala Ala Pro Ser Val Phe Ile Phe Pro Pro Ser Asp
115 120 125
Glu Gln Leu Lys Ser Gly Thr Ala Ser Val Val Cys Leu Leu Asn Asn
130 135 140
Phe Tyr Pro Arg Glu Ala Lys Val Gln Trp Lys Val Asp Asn Ala Leu
145 150 155 160
Gln Ser Gly Asn Ser Gln Glu Ser Val Thr Glu Gln Asp Ser Lys Asp
165 170 175
Ser Thr Tyr Ser Leu Ser Ser Thr Leu Thr Leu Ser Lys Ala Asp Tyr
180 185 190
Glu Lys His Lys Val Tyr Ala Cys Glu Val Thr His Gln Gly Leu Ser
195 200 205
Ser Pro Val Thr Lys Ser Phe Asn Arg Gly Glu Cys
210 215 220
<210> 3
<211> 755
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12-hu IgG1 Fc hole DANG
<400> 3
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Lys
755
<210> 4
<211> 755
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut1-hu IgG1 Fc hole DANG
<400> 4
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Lys Arg Glu Ala Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Lys
755
<210> 5
<211> 755
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2-hu IgG1 Fc hole DANG
<400> 5
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Lys
755
<210> 6
<211> 593
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> (anti-hu FAP VH)2-hu IgG1 Fc knob DANG
<400> 6
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly Gly
115 120 125
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Val
130 135 140
Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala Ser Val Lys Val Ser
145 150 155 160
Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr Thr Ile His Trp Val
165 170 175
Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile Gly Gly Ile Asn Pro
180 185 190
Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe Lys Gly Arg Val Thr
195 200 205
Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr Met Glu Leu Ser Ser
210 215 220
Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys Ala Arg Arg Arg Ile
225 230 235 240
Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp Tyr Trp Gly Gln Gly
245 250 255
Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys Gly Pro Ser Val Phe
260 265 270
Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly Gly Thr Ala Ala Leu
275 280 285
Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro Val Thr Val Ser Trp
290 295 300
Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr Phe Pro Ala Val Leu
305 310 315 320
Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val Val Thr Val Pro Ser
325 330 335
Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn Val Asn His Lys Pro
340 345 350
Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro Lys Ser Cys Asp Lys
355 360 365
Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly Gly Pro
370 375 380
Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met Ile Ser
385 390 395 400
Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His Glu Asp
405 410 415
Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val His Asn
420 425 430
Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr Arg Val
435 440 445
Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly Lys Glu
450 455 460
Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile Glu Lys
465 470 475 480
Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val Tyr Thr
485 490 495
Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser Leu Trp
500 505 510
Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu Trp Glu
515 520 525
Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro Val Leu
530 535 540
Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val Asp Lys
545 550 555 560
Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met His Glu
565 570 575
Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser Pro Gly
580 585 590
Lys
<210> 7
<211> 348
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> (anti-hu FAP VL)2
<400> 7
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
1 5 10 15
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
20 25 30
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
35 40 45
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
50 55 60
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
65 70 75 80
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
85 90 95
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
100 105 110
Lys Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
115 120 125
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
130 135 140
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
145 150 155 160
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
165 170 175
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
180 185 190
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
195 200 205
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
210 215 220
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
225 230 235 240
Lys Arg Thr Val Ala Ala Pro Ser Val Phe Ile Phe Pro Pro Ser Asp
245 250 255
Glu Gln Leu Lys Ser Gly Thr Ala Ser Val Val Cys Leu Leu Asn Asn
260 265 270
Phe Tyr Pro Arg Glu Ala Lys Val Gln Trp Lys Val Asp Asn Ala Leu
275 280 285
Gln Ser Gly Asn Ser Gln Glu Ser Val Thr Glu Gln Asp Ser Lys Asp
290 295 300
Ser Thr Tyr Ser Leu Ser Ser Thr Leu Thr Leu Ser Lys Ala Asp Tyr
305 310 315 320
Glu Lys His Lys Val Tyr Ala Cys Glu Val Thr His Gln Gly Leu Ser
325 330 335
Ser Pro Val Thr Lys Ser Phe Asn Arg Gly Glu Cys
340 345
<210> 8
<211> 726
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc knob DANG-anti-hu FAP scFv
<400> 8
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Trp Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Lys Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
450 455 460
Gly Gly Gly Gly Ser Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val
465 470 475 480
Lys Lys Pro Gly Ala Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr
485 490 495
Thr Phe Thr Glu Tyr Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln
500 505 510
Arg Leu Glu Trp Ile Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn
515 520 525
Tyr Asn Gln Lys Phe Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser
530 535 540
Ala Ser Thr Ala Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr
545 550 555 560
Ala Val Tyr Tyr Cys Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu
565 570 575
Gly His Ala Met Asp Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser
580 585 590
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
595 600 605
Gly Gly Gly Gly Ser Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu
610 615 620
Ala Val Ser Leu Gly Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln
625 630 635 640
Ser Leu Leu Tyr Ser Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln
645 650 655
Gln Lys Pro Gly Gln Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr
660 665 670
Arg Glu Ser Gly Val Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr
675 680 685
Asp Phe Thr Leu Thr Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val
690 695 700
Tyr Tyr Cys Gln Gln Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly
705 710 715 720
Thr Lys Val Glu Ile Lys
725
<210> 9
<211> 492
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LC-anti-hu FAP scFv
<400> 9
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
1 5 10 15
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
20 25 30
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
35 40 45
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
50 55 60
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
65 70 75 80
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
85 90 95
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
100 105 110
Lys Arg Thr Val Ala Ala Pro Ser Val Phe Ile Phe Pro Pro Ser Asp
115 120 125
Glu Gln Leu Lys Ser Gly Thr Ala Ser Val Val Cys Leu Leu Asn Asn
130 135 140
Phe Tyr Pro Arg Glu Ala Lys Val Gln Trp Lys Val Asp Asn Ala Leu
145 150 155 160
Gln Ser Gly Asn Ser Gln Glu Ser Val Thr Glu Gln Asp Ser Lys Asp
165 170 175
Ser Thr Tyr Ser Leu Ser Ser Thr Leu Thr Leu Ser Lys Ala Asp Tyr
180 185 190
Glu Lys His Lys Val Tyr Ala Cys Glu Val Thr His Gln Gly Leu Ser
195 200 205
Ser Pro Val Thr Lys Ser Phe Asn Arg Gly Glu Cys Gly Gly Gly Gly
210 215 220
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Val
225 230 235 240
Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala Ser Val Lys Val Ser
245 250 255
Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr Thr Ile His Trp Val
260 265 270
Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile Gly Gly Ile Asn Pro
275 280 285
Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe Lys Gly Arg Val Thr
290 295 300
Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr Met Glu Leu Ser Ser
305 310 315 320
Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys Ala Arg Arg Arg Ile
325 330 335
Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp Tyr Trp Gly Gln Gly
340 345 350
Thr Leu Val Thr Val Ser Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
355 360 365
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Asp Ile Val Met Thr
370 375 380
Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly Glu Arg Ala Thr Ile
385 390 395 400
Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser Arg Asn Gln Lys Asn
405 410 415
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Pro Pro Lys Leu Leu
420 425 430
Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val Pro Asp Arg Phe Ser
435 440 445
Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr Ile Ser Ser Leu Gln
450 455 460
Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln Tyr Phe Ser Tyr Pro
465 470 475 480
Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
485 490
<210> 10
<211> 986
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc hole DANG-hu scIL-12
<400> 10
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
450 455 460
Gly Gly Gly Ser Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu
465 470 475 480
Leu Asp Trp Tyr Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys
485 490 495
Asp Thr Pro Glu Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser
500 505 510
Glu Val Leu Gly Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe
515 520 525
Gly Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser
530 535 540
His Ser Leu Leu Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr
545 550 555 560
Asp Ile Leu Lys Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg
565 570 575
Cys Glu Ala Lys Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr
580 585 590
Thr Ile Ser Thr Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser
595 600 605
Ser Asp Pro Gln Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu
610 615 620
Arg Val Arg Gly Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln
625 630 635 640
Glu Asp Ser Ala Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val
645 650 655
Met Val Asp Ala Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser
660 665 670
Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln
675 680 685
Leu Lys Pro Leu Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr
690 695 700
Pro Asp Thr Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys
705 710 715 720
Val Gln Val Gln Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe
725 730 735
Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile
740 745 750
Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp
755 760 765
Ala Ser Val Pro Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly
785 790 795 800
Met Phe Pro Cys Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser
805 810 815
Asn Met Leu Gln Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr
820 825 830
Ser Glu Glu Ile Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr
835 840 845
Val Glu Ala Cys Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu
850 855 860
Asn Ser Arg Glu Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser
865 870 875 880
Arg Lys Thr Ser Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu
885 890 895
Asp Leu Lys Met Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu
900 905 910
Leu Met Asp Pro Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala
915 920 925
Val Ile Asp Glu Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val
930 935 940
Pro Gln Lys Ser Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile
945 950 955 960
Lys Leu Cys Ile Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile
965 970 975
Asp Arg Val Met Ser Tyr Leu Asn Ala Ser
980 985
<210> 11
<211> 986
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc hole DANG-hu scIL-12 mut2
<400> 11
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
450 455 460
Gly Gly Gly Ser Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu
465 470 475 480
Leu Asp Trp Tyr Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys
485 490 495
Asp Thr Pro Glu Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser
500 505 510
Glu Val Leu Gly Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe
515 520 525
Gly Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser
530 535 540
His Ser Leu Leu Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr
545 550 555 560
Asp Ile Leu Lys Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg
565 570 575
Cys Glu Ala Lys Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr
580 585 590
Thr Ile Ser Thr Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser
595 600 605
Ser Asp Pro Gln Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu
610 615 620
Arg Val Arg Gly Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln
625 630 635 640
Glu Asp Ser Ala Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val
645 650 655
Met Val Asp Ala Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser
660 665 670
Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln
675 680 685
Leu Lys Pro Leu Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr
690 695 700
Pro Asp Thr Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys
705 710 715 720
Val Gln Val Gln Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe
725 730 735
Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile
740 745 750
Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp
755 760 765
Ala Ser Val Pro Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly
785 790 795 800
Met Phe Pro Cys Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser
805 810 815
Asn Met Leu Gln Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr
820 825 830
Ser Glu Glu Ile Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr
835 840 845
Val Glu Ala Cys Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu
850 855 860
Asn Ser Arg Glu Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser
865 870 875 880
Arg Lys Thr Ser Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu
885 890 895
Asp Leu Lys Met Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu
900 905 910
Leu Met Asp Pro Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala
915 920 925
Val Ile Asp Glu Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val
930 935 940
Pro Gln Lys Ser Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile
945 950 955 960
Lys Leu Cys Ile Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile
965 970 975
Asp Arg Val Met Ser Tyr Leu Asn Ala Ser
980 985
<210> 12
<211> 227
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc hole DANG
<400> 12
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
1 5 10 15
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
20 25 30
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
35 40 45
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
50 55 60
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
65 70 75 80
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
85 90 95
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
100 105 110
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
115 120 125
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
130 135 140
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
145 150 155 160
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
165 170 175
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
180 185 190
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
195 200 205
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
210 215 220
Pro Gly Lys
225
<210> 13
<211> 227
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc knob DANG
<400> 13
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
1 5 10 15
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
20 25 30
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
35 40 45
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
50 55 60
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
65 70 75 80
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
85 90 95
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
100 105 110
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
115 120 125
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
130 135 140
Leu Trp Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
145 150 155 160
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
165 170 175
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
180 185 190
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
195 200 205
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
210 215 220
Pro Gly Lys
225
<210> 14
<211> 454
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc DANG
<400> 14
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Lys
450
<210> 15
<211> 755
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2-hu IgG1 Fc DANG
<400> 15
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Lys
755
<210> 16
<211> 451
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu CD20 HC hu IgG1 Fc knob DANG
<400> 16
Gln Val Gln Leu Gln Gln Pro Gly Ala Glu Leu Val Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Met Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Ser Tyr
20 25 30
Asn Met His Trp Val Lys Gln Thr Pro Gly Arg Gly Leu Glu Trp Ile
35 40 45
Gly Ala Ile Tyr Pro Gly Asn Gly Asp Thr Ser Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Lys Ser Ser Ser Thr Ala Tyr
65 70 75 80
Met Gln Leu Ser Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Ser Thr Tyr Tyr Gly Gly Asp Trp Tyr Phe Asn Val Trp Gly
100 105 110
Ala Gly Thr Thr Val Thr Val Ser Ala Ala Ser Thr Lys Gly Pro Ser
115 120 125
Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly Gly Thr Ala
130 135 140
Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro Val Thr Val
145 150 155 160
Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr Phe Pro Ala
165 170 175
Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val Val Thr Val
180 185 190
Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn Val Asn His
195 200 205
Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro Lys Ser Cys
210 215 220
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
225 230 235 240
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
245 250 255
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
260 265 270
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
275 280 285
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
290 295 300
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
305 310 315 320
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
325 330 335
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
340 345 350
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
355 360 365
Leu Trp Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
370 375 380
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
385 390 395 400
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
405 410 415
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
420 425 430
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
435 440 445
Pro Gly Lys
450
<210> 17
<211> 213
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu CD20 LC
<400> 17
Gln Ile Val Leu Ser Gln Ser Pro Ala Ile Leu Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Arg Ala Ser Ser Ser Val Ser Tyr Ile
20 25 30
His Trp Phe Gln Gln Lys Pro Gly Ser Ser Pro Lys Pro Trp Ile Tyr
35 40 45
Ala Thr Ser Asn Leu Ala Ser Gly Val Pro Val Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Arg Val Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Thr Ser Asn Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Arg Thr Val Ala Ala Pro
100 105 110
Ser Val Phe Ile Phe Pro Pro Ser Asp Glu Gln Leu Lys Ser Gly Thr
115 120 125
Ala Ser Val Val Cys Leu Leu Asn Asn Phe Tyr Pro Arg Glu Ala Lys
130 135 140
Val Gln Trp Lys Val Asp Asn Ala Leu Gln Ser Gly Asn Ser Gln Glu
145 150 155 160
Ser Val Thr Glu Gln Asp Ser Lys Asp Ser Thr Tyr Ser Leu Ser Ser
165 170 175
Thr Leu Thr Leu Ser Lys Ala Asp Tyr Glu Lys His Lys Val Tyr Ala
180 185 190
Cys Glu Val Thr His Gln Gly Leu Ser Ser Pro Val Thr Lys Ser Phe
195 200 205
Asn Arg Gly Glu Cys
210
<210> 18
<211> 447
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc knob DANG
<400> 18
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Trp Cys Met
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
435 440 445
<210> 19
<211> 213
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LC
<400> 19
Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn Phe Met
20 25 30
His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp Ile Phe
35 40 45
Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Arg Ala Asp Ala Ala Pro
100 105 110
Thr Val Ser Ile Phe Pro Pro Ser Ser Glu Gln Leu Thr Ser Gly Gly
115 120 125
Ala Ser Val Val Cys Phe Leu Asn Asn Phe Tyr Pro Lys Asp Ile Asn
130 135 140
Val Lys Trp Lys Ile Asp Gly Ser Glu Arg Gln Asn Gly Val Leu Asn
145 150 155 160
Ser Trp Thr Asp Gln Asp Ser Lys Asp Ser Thr Tyr Ser Met Ser Ser
165 170 175
Thr Leu Thr Leu Thr Lys Asp Glu Tyr Glu Arg His Asn Ser Tyr Thr
180 185 190
Cys Glu Ala Thr His Lys Thr Ser Thr Ser Pro Ile Val Lys Ser Phe
195 200 205
Asn Arg Asn Glu Cys
210
<210> 20
<211> 764
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12-mu IgG2a Fc hole DANG
<400> 20
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys
245 250 255
Glu Lys Met Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
755 760
<210> 21
<211> 764
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut1-mu IgG2a Fc hole DANG
<400> 21
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Ala Lys
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
755 760
<210> 22
<211> 764
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2-mu IgG2a Fc hole DANG
<400> 22
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
755 760
<210> 23
<211> 579
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> (anti-mu FAP VH)2, mu IgG2a Fc knob DANG
<400> 23
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
115 120 125
Gly Gly Gly Ser Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala
130 135 140
Arg Pro Gly Ala Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr
145 150 155 160
Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly
165 170 175
Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr
180 185 190
Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser
195 200 205
Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala
210 215 220
Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly
225 230 235 240
Gln Gly Thr Leu Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser
245 250 255
Val Tyr Pro Leu Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val
260 265 270
Thr Leu Gly Cys Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu
275 280 285
Thr Trp Asn Ser Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala
290 295 300
Val Leu Gln Ser Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr
305 310 315 320
Ser Ser Thr Trp Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro
325 330 335
Ala Ser Ser Thr Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr
340 345 350
Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly
355 360 365
Gly Pro Ser Val Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met
370 375 380
Ile Ser Leu Ser Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu
385 390 395 400
Asp Asp Pro Asp Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val
405 410 415
His Thr Ala Gln Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu
420 425 430
Arg Val Val Ser Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly
435 440 445
Lys Glu Phe Lys Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile
450 455 460
Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val
465 470 475 480
Tyr Val Leu Pro Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr
485 490 495
Leu Trp Cys Met Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu
500 505 510
Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro
515 520 525
Val Leu Asp Ser Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val
530 535 540
Glu Lys Lys Asn Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val
545 550 555 560
His Glu Gly Leu His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr
565 570 575
Pro Gly Lys
<210> 24
<211> 334
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> (anti-mu FAP VL)2
<400> 24
Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn Phe Met
20 25 30
His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp Ile Phe
35 40 45
Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Gly Gly Gly Gly Ser Gly
100 105 110
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Ile Val Leu Thr Gln Ser
115 120 125
Pro Ala Ile Met Ser Ala Ser Pro Gly Glu Lys Val Thr Met Thr Cys
130 135 140
Ser Ala Ser Ser Gly Val Asn Phe Met His Trp Tyr Gln Gln Lys Ser
145 150 155 160
Gly Thr Ser Pro Lys Arg Trp Ile Phe Asp Thr Ser Lys Leu Ala Ser
165 170 175
Gly Val Pro Ala Arg Phe Ser Gly Ser Gly Ser Gly Thr Ser Tyr Ser
180 185 190
Leu Thr Ile Ser Ser Met Glu Ala Glu Asp Ala Ala Thr Tyr Tyr Cys
195 200 205
Gln Gln Trp Ser Phe Asn Pro Pro Thr Phe Gly Gly Gly Thr Lys Leu
210 215 220
Glu Ile Lys Arg Ala Asp Ala Ala Pro Thr Val Ser Ile Phe Pro Pro
225 230 235 240
Ser Ser Glu Gln Leu Thr Ser Gly Gly Ala Ser Val Val Cys Phe Leu
245 250 255
Asn Asn Phe Tyr Pro Lys Asp Ile Asn Val Lys Trp Lys Ile Asp Gly
260 265 270
Ser Glu Arg Gln Asn Gly Val Leu Asn Ser Trp Thr Asp Gln Asp Ser
275 280 285
Lys Asp Ser Thr Tyr Ser Met Ser Ser Thr Leu Thr Leu Thr Lys Asp
290 295 300
Glu Tyr Glu Arg His Asn Ser Tyr Thr Cys Glu Ala Thr His Lys Thr
305 310 315 320
Ser Thr Ser Pro Ile Val Lys Ser Phe Asn Arg Asn Glu Cys
325 330
<210> 25
<211> 705
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc knob DANG-anti-mu FAP scFv
<400> 25
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Trp Cys Met
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys Gly
435 440 445
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val
450 455 460
Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala Ser Val
465 470 475 480
Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn Gly Ile
485 490 495
Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile Gly Glu
500 505 510
Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys Gly
515 520 525
Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr Met Glu
530 535 540
Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys Ala Arg
545 550 555 560
Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu Val Thr
565 570 575
Val Ser Ala Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly
580 585 590
Gly Ser Gly Gly Gly Gly Ser Gln Ile Val Leu Thr Gln Ser Pro Ala
595 600 605
Ile Met Ser Ala Ser Pro Gly Glu Lys Val Thr Met Thr Cys Ser Ala
610 615 620
Ser Ser Gly Val Asn Phe Met His Trp Tyr Gln Gln Lys Ser Gly Thr
625 630 635 640
Ser Pro Lys Arg Trp Ile Phe Asp Thr Ser Lys Leu Ala Ser Gly Val
645 650 655
Pro Ala Arg Phe Ser Gly Ser Gly Ser Gly Thr Ser Tyr Ser Leu Thr
660 665 670
Ile Ser Ser Met Glu Ala Glu Asp Ala Ala Thr Tyr Tyr Cys Gln Gln
675 680 685
Trp Ser Phe Asn Pro Pro Thr Phe Gly Gly Gly Thr Lys Leu Glu Ile
690 695 700
Lys
705
<210> 26
<211> 471
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LC-anti-mu FAP scFv
<400> 26
Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn Phe Met
20 25 30
His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp Ile Phe
35 40 45
Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Arg Ala Asp Ala Ala Pro
100 105 110
Thr Val Ser Ile Phe Pro Pro Ser Ser Glu Gln Leu Thr Ser Gly Gly
115 120 125
Ala Ser Val Val Cys Phe Leu Asn Asn Phe Tyr Pro Lys Asp Ile Asn
130 135 140
Val Lys Trp Lys Ile Asp Gly Ser Glu Arg Gln Asn Gly Val Leu Asn
145 150 155 160
Ser Trp Thr Asp Gln Asp Ser Lys Asp Ser Thr Tyr Ser Met Ser Ser
165 170 175
Thr Leu Thr Leu Thr Lys Asp Glu Tyr Glu Arg His Asn Ser Tyr Thr
180 185 190
Cys Glu Ala Thr His Lys Thr Ser Thr Ser Pro Ile Val Lys Ser Phe
195 200 205
Asn Arg Asn Glu Cys Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
210 215 220
Gly Gly Gly Ser Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala
225 230 235 240
Arg Pro Gly Ala Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr
245 250 255
Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly
260 265 270
Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr
275 280 285
Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser
290 295 300
Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala
305 310 315 320
Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly
325 330 335
Gln Gly Thr Leu Val Thr Val Ser Ala Gly Gly Gly Gly Ser Gly Gly
340 345 350
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Ile Val
355 360 365
Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser Pro Gly Glu Lys Val
370 375 380
Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn Phe Met His Trp Tyr
385 390 395 400
Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp Ile Phe Asp Thr Ser
405 410 415
Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser Gly Ser Gly Ser Gly
420 425 430
Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu Ala Glu Asp Ala Ala
435 440 445
Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro Pro Thr Phe Gly Gly
450 455 460
Gly Thr Lys Leu Glu Ile Lys
465 470
<210> 27
<211> 982
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc hole DANG-mu scIL-12
<400> 27
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly
435 440 445
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Met Trp Glu
450 455 460
Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr Pro Asp Ala
465 470 475 480
Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu Glu Asp Asp
485 490 495
Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly Ser Gly Lys
500 505 510
Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly Gln Tyr Thr
515 520 525
Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu Leu Leu His
530 535 540
Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys Asn Phe Lys
545 550 555 560
Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser Gly Arg Phe
565 570 575
Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys Phe Asn Ile
580 585 590
Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr Cys Gly Met
595 600 605
Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg Asp Tyr Glu
610 615 620
Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro Thr Ala Glu
625 630 635 640
Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln Gln Asn Lys
645 650 655
Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile Ile Lys Pro
660 665 670
Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn Ser Gln Val
675 680 685
Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro His Ser Tyr
690 695 700
Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys Glu Lys Met
705 710 715 720
Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe Leu Val Glu
725 730 735
Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val Cys Val Gln
740 745 750
Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp Ala Cys Val
755 760 765
Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro Ala Arg Cys
785 790 795 800
Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp Met Val Lys
805 810 815
Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala Glu Asp Ile
820 825 830
Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr Cys
835 840 845
Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala Thr Arg Glu
850 855 860
Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr Ser
865 870 875 880
Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys Met
885 890 895
Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln Asn His Asn
900 905 910
His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala Ile Asp Glu
915 920 925
Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg Gln Lys Pro
930 935 940
Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys Leu Cys Ile
945 950 955 960
Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn Arg Val Met
965 970 975
Gly Tyr Leu Ser Ser Ala
980
<210> 28
<211> 982
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc hole DANG-mu scIL-12 mut2
<400> 28
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly
435 440 445
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Met Trp Glu
450 455 460
Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr Pro Asp Ala
465 470 475 480
Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu Glu Asp Asp
485 490 495
Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly Ser Gly Lys
500 505 510
Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly Gln Tyr Thr
515 520 525
Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu Leu Leu His
530 535 540
Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys Asn Phe Lys
545 550 555 560
Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser Gly Arg Phe
565 570 575
Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys Phe Asn Ile
580 585 590
Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr Cys Gly Met
595 600 605
Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg Asp Tyr Glu
610 615 620
Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro Thr Ala Glu
625 630 635 640
Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln Gln Asn Lys
645 650 655
Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile Ile Lys Pro
660 665 670
Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn Ser Gln Val
675 680 685
Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro His Ser Tyr
690 695 700
Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala Glu Lys Met
705 710 715 720
Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe Leu Val Glu
725 730 735
Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val Cys Val Gln
740 745 750
Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp Ala Cys Val
755 760 765
Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro Ala Arg Cys
785 790 795 800
Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp Met Val Lys
805 810 815
Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala Glu Asp Ile
820 825 830
Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr Cys
835 840 845
Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala Thr Arg Glu
850 855 860
Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr Ser
865 870 875 880
Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys Met
885 890 895
Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln Asn His Asn
900 905 910
His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala Ile Asp Glu
915 920 925
Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg Gln Lys Pro
930 935 940
Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys Leu Cys Ile
945 950 955 960
Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn Arg Val Met
965 970 975
Gly Tyr Leu Ser Ser Ala
980
<210> 29
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc hole DANG
<400> 29
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<210> 30
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc knob DANG
<400> 30
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Trp Cys Met Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<210> 31
<211> 447
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc DANG
<400> 31
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
435 440 445
<210> 32
<211> 764
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2-mu IgG2a Fc DANG
<400> 32
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Lys
755 760
<210> 33
<211> 451
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu CD20 HC mu IgG2a Fc knob DANG
<400> 33
Gln Val Gln Leu Gln Gln Pro Gly Ala Glu Leu Val Arg Pro Gly Thr
1 5 10 15
Ser Val Lys Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Ser Tyr
20 25 30
Trp Met His Trp Ile Lys Gln Arg Pro Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Val Ile Asp Pro Ser Asp Asn Tyr Thr Lys Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Val Asp Thr Ser Ser Ser Thr Ala Tyr
65 70 75 80
Met Gln Leu Ser Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Glu Gly Tyr Tyr Gly Ser Ser Pro Trp Phe Ala Tyr Trp Gly
100 105 110
Gln Gly Thr Leu Val Thr Val Ser Ser Ala Lys Thr Thr Ala Pro Ser
115 120 125
Val Tyr Pro Leu Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val
130 135 140
Thr Leu Gly Cys Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu
145 150 155 160
Thr Trp Asn Ser Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala
165 170 175
Val Leu Gln Ser Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr
180 185 190
Ser Ser Thr Trp Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro
195 200 205
Ala Ser Ser Thr Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr
210 215 220
Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly
225 230 235 240
Gly Pro Ser Val Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met
245 250 255
Ile Ser Leu Ser Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu
260 265 270
Asp Asp Pro Asp Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val
275 280 285
His Thr Ala Gln Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu
290 295 300
Arg Val Val Ser Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly
305 310 315 320
Lys Glu Phe Lys Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile
325 330 335
Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val
340 345 350
Tyr Val Leu Pro Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr
355 360 365
Leu Trp Cys Met Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu
370 375 380
Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro
385 390 395 400
Val Leu Asp Ser Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val
405 410 415
Glu Lys Lys Asn Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val
420 425 430
His Glu Gly Leu His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr
435 440 445
Pro Gly Lys
450
<210> 34
<211> 213
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu CD20 LC
<400> 34
Gln Ile Val Met Ser Gln Ser Pro Ala Ile Leu Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Arg Ala Arg Ser Ser Val Ser Tyr Ile
20 25 30
His Trp Tyr Gln Gln Lys Pro Gly Ser Ser Pro Lys Pro Trp Ile Tyr
35 40 45
Ala Thr Ser Asn Leu Ala Ser Gly Val Pro Gly Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Thr Arg Val Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Ser Lys Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Arg Thr Asp Ala Ala Pro
100 105 110
Thr Val Ser Ile Phe Pro Pro Ser Ser Glu Gln Leu Thr Ser Gly Gly
115 120 125
Ala Ser Val Val Cys Phe Leu Asn Asn Phe Tyr Pro Lys Asp Ile Asn
130 135 140
Val Lys Trp Lys Ile Asp Gly Ser Glu Arg Gln Asn Gly Val Leu Asn
145 150 155 160
Ser Trp Thr Asp Gln Asp Ser Lys Asp Ser Thr Tyr Ser Met Ser Ser
165 170 175
Thr Leu Thr Leu Thr Lys Asp Glu Tyr Glu Arg His Asn Ser Tyr Thr
180 185 190
Cys Glu Ala Thr His Lys Thr Ser Thr Ser Pro Ile Val Lys Ser Phe
195 200 205
Asn Arg Asn Glu Cys
210
<210> 35
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc DANG
<400> 35
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Thr Cys Met Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<210> 36
<211> 1362
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP HC hu IgG1 Fc knob DANG
<400> 36
caggtgcagc tggtgcagtc cggagcagag gtgaagaagc caggagcctc tgtgaaggtg 60
agctgcaaga cctccagata caccttcaca gagtatacaa tccactgggt gcgccaggca 120
cctggacagc ggctggagtg gatcggaggc atcaacccca acaatggcat ccctaactac 180
aatcagaagt ttaagggcag agtgaccatc acagtggaca cctccgcctc tacagcctat 240
atggagctga gctccctgag gagcgaggat accgccgtgt actattgcgc ccggagaagg 300
atcgcctacg gctatgacga gggccacgcc atggattact ggggccaggg caccctggtg 360
acagtgtcta gcgcctctac caagggacca agcgtgttcc cactggcacc atcctctaag 420
agcacctccg gaggaacagc cgccctgggc tgtctggtga aggactattt cccagagccc 480
gtgacagtgt cctggaactc tggcgccctg acctccggag tgcacacatt tcctgccgtg 540
ctgcagagct ccggcctgta cagcctgtct agcgtggtga ccgtgccatc ctctagcctg 600
ggcacccaga catatatctg caacgtgaat cacaagccta gcaatacaaa ggtggacaag 660
aaggtggagc caaagtcctg tgataagacc cacacatgcc ccccttgtcc tgcaccagag 720
ctgctgggag gaccaagcgt gttcctgttt ccacccaagc ccaaggacac cctgatgatc 780
tctcgcaccc cagaggtgac atgcgtggtg gtggccgtga gccacgagga ccccgaggtg 840
aagtttaact ggtacgtgga tggcgtggag gtgcacaatg ccaagaccaa gccaagagag 900
gagcagtacg gctccaccta tagggtggtg tctgtgctga cagtgctgca ccaggattgg 960
ctgaacggca aggagtataa gtgcaaggtg tccaataagg ccctgcccgc ccctatcgag 1020
aagaccatct ctaaggcaaa gggacagcct agggagccac aggtgtacac cctgcctcca 1080
tcccgggacg agctgacaaa gaaccaggtg tctctgtggt gtctggtgaa gggcttctat 1140
ccctctgata tcgccgtgga gtgggagagc aatggccagc ctgagaacaa ttacaagacc 1200
acaccccctg tgctggacag cgatggctcc ttctttctgt atagcaagct gaccgtggat 1260
aagtcccggt ggcagcaggg caacgtgttt tcttgtagcg tgatgcacga ggccctgcac 1320
aatcactaca cacagaagtc cctgtctctg agccctggca ag 1362
<210> 37
<211> 660
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP LC
<400> 37
gacatcgtga tgacccagtc ccctgattct ctggccgtga gcctgggaga gagggcaaca 60
atcaactgca agagctccca gagcctgctg tactcccgca accagaagaa ttacctggcc 120
tggtatcagc agaagcccgg ccagccccct aagctgctga tcttctgggc atctaccagg 180
gagagcggag tgcctgacag attttctggc agcggcttcg gcacagactt caccctgaca 240
atctctagcc tgcaggccga ggacgtggcc gtgtactatt gccagcagta cttctcctat 300
cctctgacct ttggccaggg cacaaaggtg gagatcaaga ggaccgtggc agcaccaagc 360
gtgttcatct ttccaccctc cgacgagcag ctgaagtccg gcaccgcctc tgtggtgtgc 420
ctgctgaaca atttctaccc aagggaggcc aaggtgcagt ggaaggtgga taacgccctg 480
cagagcggca attcccagga gtctgtgacc gagcaggaca gcaaggattc cacatattct 540
ctgtcctcta ccctgacact gtctaaggcc gattacgaga agcacaaggt gtatgcatgc 600
gaggtgaccc accagggact gagctcccca gtgacaaagt cctttaatcg gggcgagtgt 660
660
<210> 38
<211> 2265
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu scIL-12-hu IgG1 Fc hole DANG
<400> 38
atctgggagc tgaagaagga cgtgtacgtg gtggagctgg actggtatcc tgatgcccca 60
ggcgagatgg tggtgctgac ctgcgacaca cccgaggagg atggcatcac ctggacactg 120
gatcagagct ccgaggtgct gggcagcggc aagaccctga caatccaggt gaaggagttc 180
ggcgacgccg gccagtacac ctgtcacaag ggaggagagg tgctgagcca ctccctgctg 240
ctgctgcaca agaaggagga cggcatctgg agcacagaca tcctgaagga tcagaaggag 300
ccaaagaaca agaccttcct gcggtgcgag gccaagaatt attccggccg gttcacctgt 360
tggtggctga ccacaatctc caccgatctg acattttctg tgaagtctag caggggctcc 420
tctgaccccc agggagtgac atgcggagca gccaccctga gcgccgagcg ggtgagaggc 480
gataacaagg agtacgagta ttccgtggag tgccaggagg actctgcctg tcctgcagca 540
gaggagtccc tgccaatcga agtgatggtg gatgccgtgc acaagctgaa gtacgagaat 600
tatacaagct ccttctttat cagggacatc atcaagcctg atccccctaa gaacctgcag 660
ctgaagccac tgaagaatag ccgccaggtg gaggtgtcct gggagtaccc agacacctgg 720
tccacacccc actcttattt cagcctgacc ttttgcgtgc aggtgcaggg caagtccaag 780
agggagaaga aggaccgcgt gttcaccgat aagacatctg ccaccgtgat ctgtcggaag 840
aacgcctcta tcagcgtgcg ggcccaggat agatactatt ctagctcctg gagcgagtgg 900
gcctccgtgc cttgttctgg aggaggaggc agcggcggag gaggctccgg aggaggaggc 960
tctagaaatc tgccagtggc aacccctgac ccaggaatgt tcccttgcct gcaccactct 1020
cagaacctgc tgcgggccgt gagcaatatg ctgcagaagg ccagacagac actggagttt 1080
tacccctgta ccagcgagga gatcgaccac gaggatatca caaaggataa gacctccaca 1140
gtggaggcct gcctgcctct ggagctgacc aagaacgaga gctgtctgaa cagccgggag 1200
acatctttca tcaccaacgg cagctgcctg gcctccagaa agacatcttt tatgatggcc 1260
ctgtgcctgt ctagcatcta cgaggacctg aagatgtatc aggtggagtt caagaccatg 1320
aacgccaagc tgctgatgga cccaaagcgg cagatctttc tggatcagaa tatgctggcc 1380
gtgatcgacg agctgatgca ggccctgaac ttcaatagcg agacagtgcc ccagaagtcc 1440
tctctggagg agcctgactt ctacaagacc aagatcaagc tgtgcatcct gctgcacgcc 1500
ttccggatca gagccgtgac catcgataga gtgatgagct atctgaacgc aagcggcggc 1560
ggaggctctg gaggaggcgg cagcgacaag acccacacat gcccaccatg tccagcacct 1620
gagctgctgg gaggaccatc cgtgttcctg tttcctccaa agcccaagga tacactgatg 1680
atcagccgca cacctgaggt gacctgcgtg gtggtggccg tgtcccacga ggaccccgag 1740
gtgaagttta actggtacgt ggacggcgtg gaggtgcaca atgccaagac caagcccagg 1800
gaggagcagt acggctctac atatcgcgtg gtgagcgtgc tgaccgtgct gcaccaggac 1860
tggctgaacg gcaaggagta caagtgcaag gtgtctaata aggccctgcc agcccccatc 1920
gagaagacca tcagcaaggc aaagggacag ccaagggagc ctcaggtgta tacactgccc 1980
cctagccgcg atgagctgac caagaaccag gtgtccctgt cttgtgccgt gaagggcttc 2040
tacccatccg acatcgccgt ggagtgggag tctaatggcc agcccgagaa caattataag 2100
accacaccac ccgtgctgga ctccgatggc tctttctttc tggtgagcaa gctgacagtg 2160
gacaagtcca gatggcagca gggcaacgtg tttagctgct ccgtgatgca cgaggccctg 2220
cacaatcact acacccagaa gtctctgagc ctgtcccctg gcaag 2265
<210> 39
<211> 2265
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu scIL-12 mut1-hu IgG1 Fc hole DANG
<400> 39
atctgggagc tgaagaagga cgtgtacgtg gtggagctgg actggtatcc tgatgcccca 60
ggcgagatgg tggtgctgac ctgcgacaca cccgaggagg atggcatcac ctggacactg 120
gatcagagct ccgaggtgct gggcagcggc aagaccctga caatccaggt gaaggagttc 180
ggcgacgccg gccagtacac ctgtcacaag ggaggagagg tgctgagcca ctccctgctg 240
ctgctgcaca agaaggagga cggcatctgg agcacagaca tcctgaagga tcagaaggag 300
ccaaagaaca agaccttcct gcggtgcgag gccaagaatt attccggccg gttcacctgt 360
tggtggctga ccacaatctc caccgatctg acattttctg tgaagtctag caggggctcc 420
tctgaccccc agggagtgac atgcggagca gccaccctga gcgccgagcg ggtgagaggc 480
gataacaagg agtacgagta ttccgtggag tgccaggagg actctgcctg tcctgcagca 540
gaggagtccc tgccaatcga agtgatggtg gatgccgtgc acaagctgaa gtacgagaat 600
tatacaagct ccttctttat cagggacatc atcaagcctg atccccctaa gaacctgcag 660
ctgaagccac tgaagaatag ccgccaggtg gaggtgtcct gggagtaccc agacacctgg 720
tccacacccc actcttattt cagcctgacc ttttgcgtgc aggtgcaggg agcatccaag 780
agggaggcaa aggaccgcgt gttcaccgat aagacatctg ccaccgtgat ctgtcggaag 840
aacgcctcta tcagcgtgcg ggcccaggat agatactatt ctagctcctg gagcgagtgg 900
gcctccgtgc cttgttctgg aggaggaggc agcggcggag gaggctccgg aggaggaggc 960
tctagaaatc tgccagtggc aacccctgac ccaggaatgt tcccttgcct gcaccactct 1020
cagaacctgc tgcgggccgt gagcaatatg ctgcagaagg ccagacagac actggagttt 1080
tacccctgta ccagcgagga gatcgaccac gaggatatca caaaggataa gacctccaca 1140
gtggaggcct gcctgcctct ggagctgacc aagaacgaga gctgtctgaa cagccgggag 1200
acatctttca tcaccaacgg cagctgcctg gcctccagaa agacatcttt tatgatggcc 1260
ctgtgcctgt ctagcatcta cgaggacctg aagatgtatc aggtggagtt caagaccatg 1320
aacgccaagc tgctgatgga cccaaagcgg cagatctttc tggatcagaa tatgctggcc 1380
gtgatcgacg agctgatgca ggccctgaac ttcaatagcg agacagtgcc ccagaagtcc 1440
tctctggagg agcctgactt ctacaagacc aagatcaagc tgtgcatcct gctgcacgcc 1500
ttccggatca gagccgtgac catcgataga gtgatgagct atctgaacgc aagcggcggc 1560
ggaggctctg gaggaggcgg cagcgacaag acccacacat gcccaccatg tccagcacct 1620
gagctgctgg gaggaccatc cgtgttcctg tttcctccaa agcccaagga tacactgatg 1680
atcagccgca cacctgaggt gacctgcgtg gtggtggccg tgtcccacga ggaccccgag 1740
gtgaagttta actggtacgt ggacggcgtg gaggtgcaca atgccaagac caagcccagg 1800
gaggagcagt acggctctac atatcgcgtg gtgagcgtgc tgaccgtgct gcaccaggac 1860
tggctgaacg gcaaggagta caagtgcaag gtgtctaata aggccctgcc agcccccatc 1920
gagaagacca tcagcaaggc aaagggacag ccaagggagc ctcaggtgta tacactgccc 1980
cctagccgcg atgagctgac caagaaccag gtgtccctgt cttgtgccgt gaagggcttc 2040
tacccatccg acatcgccgt ggagtgggag tctaatggcc agcccgagaa caattataag 2100
accacaccac ccgtgctgga ctccgatggc tctttctttc tggtgagcaa gctgacagtg 2160
gacaagtcca gatggcagca gggcaacgtg tttagctgct ccgtgatgca cgaggccctg 2220
cacaatcact acacccagaa gtctctgagc ctgtcccctg gcaag 2265
<210> 40
<211> 2265
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu scIL-12 mut2-hu IgG1 Fc hole DANG
<400> 40
atctgggagc tgaagaagga cgtgtacgtg gtggagctgg actggtatcc tgatgcccca 60
ggcgagatgg tggtgctgac ctgcgacaca cccgaggagg atggcatcac ctggacactg 120
gatcagagct ccgaggtgct gggcagcggc aagaccctga caatccaggt gaaggagttc 180
ggcgacgccg gccagtacac ctgtcacaag ggaggagagg tgctgagcca ctccctgctg 240
ctgctgcaca agaaggagga cggcatctgg agcacagaca tcctgaagga tcagaaggag 300
ccaaagaaca agaccttcct gcggtgcgag gccaagaatt attccggccg gttcacctgt 360
tggtggctga ccacaatctc caccgatctg acattttctg tgaagtctag caggggctcc 420
tctgaccccc agggagtgac atgcggagca gccaccctga gcgccgagcg ggtgagaggc 480
gataacaagg agtacgagta ttccgtggag tgccaggagg actctgcctg tcctgcagca 540
gaggagtccc tgccaatcga agtgatggtg gatgccgtgc acaagctgaa gtacgagaat 600
tatacaagct ccttctttat cagggacatc atcaagcctg atccccctaa gaacctgcag 660
ctgaagccac tgaagaatag ccgccaggtg gaggtgtcct gggagtaccc agacacctgg 720
tccacacccc actcttattt cagcctgacc ttttgcgtgc aggtgcaggg cgcctccgct 780
agggaggccg ctgaccgcgt gttcaccgat aagacatctg ccaccgtgat ctgtcggaag 840
aacgcctcta tcagcgtgcg ggcccaggat agatactatt ctagctcctg gagcgagtgg 900
gcctccgtgc cttgttctgg aggaggaggc agcggcggag gaggctccgg aggaggaggc 960
tctagaaatc tgccagtggc aacccctgac ccaggaatgt tcccttgcct gcaccactct 1020
cagaacctgc tgcgggccgt gagcaatatg ctgcagaagg ccagacagac actggagttt 1080
tacccctgta ccagcgagga gatcgaccac gaggatatca caaaggataa gacctccaca 1140
gtggaggcct gcctgcctct ggagctgacc aagaacgaga gctgtctgaa cagccgggag 1200
acatctttca tcaccaacgg cagctgcctg gcctccagaa agacatcttt tatgatggcc 1260
ctgtgcctgt ctagcatcta cgaggacctg aagatgtatc aggtggagtt caagaccatg 1320
aacgccaagc tgctgatgga cccaaagcgg cagatctttc tggatcagaa tatgctggcc 1380
gtgatcgacg agctgatgca ggccctgaac ttcaatagcg agacagtgcc ccagaagtcc 1440
tctctggagg agcctgactt ctacaagacc aagatcaagc tgtgcatcct gctgcacgcc 1500
ttccggatca gagccgtgac catcgataga gtgatgagct atctgaacgc aagcggcggc 1560
ggaggctctg gaggaggcgg cagcgacaag acccacacat gcccaccatg tccagcacct 1620
gagctgctgg gaggaccatc cgtgttcctg tttcctccaa agcccaagga tacactgatg 1680
atcagccgca cacctgaggt gacctgcgtg gtggtggccg tgtcccacga ggaccccgag 1740
gtgaagttta actggtacgt ggacggcgtg gaggtgcaca atgccaagac caagcccagg 1800
gaggagcagt acggctctac atatcgcgtg gtgagcgtgc tgaccgtgct gcaccaggac 1860
tggctgaacg gcaaggagta caagtgcaag gtgtctaata aggccctgcc agcccccatc 1920
gagaagacca tcagcaaggc aaagggacag ccaagggagc ctcaggtgta tacactgccc 1980
cctagccgcg atgagctgac caagaaccag gtgtccctgt cttgtgccgt gaagggcttc 2040
tacccatccg acatcgccgt ggagtgggag tctaatggcc agcccgagaa caattataag 2100
accacaccac ccgtgctgga ctccgatggc tctttctttc tggtgagcaa gctgacagtg 2160
gacaagtcca gatggcagca gggcaacgtg tttagctgct ccgtgatgca cgaggccctg 2220
cacaatcact acacccagaa gtctctgagc ctgtcccctg gcaag 2265
<210> 41
<211> 1779
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК (anti-hu FAP VH)2-hu IgG1 Fc knob DANG
<400> 41
caagtgcagc tggtgcagag cggcgccgag gtgaaaaagc ctggcgcttc tgtgaaggtg 60
tcttgcaaga cctccagata cacattcacc gagtacacca tccactgggt gcggcaggcc 120
cctggacagc ggctggaatg gatcggaggc atcaacccca acaacggcat tccaaattac 180
aaccagaagt tcaagggcag agtgacaatc accgttgaca ccagcgccag caccgcttat 240
atggaactga gcagcctgag aagcgaggat acagccgtgt actactgtgc cagaagacgg 300
atcgcctacg gctacgacga gggccacgcc atggactact ggggccaggg cacactggtc 360
accgtgtcct ctggcggcgg cggcagcggc ggcggcggca gcggaggagg aggtagccag 420
gtccagctgg tgcagtctgg agcagaggtg aagaagccag gagcctctgt gaaggtgagc 480
tgcaagacct ccagatacac cttcacagag tatacaatcc actgggtgcg ccaggcacct 540
ggacagcggc tggagtggat cggaggcatc aaccccaaca atggcatccc taactacaat 600
cagaagttta agggcagagt gaccatcaca gtggacacct ccgcctctac agcctatatg 660
gagctgagct ccctgaggag cgaggatacc gccgtgtact attgcgcccg gagaaggatc 720
gcctacggct atgacgaggg ccacgccatg gattactggg gccagggcac cctggtgaca 780
gtgtctagcg cctctaccaa gggaccaagc gtgttcccac tggcaccatc ctctaagagc 840
acctccggag gaacagccgc cctgggctgt ctggtgaagg actatttccc agagcccgtg 900
acagtgtcct ggaactctgg cgccctgacc tccggagtgc acacatttcc tgccgtgctg 960
cagagctccg gcctgtacag cctgtctagc gtggtgaccg tgccatcctc tagcctgggc 1020
acccagacat atatctgcaa cgtgaatcac aagcctagca atacaaaggt ggacaagaag 1080
gtggagccaa agtcctgtga taagacccac acatgccccc cttgtcctgc accagagctg 1140
ctgggaggac caagcgtgtt cctgtttcca cccaagccca aggacaccct gatgatctct 1200
cgcaccccag aggtgacatg cgtggtggtg gccgtgagcc acgaggaccc cgaggtgaag 1260
tttaactggt acgtggatgg cgtggaggtg cacaatgcca agaccaagcc aagagaggag 1320
cagtacggct ccacctatag ggtggtgtct gtgctgacag tgctgcacca ggattggctg 1380
aacggcaagg agtataagtg caaggtgtcc aataaggccc tgcccgcccc tatcgagaag 1440
accatctcta aggcaaaggg acagcctagg gagccacagg tgtacaccct gcctccatcc 1500
cgggacgagc tgacaaagaa ccaggtgtct ctgtggtgtc tggtgaaggg cttctatccc 1560
tctgatatcg ccgtggagtg ggagagcaat ggccagcctg agaacaatta caagaccaca 1620
ccccctgtgc tggacagcga tggctccttc tttctgtata gcaagctgac cgtggataag 1680
tcccggtggc agcagggcaa cgtgttttct tgtagcgtga tgcacgaggc cctgcacaat 1740
cactacacac agaagtccct gtctctgagc cctggcaag 1779
<210> 42
<211> 1044
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК (anti-hu FAP VL)2
<400> 42
gatatcgtga tgacccagag ccccgacagc ctggccgtgt ccctgggcga acgggccaca 60
atcaactgca agtccagcca gtctctgctg tacagcagaa accagaagaa ttacctggct 120
tggtatcagc agaaacctgg ccaacctcca aagctgctga tcttctgggc cagcaccaga 180
gagagcggcg tgcctgatag attcagcggc agcggatttg gcaccgactt caccctgacc 240
atcagcagcc tccaggccga ggacgtggcc gtctactact gtcagcaata cttcagctac 300
cccctgacat tcggccaggg cacaaaggtg gaaatcaagg gcggcggagg ctctggcggc 360
ggcggatctg gaggtggcgg ctccgacatc gtgatgacac agtctcctga ttctctggcc 420
gtgagcctgg gagagagggc aacaatcaac tgcaagagct cccagagcct gctgtactcc 480
cgcaaccaga agaattacct ggcctggtat cagcagaagc ccggccagcc ccctaagctg 540
ctgatcttct gggcatctac cagggagagc ggagtgcctg acagattttc tggcagcggc 600
ttcggcacag acttcaccct gacaatctct agcctgcagg ccgaggacgt ggccgtgtac 660
tattgccagc agtacttctc ctatcctctg acctttggcc agggcacaaa ggtggagatc 720
aagaggaccg tggcagcacc aagcgtgttc atctttccac cctccgacga gcagctgaag 780
tccggcaccg cctctgtggt gtgcctgctg aacaatttct acccaaggga ggccaaggtg 840
cagtggaagg tggataacgc cctgcagagc ggcaattccc aggagtctgt gaccgagcag 900
gacagcaagg attccacata ttctctgtcc tctaccctga cactgtctaa ggccgattac 960
gagaagcaca aggtgtatgc atgcgaggtg acccaccagg gactgagctc cccagtgaca 1020
aagtccttta atcggggcga gtgt 1044
<210> 43
<211> 2178
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP HC hu IgG1 Fc knob
DANG-anti-hu FAP scFv
<400> 43
caggtgcagc tggtgcagtc cggagcagag gtgaagaagc caggagcctc tgtgaaggtg 60
agctgcaaga cctccagata caccttcaca gagtatacaa tccactgggt gcgccaggca 120
cctggacagc ggctggagtg gatcggaggc atcaacccca acaatggcat ccctaactac 180
aatcagaagt ttaagggcag agtgaccatc acagtggaca cctccgcctc tacagcctat 240
atggagctga gctccctgag gagcgaggat accgccgtgt actattgcgc ccggagaagg 300
atcgcctacg gctatgacga gggccacgcc atggattact ggggccaggg caccctggtg 360
acagtgtcta gcgcctctac caagggacca agcgtgttcc cactggcacc atcctctaag 420
agcacctccg gaggaacagc cgccctgggc tgtctggtga aggactattt cccagagccc 480
gtgacagtgt cctggaactc tggcgccctg acctccggag tgcacacatt tcctgccgtg 540
ctgcagagct ccggcctgta cagcctgtct agcgtggtga ccgtgccatc ctctagcctg 600
ggcacccaga catatatctg caacgtgaat cacaagccta gcaatacaaa ggtggacaag 660
aaggtggagc caaagtcctg tgataagacc cacacatgcc ccccttgtcc tgcaccagag 720
ctgctgggag gaccaagcgt gttcctgttt ccacccaagc ccaaggacac cctgatgatc 780
tctcgcaccc cagaggtgac atgcgtggtg gtggccgtga gccacgagga ccccgaggtg 840
aagtttaact ggtacgtgga tggcgtggag gtgcacaatg ccaagaccaa gccaagagag 900
gagcagtacg gctccaccta tagggtggtg tctgtgctga cagtgctgca ccaggattgg 960
ctgaacggca aggagtataa gtgcaaggtg tccaataagg ccctgcccgc ccctatcgag 1020
aagaccatct ctaaggcaaa gggacagcct agggagccac aggtgtacac cctgcctcca 1080
tcccgggacg agctgacaaa gaaccaggtg tctctgtggt gtctggtgaa gggcttctat 1140
ccctctgata tcgccgtgga gtgggagagc aatggccagc ctgagaacaa ttacaagacc 1200
acaccccctg tgctggacag cgatggctcc ttctttctgt atagcaagct gaccgtggat 1260
aagtcccggt ggcagcaggg caacgtgttt tcttgtagcg tgatgcacga ggccctgcac 1320
aatcactaca cacagaagtc cctgtctctg agccctggca agggcggcgg cggcagcggc 1380
ggcggcggca gcggaggagg aggtagccaa gtgcagctgg tgcagagcgg cgccgaggtg 1440
aaaaagcctg gcgcttctgt gaaggtgtct tgcaagacct ccagatacac attcaccgag 1500
tacaccatcc actgggtgcg gcaggcccct ggacagcggc tggaatggat cggaggcatc 1560
aaccccaaca acggcattcc aaattacaac cagaagttca agggcagagt gacaatcacc 1620
gttgacacca gcgccagcac cgcttatatg gaactgagca gcctgagaag cgaggataca 1680
gccgtgtact actgtgccag aagacggatc gcctacggct acgacgaggg ccacgccatg 1740
gactactggg gccagggcac actggtcacc gtgtcctctg gtggaggtgg ctcaggagga 1800
ggcggttctg gcggaggagg tagtggaggt ggcggctccg atatcgtgat gacccagagc 1860
cccgacagcc tggccgtgtc cctgggcgaa cgggccacaa tcaactgcaa gtccagccag 1920
tctctgctgt acagcagaaa ccagaagaat tacctggctt ggtatcagca gaaacctggc 1980
caacctccaa agctgctgat cttctgggcc agcaccagag agagcggcgt gcctgataga 2040
ttcagcggca gcggatttgg caccgacttc accctgacca tcagcagcct ccaggccgag 2100
gacgtggccg tctactactg tcagcaatac ttcagctacc ccctgacatt cggccagggc 2160
acaaaggtgg aaatcaag 2178
<210> 44
<211> 1476
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP LC-anti-hu FAP scFv
<400> 44
gacatcgtga tgacccagtc ccctgattct ctggccgtga gcctgggaga gagggcaaca 60
atcaactgca agagctccca gagcctgctg tactcccgca accagaagaa ttacctggcc 120
tggtatcagc agaagcccgg ccagccccct aagctgctga tcttctgggc atctaccagg 180
gagagcggag tgcctgacag attttctggc agcggcttcg gcacagactt caccctgaca 240
atctctagcc tgcaggccga ggacgtggcc gtgtactatt gccagcagta cttctcctat 300
cctctgacct ttggccaggg cacaaaggtg gagatcaaga ggaccgtggc agcaccaagc 360
gtgttcatct ttccaccctc cgacgagcag ctgaagtccg gcaccgcctc tgtggtgtgc 420
ctgctgaaca atttctaccc aagggaggcc aaggtgcagt ggaaggtgga taacgccctg 480
cagagcggca attcccagga gtctgtgacc gagcaggaca gcaaggattc cacatattct 540
ctgtcctcta ccctgacact gtctaaggcc gattacgaga agcacaaggt gtatgcatgc 600
gaggtgaccc accagggact gagctcccca gtgacaaagt cctttaatcg gggcgagtgt 660
ggcggcggcg gcagcggcgg cggcggcagc ggaggaggag gtagccaagt gcagctggtg 720
cagagcggcg ccgaggtgaa aaagcctggc gcttctgtga aggtgtcttg caagacctcc 780
agatacacat tcaccgagta caccatccac tgggtgcggc aggcccctgg acagcggctg 840
gaatggatcg gaggcatcaa ccccaacaac ggcattccaa attacaacca gaagttcaag 900
ggcagagtga caatcaccgt tgacaccagc gccagcaccg cttatatgga actgagcagc 960
ctgagaagcg aggatacagc cgtgtactac tgtgccagaa gacggatcgc ctacggctac 1020
gacgagggcc acgccatgga ctactggggc cagggcacac tggtcaccgt gtcctctggt 1080
ggaggtggct caggaggagg cggttctggc ggaggaggta gtggaggtgg cggctccgat 1140
atcgtgatga cccagagccc cgacagcctg gccgtgtccc tgggcgaacg ggccacaatc 1200
aactgcaagt ccagccagtc tctgctgtac agcagaaacc agaagaatta cctggcttgg 1260
tatcagcaga aacctggcca acctccaaag ctgctgatct tctgggccag caccagagag 1320
agcggcgtgc ctgatagatt cagcggcagc ggatttggca ccgacttcac cctgaccatc 1380
agcagcctcc aggccgagga cgtggccgtc tactactgtc agcaatactt cagctacccc 1440
ctgacattcg gccagggcac aaaggtggaa atcaag 1476
<210> 45
<211> 2958
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP HC hu IgG1 Fc hole
DANG-hu scIL-12
<400> 45
caggtgcagc tggtgcagtc cggagcagag gtgaagaagc caggagcctc tgtgaaggtg 60
agctgcaaga cctccagata caccttcaca gagtatacaa tccactgggt gcgccaggca 120
cctggacagc ggctggagtg gatcggaggc atcaacccca acaatggcat ccctaactac 180
aatcagaagt ttaagggcag agtgaccatc acagtggaca cctccgcctc tacagcctat 240
atggagctga gctccctgag gagcgaggat accgccgtgt actattgcgc ccggagaagg 300
atcgcctacg gctatgacga gggccacgcc atggattact ggggccaggg caccctggtg 360
acagtgtcta gcgcctctac caagggacca agcgtgttcc cactggcacc atcctctaag 420
agcacctccg gaggaacagc cgccctgggc tgtctggtga aggactattt cccagagccc 480
gtgacagtgt cctggaactc tggcgccctg acctccggag tgcacacatt tcctgccgtg 540
ctgcagagct ccggcctgta cagcctgtct agcgtggtga ccgtgccatc ctctagcctg 600
ggcacccaga catatatctg caacgtgaat cacaagccta gcaatacaaa ggtggacaag 660
aaggtggagc caaagtcctg tgacaagacc cacacatgcc caccatgtcc agcacctgag 720
ctgctgggag gaccatccgt gttcctgttt cctccaaagc ccaaggatac actgatgatc 780
agccgcacac ctgaggtgac ctgcgtggtg gtggccgtgt cccacgagga ccccgaggtg 840
aagtttaact ggtacgtgga cggcgtggag gtgcacaatg ccaagaccaa gcccagggag 900
gagcagtacg gctctacata tcgcgtggtg agcgtgctga ccgtgctgca ccaggactgg 960
ctgaacggca aggagtacaa gtgcaaggtg tctaataagg ccctgccagc ccccatcgag 1020
aagaccatca gcaaggcaaa gggacagcca agggagcctc aggtgtatac actgccccct 1080
agccgcgatg agctgaccaa gaaccaggtg tccctgtctt gtgccgtgaa gggcttctac 1140
ccatccgaca tcgccgtgga gtgggagtct aatggccagc ccgagaacaa ttataagacc 1200
acaccacccg tgctggactc cgatggctct ttctttctgg tgagcaagct gacagtggac 1260
aagtccagat ggcagcaggg caacgtgttt agctgctccg tgatgcacga ggccctgcac 1320
aatcactaca cccagaagtc tctgagcctg tcccctggcg gtggaggtgg ctcaggagga 1380
ggcggttctg gcggaggagg tagtatctgg gagctgaaga aggacgtgta cgtggtggag 1440
ctggactggt atcctgatgc cccaggcgag atggtggtgc tgacctgcga cacacccgag 1500
gaggatggca tcacctggac actggatcag agctccgagg tgctgggcag cggcaagacc 1560
ctgacaatcc aggtgaagga gttcggcgac gccggccagt acacctgtca caagggagga 1620
gaggtgctga gccactccct gctgctgctg cacaagaagg aggacggcat ctggagcaca 1680
gacatcctga aggatcagaa ggagccaaag aacaagacct tcctgcggtg cgaggccaag 1740
aattattccg gccggttcac ctgttggtgg ctgaccacaa tctccaccga tctgacattt 1800
tctgtgaagt ctagcagggg ctcctctgac ccccagggag tgacatgcgg agcagccacc 1860
ctgagcgccg agcgggtgag aggcgataac aaggagtacg agtattccgt ggagtgccag 1920
gaggactctg cctgtcctgc agcagaggag tccctgccaa tcgaagtgat ggtggatgcc 1980
gtgcacaagc tgaagtacga gaattataca agctccttct ttatcaggga catcatcaag 2040
cctgatcccc ctaagaacct gcagctgaag ccactgaaga atagccgcca ggtggaggtg 2100
tcctgggagt acccagacac ctggtccaca ccccactctt atttcagcct gaccttttgc 2160
gtgcaggtgc agggcaagtc caagagggag aagaaggacc gcgtgttcac cgataagaca 2220
tctgccaccg tgatctgtcg gaagaacgcc tctatcagcg tgcgggccca ggatagatac 2280
tattctagct cctggagcga gtgggcctcc gtgccttgtt ctggaggagg aggcagcggc 2340
ggaggaggct ccggaggagg aggctctaga aatctgccag tggcaacccc tgacccagga 2400
atgttccctt gcctgcacca ctctcagaac ctgctgcggg ccgtgagcaa tatgctgcag 2460
aaggccagac agacactgga gttttacccc tgtaccagcg aggagatcga ccacgaggat 2520
atcacaaagg ataagacctc cacagtggag gcctgcctgc ctctggagct gaccaagaac 2580
gagagctgtc tgaacagccg ggagacatct ttcatcacca acggcagctg cctggcctcc 2640
agaaagacat cttttatgat ggccctgtgc ctgtctagca tctacgagga cctgaagatg 2700
tatcaggtgg agttcaagac catgaacgcc aagctgctga tggacccaaa gcggcagatc 2760
tttctggatc agaatatgct ggccgtgatc gacgagctga tgcaggccct gaacttcaat 2820
agcgagacag tgccccagaa gtcctctctg gaggagcctg acttctacaa gaccaagatc 2880
aagctgtgca tcctgctgca cgccttccgg atcagagccg tgaccatcga tagagtgatg 2940
agctatctga acgcaagc 2958
<210> 46
<211> 2958
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP HC hu IgG1 Fc hole DANG-hu
scIL-12 mut2
<400> 46
caggtgcagc tggtgcagtc cggagcagag gtgaagaagc caggagcctc tgtgaaggtg 60
agctgcaaga cctccagata caccttcaca gagtatacaa tccactgggt gcgccaggca 120
cctggacagc ggctggagtg gatcggaggc atcaacccca acaatggcat ccctaactac 180
aatcagaagt ttaagggcag agtgaccatc acagtggaca cctccgcctc tacagcctat 240
atggagctga gctccctgag gagcgaggat accgccgtgt actattgcgc ccggagaagg 300
atcgcctacg gctatgacga gggccacgcc atggattact ggggccaggg caccctggtg 360
acagtgtcta gcgcctctac caagggacca agcgtgttcc cactggcacc atcctctaag 420
agcacctccg gaggaacagc cgccctgggc tgtctggtga aggactattt cccagagccc 480
gtgacagtgt cctggaactc tggcgccctg acctccggag tgcacacatt tcctgccgtg 540
ctgcagagct ccggcctgta cagcctgtct agcgtggtga ccgtgccatc ctctagcctg 600
ggcacccaga catatatctg caacgtgaat cacaagccta gcaatacaaa ggtggacaag 660
aaggtggagc caaagtcctg tgacaagacc cacacatgcc caccatgtcc agcacctgag 720
ctgctgggag gaccatccgt gttcctgttt cctccaaagc ccaaggatac actgatgatc 780
agccgcacac ctgaggtgac ctgcgtggtg gtggccgtgt cccacgagga ccccgaggtg 840
aagtttaact ggtacgtgga cggcgtggag gtgcacaatg ccaagaccaa gcccagggag 900
gagcagtacg gctctacata tcgcgtggtg agcgtgctga ccgtgctgca ccaggactgg 960
ctgaacggca aggagtacaa gtgcaaggtg tctaataagg ccctgccagc ccccatcgag 1020
aagaccatca gcaaggcaaa gggacagcca agggagcctc aggtgtatac actgccccct 1080
agccgcgatg agctgaccaa gaaccaggtg tccctgtctt gtgccgtgaa gggcttctac 1140
ccatccgaca tcgccgtgga gtgggagtct aatggccagc ccgagaacaa ttataagacc 1200
acaccacccg tgctggactc cgatggctct ttctttctgg tgagcaagct gacagtggac 1260
aagtccagat ggcagcaggg caacgtgttt agctgctccg tgatgcacga ggccctgcac 1320
aatcactaca cccagaagtc tctgagcctg tcccctggcg gtggaggtgg ctcaggagga 1380
ggcggttctg gcggaggagg tagtatctgg gagctgaaga aggacgtgta cgtggtggag 1440
ctggactggt atcctgatgc cccaggcgag atggtggtgc tgacctgcga cacacccgag 1500
gaggatggca tcacctggac actggatcag agctccgagg tgctgggcag cggcaagacc 1560
ctgacaatcc aggtgaagga gttcggcgac gccggccagt acacctgtca caagggagga 1620
gaggtgctga gccactccct gctgctgctg cacaagaagg aggacggcat ctggagcaca 1680
gacatcctga aggatcagaa ggagccaaag aacaagacct tcctgcggtg cgaggccaag 1740
aattattccg gccggttcac ctgttggtgg ctgaccacaa tctccaccga tctgacattt 1800
tctgtgaagt ctagcagggg ctcctctgac ccccagggag tgacatgcgg agcagccacc 1860
ctgagcgccg agcgggtgag aggcgataac aaggagtacg agtattccgt ggagtgccag 1920
gaggactctg cctgtcctgc agcagaggag tccctgccaa tcgaagtgat ggtggatgcc 1980
gtgcacaagc tgaagtacga gaattataca agctccttct ttatcaggga catcatcaag 2040
cctgatcccc ctaagaacct gcagctgaag ccactgaaga atagccgcca ggtggaggtg 2100
tcctgggagt acccagacac ctggtccaca ccccactctt atttcagcct gaccttttgc 2160
gtgcaggtgc agggcgcctc cgctagggag gccgctgacc gcgtgttcac cgataagaca 2220
tctgccaccg tgatctgtcg gaagaacgcc tctatcagcg tgcgggccca ggatagatac 2280
tattctagct cctggagcga gtgggcctcc gtgccttgtt ctggaggagg aggcagcggc 2340
ggaggaggct ccggaggagg aggctctaga aatctgccag tggcaacccc tgacccagga 2400
atgttccctt gcctgcacca ctctcagaac ctgctgcggg ccgtgagcaa tatgctgcag 2460
aaggccagac agacactgga gttttacccc tgtaccagcg aggagatcga ccacgaggat 2520
atcacaaagg ataagacctc cacagtggag gcctgcctgc ctctggagct gaccaagaac 2580
gagagctgtc tgaacagccg ggagacatct ttcatcacca acggcagctg cctggcctcc 2640
agaaagacat cttttatgat ggccctgtgc ctgtctagca tctacgagga cctgaagatg 2700
tatcaggtgg agttcaagac catgaacgcc aagctgctga tggacccaaa gcggcagatc 2760
tttctggatc agaatatgct ggccgtgatc gacgagctga tgcaggccct gaacttcaat 2820
agcgagacag tgccccagaa gtcctctctg gaggagcctg acttctacaa gaccaagatc 2880
aagctgtgca tcctgctgca cgccttccgg atcagagccg tgaccatcga tagagtgatg 2940
agctatctga acgcaagc 2958
<210> 47
<211> 681
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu IgG1 Fc hole DANG
<400> 47
gacaagaccc acacatgccc accttgtcca gcaccagagc tgctgggagg accatccgtg 60
ttcctgtttc cacccaagcc caaggatacc ctgatgatca gcaggacccc agaggtgaca 120
tgcgtggtgg tggccgtgtc ccacgaggac cctgaggtga agttcaactg gtacgtggat 180
ggcgtggagg tgcacaatgc caagacaaag ccacgggagg agcagtacgg cagcacctat 240
agagtggtgt ccgtgctgac agtgctgcac caggactggc tgaacggcaa ggagtacaag 300
tgcaaggtgt ctaataaggc cctgcctgcc ccaatcgaga agaccatcag caaggcaaag 360
ggacagccaa gggagcctca ggtgtatacc ctgcctccaa gccgcgacga gctgacaaag 420
aaccaggtga gcctgtcctg tgccgtgaag ggcttctacc cttccgatat cgccgtggag 480
tgggagtcta atggccagcc agagaacaat tataagacca caccccctgt gctggactcc 540
gatggctctt tctttctggt gtctaagctg accgtggata agagcaggtg gcagcagggc 600
aacgtgtttt cttgtagcgt gatgcacgag gccctgcaca atcactatac acagaagtcc 660
ctgtctctga gccctggcaa g 681
<210> 48
<211> 681
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu IgG1 Fc knob DANG
<400> 48
gacaagaccc acacatgccc accttgtcca gcaccagagc tgctgggagg accatccgtg 60
ttcctgtttc cacccaagcc caaggatacc ctgatgatca gcaggacccc agaggtgaca 120
tgcgtggtgg tggccgtgtc ccacgaggac cctgaggtga agttcaactg gtacgtggat 180
ggcgtggagg tgcacaatgc caagacaaag ccacgggagg agcagtacgg ctccacctat 240
agagtggtgt ctgtgctgac agtgctgcac caggactggc tgaacggcaa ggagtataag 300
tgcaaggtgt ctaataaggc cctgcctgcc ccaatcgaga agaccatcag caaggcaaag 360
ggacagccaa gggagcctca ggtgtacacc ctgcctccat cccgcgacga gctgacaaag 420
aaccaggtgt ctctgtggtg tctggtgaag ggcttctatc cttctgatat cgccgtggag 480
tgggagagca atggccagcc agagaacaat tacaagacca caccccctgt gctggactct 540
gatggcagct tctttctgta tagcaagctg accgtggata agtccaggtg gcagcagggc 600
aacgtgttta gctgttccgt gatgcacgag gccctgcaca atcactacac acagaagtct 660
ctgagcctgt cccctggcaa g 681
<210> 49
<211> 1365
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu FAP HC hu IgG1 Fc DANG
<400> 49
caggtgcagc tggtgcagtc cggagcagag gtgaagaagc caggagcctc tgtgaaggtg 60
agctgcaaga cctccagata caccttcaca gagtatacaa tccactgggt gcgccaggca 120
cctggacagc ggctggagtg gatcggaggc atcaacccca acaatggcat ccctaactac 180
aatcagaagt ttaagggcag agtgaccatc acagtggaca cctccgcctc tacagcctat 240
atggagctga gctccctgag gagcgaggat accgccgtgt actattgcgc ccggagaagg 300
atcgcctacg gctatgacga gggccacgcc atggattact ggggccaggg caccctggtg 360
acagtgtcta gcgcctctac caagggacca agcgtgttcc cactggcacc atcctctaag 420
agcacctccg gaggaacagc cgccctgggc tgtctggtga aggactattt cccagagccc 480
gtgacagtgt cctggaactc tggcgccctg acctccggag tgcacacatt tcctgccgtg 540
ctgcagagct ccggcctgta cagcctgtct agcgtggtga ccgtgccatc ctctagcctg 600
ggcacccaga catatatctg caacgtgaat cacaagccta gcaatacaaa ggtggacaag 660
aaggtggagc caaagtcctg tgataagacc cacacatgcc ccccttgtcc tgcaccagag 720
ctgctgggag gaccaagcgt gttcctgttt ccacccaagc ccaaggacac cctgatgatc 780
tctcgcaccc cagaggtgac atgcgtggtg gtggccgtga gccacgagga ccccgaggtg 840
aagtttaact ggtacgtgga tggcgtggag gtgcacaatg ccaagaccaa gccaagagag 900
gagcagtacg gctccaccta tagggtggtg tctgtgctga cagtgctgca ccaggattgg 960
ctgaacggca aggagtataa gtgcaaggtg tccaataagg ccctgcccgc ccctatcgag 1020
aagaccatct ctaaggcaaa gggacagcct agggagccac aggtgtacac cctgcctcca 1080
tcccgggacg agctgacaaa gaaccaggtg tctctgacgt gtctggtgaa gggcttctat 1140
ccctctgata tcgccgtgga gtgggagagc aatggccagc ctgagaacaa ttacaagacc 1200
acaccccctg tgctggacag cgatggctcc ttctttctgt atagcaagct gaccgtggat 1260
aagtcccggt ggcagcaggg caacgtgttt tcttgtagcg tgatgcacga ggccctgcac 1320
aatcactaca cacagaagtc cctgtctctg agccctggca agtga 1365
<210> 50
<211> 2268
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК hu scIL-12 mut2-hu IgG1 Fc DANG
<400> 50
atctgggagc tgaagaagga cgtgtacgtg gtggagctgg actggtatcc tgatgcccca 60
ggcgagatgg tggtgctgac ctgcgacaca cccgaggagg atggcatcac ctggacactg 120
gatcagagct ccgaggtgct gggcagcggc aagaccctga caatccaggt gaaggagttc 180
ggcgacgccg gccagtacac ctgtcacaag ggaggagagg tgctgagcca ctccctgctg 240
ctgctgcaca agaaggagga cggcatctgg agcacagaca tcctgaagga tcagaaggag 300
ccaaagaaca agaccttcct gcggtgcgag gccaagaatt attccggccg gttcacctgt 360
tggtggctga ccacaatctc caccgatctg acattttctg tgaagtctag caggggctcc 420
tctgaccccc agggagtgac atgcggagca gccaccctga gcgccgagcg ggtgagaggc 480
gataacaagg agtacgagta ttccgtggag tgccaggagg actctgcctg tcctgcagca 540
gaggagtccc tgccaatcga agtgatggtg gatgccgtgc acaagctgaa gtacgagaat 600
tatacaagct ccttctttat cagggacatc atcaagcctg atccccctaa gaacctgcag 660
ctgaagccac tgaagaatag ccgccaggtg gaggtgtcct gggagtaccc agacacctgg 720
tccacacccc actcttattt cagcctgacc ttttgcgtgc aggtgcaggg cgcctccgct 780
agggaggccg ctgaccgcgt gttcaccgat aagacatctg ccaccgtgat ctgtcggaag 840
aacgcctcta tcagcgtgcg ggcccaggat agatactatt ctagctcctg gagcgagtgg 900
gcctccgtgc cttgttctgg aggaggaggc agcggcggag gaggctccgg aggaggaggc 960
tctagaaatc tgccagtggc aacccctgac ccaggaatgt tcccttgcct gcaccactct 1020
cagaacctgc tgcgggccgt gagcaatatg ctgcagaagg ccagacagac actggagttt 1080
tacccctgta ccagcgagga gatcgaccac gaggatatca caaaggataa gacctccaca 1140
gtggaggcct gcctgcctct ggagctgacc aagaacgaga gctgtctgaa cagccgggag 1200
acatctttca tcaccaacgg cagctgcctg gcctccagaa agacatcttt tatgatggcc 1260
ctgtgcctgt ctagcatcta cgaggacctg aagatgtatc aggtggagtt caagaccatg 1320
aacgccaagc tgctgatgga cccaaagcgg cagatctttc tggatcagaa tatgctggcc 1380
gtgatcgacg agctgatgca ggccctgaac ttcaatagcg agacagtgcc ccagaagtcc 1440
tctctggagg agcctgactt ctacaagacc aagatcaagc tgtgcatcct gctgcacgcc 1500
ttccggatca gagccgtgac catcgataga gtgatgagct atctgaacgc aagcggcggc 1560
ggaggctctg gaggaggcgg cagcgacaag acccacacat gcccaccatg tccagcacct 1620
gagctgctgg gaggaccatc cgtgttcctg tttcctccaa agcccaagga tacactgatg 1680
atcagccgca cacctgaggt gacctgcgtg gtggtggccg tgtcccacga ggaccccgag 1740
gtgaagttta actggtacgt ggacggcgtg gaggtgcaca atgccaagac caagcccagg 1800
gaggagcagt acggctctac atatcgcgtg gtgagcgtgc tgaccgtgct gcaccaggac 1860
tggctgaacg gcaaggagta caagtgcaag gtgtctaata aggccctgcc agcccccatc 1920
gagaagacca tcagcaaggc aaagggacag ccaagggagc ctcaggtgta tacactgccc 1980
cctagccgcg atgagctgac caagaaccag gtgtccctga cttgtctcgt gaagggcttc 2040
tacccatccg acatcgccgt ggagtgggag tctaatggcc agcccgagaa caattataag 2100
accacaccac ccgtgctgga ctccgatggc tctttctttc tgtacagcaa gctgacagtg 2160
gacaagtcca gatggcagca gggcaacgtg tttagctgct ccgtgatgca cgaggccctg 2220
cacaatcact acacccagaa gtctctgagc ctgtcccctg gcaagtga 2268
<210> 51
<211> 1353
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu CD20 HC hu IgG1 Fc knob DANG
<400> 51
caggtgcagc tgcagcagcc aggagcagag ctggtgaagc ctggagcctc tgtgaagatg 60
agctgcaagg cctccggcta caccttcaca agctataaca tgcactgggt gaagcagacc 120
ccaggaaggg gactggagtg gatcggagcc atctaccctg gcaacggcga cacatcctat 180
aatcagaagt ttaagggcaa ggccaccctg acagccgata agagctcctc taccgcctac 240
atgcagctga gctccctgac aagcgaggac tccgccgtgt actattgcgc cagaagcacc 300
tactatggcg gcgattggta cttcaacgtg tggggagcag gaaccacagt gaccgtgtct 360
gccgccagca caaagggacc atccgtgttt ccactggcac catctagcaa gtctaccagc 420
ggaggaacag ccgccctggg atgtctggtg aaggactact tcccagagcc cgtgaccgtg 480
tcctggaact ctggcgccct gacctccgga gtgcacacat ttcccgccgt gctgcagtcc 540
tctggcctgt actctctgag ctccgtggtg accgtgcctt ctagctccct gggcacccag 600
acatatatct gcaacgtgaa tcacaagcct tccaatacaa aggtggacaa gaaggtggag 660
ccaaagtctt gtgataagac ccacacatgc cccccttgtc ctgcaccaga gctgctggga 720
ggaccaagcg tgttcctgtt tccacccaag cccaaggaca ccctgatgat cagcaggacc 780
cctgaggtga catgcgtggt ggtggccgtg tcccacgagg acccagaggt gaagttcaac 840
tggtacgtgg atggcgtgga ggtgcacaat gccaagacaa agccacggga ggagcagtac 900
ggctctacct atagagtggt gagcgtgctg acagtgctgc accaggattg gctgaacggc 960
aaggagtata agtgcaaggt gtctaataag gccctgcccg cccctatcga gaagaccatc 1020
agcaaggcca agggccagcc tagggagcca caggtgtaca ccctgcctcc atctcgcgac 1080
gagctgacaa agaaccaggt gagcctgtgg tgtctggtga agggcttcta tccaagcgat 1140
atcgccgtgg agtgggagtc caatggccag cccgagaaca attacaagac cacaccccct 1200
gtgctggaca gcgatggctc cttctttctg tattccaagc tgaccgtgga taagtctaga 1260
tggcagcagg gcaacgtgtt ttcctgttct gtgatgcacg aggccctgca caatcactac 1320
acacagaaga gcctgtccct gtctcctggc aag 1353
<210> 52
<211> 639
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-hu CD20 LC
<400> 52
cagatcgtgc tgagccagtc cccagcaatc ctgtctgcca gccctggaga gaaggtgacc 60
atgacatgcc gggccagctc ctctgtgagc tacatccact ggttccagca gaagccaggc 120
agctccccta agccatggat ctatgccaca agcaacctgg catccggagt gcccgtgcgg 180
ttttccggct ctggcagcgg cacctcctac tctctgacaa tcagcagagt ggaggcagag 240
gacgcagcaa cctactattg ccagcagtgg acctccaatc cccctacatt cggcggcggc 300
accaagctgg agatcaagag gacagtggcc gccccttccg tgttcatctt tccaccctct 360
gacgagcagc tgaagtctgg caccgccagc gtggtgtgcc tgctgaacaa cttctaccca 420
cgcgaggcca aggtgcagtg gaaggtggat aacgccctgc agagcggcaa ttcccaggag 480
tctgtgacag agcaggacag caaggattcc acctattctc tgtctagcac cctgacactg 540
agcaaggccg attacgagaa gcacaaggtg tatgcctgcg aggtgacaca ccagggcctg 600
tcctctcccg tgaccaagtc cttcaacagg ggcgagtgt 639
<210> 53
<211> 1341
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP HC mu IgG2a Fc knob DANG
<400> 53
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cgccaagacc 360
acagcaccaa gcgtgtatcc actggcaccc gtgtgcggcg ataccacagg ctctagcgtg 420
accctgggct gtctggtgaa gggctacttc cctgagccag tgaccctgac atggaacagc 480
ggctctctgt cctctggcgt gcacaccttt cctgccgtgc tgcagtccga tctgtataca 540
ctgagctcct ctgtgaccgt gacaagctcc acctggccca gccagtccat cacatgcaac 600
gtggcccacc ctgcctctag caccaaggtg gacaagaaga tcgagccacg gggccccaca 660
atcaagccat gtccaccttg caagtgtcca gcacctaatc tgctgggagg acctagcgtg 720
ttcatctttc cacccaagat caaggacgtg ctgatgatct ctctgagccc tatcgtgacc 780
tgcgtggtgg tggccgtgtc tgaggacgat ccagatgtgc agatcagctg gttcgtgaac 840
aatgtggagg tgcacaccgc ccagacccag acacaccggg aggactacgg ctccacactg 900
agagtggtgt ctgccctgcc catccagcac caggactgga tgtccggcaa ggagtttaag 960
tgcaaggtga acaataagga tctgccagcc cccatcgaga ggaccatctc taagcctaag 1020
ggcagcgtgc gcgcaccaca ggtgtatgtg ctgcctccac ccgaggagga gatgaccaag 1080
aagcaggtga cactgtggtg tatggtgacc gacttcatgc cagaggatat ctacgtggag 1140
tggaccaaca atggcaagac agagctgaac tataagaata cagagcccgt gctggacagc 1200
gatggctcct actttatgta tagcaagctg agggtggaga agaagaactg ggtggagcgc 1260
aattcctact cttgtagcgt ggtgcacgag ggcctgcaca accaccacac cacaaagtcc 1320
ttttctagaa cccccggcaa g 1341
<210> 54
<211> 639
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP LC
<400> 54
cagatcgtgc tgacacagtc ccctgccatc atgtctgcca gcccaggcga gaaggtgacc 60
atgacatgct ctgccagctc cggcgtgaac ttcatgcact ggtaccagca gaagtctggc 120
acaagcccca agcggtggat cttcgacacc tccaagctgg cctctggcgt gcctgccaga 180
ttttccggct ctggcagcgg cacatcctat tctctgacca tctctagcat ggaggccgag 240
gacgccgcca cctactattg ccagcagtgg agcttcaatc cccctacatt tggcggcggc 300
accaagctgg agatcaagag ggcagatgca gcaccaacag tgtccatctt tccaccctcc 360
tctgagcagc tgaccagcgg aggagcatcc gtggtgtgct tcctgaacaa cttctacccc 420
aaggacatca acgtgaagtg gaagatcgat ggctctgaga ggcagaacgg cgtgctgaat 480
agctggacag accaggattc caaggactct acctatagca tgagctccac cctgacactg 540
accaaggatg agtacgagag gcacaatagc tatacatgcg aggccaccca caagacaagc 600
acctccccta tcgtgaagtc cttcaaccgc aatgagtgt 639
<210> 55
<211> 2292
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu scIL-12-mu IgG2a Fc hole DANG
<400> 55
atgtgggagc tggagaagga cgtgtacgtg gtggaggtgg attggacacc tgacgccccc 60
ggcgagacag tgaacctgac atgcgatacc cctgaggagg atgatatcac atggacctcc 120
gatcagagac acggcgtgat cggcagcggc aagaccctga caatcaccgt gaaggagttt 180
ctggatgccg gccagtacac ctgtcacaag ggcggcgaga cactgagcca ctcccacctg 240
ctgctgcaca agaaggagaa tggcatctgg tccaccgaga tcctgaagaa cttcaagaac 300
aagaccttcc tgaagtgtga ggcccctaat tactccggca ggtttacatg ctcctggctg 360
gtgcagagaa acatggacct gaagtttaat atcaagagct cctcctccag ccccgatagc 420
agagccgtga cctgtggcat ggccagcctg agcgccgaga aggtgaccct ggatcagagg 480
gattacgaga agtactccgt gtcctgtcag gaggatgtga catgtcctac agccgaggag 540
acactgccta tcgagctggc cctggaggcc aggcagcaga ataagtacga gaactacagc 600
acaagctttt tcatcaggga catcatcaag cccgatcccc ccaagaacct gcagatgaag 660
cccctgaaga acagccaggt ggaggtgtcc tgggagtacc ctgatagctg gtccacccct 720
cactcctact tctccctgaa gttctttgtg agaatccaga gaaagaagga gaagatgaag 780
gagacagagg agggctgcaa tcagaagggc gccttcctgg tggagaagac atccaccgag 840
gtgcagtgta agggcggcaa cgtgtgcgtg caggcccagg acagatacta caattccagc 900
tgtagcaagt gggcctgtgt gccttgtaga gtgagatccg gcggcggcgg ctccggagga 960
ggaggaagcg gaggaggcgg ctccagagtg atccctgtgt ccggccctgc cagatgtctg 1020
tcccagagca gaaacctgct gaagaccaca gacgacatgg tgaagacagc cagagagaag 1080
ctgaagcact acagctgcac cgccgaggac atcgaccacg aggatatcac aagagaccag 1140
acatccaccc tgaagacatg tctgcctctg gagctgcaca agaatgagtc ctgcctggcc 1200
accagagaga cctccagcac caccaggggc agctgcctgc cccctcagaa gacctccctg 1260
atgatgacac tgtgcctggg cagcatctac gaggacctga agatgtacca gaccgagttc 1320
caggccatca atgccgccct gcagaaccac aaccaccagc agatcatcct ggataagggc 1380
atgctggtgg ccatcgacga gctgatgcag agcctgaacc acaatggcga gaccctgagg 1440
cagaagcctc ctgtgggcga ggccgatccc tacagagtga agatgaagct gtgtatcctg 1500
ctgcacgcct tttccacaag ggtggtgacc atcaacaggg tcatgggcta cctgtccagc 1560
gccggcggcg gcggcagcgg aggaggaggc tccgagccac gcggccccac aatcaagcca 1620
tgcccccctt gcaagtgtcc tgcaccaaat ctgctgggag gaccatccgt gttcatcttt 1680
ccacccaaga tcaaggacgt gctgatgatc agcctgtccc caatcgtgac ctgcgtggtc 1740
gtggccgtga gcgaggacga tcctgatgtg cagatctcct ggttcgtgaa caatgtggag 1800
gtgcacaccg cccagaccca gacacaccgg gaggactacg gctccacact gagagtggtg 1860
tctgccctgc ccatccagca ccaggactgg atgagcggca aggagtttaa gtgcaaggtg 1920
aacaataagg atctgcccgc ccctatcgag cggacaatct ctaagcctaa gggcagcgtg 1980
agagccccac aggtgtatgt gctgcctcca cccgaggagg agatgaccaa gaagcaggtg 2040
acactgtctt gtgccgtgac cgacttcatg cctgaggata tctatgtgga gtggaccaac 2100
aatggcaaga cagagctgaa ctacaagaat acagagccag tgctggactc cgatggctct 2160
tacttcatgg tgagcaagct gagggtggag aagaagaact gggtggagcg caattcttac 2220
agctgctccg tggtgcacga gggcctgcac aaccaccaca ccacaaagtc ttttagccgg 2280
acccctggca ag 2292
<210> 56
<211> 2292
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu scIL-12 mut1-mu IgG2a Fc hole DANG
<400> 56
atgtgggagc tggagaagga cgtgtacgtg gtggaggtgg attggacacc tgacgccccc 60
ggcgagacag tgaacctgac atgcgatacc cctgaggagg atgatatcac atggacctcc 120
gatcagagac acggcgtgat cggcagcggc aagaccctga caatcaccgt gaaggagttt 180
ctggatgccg gccagtacac ctgtcacaag ggcggcgaga cactgagcca ctcccacctg 240
ctgctgcaca agaaggagaa tggcatctgg tccaccgaga tcctgaagaa cttcaagaac 300
aagaccttcc tgaagtgtga ggcccctaat tactccggca ggtttacatg ctcctggctg 360
gtgcagagaa acatggacct gaagtttaat atcaagagct cctcctccag ccccgatagc 420
agagccgtga cctgtggcat ggccagcctg agcgccgaga aggtgaccct ggatcagagg 480
gattacgaga agtactccgt gtcctgtcag gaggatgtga catgtcctac agccgaggag 540
acactgccta tcgagctggc cctggaggcc aggcagcaga ataagtacga gaactacagc 600
acaagctttt tcatcaggga catcatcaag cccgatcccc ccaagaacct gcagatgaag 660
cccctgaaga acagccaggt ggaggtgtcc tgggagtacc ctgatagctg gtccacccct 720
cactcctact tctccctgaa gttctttgtg agaatccaga gagccaagga gaagatggcc 780
gagacagagg agggctgcaa tcagaagggc gccttcctgg tggagaagac atccaccgag 840
gtgcagtgta agggcggcaa cgtgtgcgtg caggcccagg acagatacta caattccagc 900
tgtagcaagt gggcctgtgt gccttgtaga gtgagatccg gcggcggcgg ctccggagga 960
ggaggaagcg gaggaggcgg ctccagagtg atccctgtgt ccggccctgc cagatgtctg 1020
tcccagagca gaaacctgct gaagaccaca gacgacatgg tgaagacagc cagagagaag 1080
ctgaagcact acagctgcac cgccgaggac atcgaccacg aggatatcac aagagaccag 1140
acatccaccc tgaagacatg tctgcctctg gagctgcaca agaatgagtc ctgcctggcc 1200
accagagaga cctccagcac caccaggggc agctgcctgc cccctcagaa gacctccctg 1260
atgatgacac tgtgcctggg cagcatctac gaggacctga agatgtacca gaccgagttc 1320
caggccatca atgccgccct gcagaaccac aaccaccagc agatcatcct ggataagggc 1380
atgctggtgg ccatcgacga gctgatgcag agcctgaacc acaatggcga gaccctgagg 1440
cagaagcctc ctgtgggcga ggccgatccc tacagagtga agatgaagct gtgtatcctg 1500
ctgcacgcct tttccacaag ggtggtgacc atcaacaggg tcatgggcta cctgtccagc 1560
gccggcggcg gcggcagcgg aggaggaggc tccgagccac gcggccccac aatcaagcca 1620
tgcccccctt gcaagtgtcc tgcaccaaat ctgctgggag gaccatccgt gttcatcttt 1680
ccacccaaga tcaaggacgt gctgatgatc agcctgtccc caatcgtgac ctgcgtggtc 1740
gtggccgtga gcgaggacga tcctgatgtg cagatctcct ggttcgtgaa caatgtggag 1800
gtgcacaccg cccagaccca gacacaccgg gaggactacg gctccacact gagagtggtg 1860
tctgccctgc ccatccagca ccaggactgg atgagcggca aggagtttaa gtgcaaggtg 1920
aacaataagg atctgcccgc ccctatcgag cggacaatct ctaagcctaa gggcagcgtg 1980
agagccccac aggtgtatgt gctgcctcca cccgaggagg agatgaccaa gaagcaggtg 2040
acactgtctt gtgccgtgac cgacttcatg cctgaggata tctatgtgga gtggaccaac 2100
aatggcaaga cagagctgaa ctacaagaat acagagccag tgctggactc cgatggctct 2160
tacttcatgg tgagcaagct gagggtggag aagaagaact gggtggagcg caattcttac 2220
agctgctccg tggtgcacga gggcctgcac aaccaccaca ccacaaagtc ttttagccgg 2280
acccctggca ag 2292
<210> 57
<211> 2292
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu scIL-12 mut2-mu IgG2a Fc hole DANG
<400> 57
atgtgggagc tggagaagga cgtgtacgtg gtggaggtgg attggacacc tgacgccccc 60
ggcgagacag tgaacctgac atgcgatacc cctgaggagg atgatatcac atggacctcc 120
gatcagagac acggcgtgat cggcagcggc aagaccctga caatcaccgt gaaggagttt 180
ctggatgccg gccagtacac ctgtcacaag ggcggcgaga cactgagcca ctcccacctg 240
ctgctgcaca agaaggagaa tggcatctgg tccaccgaga tcctgaagaa cttcaagaac 300
aagaccttcc tgaagtgtga ggcccctaat tactccggca ggtttacatg ctcctggctg 360
gtgcagagaa acatggacct gaagtttaat atcaagagct cctcctccag ccccgatagc 420
agagccgtga cctgtggcat ggccagcctg agcgccgaga aggtgaccct ggatcagagg 480
gattacgaga agtactccgt gtcctgtcag gaggatgtga catgtcctac agccgaggag 540
acactgccta tcgagctggc cctggaggcc aggcagcaga ataagtacga gaactacagc 600
acaagctttt tcatcaggga catcatcaag cccgatcccc ccaagaacct gcagatgaag 660
cccctgaaga acagccaggt ggaggtgtcc tgggagtacc ctgatagctg gtccacccct 720
cactcctact tctccctgaa gttctttgtg agaatccagg ctgccgccga gaagatggcc 780
gagacagagg agggctgcaa tcagaagggc gccttcctgg tggagaagac atccaccgag 840
gtgcagtgta agggcggcaa cgtgtgcgtg caggcccagg acagatacta caattccagc 900
tgtagcaagt gggcctgtgt gccttgtaga gtgagatccg gcggcggcgg ctccggagga 960
ggaggaagcg gaggaggcgg ctccagagtg atccctgtgt ccggccctgc cagatgtctg 1020
tcccagagca gaaacctgct gaagaccaca gacgacatgg tgaagacagc cagagagaag 1080
ctgaagcact acagctgcac cgccgaggac atcgaccacg aggatatcac aagagaccag 1140
acatccaccc tgaagacatg tctgcctctg gagctgcaca agaatgagtc ctgcctggcc 1200
accagagaga cctccagcac caccaggggc agctgcctgc cccctcagaa gacctccctg 1260
atgatgacac tgtgcctggg cagcatctac gaggacctga agatgtacca gaccgagttc 1320
caggccatca atgccgccct gcagaaccac aaccaccagc agatcatcct ggataagggc 1380
atgctggtgg ccatcgacga gctgatgcag agcctgaacc acaatggcga gaccctgagg 1440
cagaagcctc ctgtgggcga ggccgatccc tacagagtga agatgaagct gtgtatcctg 1500
ctgcacgcct tttccacaag ggtggtgacc atcaacaggg tcatgggcta cctgtccagc 1560
gccggcggcg gcggcagcgg aggaggaggc tccgagccac gcggccccac aatcaagcca 1620
tgcccccctt gcaagtgtcc tgcaccaaat ctgctgggag gaccatccgt gttcatcttt 1680
ccacccaaga tcaaggacgt gctgatgatc agcctgtccc caatcgtgac ctgcgtggtc 1740
gtggccgtga gcgaggacga tcctgatgtg cagatctcct ggttcgtgaa caatgtggag 1800
gtgcacaccg cccagaccca gacacaccgg gaggactacg gctccacact gagagtggtg 1860
tctgccctgc ccatccagca ccaggactgg atgagcggca aggagtttaa gtgcaaggtg 1920
aacaataagg atctgcccgc ccctatcgag cggacaatct ctaagcctaa gggcagcgtg 1980
agagccccac aggtgtatgt gctgcctcca cccgaggagg agatgaccaa gaagcaggtg 2040
acactgtctt gtgccgtgac cgacttcatg cctgaggata tctatgtgga gtggaccaac 2100
aatggcaaga cagagctgaa ctacaagaat acagagccag tgctggactc cgatggctct 2160
tacttcatgg tgagcaagct gagggtggag aagaagaact gggtggagcg caattcttac 2220
agctgctccg tggtgcacga gggcctgcac aaccaccaca ccacaaagtc ttttagccgg 2280
acccctggca ag 2292
<210> 58
<211> 1737
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК (anti-mu FAP VH)2, mu IgG2a knob DANG
<400> 58
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cggaggtgga 360
ggctcaggtg gtggcggatc tggaggaggc ggtagtcagg tgcagctgca gcagtccgga 420
gcagagctgg caaggcctgg agcctctgtg aacctgagct gcaaggcctc cggctacacc 480
ttcacaaaca atggcatcaa ttggctgaag cagaggaccg gacagggact ggagtggatc 540
ggcgagatct acccaagatc taccaacaca ctgtataatg agaagttcaa gggcaaggcc 600
accctgacag cagaccggag ctccaacacc gcctacatgg agctgagaag cctgacatcc 660
gaggattctg ccgtgtattt ttgtgcacgc accctgacag cacccttcgc cttttgggga 720
cagggcaccc tggtgacagt gagcgccgcc aagaccacag caccaagcgt gtatccactg 780
gcacccgtgt gcggcgatac cacaggctct agcgtgaccc tgggctgtct ggtgaagggc 840
tacttccctg agccagtgac cctgacatgg aacagcggct ctctgtcctc tggcgtgcac 900
acctttcctg ccgtgctgca gtccgatctg tatacactga gctcctctgt gaccgtgaca 960
agctccacct ggcccagcca gtccatcaca tgcaacgtgg cccaccctgc ctctagcacc 1020
aaggtggaca agaagatcga gccacggggc cccacaatca agccatgtcc accttgcaag 1080
tgtccagcac ctaatctgct gggaggacct agcgtgttca tctttccacc caagatcaag 1140
gacgtgctga tgatctctct gagccctatc gtgacctgcg tggtggtggc cgtgtctgag 1200
gacgatccag atgtgcagat cagctggttc gtgaacaatg tggaggtgca caccgcccag 1260
acccagacac accgggagga ctacggctcc acactgagag tggtgtctgc cctgcccatc 1320
cagcaccagg actggatgtc cggcaaggag tttaagtgca aggtgaacaa taaggatctg 1380
ccagccccca tcgagaggac catctctaag cctaagggca gcgtgcgcgc accacaggtg 1440
tatgtgctgc ctccacccga ggaggagatg accaagaagc aggtgacact gtggtgtatg 1500
gtgaccgact tcatgccaga ggatatctac gtggagtgga ccaacaatgg caagacagag 1560
ctgaactata agaatacaga gcccgtgctg gacagcgatg gctcctactt tatgtatagc 1620
aagctgaggg tggagaagaa gaactgggtg gagcgcaatt cctactcttg tagcgtggtg 1680
cacgagggcc tgcacaacca ccacaccaca aagtcctttt ctagaacccc cggcaag 1737
<210> 59
<211> 1002
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК (anti-mu FAP VL)2
<400> 59
cagatcgtgc tgacacagtc ccctgccatc atgtctgcca gcccaggcga gaaggtgacc 60
atgacatgct ctgccagctc cggcgtgaac ttcatgcact ggtaccagca gaagtctggc 120
acaagcccca agcggtggat cttcgacacc tccaagctgg cctctggcgt gcctgccaga 180
ttttccggct ctggcagcgg cacatcctat tctctgacca tctctagcat ggaggccgag 240
gacgccgcca cctactattg ccagcagtgg agcttcaatc cccctacatt tggcggcggc 300
accaagctgg agatcaaggg aggtggaggc tcaggtggtg gcggatctgg aggaggcggt 360
agtcagatcg tgctgacaca gtcccctgcc atcatgtctg ccagcccagg cgagaaggtg 420
accatgacat gctctgccag ctccggcgtg aacttcatgc actggtacca gcagaagtct 480
ggcacaagcc ccaagcggtg gatcttcgac acctccaagc tggcctctgg cgtgcctgcc 540
agattttccg gctctggcag cggcacatcc tattctctga ccatctctag catggaggcc 600
gaggacgccg ccacctacta ttgccagcag tggagcttca atccccctac atttggcggc 660
ggcaccaagc tggagatcaa gagggcagat gcagcaccaa cagtgtccat ctttccaccc 720
tcctctgagc agctgaccag cggaggagca tccgtggtgt gcttcctgaa caacttctac 780
cccaaggaca tcaacgtgaa gtggaagatc gatggctctg agaggcagaa cggcgtgctg 840
aatagctgga cagaccagga ttccaaggac tctacctata gcatgagctc caccctgaca 900
ctgaccaagg atgagtacga gaggcacaat agctatacat gcgaggccac ccacaagaca 960
agcacctccc ctatcgtgaa gtccttcaac cgcaatgagt gt 1002
<210> 60
<211> 2115
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP HC mu IgG2a Fc knob
DANG-anti-mu FAP scFv
<400> 60
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cgccaagacc 360
acagcaccaa gcgtgtatcc actggcaccc gtgtgcggcg ataccacagg ctctagcgtg 420
accctgggct gtctggtgaa gggctacttc cctgagccag tgaccctgac atggaacagc 480
ggctctctgt cctctggcgt gcacaccttt cctgccgtgc tgcagtccga tctgtataca 540
ctgagctcct ctgtgaccgt gacaagctcc acctggccca gccagtccat cacatgcaac 600
gtggcccacc ctgcctctag caccaaggtg gacaagaaga tcgagccacg gggccccaca 660
atcaagccat gtccaccttg caagtgtcca gcacctaatc tgctgggagg acctagcgtg 720
ttcatctttc cacccaagat caaggacgtg ctgatgatct ctctgagccc tatcgtgacc 780
tgcgtggtgg tggccgtgtc tgaggacgat ccagatgtgc agatcagctg gttcgtgaac 840
aatgtggagg tgcacaccgc ccagacccag acacaccggg aggactacgg ctccacactg 900
agagtggtgt ctgccctgcc catccagcac caggactgga tgtccggcaa ggagtttaag 960
tgcaaggtga acaataagga tctgccagcc cccatcgaga ggaccatctc taagcctaag 1020
ggcagcgtgc gcgcaccaca ggtgtatgtg ctgcctccac ccgaggagga gatgaccaag 1080
aagcaggtga cactgtggtg tatggtgacc gacttcatgc cagaggatat ctacgtggag 1140
tggaccaaca atggcaagac agagctgaac tataagaata cagagcccgt gctggacagc 1200
gatggctcct actttatgta tagcaagctg agggtggaga agaagaactg ggtggagcgc 1260
aattcctact cttgtagcgt ggtgcacgag ggcctgcaca accaccacac cacaaagtcc 1320
ttttctagaa cccccggcaa gggaggtgga ggctcaggtg gtggcggatc tggaggaggc 1380
ggtagtcagg tgcagctgca gcagtccgga gcagagctgg caaggcctgg agcctctgtg 1440
aacctgagct gcaaggcctc cggctacacc ttcacaaaca atggcatcaa ttggctgaag 1500
cagaggaccg gacagggact ggagtggatc ggcgagatct acccaagatc taccaacaca 1560
ctgtataatg agaagttcaa gggcaaggcc accctgacag cagaccggag ctccaacacc 1620
gcctacatgg agctgagaag cctgacatcc gaggattctg ccgtgtattt ttgtgcacgc 1680
accctgacag cacccttcgc cttttgggga cagggcaccc tggtgacagt gagcgccggt 1740
ggcggaggat caggaggagg cggtagtggc ggcggaggtt ctggtggagg aggtagccag 1800
atcgtgctga cacagtcccc tgccatcatg tctgccagcc caggcgagaa ggtgaccatg 1860
acatgctctg ccagctccgg cgtgaacttc atgcactggt accagcagaa gtctggcaca 1920
agccccaagc ggtggatctt cgacacctcc aagctggcct ctggcgtgcc tgccagattt 1980
tccggctctg gcagcggcac atcctattct ctgaccatct ctagcatgga ggccgaggac 2040
gccgccacct actattgcca gcagtggagc ttcaatcccc ctacatttgg cggcggcacc 2100
aagctggaga tcaag 2115
<210> 61
<211> 1413
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP LC-anti-mu FAP scFv
<400> 61
cagatcgtgc tgacacagtc ccctgccatc atgtctgcca gcccaggcga gaaggtgacc 60
atgacatgct ctgccagctc cggcgtgaac ttcatgcact ggtaccagca gaagtctggc 120
acaagcccca agcggtggat cttcgacacc tccaagctgg cctctggcgt gcctgccaga 180
ttttccggct ctggcagcgg cacatcctat tctctgacca tctctagcat ggaggccgag 240
gacgccgcca cctactattg ccagcagtgg agcttcaatc cccctacatt tggcggcggc 300
accaagctgg agatcaagag ggcagatgca gcaccaacag tgtccatctt tccaccctcc 360
tctgagcagc tgaccagcgg aggagcatcc gtggtgtgct tcctgaacaa cttctacccc 420
aaggacatca acgtgaagtg gaagatcgat ggctctgaga ggcagaacgg cgtgctgaat 480
agctggacag accaggattc caaggactct acctatagca tgagctccac cctgacactg 540
accaaggatg agtacgagag gcacaatagc tatacatgcg aggccaccca caagacaagc 600
acctccccta tcgtgaagtc cttcaaccgc aatgagtgtg gaggtggagg ctcaggtggt 660
ggcggatctg gaggaggcgg tagtcaggtg cagctgcagc agtccggagc agagctggca 720
aggcctggag cctctgtgaa cctgagctgc aaggcctccg gctacacctt cacaaacaat 780
ggcatcaatt ggctgaagca gaggaccgga cagggactgg agtggatcgg cgagatctac 840
ccaagatcta ccaacacact gtataatgag aagttcaagg gcaaggccac cctgacagca 900
gaccggagct ccaacaccgc ctacatggag ctgagaagcc tgacatccga ggattctgcc 960
gtgtattttt gtgcacgcac cctgacagca cccttcgcct tttggggaca gggcaccctg 1020
gtgacagtga gcgccggtgg cggaggatca ggaggaggcg gtagtggcgg cggaggttct 1080
ggtggaggag gtagccagat cgtgctgaca cagtcccctg ccatcatgtc tgccagccca 1140
ggcgagaagg tgaccatgac atgctctgcc agctccggcg tgaacttcat gcactggtac 1200
cagcagaagt ctggcacaag ccccaagcgg tggatcttcg acacctccaa gctggcctct 1260
ggcgtgcctg ccagattttc cggctctggc agcggcacat cctattctct gaccatctct 1320
agcatggagg ccgaggacgc cgccacctac tattgccagc agtggagctt caatccccct 1380
acatttggcg gcggcaccaa gctggagatc aag 1413
<210> 62
<211> 2946
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP HC mu IgG2a Fc hole
DANG-mu scIL-12
<400> 62
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cgccaagacc 360
acagcaccaa gcgtgtatcc actggcaccc gtgtgcggcg ataccacagg ctctagcgtg 420
accctgggct gtctggtgaa gggctacttc cctgagccag tgaccctgac atggaacagc 480
ggctctctgt cctctggcgt gcacaccttt cctgccgtgc tgcagtccga tctgtataca 540
ctgagctcct ctgtgaccgt gacaagctcc acctggccca gccagtccat cacatgcaac 600
gtggcccacc ctgcctctag caccaaggtg gacaagaaga tcgagccacg cggccccaca 660
atcaagccat gccccccttg caagtgtcct gcaccaaatc tgctgggagg accatccgtg 720
ttcatctttc cacccaagat caaggacgtg ctgatgatca gcctgtcccc aatcgtgacc 780
tgcgtggtcg tggccgtgag cgaggacgat cctgatgtgc agatctcctg gttcgtgaac 840
aatgtggagg tgcacaccgc ccagacccag acacaccggg aggactacgg ctccacactg 900
agagtggtgt ctgccctgcc catccagcac caggactgga tgagcggcaa ggagtttaag 960
tgcaaggtga acaataagga tctgcccgcc cctatcgagc ggacaatctc taagcctaag 1020
ggcagcgtga gagccccaca ggtgtatgtg ctgcctccac ccgaggagga gatgaccaag 1080
aagcaggtga cactgtcttg tgccgtgacc gacttcatgc ctgaggatat ctatgtggag 1140
tggaccaaca atggcaagac agagctgaac tacaagaata cagagccagt gctggactcc 1200
gatggctctt acttcatggt gagcaagctg agggtggaga agaagaactg ggtggagcgc 1260
aattcttaca gctgctccgt ggtgcacgag ggcctgcaca accaccacac cacaaagtct 1320
tttagccgga cccctggcgg tggaggtggc tcaggaggag gcggttctgg cggaggaggt 1380
agtatgtggg agctggagaa ggacgtgtac gtggtggagg tggattggac acctgacgcc 1440
cccggcgaga cagtgaacct gacatgcgat acccctgagg aggatgatat cacatggacc 1500
tccgatcaga gacacggcgt gatcggcagc ggcaagaccc tgacaatcac cgtgaaggag 1560
tttctggatg ccggccagta cacctgtcac aagggcggcg agacactgag ccactcccac 1620
ctgctgctgc acaagaagga gaatggcatc tggtccaccg agatcctgaa gaacttcaag 1680
aacaagacct tcctgaagtg tgaggcccct aattactccg gcaggtttac atgctcctgg 1740
ctggtgcaga gaaacatgga cctgaagttt aatatcaaga gctcctcctc cagccccgat 1800
agcagagccg tgacctgtgg catggccagc ctgagcgccg agaaggtgac cctggatcag 1860
agggattacg agaagtactc cgtgtcctgt caggaggatg tgacatgtcc tacagccgag 1920
gagacactgc ctatcgagct ggccctggag gccaggcagc agaataagta cgagaactac 1980
agcacaagct ttttcatcag ggacatcatc aagcccgatc cccccaagaa cctgcagatg 2040
aagcccctga agaacagcca ggtggaggtg tcctgggagt accctgatag ctggtccacc 2100
cctcactcct acttctccct gaagttcttt gtgagaatcc agagaaagaa ggagaagatg 2160
aaggagacag aggagggctg caatcagaag ggcgccttcc tggtggagaa gacatccacc 2220
gaggtgcagt gtaagggcgg caacgtgtgc gtgcaggccc aggacagata ctacaattcc 2280
agctgtagca agtgggcctg tgtgccttgt agagtgagat ccggcggcgg cggctccgga 2340
ggaggaggaa gcggaggagg cggctccaga gtgatccctg tgtccggccc tgccagatgt 2400
ctgtcccaga gcagaaacct gctgaagacc acagacgaca tggtgaagac agccagagag 2460
aagctgaagc actacagctg caccgccgag gacatcgacc acgaggatat cacaagagac 2520
cagacatcca ccctgaagac atgtctgcct ctggagctgc acaagaatga gtcctgcctg 2580
gccaccagag agacctccag caccaccagg ggcagctgcc tgccccctca gaagacctcc 2640
ctgatgatga cactgtgcct gggcagcatc tacgaggacc tgaagatgta ccagaccgag 2700
ttccaggcca tcaatgccgc cctgcagaac cacaaccacc agcagatcat cctggataag 2760
ggcatgctgg tggccatcga cgagctgatg cagagcctga accacaatgg cgagaccctg 2820
aggcagaagc ctcctgtggg cgaggccgat ccctacagag tgaagatgaa gctgtgtatc 2880
ctgctgcacg ccttttccac aagggtggtg accatcaaca gggtcatggg ctacctgtcc 2940
agcgcc 2946
<210> 63
<211> 2946
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP HC mu IgG2a Fc hole
DANG-mu scIL-12 mut2
<400> 63
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cgccaagacc 360
acagcaccaa gcgtgtatcc actggcaccc gtgtgcggcg ataccacagg ctctagcgtg 420
accctgggct gtctggtgaa gggctacttc cctgagccag tgaccctgac atggaacagc 480
ggctctctgt cctctggcgt gcacaccttt cctgccgtgc tgcagtccga tctgtataca 540
ctgagctcct ctgtgaccgt gacaagctcc acctggccca gccagtccat cacatgcaac 600
gtggcccacc ctgcctctag caccaaggtg gacaagaaga tcgagccacg cggccccaca 660
atcaagccat gccccccttg caagtgtcct gcaccaaatc tgctgggagg accatccgtg 720
ttcatctttc cacccaagat caaggacgtg ctgatgatca gcctgtcccc aatcgtgacc 780
tgcgtggtcg tggccgtgag cgaggacgat cctgatgtgc agatctcctg gttcgtgaac 840
aatgtggagg tgcacaccgc ccagacccag acacaccggg aggactacgg ctccacactg 900
agagtggtgt ctgccctgcc catccagcac caggactgga tgagcggcaa ggagtttaag 960
tgcaaggtga acaataagga tctgcccgcc cctatcgagc ggacaatctc taagcctaag 1020
ggcagcgtga gagccccaca ggtgtatgtg ctgcctccac ccgaggagga gatgaccaag 1080
aagcaggtga cactgtcttg tgccgtgacc gacttcatgc ctgaggatat ctatgtggag 1140
tggaccaaca atggcaagac agagctgaac tacaagaata cagagccagt gctggactcc 1200
gatggctctt acttcatggt gagcaagctg agggtggaga agaagaactg ggtggagcgc 1260
aattcttaca gctgctccgt ggtgcacgag ggcctgcaca accaccacac cacaaagtct 1320
tttagccgga cccctggcgg tggaggtggc tcaggaggag gcggttctgg cggaggaggt 1380
agtatgtggg agctggagaa ggacgtgtac gtggtggagg tggattggac acctgacgcc 1440
cccggcgaga cagtgaacct gacatgcgat acccctgagg aggatgatat cacatggacc 1500
tccgatcaga gacacggcgt gatcggcagc ggcaagaccc tgacaatcac cgtgaaggag 1560
tttctggatg ccggccagta cacctgtcac aagggcggcg agacactgag ccactcccac 1620
ctgctgctgc acaagaagga gaatggcatc tggtccaccg agatcctgaa gaacttcaag 1680
aacaagacct tcctgaagtg tgaggcccct aattactccg gcaggtttac atgctcctgg 1740
ctggtgcaga gaaacatgga cctgaagttt aatatcaaga gctcctcctc cagccccgat 1800
agcagagccg tgacctgtgg catggccagc ctgagcgccg agaaggtgac cctggatcag 1860
agggattacg agaagtactc cgtgtcctgt caggaggatg tgacatgtcc tacagccgag 1920
gagacactgc ctatcgagct ggccctggag gccaggcagc agaataagta cgagaactac 1980
agcacaagct ttttcatcag ggacatcatc aagcccgatc cccccaagaa cctgcagatg 2040
aagcccctga agaacagcca ggtggaggtg tcctgggagt accctgatag ctggtccacc 2100
cctcactcct acttctccct gaagttcttt gtgagaatcc aggctgccgc cgagaagatg 2160
gccgagacag aggagggctg caatcagaag ggcgccttcc tggtggagaa gacatccacc 2220
gaggtgcagt gtaagggcgg caacgtgtgc gtgcaggccc aggacagata ctacaattcc 2280
agctgtagca agtgggcctg tgtgccttgt agagtgagat ccggcggcgg cggctccgga 2340
ggaggaggaa gcggaggagg cggctccaga gtgatccctg tgtccggccc tgccagatgt 2400
ctgtcccaga gcagaaacct gctgaagacc acagacgaca tggtgaagac agccagagag 2460
aagctgaagc actacagctg caccgccgag gacatcgacc acgaggatat cacaagagac 2520
cagacatcca ccctgaagac atgtctgcct ctggagctgc acaagaatga gtcctgcctg 2580
gccaccagag agacctccag caccaccagg ggcagctgcc tgccccctca gaagacctcc 2640
ctgatgatga cactgtgcct gggcagcatc tacgaggacc tgaagatgta ccagaccgag 2700
ttccaggcca tcaatgccgc cctgcagaac cacaaccacc agcagatcat cctggataag 2760
ggcatgctgg tggccatcga cgagctgatg cagagcctga accacaatgg cgagaccctg 2820
aggcagaagc ctcctgtggg cgaggccgat ccctacagag tgaagatgaa gctgtgtatc 2880
ctgctgcacg ccttttccac aagggtggtg accatcaaca gggtcatggg ctacctgtcc 2940
agcgcc 2946
<210> 64
<211> 699
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu IgG2a Fc hole DANG
<400> 64
gagccaaggg gccccaccat caagccatgc cccccttgca agtgtcctgc accaaacctg 60
ctgggaggac caagcgtgtt catctttcca cccaagatca aggacgtgct gatgatcagc 120
ctgtccccca tcgtgacatg cgtggtggtg gccgtgtccg aggacgatcc tgatgtgcag 180
atctcttggt tcgtgaacaa tgtggaggtg cacaccgccc agacccagac acaccgggag 240
gactatggct ctacactgag agtggtgagc gccctgccca tccagcacca ggactggatg 300
agcggcaagg agtttaagtg caaggtgaac aataaggatc tgcccgcccc tatcgagcgg 360
accatcagca agcctaaggg ctccgtgaga gccccacagg tgtacgtgct gcctccaccc 420
gaggaggaga tgaccaagaa gcaggtgaca ctgagctgtg ccgtgaccga cttcatgcct 480
gaggatatct acgtggagtg gaccaacaat ggcaagacag agctgaacta taagaataca 540
gagccagtgc tggactccga tggctcttac tttatggtgt ccaagctgag ggtggagaag 600
aagaactggg tggagcgcaa ttcttatagc tgctccgtgg tgcacgaggg cctgcacaat 660
caccacacca caaagtcttt cagcagaacc cctggcaag 699
<210> 65
<211> 699
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu IgG2a Fc knob DANG
<400> 65
gagccaaggg gccccaccat caagccatgc cccccttgca agtgtcctgc accaaacctg 60
ctgggaggac caagcgtgtt catctttcca cccaagatca aggacgtgct gatgatcagc 120
ctgtccccca tcgtgacatg cgtggtggtg gccgtgtccg aggacgatcc tgatgtgcag 180
atctcttggt tcgtgaacaa tgtggaggtg cacaccgccc agacccagac acaccgggag 240
gactacggct ctacactgag agtggtgagc gccctgccca tccagcacca ggactggatg 300
tccggcaagg agtttaagtg caaggtgaac aataaggatc tgcccgcccc tatcgagcgg 360
accatcagca agcctaaggg ctccgtgaga gccccacagg tgtatgtgct gcctccaccc 420
gaggaggaga tgaccaagaa gcaggtgaca ctgtggtgta tggtgaccga cttcatgcct 480
gaggatatct acgtggagtg gaccaacaat ggcaagacag agctgaacta taagaataca 540
gagccagtgc tggactccga tggctcttac tttatgtatt ctaagctgag ggtggagaag 600
aagaactggg tggagcgcaa ttcttacagc tgctccgtgg tgcacgaggg cctgcacaat 660
caccacacca caaagtcttt cagcagaacc cctggcaag 699
<210> 66
<211> 1344
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu FAP HC mu IgG2a Fc DANG
<400> 66
caggtgcagc tgcagcagtc cggagcagag ctggcaaggc ctggagcctc tgtgaacctg 60
agctgcaagg cctccggcta caccttcaca aacaatggca tcaattggct gaagcagagg 120
accggacagg gactggagtg gatcggcgag atctacccaa gatctaccaa cacactgtat 180
aatgagaagt tcaagggcaa ggccaccctg acagcagacc ggagctccaa caccgcctac 240
atggagctga gaagcctgac atccgaggat tctgccgtgt atttttgtgc acgcaccctg 300
acagcaccct tcgccttttg gggacagggc accctggtga cagtgagcgc cgccaagacc 360
acagcaccaa gcgtgtatcc actggcaccc gtgtgcggcg ataccacagg ctctagcgtg 420
accctgggct gtctggtgaa gggctacttc cctgagccag tgaccctgac atggaacagc 480
ggctctctgt cctctggcgt gcacaccttt cctgccgtgc tgcagtccga tctgtataca 540
ctgagctcct ctgtgaccgt gacaagctcc acctggccca gccagtccat cacatgcaac 600
gtggcccacc ctgcctctag caccaaggtg gacaagaaga tcgagccacg gggccccaca 660
atcaagccat gtccaccttg caagtgtcca gcacctaatc tgctgggagg acctagcgtg 720
ttcatctttc cacccaagat caaggacgtg ctgatgatct ctctgagccc tatcgtgacc 780
tgcgtggtgg tggccgtgtc tgaggacgat ccagatgtgc agatcagctg gttcgtgaac 840
aatgtggagg tgcacaccgc ccagacccag acacaccggg aggactacgg ctccacactg 900
agagtggtgt ctgccctgcc catccagcac caggactgga tgtccggcaa ggagtttaag 960
tgcaaggtga acaataagga tctgccagcc cccatcgaga ggaccatctc taagcctaag 1020
ggcagcgtgc gcgcaccaca ggtgtatgtg ctgcctccac ccgaggagga gatgaccaag 1080
aagcaggtga cactgacgtg tatggtgacc gacttcatgc cagaggatat ctacgtggag 1140
tggaccaaca atggcaagac agagctgaac tataagaata cagagcccgt gctggacagc 1200
gatggctcct actttatgta tagcaagctg agggtggaga agaagaactg ggtggagcgc 1260
aattcctact cttgtagcgt ggtgcacgag ggcctgcaca accaccacac cacaaagtcc 1320
ttttctagaa cccccggcaa gtga 1344
<210> 67
<211> 2292
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu scIL-12 mut2-mu IgG2a Fc DANG
<400> 67
atgtgggagc tggagaagga cgtgtacgtg gtggaggtgg attggacacc tgacgccccc 60
ggcgagacag tgaacctgac atgcgatacc cctgaggagg atgatatcac atggacctcc 120
gatcagagac acggcgtgat cggcagcggc aagaccctga caatcaccgt gaaggagttt 180
ctggatgccg gccagtacac ctgtcacaag ggcggcgaga cactgagcca ctcccacctg 240
ctgctgcaca agaaggagaa tggcatctgg tccaccgaga tcctgaagaa cttcaagaac 300
aagaccttcc tgaagtgtga ggcccctaat tactccggca ggtttacatg ctcctggctg 360
gtgcagagaa acatggacct gaagtttaat atcaagagct cctcctccag ccccgatagc 420
agagccgtga cctgtggcat ggccagcctg agcgccgaga aggtgaccct ggatcagagg 480
gattacgaga agtactccgt gtcctgtcag gaggatgtga catgtcctac agccgaggag 540
acactgccta tcgagctggc cctggaggcc aggcagcaga ataagtacga gaactacagc 600
acaagctttt tcatcaggga catcatcaag cccgatcccc ccaagaacct gcagatgaag 660
cccctgaaga acagccaggt ggaggtgtcc tgggagtacc ctgatagctg gtccacccct 720
cactcctact tctccctgaa gttctttgtg agaatccagg ctgccgccga gaagatggcc 780
gagacagagg agggctgcaa tcagaagggc gccttcctgg tggagaagac atccaccgag 840
gtgcagtgta agggcggcaa cgtgtgcgtg caggcccagg acagatacta caattccagc 900
tgtagcaagt gggcctgtgt gccttgtaga gtgagatccg gcggcggcgg ctccggagga 960
ggaggaagcg gaggaggcgg ctccagagtg atccctgtgt ccggccctgc cagatgtctg 1020
tcccagagca gaaacctgct gaagaccaca gacgacatgg tgaagacagc cagagagaag 1080
ctgaagcact acagctgcac cgccgaggac atcgaccacg aggatatcac aagagaccag 1140
acatccaccc tgaagacatg tctgcctctg gagctgcaca agaatgagtc ctgcctggcc 1200
accagagaga cctccagcac caccaggggc agctgcctgc cccctcagaa gacctccctg 1260
atgatgacac tgtgcctggg cagcatctac gaggacctga agatgtacca gaccgagttc 1320
caggccatca atgccgccct gcagaaccac aaccaccagc agatcatcct ggataagggc 1380
atgctggtgg ccatcgacga gctgatgcag agcctgaacc acaatggcga gaccctgagg 1440
cagaagcctc ctgtgggcga ggccgatccc tacagagtga agatgaagct gtgtatcctg 1500
ctgcacgcct tttccacaag ggtggtgacc atcaacaggg tcatgggcta cctgtccagc 1560
gccggcggcg gcggcagcgg aggaggaggc tccgagccac gcggccccac aatcaagcca 1620
tgcccccctt gcaagtgtcc tgcaccaaat ctgctgggag gaccatccgt gttcatcttt 1680
ccacccaaga tcaaggacgt gctgatgatc agcctgtccc caatcgtgac ctgcgtggtc 1740
gtggccgtga gcgaggacga tcctgatgtg cagatctcct ggttcgtgaa caatgtggag 1800
gtgcacaccg cccagaccca gacacaccgg gaggactacg gctccacact gagagtggtg 1860
tctgccctgc ccatccagca ccaggactgg atgagcggca aggagtttaa gtgcaaggtg 1920
aacaataagg atctgcccgc ccctatcgag cggacaatct ctaagcctaa gggcagcgtg 1980
agagccccac aggtgtatgt gctgcctcca cccgaggagg agatgaccaa gaagcaggtg 2040
acactgactt gtatggtgac cgacttcatg cctgaggata tctatgtgga gtggaccaac 2100
aatggcaaga cagagctgaa ctacaagaat acagagccag tgctggactc cgatggctct 2160
tacttcatgt acagcaagct gagggtggag aagaagaact gggtggagcg caattcttac 2220
agctgctccg tggtgcacga gggcctgcac aaccaccaca ccacaaagtc ttttagccgg 2280
acccctggca ag 2292
<210> 68
<211> 1353
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu CD20 HC mu IgG2a Fc knob DANG
<400> 68
caggtgcagc tgcagcagcc aggagcagag ctggtgaggc caggcacctc tgtgaagctg 60
agctgcaagg cctccggcta caccttcaca tcttattgga tgcactggat caagcagagg 120
ccaggacagg gactggagtg gatcggcgtg atcgacccct ccgataacta caccaagtac 180
aaccagaagt ttaagggcaa ggccaccctg acagtggaca ccagctcctc tacagcctac 240
atgcagctga gctccctgac atccgaggat tctgccgtgt atttctgtgc ccgggagggc 300
tactatggct ctagcccatg gtttgcctac tggggccagg gcaccctggt gacagtgtcc 360
tctgccaaga ccacagcccc cagcgtgtat cctctggccc cagtgtgcgg cgataccaca 420
ggcagctccg tgaccctggg ctgtctggtg aagggctact tccctgagcc agtgaccctg 480
acatggaact ctggcagcct gtctagcgga gtgcacacct ttccagccgt gctgcagtcc 540
gatctgtata cactgtcctc tagcgtgacc gtgacatcct ctacctggcc ctcccagtct 600
atcacatgca acgtggccca ccctgccagc tccaccaagg tggacaagaa gatcgagccc 660
cggggcccta caatcaagcc atgtccacct tgcaagtgtc cagcacctaa tctgctggga 720
ggacctagcg tgttcatctt tccacccaag atcaaggacg tgctgatgat cagcctgtcc 780
cctatcgtga cctgcgtggt ggtggccgtg agcgaggacg atccagatgt gcagatctcc 840
tggttcgtga acaatgtgga ggtgcacacc gcccagaccc agacacaccg ggaggactac 900
ggctccacac tgagagtggt gtctgccctg cctatccagc accaggactg gatgtccggc 960
aaggagttta agtgcaaggt gaacaataag gatctgccag cccccatcga gcggaccatc 1020
tctaagccta agggcagcgt gagagcccca caggtgtatg tgctgcctcc acccgaggag 1080
gagatgacca agaagcaggt gacactgtgg tgtatggtga ccgacttcat gcctgaggat 1140
atctacgtgg agtggaccaa caatggcaag acagagctga actataagaa tacagagcca 1200
gtgctggaca gcgatggctc ctactttatg tatagcaagc tgagggtgga gaagaagaac 1260
tgggtggagc gcaattctta cagctgttcc gtggtgcacg agggcctgca caatcaccac 1320
accacaaagt ctttcagcag aacccccggc aag 1353
<210> 69
<211> 639
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК anti-mu CD20 LC
<400> 69
cagatcgtga tgagccagtc ccctgccatc ctgtccgcca gccctggcga gaaggtgaca 60
atgacctgca gggccagatc ctccgtgtcc tacatccact ggtaccagca gaagcccggc 120
agcagcccta agccctggat ctacgccacc agcaacctgg ccagcggcgt gcctggcaga 180
ttttccggct ccggcagcgg caccagctac agcctgacaa tcacaagggt ggaggccgag 240
gatgccgcca catactactg ccagcagtgg agctccaagc ctcccacctt cggcggcggc 300
accaagctgg agatcaagag gaccgacgcc gcccccaccg tgtccatctt tcccccttcc 360
tccgagcagc tgacctccgg cggcgcttcc gtggtgtgtt tcctgaataa tttctaccct 420
aaggatatca acgtgaagtg gaagatcgat ggcagcgaga ggcagaatgg cgtgctgaat 480
agctggaccg accaggacag caaggatagc acctacagca tgagctccac actgaccctg 540
acaaaggacg agtacgagag gcacaattcc tacacatgtg aggccacaca caagacctcc 600
acctccccta tcgtgaagtc cttcaacagg aacgagtgc 639
<210> 70
<211> 702
<212> ДНК
<213> Искусственная последовательность
<220>
<223> последовательности ДНК mu IgG2a Fc DANG
<400> 70
gagcccagag gccccacaat caagccttgc cccccttgca aatgtcccgc ccccaatctg 60
ctgggaggcc cttccgtctt catcttcccc cccaagatca aggacgtgct gatgatctct 120
ctgagcccca tcgtgacatg cgtggtggtg gccgtgagcg aggacgatcc cgacgtgcag 180
atcagctggt tcgtcaacaa cgtggaggtg cataccgccc aaacacagac ccatagagag 240
gactacggct ccacactgag agtggtgtcc gctctgccca tccagcatca agactggatg 300
agcggcaagg agttcaagtg caaggtgaac aacaaggatc tgcccgcccc tatcgagagg 360
accatctcca agcccaaagg ctccgtgaga gctccccaag tgtatgtgct gcctcccccc 420
gaggaggaga tgaccaagaa gcaagtgaca ctgacatgca tggtgaccga tttcatgccc 480
gaagacatct acgtggagtg gaccaacaac ggcaagaccg agctcaacta caagaacacc 540
gagcccgtgc tcgacagcga cggcagctac ttcatgtaca gcaagctgag ggtcgagaag 600
aaaaactggg tggagaggaa cagctacagc tgtagcgtgg tgcacgaggg actgcacaac 660
caccatacca ccaagagctt ctccagaaca cccggcaagt ga 702
<210> 71
<211> 222
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC
<400> 71
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val
210 215 220
<210> 72
<211> 257
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP scFv
<400> 72
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly Gly
115 120 125
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
130 135 140
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
145 150 155 160
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
165 170 175
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
180 185 190
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
195 200 205
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
210 215 220
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
225 230 235 240
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
245 250 255
Lys
<210> 73
<211> 518
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12
<400> 73
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser
515
<210> 74
<211> 306
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 p40
<400> 74
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser
305
<210> 75
<211> 197
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 p35
<400> 75
Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys Leu
1 5 10 15
His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln Lys
20 25 30
Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile Asp
35 40 45
His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys Leu
50 55 60
Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu Thr
65 70 75 80
Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser Phe
85 90 95
Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met Tyr
100 105 110
Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro Lys
115 120 125
Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu Leu
130 135 140
Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser Ser
145 150 155 160
Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile Leu
165 170 175
Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met Ser
180 185 190
Tyr Leu Asn Ala Ser
195
<210> 76
<211> 518
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut1
<400> 76
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Lys Arg Glu Ala Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser
515
<210> 77
<211> 306
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut1 p40
<400> 77
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Lys Arg Glu Ala Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser
305
<210> 78
<211> 518
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2
<400> 78
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser
515
<210> 79
<211> 306
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2 p40
<400> 79
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser
305
<210> 80
<211> 224
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu CD20 HC
<400> 80
Gln Val Gln Leu Gln Gln Pro Gly Ala Glu Leu Val Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Met Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Ser Tyr
20 25 30
Asn Met His Trp Val Lys Gln Thr Pro Gly Arg Gly Leu Glu Trp Ile
35 40 45
Gly Ala Ile Tyr Pro Gly Asn Gly Asp Thr Ser Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Lys Ser Ser Ser Thr Ala Tyr
65 70 75 80
Met Gln Leu Ser Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Ser Thr Tyr Tyr Gly Gly Asp Trp Tyr Phe Asn Val Trp Gly
100 105 110
Ala Gly Thr Thr Val Thr Val Ser Ala Ala Ser Thr Lys Gly Pro Ser
115 120 125
Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly Gly Thr Ala
130 135 140
Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro Val Thr Val
145 150 155 160
Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr Phe Pro Ala
165 170 175
Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val Val Thr Val
180 185 190
Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn Val Asn His
195 200 205
Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro Lys Ser Cys
210 215 220
<210> 81
<211> 361
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> (anti-hu FAP VH)2
<400> 81
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly Gly
115 120 125
Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Val
130 135 140
Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala Ser Val Lys Val Ser
145 150 155 160
Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr Thr Ile His Trp Val
165 170 175
Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile Gly Gly Ile Asn Pro
180 185 190
Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe Lys Gly Arg Val Thr
195 200 205
Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr Met Glu Leu Ser Ser
210 215 220
Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys Ala Arg Arg Arg Ile
225 230 235 240
Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp Tyr Trp Gly Gln Gly
245 250 255
Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys Gly Pro Ser Val Phe
260 265 270
Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly Gly Thr Ala Ala Leu
275 280 285
Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro Val Thr Val Ser Trp
290 295 300
Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr Phe Pro Ala Val Leu
305 310 315 320
Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val Val Thr Val Pro Ser
325 330 335
Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn Val Asn His Lys Pro
340 345 350
Ser Asn Thr Lys Val Asp Lys Lys Val
355 360
<210> 82
<211> 209
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc DANG
<400> 82
Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met Ile Ser
1 5 10 15
Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His Glu Asp
20 25 30
Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val His Asn
35 40 45
Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr Arg Val
50 55 60
Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly Lys Glu
65 70 75 80
Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile Glu Lys
85 90 95
Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val Tyr Thr
100 105 110
Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser Leu Thr
115 120 125
Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu Trp Glu
130 135 140
Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro Val Leu
145 150 155 160
Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val Asp Lys
165 170 175
Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met His Glu
180 185 190
Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser Pro Gly
195 200 205
Lys
<210> 83
<211> 214
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC
<400> 83
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile
210
<210> 84
<211> 243
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP scFv
<400> 84
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
115 120 125
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Ile Val Leu Thr Gln Ser
130 135 140
Pro Ala Ile Met Ser Ala Ser Pro Gly Glu Lys Val Thr Met Thr Cys
145 150 155 160
Ser Ala Ser Ser Gly Val Asn Phe Met His Trp Tyr Gln Gln Lys Ser
165 170 175
Gly Thr Ser Pro Lys Arg Trp Ile Phe Asp Thr Ser Lys Leu Ala Ser
180 185 190
Gly Val Pro Ala Arg Phe Ser Gly Ser Gly Ser Gly Thr Ser Tyr Ser
195 200 205
Leu Thr Ile Ser Ser Met Glu Ala Glu Asp Ala Ala Thr Tyr Tyr Cys
210 215 220
Gln Gln Trp Ser Phe Asn Pro Pro Thr Phe Gly Gly Gly Thr Lys Leu
225 230 235 240
Glu Ile Lys
<210> 85
<211> 521
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12
<400> 85
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys
245 250 255
Glu Lys Met Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala
515 520
<210> 86
<211> 313
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 p40
<400> 86
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys
245 250 255
Glu Lys Met Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser
305 310
<210> 87
<211> 193
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 p35
<400> 87
Arg Val Ile Pro Val Ser Gly Pro Ala Arg Cys Leu Ser Gln Ser Arg
1 5 10 15
Asn Leu Leu Lys Thr Thr Asp Asp Met Val Lys Thr Ala Arg Glu Lys
20 25 30
Leu Lys His Tyr Ser Cys Thr Ala Glu Asp Ile Asp His Glu Asp Ile
35 40 45
Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr Cys Leu Pro Leu Glu Leu
50 55 60
His Lys Asn Glu Ser Cys Leu Ala Thr Arg Glu Thr Ser Ser Thr Thr
65 70 75 80
Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr Ser Leu Met Met Thr Leu
85 90 95
Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys Met Tyr Gln Thr Glu Phe
100 105 110
Gln Ala Ile Asn Ala Ala Leu Gln Asn His Asn His Gln Gln Ile Ile
115 120 125
Leu Asp Lys Gly Met Leu Val Ala Ile Asp Glu Leu Met Gln Ser Leu
130 135 140
Asn His Asn Gly Glu Thr Leu Arg Gln Lys Pro Pro Val Gly Glu Ala
145 150 155 160
Asp Pro Tyr Arg Val Lys Met Lys Leu Cys Ile Leu Leu His Ala Phe
165 170 175
Ser Thr Arg Val Val Thr Ile Asn Arg Val Met Gly Tyr Leu Ser Ser
180 185 190
Ala
<210> 88
<211> 521
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut1
<400> 88
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Ala Lys
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala
515 520
<210> 89
<211> 313
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut1 p40
<400> 89
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Ala Lys
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser
305 310
<210> 90
<211> 521
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2
<400> 90
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala
515 520
<210> 91
<211> 313
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2 p40
<400> 91
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser
305 310
<210> 92
<211> 218
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu CD20 HC
<400> 92
Gln Val Gln Leu Gln Gln Pro Gly Ala Glu Leu Val Arg Pro Gly Thr
1 5 10 15
Ser Val Lys Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Ser Tyr
20 25 30
Trp Met His Trp Ile Lys Gln Arg Pro Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Val Ile Asp Pro Ser Asp Asn Tyr Thr Lys Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Val Asp Thr Ser Ser Ser Thr Ala Tyr
65 70 75 80
Met Gln Leu Ser Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Glu Gly Tyr Tyr Gly Ser Ser Pro Trp Phe Ala Tyr Trp Gly
100 105 110
Gln Gly Thr Leu Val Thr Val Ser Ser Ala Lys Thr Thr Ala Pro Ser
115 120 125
Val Tyr Pro Leu Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val
130 135 140
Thr Leu Gly Cys Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu
145 150 155 160
Thr Trp Asn Ser Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala
165 170 175
Val Leu Gln Ser Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr
180 185 190
Ser Ser Thr Trp Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro
195 200 205
Ala Ser Ser Thr Lys Val Asp Lys Lys Ile
210 215
<210> 93
<211> 10
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> линкер 1
<400> 93
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
1 5 10
<210> 94
<211> 15
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> линкер 2
<400> 94
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
1 5 10 15
<210> 95
<211> 20
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> линкер 3
<400> 95
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
1 5 10 15
Gly Gly Gly Ser
20
<210> 96
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HCDR1
<400> 96
Glu Tyr Thr Ile His
1 5
<210> 97
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HCDR2
<400> 97
Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe Lys
1 5 10 15
Gly
<210> 98
<211> 15
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HCDR3
<400> 98
Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp Tyr
1 5 10 15
<210> 99
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LCDR1
<400> 99
Lys Ser Ser Gln Ser Leu Leu Tyr Ser Arg Asn Gln Lys Asn Tyr Leu
1 5 10 15
Ala
<210> 100
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LCDR2
<400> 100
Trp Ala Ser Thr Arg Glu Ser
1 5
<210> 101
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LCDR3
<400> 101
Gln Gln Tyr Phe Ser Tyr Pro Leu Thr
1 5
<210> 102
<211> 124
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HCVR
<400> 102
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser
115 120
<210> 103
<211> 113
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP LCVR
<400> 103
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
1 5 10 15
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
20 25 30
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
35 40 45
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
50 55 60
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
65 70 75 80
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
85 90 95
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
100 105 110
Lys
<210> 104
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HCDR1
<400> 104
Asn Asn Gly Ile Asn
1 5
<210> 105
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HCDR2
<400> 105
Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys
1 5 10 15
Gly
<210> 106
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HCDR3
<400> 106
Thr Leu Thr Ala Pro Phe Ala Phe
1 5
<210> 107
<211> 10
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LCDR1
<400> 107
Ser Ala Ser Ser Gly Val Asn Phe Met His
1 5 10
<210> 108
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LCDR2
<400> 108
Asp Thr Ser Lys Leu Ala Ser
1 5
<210> 109
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LCDR3
<400> 109
Gln Gln Trp Ser Phe Asn Pro Pro Thr
1 5
<210> 110
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HCVR
<400> 110
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala
115
<210> 111
<211> 107
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP LCVR
<400> 111
Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser Pro Gly
1 5 10 15
Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn Phe Met
20 25 30
His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp Ile Phe
35 40 45
Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser Gly Ser
50 55 60
Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu Ala Glu
65 70 75 80
Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro Pro Thr
85 90 95
Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys Arg
100 105
<210> 112
<211> 23
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge
<400> 112
Glu Pro Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala
1 5 10 15
Pro Glu Leu Leu Gly Gly Pro
20
<210> 113
<211> 14
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge-core 1
<400> 113
Glu Pro Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys
1 5 10
<210> 114
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge-core 2
<400> 114
Asp Lys Thr His Thr Cys Pro Pro Cys
1 5
<210> 115
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge-core 3
<400> 115
Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro
1 5 10
<210> 116
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge-core 4
<400> 116
Cys Pro Pro Cys Pro
1 5
<210> 117
<211> 4
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge-core 5
<400> 117
Cys Pro Pro Cys
1
<210> 118
<211> 28
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Hinge линкер
<400> 118
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Asp Lys Thr His Thr Cys
1 5 10 15
Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly Gly Pro
20 25
<210> 119
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Hinge
<400> 119
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
<210> 120
<211> 26
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Hinge линкер
<400> 120
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Glu Pro Arg Gly Pro Thr
1 5 10 15
Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
20 25
<210> 121
<211> 328
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IL-12 p40 wt_AAD56386
<400> 121
Met Cys His Gln Gln Leu Val Ile Ser Trp Phe Ser Leu Val Phe Leu
1 5 10 15
Ala Ser Pro Leu Val Ala Ile Trp Glu Leu Lys Lys Asp Val Tyr Val
20 25 30
Val Glu Leu Asp Trp Tyr Pro Asp Ala Pro Gly Glu Met Val Val Leu
35 40 45
Thr Cys Asp Thr Pro Glu Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln
50 55 60
Ser Ser Glu Val Leu Gly Ser Gly Lys Thr Leu Thr Ile Gln Val Lys
65 70 75 80
Glu Phe Gly Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Val
85 90 95
Leu Ser His Ser Leu Leu Leu Leu His Lys Lys Glu Asp Gly Ile Trp
100 105 110
Ser Thr Asp Ile Leu Lys Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe
115 120 125
Leu Arg Cys Glu Ala Lys Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp
130 135 140
Leu Thr Thr Ile Ser Thr Asp Leu Thr Phe Ser Val Lys Ser Ser Arg
145 150 155 160
Gly Ser Ser Asp Pro Gln Gly Val Thr Cys Gly Ala Ala Thr Leu Ser
165 170 175
Ala Glu Arg Val Arg Gly Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu
180 185 190
Cys Gln Glu Asp Ser Ala Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile
195 200 205
Glu Val Met Val Asp Ala Val His Lys Leu Lys Tyr Glu Asn Tyr Thr
210 215 220
Ser Ser Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn
225 230 235 240
Leu Gln Leu Lys Pro Leu Lys Asn Ser Arg Gln Val Glu Val Ser Trp
245 250 255
Glu Tyr Pro Asp Thr Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Thr
260 265 270
Phe Cys Val Gln Val Gln Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg
275 280 285
Val Phe Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys Asn Ala
290 295 300
Ser Ile Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser
305 310 315 320
Glu Trp Ala Ser Val Pro Cys Ser
325
<210> 122
<211> 219
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IL-12 p35 wt_AAK84425
<400> 122
Met Cys Pro Ala Arg Ser Leu Leu Leu Val Ala Thr Leu Val Leu Leu
1 5 10 15
Asp His Leu Ser Leu Ala Arg Asn Leu Pro Val Ala Thr Pro Asp Pro
20 25 30
Gly Met Phe Pro Cys Leu His His Ser Gln Asn Leu Leu Arg Ala Val
35 40 45
Ser Asn Met Leu Gln Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys
50 55 60
Thr Ser Glu Glu Ile Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser
65 70 75 80
Thr Val Glu Ala Cys Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys
85 90 95
Leu Asn Ser Arg Glu Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala
100 105 110
Ser Arg Lys Thr Ser Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr
115 120 125
Glu Asp Leu Lys Met Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys
130 135 140
Leu Leu Met Asp Pro Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu
145 150 155 160
Ala Val Ile Asp Glu Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr
165 170 175
Val Pro Gln Lys Ser Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys
180 185 190
Ile Lys Leu Cys Ile Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr
195 200 205
Ile Asp Arg Val Met Ser Tyr Leu Asn Ala Ser
210 215
<210> 123
<211> 335
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IL-12 p40 wt_AAA39296
<400> 123
Met Cys Pro Gln Lys Leu Thr Ile Ser Trp Phe Ala Ile Val Leu Leu
1 5 10 15
Val Ser Pro Leu Met Ala Met Trp Glu Leu Glu Lys Asp Val Tyr Val
20 25 30
Val Glu Val Asp Trp Thr Pro Asp Ala Pro Gly Glu Thr Val Asn Leu
35 40 45
Thr Cys Asp Thr Pro Glu Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln
50 55 60
Arg His Gly Val Ile Gly Ser Gly Lys Thr Leu Thr Ile Thr Val Lys
65 70 75 80
Glu Phe Leu Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Thr
85 90 95
Leu Ser His Ser His Leu Leu Leu His Lys Lys Glu Asn Gly Ile Trp
100 105 110
Ser Thr Glu Ile Leu Lys Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys
115 120 125
Glu Ala Pro Asn Tyr Ser Gly Arg Phe Thr Cys Ser Trp Leu Val Gln
130 135 140
Arg Asn Met Asp Leu Lys Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro
145 150 155 160
Asp Ser Arg Ala Val Thr Cys Gly Met Ala Ser Leu Ser Ala Glu Lys
165 170 175
Val Thr Leu Asp Gln Arg Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln
180 185 190
Glu Asp Val Thr Cys Pro Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu
195 200 205
Ala Leu Glu Ala Arg Gln Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser
210 215 220
Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln
225 230 235 240
Met Lys Pro Leu Lys Asn Ser Gln Val Glu Val Ser Trp Glu Tyr Pro
245 250 255
Asp Ser Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Lys Phe Phe Val
260 265 270
Arg Ile Gln Arg Lys Lys Glu Lys Met Lys Glu Thr Glu Glu Gly Cys
275 280 285
Asn Gln Lys Gly Ala Phe Leu Val Glu Lys Thr Ser Thr Glu Val Gln
290 295 300
Cys Lys Gly Gly Asn Val Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn
305 310 315 320
Ser Ser Cys Ser Lys Trp Ala Cys Val Pro Cys Arg Val Arg Ser
325 330 335
<210> 124
<211> 215
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IL-12 p35 wt_AAK39292
<400> 124
Met Cys Gln Ser Arg Tyr Leu Leu Phe Leu Ala Thr Leu Ala Leu Leu
1 5 10 15
Asn His Leu Ser Leu Ala Arg Val Ile Pro Val Ser Gly Pro Ala Arg
20 25 30
Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp Met Val
35 40 45
Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala Glu Asp
50 55 60
Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr
65 70 75 80
Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala Thr Arg
85 90 95
Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr
100 105 110
Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys
115 120 125
Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln Asn His
130 135 140
Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala Ile Asp
145 150 155 160
Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg Gln Lys
165 170 175
Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys Leu Cys
180 185 190
Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn Arg Val
195 200 205
Met Gly Tyr Leu Ser Ser Ala
210 215
<210> 125
<211> 252
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IL-12 p40_X1
<400> 125
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys
245 250
<210> 126
<211> 42
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IL-12 p40_X2
<400> 126
Asp Arg Val Phe Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys
1 5 10 15
Asn Ala Ser Ile Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser
20 25 30
Trp Ser Glu Trp Ala Ser Val Pro Cys Ser
35 40
<210> 127
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 HCDR1
<400> 127
Glu Tyr Thr Ile His
1 5
<210> 128
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 HCDR2
<400> 128
Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe Lys
1 5 10 15
Gly
<210> 129
<211> 15
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 HCDR3
<400> 129
Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp Tyr
1 5 10 15
<210> 130
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 LCDR1
<400> 130
Lys Ser Ser Gln Ser Leu Leu Tyr Ser Arg Asn Gln Lys Asn Tyr Leu
1 5 10 15
Ala
<210> 131
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 LCDR2
<400> 131
Trp Ala Ser Thr Arg Glu Ser
1 5
<210> 132
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> NG-641 LCDR3
<400> 132
Gln Gln Tyr Phe Ser Tyr Pro Leu Thr
1 5
<210> 133
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 HCDR1
<400> 133
Ser His Ala Met Ser
1 5
<210> 134
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 HCDR2
<400> 134
Ala Ile Trp Ala Ser Gly Glu Gln Tyr Tyr Ala Asp Ser Val Lys Gly
1 5 10 15
<210> 135
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 HCDR3
<400> 135
Gly Trp Leu Gly Asn Phe Asp Tyr
1 5
<210> 136
<211> 12
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 LCDR1
<400> 136
Arg Ala Ser Gln Ser Val Ser Arg Ser Tyr Leu Ala
1 5 10
<210> 137
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 LCDR2
<400> 137
Gly Ala Ser Thr Arg Ala Thr
1 5
<210> 138
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 28H1 LCDR3
<400> 138
Gln Gln Gly Gln Val Ile Pro Pro Thr
1 5
<210> 139
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 HCDR1
<400> 139
Ser Tyr Ala Met Ser
1 5
<210> 140
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 HCDR2
<400> 140
Ala Ile Ile Gly Ser Gly Ala Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
Gly
<210> 141
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 HCDR3
<400> 141
Gly Trp Phe Gly Gly Phe Asn Tyr
1 5
<210> 142
<211> 12
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 LCDR1
<400> 142
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu Ala
1 5 10
<210> 143
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 LCDR2
<400> 143
Val Gly Ser Arg Arg Ala Thr
1 5
<210> 144
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B9 LCDR3
<400> 144
Gln Gln Gly Ile Met Leu Pro Pro Thr
1 5
<210> 145
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 HCDR1
<400> 145
Glu Asn Ile Ile His
1 5
<210> 146
<211> 17
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 HCDR2
<400> 146
Trp Phe His Pro Gly Ser Gly Ser Ile Lys Tyr Asn Glu Lys Phe Lys
1 5 10 15
Asp
<210> 147
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 HCDR3
<400> 147
His Gly Gly Thr Gly Arg Gly Ala Met Asp Tyr
1 5 10
<210> 148
<211> 15
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 LCDR1
<400> 148
Arg Ala Ser Lys Ser Val Ser Thr Ser Ala Tyr Ser Tyr Met His
1 5 10 15
<210> 149
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 LCDR2
<400> 149
Leu Ala Ser Asn Leu Glu Ser
1 5
<210> 150
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> OMTX-705 LCDR3
<400> 150
Gln His Ser Arg Glu Leu Pro Tyr Thr
1 5
<210> 151
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 HCDR1
<400> 151
Ser Tyr Ala Met Ser
1 5
<210> 152
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 HCDR2
<400> 152
Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 153
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 HCDR3
<400> 153
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 154
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 LCDR1
<400> 154
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 155
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 LCDR2
<400> 155
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 156
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3F2 LCDR3
<400> 156
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 157
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 HCDR1
<400> 157
Ser Tyr Ala Met Ser
1 5
<210> 158
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 HCDR2
<400> 158
Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 159
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 HCDR3
<400> 159
Tyr Cys Ala Lys Gly Trp Leu Gly
1 5
<210> 160
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 LCDR1
<400> 160
Arg Ala Ser Gln Ser Val Ser Arg Ser Tyr Leu
1 5 10
<210> 161
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 LCDR2
<400> 161
Ile Gly Ala Ser Thr Arg Ala
1 5
<210> 162
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4G8 LCDR3
<400> 162
Cys Gln Gln Gly Gln Val Ile Pro Pro
1 5
<210> 163
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 HCDR1
<400> 163
Ser Tyr Ala Met Ser
1 5
<210> 164
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 HCDR2
<400> 164
Ala Ile Gly Val Ser Thr Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 165
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 HCDR3
<400> 165
Tyr Cys Ala Lys Gly Trp Leu Gly
1 5
<210> 166
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 LCDR1
<400> 166
Arg Ala Ser Gln Ser Val Ser Ser Ser Tyr Leu
1 5 10
<210> 167
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 LCDR2
<400> 167
Tyr Gly Ala Ser Ser Arg Ala
1 5
<210> 168
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 3D9 LCDR3
<400> 168
Cys Gln Gln Gly Gln Leu Ile Pro Pro
1 5
<210> 169
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 HCDR1
<400> 169
Ser Tyr Ala Met Ser
1 5
<210> 170
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 HCDR2
<400> 170
Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 171
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 HCDR3
<400> 171
Tyr Cys Ala Lys Gly Trp Leu Gly
1 5
<210> 172
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 LCDR1
<400> 172
Arg Ala Ser Gln Ser Val Ser Ser Asn Tyr Leu
1 5 10
<210> 173
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 LCDR2
<400> 173
Tyr Gly Ala Tyr Ile Arg Ala
1 5
<210> 174
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 4B3 LCDR3
<400> 174
Cys Gln Gln Gly Gln Val Ile Pro Pro
1 5
<210> 175
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 HCDR1
<400> 175
Ser Tyr Ala Met Ser
1 5
<210> 176
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 HCDR2
<400> 176
Ala Ile Ile Ser Ser Gly Gly Leu Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 177
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 HCDR3
<400> 177
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 178
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 LCDR1
<400> 178
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 179
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 LCDR2
<400> 179
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 180
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 19G1 LCDR3
<400> 180
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 181
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 HCDR1
<400> 181
Ser Tyr Ala Met Ser
1 5
<210> 182
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 HCDR2
<400> 182
Ala Ile Ile Gly Ser Gly Ser Arg Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 183
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 HCDR3
<400> 183
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 184
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 LCDR1
<400> 184
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 185
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 LCDR2
<400> 185
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 186
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 20G8 LCDR3
<400> 186
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 187
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 HCDR1
<400> 187
Ser Tyr Ala Met Ser
1 5
<210> 188
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 HCDR2
<400> 188
Ala Ile Trp Gly Gly Gly Arg Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 189
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 HCDR3
<400> 189
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 190
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 LCDR1
<400> 190
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 191
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 LCDR2
<400> 191
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 192
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5B8 LCDR3
<400> 192
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 193
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 HCDR1
<400> 193
Ser Tyr Ala Met Ser
1 5
<210> 194
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 HCDR2
<400> 194
Ala Ile Ile Ser Ser Gly Ala Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 195
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 HCDR3
<400> 195
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 196
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 LCDR1
<400> 196
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 197
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 LCDR2
<400> 197
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 198
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 5F1 LCDR3
<400> 198
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 199
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 HCDR1
<400> 199
Ser Tyr Ala Met Ser
1 5
<210> 200
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 HCDR2
<400> 200
Ala Ile Leu Ala Ser Gly Ala Ile Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 201
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 HCDR3
<400> 201
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 202
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 LCDR1
<400> 202
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 203
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 LCDR2
<400> 203
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 204
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 14B3 LCDR3
<400> 204
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 205
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 HCDR1
<400> 205
Ser Tyr Ala Met Ser
1 5
<210> 206
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 HCDR2
<400> 206
Gly Ile Ile Gly Ser Gly Gly Ile Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 207
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 HCDR3
<400> 207
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 208
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 LCDR1
<400> 208
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 209
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 LCDR2
<400> 209
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 210
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F1 LCDR3
<400> 210
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 211
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 HCDR1
<400> 211
Ser Tyr Ala Met Ser
1 5
<210> 212
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 HCDR2
<400> 212
Ala Ile Leu Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 213
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 HCDR3
<400> 213
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 214
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 LCDR1
<400> 214
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 215
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 LCDR2
<400> 215
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 216
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 16F8 LCDR3
<400> 216
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 217
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 HCDR1
<400> 217
Ser Phe Ala Met Ser
1 5
<210> 218
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 HCDR2
<400> 218
Ala Ile Ile Gly Ser Gly Ser Asn Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 219
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 HCDR3
<400> 219
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 220
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 LCDR1
<400> 220
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 221
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 LCDR2
<400> 221
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 222
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O3C9 LCDR3
<400> 222
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 223
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 HCDR1
<400> 223
Ser Tyr Ala Met Ser
1 5
<210> 224
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 HCDR2
<400> 224
Ala Ile Ile Gly Ser Gly Ser Ile Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 225
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 HCDR3
<400> 225
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 226
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 LCDR1
<400> 226
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 227
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 LCDR2
<400> 227
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 228
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 22A3 LCDR3
<400> 228
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 229
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 HCDR1
<400> 229
Ser Tyr Ala Met Ser
1 5
<210> 230
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 HCDR2
<400> 230
Ala Ile Ile Gly Ser Gly Gly Ile Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 231
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 HCDR3
<400> 231
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 232
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 LCDR1
<400> 232
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 233
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 LCDR2
<400> 233
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 234
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 29B11 LCDR3
<400> 234
Cys Gln Gln Gly Ile Met Leu Pro Pro
1 5
<210> 235
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 HCDR1
<400> 235
Ser Tyr Ala Met Ser
1 5
<210> 236
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 HCDR2
<400> 236
Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 237
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 HCDR3
<400> 237
Tyr Cys Ala Lys Gly Trp Phe Gly
1 5
<210> 238
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 LCDR1
<400> 238
Arg Ala Ser Gln Ser Val Thr Ser Ser Tyr Leu
1 5 10
<210> 239
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 LCDR2
<400> 239
Asn Val Gly Ser Arg Arg Ala
1 5
<210> 240
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> O2D7 LCDR3
<400> 240
Cys Gln Gln Ala Ile Met Leu Pro Pro
1 5
<210> 241
<211> 5
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 HCDR1
<400> 241
Ser Ser Ala Met Ser
1 5
<210> 242
<211> 16
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 HCDR2
<400> 242
Ala Ile Ser Thr Asn Gly Asn Tyr Thr Tyr Tyr Ala Asp Ser Val Lys
1 5 10 15
<210> 243
<211> 8
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 HCDR3
<400> 243
Tyr Cys Ala Lys Gly Trp Leu Gly
1 5
<210> 244
<211> 11
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 LCDR1
<400> 244
Arg Ala Ser Gln Ser Val Ser Arg Ser Tyr Leu
1 5 10
<210> 245
<211> 7
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 LCDR2
<400> 245
Ile Gly Ala Ser Thr Arg Ala
1 5
<210> 246
<211> 9
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> 23C10 LCDR3
<400> 246
Cys Gln Gln Gly Gln Val Ile Pro Pro
1 5
<210> 247
<211> 157
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> DARPin AMG-506/MP-0310
<400> 247
Asp Leu Gly Lys Lys Leu Leu Glu Ala Ala Arg Ala Gly Gln Asp Asp
1 5 10 15
Glu Val Arg Glu Leu Leu Lys Ala Gly Ala Asp Val Asn Ala Lys Asp
20 25 30
Val Leu Gly Trp Thr Pro Leu His Leu Ala Ala Phe Glu Gly His Leu
35 40 45
Glu Ile Val Glu Val Leu Leu Lys Ala Gly Ala Asp Val Asn Ala Lys
50 55 60
Asp Lys Lys Gly Trp Thr Pro Leu Gln Leu Ala Ala Arg Thr Gly His
65 70 75 80
Leu Glu Ile Val Glu Val Leu Leu Lys Ala Gly Ala Asp Val Asn Ala
85 90 95
Lys Asp His Ile Gly Ala Thr Pro Leu His Leu Ala Ala Trp Gln Gly
100 105 110
His Pro Glu Ile Val Glu Val Leu Leu Lys Ala Gly Ala Asp Val Asn
115 120 125
Ala Gln Asp Lys Ser Gly Lys Thr Pro Ala Asp Leu Ala Ala Asp Ala
130 135 140
Gly His Glu Asp Ile Ala Glu Val Leu Gln Lys Ala Ala
145 150 155
<210> 248
<211> 124
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область NG-641
<400> 248
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser
115 120
<210> 249
<211> 113
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область NG-641
<400> 249
Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu Gly
1 5 10 15
Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr Ser
20 25 30
Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln
35 40 45
Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly Val
50 55 60
Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu Thr
65 70 75 80
Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln Gln
85 90 95
Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu Ile
100 105 110
Lys
<210> 250
<211> 116
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 28H1
<400> 250
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser His
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Trp Ala Ser Gly Glu Gln Tyr Tyr Ala Asp Ser Val Lys
50 55 60
Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr Leu
65 70 75 80
Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys Ala
85 90 95
Lys Gly Trp Leu Gly Asn Phe Asp Tyr Trp Gly Gln Gly Thr Leu Val
100 105 110
Thr Val Ser Ser
115
<210> 251
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 28H1
<400> 251
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Ser Arg Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Ile Gly Ala Ser Thr Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Gln Val Ile Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 252
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 4B9
<400> 252
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Gly Ser Gly Ala Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 253
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 4B9
<400> 253
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 254
<211> 121
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область OMTX-705
<400> 254
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Glu Asn
20 25 30
Ile Ile His Trp Val Arg Gln Ala Pro Gly Gln Gly Leu Glu Trp Met
35 40 45
Gly Trp Phe His Pro Gly Ser Gly Ser Ile Lys Tyr Asn Glu Lys Phe
50 55 60
Lys Asp Arg Val Thr Met Thr Thr Ala Asp Thr Ser Thr Ser Thr Val
65 70 75 80
Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr
85 90 95
Cys Ala Arg His Gly Gly Thr Gly Arg Gly Ala Met Asp Tyr Trp Gly
100 105 110
Gln Gly Thr Leu Val Thr Val Ser Ser
115 120
<210> 255
<211> 112
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область OMTX-705
<400> 255
Asp Ile Gln Met Ile Gln Ser Pro Ser Ser Leu Ser Ala Ser Val Gly
1 5 10 15
Asp Arg Val Thr Ile Thr Cys Arg Ala Ser Lys Ser Val Ser Thr Ser
20 25 30
Ala Tyr Ser Tyr Met His Trp Tyr Gln Gln Lys Pro Gly Lys Ala Pro
35 40 45
Lys Leu Leu Ile Tyr Leu Ala Ser Asn Leu Glu Ser Gly Val Pro Ser
50 55 60
Arg Phe Ser Gly Ser Gly Ser Gly Thr Asp Phe Ile Leu Thr Ile Ser
65 70 75 80
Ser Leu Gln Pro Glu Asp Phe Ala Thr Tyr Tyr Cys Gln His Ser Arg
85 90 95
Glu Leu Pro Tyr Thr Phe Gly Gln Gly Thr Lys Leu Glu Ile Lys Arg
100 105 110
<210> 256
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 3F2
<400> 256
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 257
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 3F2
<400> 257
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Tyr Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 258
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 4G8
<400> 258
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Leu Gly Asn Phe Asp Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 259
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 4G8
<400> 259
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Ser Arg Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Ile Gly Ala Ser Thr Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Gln Val Ile Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 260
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 3D9
<400> 260
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Thr Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Gly Val Ser Thr Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Leu Gly Pro Phe Asp Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 261
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 3D9
<400> 261
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Lys Arg Ala Ser Gln Ser Val Ser Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Tyr Gly Ala Ser Ser Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Gln Leu Ile Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 262
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 4B3
<400> 262
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Leu Gly Asn Phe Asp Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 263
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 4B3
<400> 263
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Ser Ser Asn
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Tyr Gly Ala Tyr Ile Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Gln Val Ile Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 264
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 19G1
<400> 264
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Ser Ser Gly Gly Leu Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 265
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 19G1
<400> 265
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Gly Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 266
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 20G8
<400> 266
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Lys Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Gly Ser Gly Ser Arg Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 267
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 20G8
<400> 267
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 268
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 5B8
<400> 268
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Trp Gly Gly Gly Arg Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 269
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 5B8
<400> 269
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 270
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 5F1
<400> 270
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Ser Ser Gly Ala Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 271
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 5F1
<400> 271
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 272
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 14B3
<400> 272
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Leu Ala Ser Gly Ala Ile Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 273
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 14B3
<400> 273
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Gly Pro Gly Gly Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 274
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 16F1
<400> 274
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Gly Ile Ile Gly Ser Gly Gly Ile Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Asp Phe Thr Ile Ser Arg Asp Asn Ser Gly Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 275
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 16F1
<400> 275
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 276
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 16F8
<400> 276
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Leu Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 277
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 16F8
<400> 277
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 278
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область O3C9
<400> 278
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Phe
20 25 30
Ala Met Ser Trp Val Arg Gln Ser Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Gly Ser Gly Ser Asn Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 279
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область O3C9
<400> 279
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 280
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 22A3
<400> 280
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Gly Ser Gly Ser Ile Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 281
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 22A3
<400> 281
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 282
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 29B11
<400> 282
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ile Gly Ser Gly Gly Ile Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 283
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 29B11
<400> 283
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 284
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область O2D7
<400> 284
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Tyr
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ser Gly Ser Gly Gly Ser Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Phe Gly Gly Phe Asn Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 285
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область O2D7
<400> 285
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Thr Ser Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Asn Val Gly Ser Arg Arg Ala Thr Gly Thr Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Ala Ile Met Leu Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 286
<211> 117
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VH-область 23C10
<400> 286
Glu Val Gln Leu Leu Glu Ser Gly Gly Gly Leu Val Gln Pro Gly Gly
1 5 10 15
Ser Leu Arg Leu Ser Cys Ala Ala Ser Gly Phe Thr Phe Ser Ser Ser
20 25 30
Ala Met Ser Trp Val Arg Gln Ala Pro Gly Lys Gly Leu Glu Trp Val
35 40 45
Ser Ala Ile Ser Thr Asn Gly Asn Tyr Thr Tyr Tyr Ala Asp Ser Val
50 55 60
Lys Gly Arg Phe Thr Ile Ser Arg Asp Asn Ser Lys Asn Thr Leu Tyr
65 70 75 80
Leu Gln Met Asn Ser Leu Arg Ala Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Lys Gly Trp Leu Gly Asn Phe Asp Tyr Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ser
115
<210> 287
<211> 108
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> VL-область 23C10
<400> 287
Glu Ile Val Leu Thr Gln Ser Pro Gly Thr Leu Ser Leu Ser Pro Gly
1 5 10 15
Glu Arg Ala Thr Leu Ser Cys Arg Ala Ser Gln Ser Val Ser Arg Ser
20 25 30
Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly Gln Ala Pro Arg Leu Leu
35 40 45
Ile Ile Gly Ala Ser Thr Arg Ala Thr Gly Ile Pro Asp Arg Phe Ser
50 55 60
Gly Ser Gly Ser Gly Thr Asp Phe Thr Leu Thr Ile Ser Arg Leu Glu
65 70 75 80
Pro Glu Asp Phe Ala Val Tyr Tyr Cys Gln Gln Gly Gln Val Ile Pro
85 90 95
Pro Thr Phe Gly Gln Gly Thr Lys Val Glu Ile Lys
100 105
<210> 288
<211> 227
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc knob
<400> 288
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
1 5 10 15
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
20 25 30
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Asp Val Ser His
35 40 45
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
50 55 60
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Asn Ser Thr Tyr
65 70 75 80
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
85 90 95
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
100 105 110
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
115 120 125
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
130 135 140
Leu Trp Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
145 150 155 160
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
165 170 175
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
180 185 190
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
195 200 205
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
210 215 220
Pro Gly Lys
225
<210> 289
<211> 227
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc hole
<400> 289
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
1 5 10 15
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
20 25 30
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Asp Val Ser His
35 40 45
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
50 55 60
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Asn Ser Thr Tyr
65 70 75 80
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
85 90 95
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
100 105 110
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
115 120 125
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
130 135 140
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
145 150 155 160
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
165 170 175
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
180 185 190
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
195 200 205
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
210 215 220
Pro Gly Lys
225
<210> 290
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc knob
<400> 290
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Asp Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Asn Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Trp Cys Met Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<210> 291
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc hole
<400> 291
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Asp Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Asn Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<210> 292
<211> 1026
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12-hu IgG1 Fc hole DANG-anti-hu FAP scFv
<400> 292
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
755 760 765
Ser Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly
770 775 780
Ala Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu
785 790 795 800
Tyr Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp
805 810 815
Ile Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys
820 825 830
Phe Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala
835 840 845
Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr
850 855 860
Cys Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met
865 870 875 880
Asp Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly
885 890 895
Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
900 905 910
Ser Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu
915 920 925
Gly Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr
930 935 940
Ser Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly
945 950 955 960
Gln Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly
965 970 975
Val Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu
980 985 990
Thr Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln
995 1000 1005
Gln Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu
1010 1015 1020
Ile Lys
1025
<210> 293
<211> 1026
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2-hu IgG1 Fc hole DANG-anti-hu FAP scFv
<400> 293
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Ser Cys Ala Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Val Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
755 760 765
Ser Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly
770 775 780
Ala Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu
785 790 795 800
Tyr Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp
805 810 815
Ile Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys
820 825 830
Phe Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala
835 840 845
Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr
850 855 860
Cys Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met
865 870 875 880
Asp Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly
885 890 895
Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
900 905 910
Ser Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu
915 920 925
Gly Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr
930 935 940
Ser Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly
945 950 955 960
Gln Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly
965 970 975
Val Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu
980 985 990
Thr Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln
995 1000 1005
Gln Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu
1010 1015 1020
Ile Lys
1025
<210> 294
<211> 986
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc DANG-hu scIL-12
<400> 294
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
450 455 460
Gly Gly Gly Ser Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu
465 470 475 480
Leu Asp Trp Tyr Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys
485 490 495
Asp Thr Pro Glu Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser
500 505 510
Glu Val Leu Gly Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe
515 520 525
Gly Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser
530 535 540
His Ser Leu Leu Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr
545 550 555 560
Asp Ile Leu Lys Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg
565 570 575
Cys Glu Ala Lys Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr
580 585 590
Thr Ile Ser Thr Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser
595 600 605
Ser Asp Pro Gln Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu
610 615 620
Arg Val Arg Gly Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln
625 630 635 640
Glu Asp Ser Ala Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val
645 650 655
Met Val Asp Ala Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser
660 665 670
Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln
675 680 685
Leu Lys Pro Leu Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr
690 695 700
Pro Asp Thr Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys
705 710 715 720
Val Gln Val Gln Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe
725 730 735
Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile
740 745 750
Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp
755 760 765
Ala Ser Val Pro Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly
785 790 795 800
Met Phe Pro Cys Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser
805 810 815
Asn Met Leu Gln Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr
820 825 830
Ser Glu Glu Ile Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr
835 840 845
Val Glu Ala Cys Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu
850 855 860
Asn Ser Arg Glu Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser
865 870 875 880
Arg Lys Thr Ser Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu
885 890 895
Asp Leu Lys Met Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu
900 905 910
Leu Met Asp Pro Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala
915 920 925
Val Ile Asp Glu Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val
930 935 940
Pro Gln Lys Ser Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile
945 950 955 960
Lys Leu Cys Ile Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile
965 970 975
Asp Arg Val Met Ser Tyr Leu Asn Ala Ser
980 985
<210> 295
<211> 986
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-hu FAP HC hu IgG1 Fc DANG-hu scIL-12 mut2
<400> 295
Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly Ala
1 5 10 15
Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu Tyr
20 25 30
Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp Ile
35 40 45
Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys Phe
50 55 60
Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala Tyr
65 70 75 80
Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr Cys
85 90 95
Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met Asp
100 105 110
Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Ala Ser Thr Lys
115 120 125
Gly Pro Ser Val Phe Pro Leu Ala Pro Ser Ser Lys Ser Thr Ser Gly
130 135 140
Gly Thr Ala Ala Leu Gly Cys Leu Val Lys Asp Tyr Phe Pro Glu Pro
145 150 155 160
Val Thr Val Ser Trp Asn Ser Gly Ala Leu Thr Ser Gly Val His Thr
165 170 175
Phe Pro Ala Val Leu Gln Ser Ser Gly Leu Tyr Ser Leu Ser Ser Val
180 185 190
Val Thr Val Pro Ser Ser Ser Leu Gly Thr Gln Thr Tyr Ile Cys Asn
195 200 205
Val Asn His Lys Pro Ser Asn Thr Lys Val Asp Lys Lys Val Glu Pro
210 215 220
Lys Ser Cys Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu
225 230 235 240
Leu Leu Gly Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp
245 250 255
Thr Leu Met Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala
260 265 270
Val Ser His Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly
275 280 285
Val Glu Val His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly
290 295 300
Ser Thr Tyr Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp
305 310 315 320
Leu Asn Gly Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro
325 330 335
Ala Pro Ile Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu
340 345 350
Pro Gln Val Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn
355 360 365
Gln Val Ser Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile
370 375 380
Ala Val Glu Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr
385 390 395 400
Thr Pro Pro Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys
405 410 415
Leu Thr Val Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys
420 425 430
Ser Val Met His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu
435 440 445
Ser Leu Ser Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly
450 455 460
Gly Gly Gly Ser Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu
465 470 475 480
Leu Asp Trp Tyr Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys
485 490 495
Asp Thr Pro Glu Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser
500 505 510
Glu Val Leu Gly Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe
515 520 525
Gly Asp Ala Gly Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser
530 535 540
His Ser Leu Leu Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr
545 550 555 560
Asp Ile Leu Lys Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg
565 570 575
Cys Glu Ala Lys Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr
580 585 590
Thr Ile Ser Thr Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser
595 600 605
Ser Asp Pro Gln Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu
610 615 620
Arg Val Arg Gly Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln
625 630 635 640
Glu Asp Ser Ala Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val
645 650 655
Met Val Asp Ala Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser
660 665 670
Phe Phe Ile Arg Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln
675 680 685
Leu Lys Pro Leu Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr
690 695 700
Pro Asp Thr Trp Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys
705 710 715 720
Val Gln Val Gln Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe
725 730 735
Thr Asp Lys Thr Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile
740 745 750
Ser Val Arg Ala Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp
755 760 765
Ala Ser Val Pro Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly
785 790 795 800
Met Phe Pro Cys Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser
805 810 815
Asn Met Leu Gln Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr
820 825 830
Ser Glu Glu Ile Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr
835 840 845
Val Glu Ala Cys Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu
850 855 860
Asn Ser Arg Glu Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser
865 870 875 880
Arg Lys Thr Ser Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu
885 890 895
Asp Leu Lys Met Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu
900 905 910
Leu Met Asp Pro Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala
915 920 925
Val Ile Asp Glu Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val
930 935 940
Pro Gln Lys Ser Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile
945 950 955 960
Lys Leu Cys Ile Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile
965 970 975
Asp Arg Val Met Ser Tyr Leu Asn Ala Ser
980 985
<210> 296
<211> 1026
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12-hu IgG1 Fc DANG-anti-hu FAP scFv
<400> 296
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Lys Ser Lys Arg Glu Lys Lys Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
755 760 765
Ser Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly
770 775 780
Ala Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu
785 790 795 800
Tyr Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp
805 810 815
Ile Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys
820 825 830
Phe Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala
835 840 845
Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr
850 855 860
Cys Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met
865 870 875 880
Asp Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly
885 890 895
Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
900 905 910
Ser Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu
915 920 925
Gly Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr
930 935 940
Ser Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly
945 950 955 960
Gln Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly
965 970 975
Val Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu
980 985 990
Thr Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln
995 1000 1005
Gln Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu
1010 1015 1020
Ile Lys
1025
<210> 297
<211> 1026
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu scIL-12 mut2-hu IgG1 Fc DANG-anti-hu FAP scFv
<400> 297
Ile Trp Glu Leu Lys Lys Asp Val Tyr Val Val Glu Leu Asp Trp Tyr
1 5 10 15
Pro Asp Ala Pro Gly Glu Met Val Val Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Gly Ile Thr Trp Thr Leu Asp Gln Ser Ser Glu Val Leu Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Gln Val Lys Glu Phe Gly Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Val Leu Ser His Ser Leu Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asp Gly Ile Trp Ser Thr Asp Ile Leu Lys
85 90 95
Asp Gln Lys Glu Pro Lys Asn Lys Thr Phe Leu Arg Cys Glu Ala Lys
100 105 110
Asn Tyr Ser Gly Arg Phe Thr Cys Trp Trp Leu Thr Thr Ile Ser Thr
115 120 125
Asp Leu Thr Phe Ser Val Lys Ser Ser Arg Gly Ser Ser Asp Pro Gln
130 135 140
Gly Val Thr Cys Gly Ala Ala Thr Leu Ser Ala Glu Arg Val Arg Gly
145 150 155 160
Asp Asn Lys Glu Tyr Glu Tyr Ser Val Glu Cys Gln Glu Asp Ser Ala
165 170 175
Cys Pro Ala Ala Glu Glu Ser Leu Pro Ile Glu Val Met Val Asp Ala
180 185 190
Val His Lys Leu Lys Tyr Glu Asn Tyr Thr Ser Ser Phe Phe Ile Arg
195 200 205
Asp Ile Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Leu Lys Pro Leu
210 215 220
Lys Asn Ser Arg Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Thr Trp
225 230 235 240
Ser Thr Pro His Ser Tyr Phe Ser Leu Thr Phe Cys Val Gln Val Gln
245 250 255
Gly Ala Ser Ala Arg Glu Ala Ala Asp Arg Val Phe Thr Asp Lys Thr
260 265 270
Ser Ala Thr Val Ile Cys Arg Lys Asn Ala Ser Ile Ser Val Arg Ala
275 280 285
Gln Asp Arg Tyr Tyr Ser Ser Ser Trp Ser Glu Trp Ala Ser Val Pro
290 295 300
Cys Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
305 310 315 320
Ser Arg Asn Leu Pro Val Ala Thr Pro Asp Pro Gly Met Phe Pro Cys
325 330 335
Leu His His Ser Gln Asn Leu Leu Arg Ala Val Ser Asn Met Leu Gln
340 345 350
Lys Ala Arg Gln Thr Leu Glu Phe Tyr Pro Cys Thr Ser Glu Glu Ile
355 360 365
Asp His Glu Asp Ile Thr Lys Asp Lys Thr Ser Thr Val Glu Ala Cys
370 375 380
Leu Pro Leu Glu Leu Thr Lys Asn Glu Ser Cys Leu Asn Ser Arg Glu
385 390 395 400
Thr Ser Phe Ile Thr Asn Gly Ser Cys Leu Ala Ser Arg Lys Thr Ser
405 410 415
Phe Met Met Ala Leu Cys Leu Ser Ser Ile Tyr Glu Asp Leu Lys Met
420 425 430
Tyr Gln Val Glu Phe Lys Thr Met Asn Ala Lys Leu Leu Met Asp Pro
435 440 445
Lys Arg Gln Ile Phe Leu Asp Gln Asn Met Leu Ala Val Ile Asp Glu
450 455 460
Leu Met Gln Ala Leu Asn Phe Asn Ser Glu Thr Val Pro Gln Lys Ser
465 470 475 480
Ser Leu Glu Glu Pro Asp Phe Tyr Lys Thr Lys Ile Lys Leu Cys Ile
485 490 495
Leu Leu His Ala Phe Arg Ile Arg Ala Val Thr Ile Asp Arg Val Met
500 505 510
Ser Tyr Leu Asn Ala Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
515 520 525
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
530 535 540
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
545 550 555 560
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Ala Val Ser His
565 570 575
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
580 585 590
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Gly Ser Thr Tyr
595 600 605
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
610 615 620
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
625 630 635 640
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
645 650 655
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
660 665 670
Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
675 680 685
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
690 695 700
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
705 710 715 720
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
725 730 735
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
740 745 750
Pro Gly Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
755 760 765
Ser Gln Val Gln Leu Val Gln Ser Gly Ala Glu Val Lys Lys Pro Gly
770 775 780
Ala Ser Val Lys Val Ser Cys Lys Thr Ser Arg Tyr Thr Phe Thr Glu
785 790 795 800
Tyr Thr Ile His Trp Val Arg Gln Ala Pro Gly Gln Arg Leu Glu Trp
805 810 815
Ile Gly Gly Ile Asn Pro Asn Asn Gly Ile Pro Asn Tyr Asn Gln Lys
820 825 830
Phe Lys Gly Arg Val Thr Ile Thr Val Asp Thr Ser Ala Ser Thr Ala
835 840 845
Tyr Met Glu Leu Ser Ser Leu Arg Ser Glu Asp Thr Ala Val Tyr Tyr
850 855 860
Cys Ala Arg Arg Arg Ile Ala Tyr Gly Tyr Asp Glu Gly His Ala Met
865 870 875 880
Asp Tyr Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ser Gly Gly Gly
885 890 895
Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly
900 905 910
Ser Asp Ile Val Met Thr Gln Ser Pro Asp Ser Leu Ala Val Ser Leu
915 920 925
Gly Glu Arg Ala Thr Ile Asn Cys Lys Ser Ser Gln Ser Leu Leu Tyr
930 935 940
Ser Arg Asn Gln Lys Asn Tyr Leu Ala Trp Tyr Gln Gln Lys Pro Gly
945 950 955 960
Gln Pro Pro Lys Leu Leu Ile Phe Trp Ala Ser Thr Arg Glu Ser Gly
965 970 975
Val Pro Asp Arg Phe Ser Gly Ser Gly Phe Gly Thr Asp Phe Thr Leu
980 985 990
Thr Ile Ser Ser Leu Gln Ala Glu Asp Val Ala Val Tyr Tyr Cys Gln
995 1000 1005
Gln Tyr Phe Ser Tyr Pro Leu Thr Phe Gly Gln Gly Thr Lys Val Glu
1010 1015 1020
Ile Lys
1025
<210> 298
<211> 1021
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12-mu IgG2a Fc hole DANG-anti-mu FAP scFv
<400> 298
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys
245 250 255
Glu Lys Met Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly Gly Gly Ser
755 760 765
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Gln Gln
770 775 780
Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala Ser Val Asn Leu Ser Cys
785 790 795 800
Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys
805 810 815
Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg
820 825 830
Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu
835 840 845
Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu
850 855 860
Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala
865 870 875 880
Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ala Gly
885 890 895
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly
900 905 910
Gly Gly Ser Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala
915 920 925
Ser Pro Gly Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val
930 935 940
Asn Phe Met His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg
945 950 955 960
Trp Ile Phe Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe
965 970 975
Ser Gly Ser Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met
980 985 990
Glu Ala Glu Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn
995 1000 1005
Pro Pro Thr Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys
1010 1015 1020
<210> 299
<211> 1021
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2-mu IgG2a Fc hole DANG-anti-mu FAP scFv
<400> 299
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Ser Cys Ala Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Val Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly Gly Gly Ser
755 760 765
Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Gln Gln
770 775 780
Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala Ser Val Asn Leu Ser Cys
785 790 795 800
Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys
805 810 815
Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg
820 825 830
Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu
835 840 845
Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu
850 855 860
Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala
865 870 875 880
Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ala Gly
885 890 895
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly
900 905 910
Gly Gly Ser Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala
915 920 925
Ser Pro Gly Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val
930 935 940
Asn Phe Met His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg
945 950 955 960
Trp Ile Phe Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe
965 970 975
Ser Gly Ser Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met
980 985 990
Glu Ala Glu Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn
995 1000 1005
Pro Pro Thr Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys
1010 1015 1020
<210> 300
<211> 982
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc DANG-mu scIL-12
<400> 300
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly
435 440 445
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Met Trp Glu
450 455 460
Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr Pro Asp Ala
465 470 475 480
Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu Glu Asp Asp
485 490 495
Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly Ser Gly Lys
500 505 510
Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly Gln Tyr Thr
515 520 525
Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu Leu Leu His
530 535 540
Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys Asn Phe Lys
545 550 555 560
Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser Gly Arg Phe
565 570 575
Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys Phe Asn Ile
580 585 590
Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr Cys Gly Met
595 600 605
Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg Asp Tyr Glu
610 615 620
Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro Thr Ala Glu
625 630 635 640
Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln Gln Asn Lys
645 650 655
Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile Ile Lys Pro
660 665 670
Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn Ser Gln Val
675 680 685
Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro His Ser Tyr
690 695 700
Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys Glu Lys Met
705 710 715 720
Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe Leu Val Glu
725 730 735
Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val Cys Val Gln
740 745 750
Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp Ala Cys Val
755 760 765
Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro Ala Arg Cys
785 790 795 800
Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp Met Val Lys
805 810 815
Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala Glu Asp Ile
820 825 830
Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr Cys
835 840 845
Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala Thr Arg Glu
850 855 860
Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr Ser
865 870 875 880
Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys Met
885 890 895
Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln Asn His Asn
900 905 910
His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala Ile Asp Glu
915 920 925
Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg Gln Lys Pro
930 935 940
Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys Leu Cys Ile
945 950 955 960
Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn Arg Val Met
965 970 975
Gly Tyr Leu Ser Ser Ala
980
<210> 301
<211> 982
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> anti-mu FAP HC mu IgG2a Fc DANG-mu scIL-12 mut2
<400> 301
Gln Val Gln Leu Gln Gln Ser Gly Ala Glu Leu Ala Arg Pro Gly Ala
1 5 10 15
Ser Val Asn Leu Ser Cys Lys Ala Ser Gly Tyr Thr Phe Thr Asn Asn
20 25 30
Gly Ile Asn Trp Leu Lys Gln Arg Thr Gly Gln Gly Leu Glu Trp Ile
35 40 45
Gly Glu Ile Tyr Pro Arg Ser Thr Asn Thr Leu Tyr Asn Glu Lys Phe
50 55 60
Lys Gly Lys Ala Thr Leu Thr Ala Asp Arg Ser Ser Asn Thr Ala Tyr
65 70 75 80
Met Glu Leu Arg Ser Leu Thr Ser Glu Asp Ser Ala Val Tyr Phe Cys
85 90 95
Ala Arg Thr Leu Thr Ala Pro Phe Ala Phe Trp Gly Gln Gly Thr Leu
100 105 110
Val Thr Val Ser Ala Ala Lys Thr Thr Ala Pro Ser Val Tyr Pro Leu
115 120 125
Ala Pro Val Cys Gly Asp Thr Thr Gly Ser Ser Val Thr Leu Gly Cys
130 135 140
Leu Val Lys Gly Tyr Phe Pro Glu Pro Val Thr Leu Thr Trp Asn Ser
145 150 155 160
Gly Ser Leu Ser Ser Gly Val His Thr Phe Pro Ala Val Leu Gln Ser
165 170 175
Asp Leu Tyr Thr Leu Ser Ser Ser Val Thr Val Thr Ser Ser Thr Trp
180 185 190
Pro Ser Gln Ser Ile Thr Cys Asn Val Ala His Pro Ala Ser Ser Thr
195 200 205
Lys Val Asp Lys Lys Ile Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys
210 215 220
Pro Pro Cys Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val
225 230 235 240
Phe Ile Phe Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser
245 250 255
Pro Ile Val Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp
260 265 270
Val Gln Ile Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln
275 280 285
Thr Gln Thr His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser
290 295 300
Ala Leu Pro Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys
305 310 315 320
Cys Lys Val Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile
325 330 335
Ser Lys Pro Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro
340 345 350
Pro Pro Glu Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met
355 360 365
Val Thr Asp Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn
370 375 380
Gly Lys Thr Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser
385 390 395 400
Asp Gly Ser Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn
405 410 415
Trp Val Glu Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu
420 425 430
His Asn His His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly
435 440 445
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Met Trp Glu
450 455 460
Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr Pro Asp Ala
465 470 475 480
Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu Glu Asp Asp
485 490 495
Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly Ser Gly Lys
500 505 510
Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly Gln Tyr Thr
515 520 525
Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu Leu Leu His
530 535 540
Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys Asn Phe Lys
545 550 555 560
Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser Gly Arg Phe
565 570 575
Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys Phe Asn Ile
580 585 590
Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr Cys Gly Met
595 600 605
Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg Asp Tyr Glu
610 615 620
Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro Thr Ala Glu
625 630 635 640
Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln Gln Asn Lys
645 650 655
Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile Ile Lys Pro
660 665 670
Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn Ser Gln Val
675 680 685
Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro His Ser Tyr
690 695 700
Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala Glu Lys Met
705 710 715 720
Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe Leu Val Glu
725 730 735
Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val Cys Val Gln
740 745 750
Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp Ala Cys Val
755 760 765
Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser
770 775 780
Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro Ala Arg Cys
785 790 795 800
Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp Met Val Lys
805 810 815
Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala Glu Asp Ile
820 825 830
Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu Lys Thr Cys
835 840 845
Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala Thr Arg Glu
850 855 860
Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln Lys Thr Ser
865 870 875 880
Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp Leu Lys Met
885 890 895
Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln Asn His Asn
900 905 910
His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala Ile Asp Glu
915 920 925
Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg Gln Lys Pro
930 935 940
Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys Leu Cys Ile
945 950 955 960
Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn Arg Val Met
965 970 975
Gly Tyr Leu Ser Ser Ala
980
<210> 302
<211> 1020
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12-mu IgG2a Fc DANG-anti-mu FAP scFv
<400> 302
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Arg Lys Lys
245 250 255
Glu Lys Met Lys Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly Gly Ser Gly
755 760 765
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Gln Gln Ser
770 775 780
Gly Ala Glu Leu Ala Arg Pro Gly Ala Ser Val Asn Leu Ser Cys Lys
785 790 795 800
Ala Ser Gly Tyr Thr Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys Gln
805 810 815
Arg Thr Gly Gln Gly Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg Ser
820 825 830
Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu Thr
835 840 845
Ala Asp Arg Ser Ser Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu Thr
850 855 860
Ser Glu Asp Ser Ala Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala Pro
865 870 875 880
Phe Ala Phe Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ala Gly Gly
885 890 895
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly
900 905 910
Gly Ser Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser
915 920 925
Pro Gly Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn
930 935 940
Phe Met His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp
945 950 955 960
Ile Phe Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser
965 970 975
Gly Ser Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu
980 985 990
Ala Glu Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro
995 1000 1005
Pro Thr Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys
1010 1015 1020
<210> 303
<211> 1020
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu scIL-12 mut2-mu IgG2a Fc DANG-anti-mu FAP scFv
<400> 303
Met Trp Glu Leu Glu Lys Asp Val Tyr Val Val Glu Val Asp Trp Thr
1 5 10 15
Pro Asp Ala Pro Gly Glu Thr Val Asn Leu Thr Cys Asp Thr Pro Glu
20 25 30
Glu Asp Asp Ile Thr Trp Thr Ser Asp Gln Arg His Gly Val Ile Gly
35 40 45
Ser Gly Lys Thr Leu Thr Ile Thr Val Lys Glu Phe Leu Asp Ala Gly
50 55 60
Gln Tyr Thr Cys His Lys Gly Gly Glu Thr Leu Ser His Ser His Leu
65 70 75 80
Leu Leu His Lys Lys Glu Asn Gly Ile Trp Ser Thr Glu Ile Leu Lys
85 90 95
Asn Phe Lys Asn Lys Thr Phe Leu Lys Cys Glu Ala Pro Asn Tyr Ser
100 105 110
Gly Arg Phe Thr Cys Ser Trp Leu Val Gln Arg Asn Met Asp Leu Lys
115 120 125
Phe Asn Ile Lys Ser Ser Ser Ser Ser Pro Asp Ser Arg Ala Val Thr
130 135 140
Cys Gly Met Ala Ser Leu Ser Ala Glu Lys Val Thr Leu Asp Gln Arg
145 150 155 160
Asp Tyr Glu Lys Tyr Ser Val Ser Cys Gln Glu Asp Val Thr Cys Pro
165 170 175
Thr Ala Glu Glu Thr Leu Pro Ile Glu Leu Ala Leu Glu Ala Arg Gln
180 185 190
Gln Asn Lys Tyr Glu Asn Tyr Ser Thr Ser Phe Phe Ile Arg Asp Ile
195 200 205
Ile Lys Pro Asp Pro Pro Lys Asn Leu Gln Met Lys Pro Leu Lys Asn
210 215 220
Ser Gln Val Glu Val Ser Trp Glu Tyr Pro Asp Ser Trp Ser Thr Pro
225 230 235 240
His Ser Tyr Phe Ser Leu Lys Phe Phe Val Arg Ile Gln Ala Ala Ala
245 250 255
Glu Lys Met Ala Glu Thr Glu Glu Gly Cys Asn Gln Lys Gly Ala Phe
260 265 270
Leu Val Glu Lys Thr Ser Thr Glu Val Gln Cys Lys Gly Gly Asn Val
275 280 285
Cys Val Gln Ala Gln Asp Arg Tyr Tyr Asn Ser Ser Cys Ser Lys Trp
290 295 300
Ala Cys Val Pro Cys Arg Val Arg Ser Gly Gly Gly Gly Ser Gly Gly
305 310 315 320
Gly Gly Ser Gly Gly Gly Gly Ser Arg Val Ile Pro Val Ser Gly Pro
325 330 335
Ala Arg Cys Leu Ser Gln Ser Arg Asn Leu Leu Lys Thr Thr Asp Asp
340 345 350
Met Val Lys Thr Ala Arg Glu Lys Leu Lys His Tyr Ser Cys Thr Ala
355 360 365
Glu Asp Ile Asp His Glu Asp Ile Thr Arg Asp Gln Thr Ser Thr Leu
370 375 380
Lys Thr Cys Leu Pro Leu Glu Leu His Lys Asn Glu Ser Cys Leu Ala
385 390 395 400
Thr Arg Glu Thr Ser Ser Thr Thr Arg Gly Ser Cys Leu Pro Pro Gln
405 410 415
Lys Thr Ser Leu Met Met Thr Leu Cys Leu Gly Ser Ile Tyr Glu Asp
420 425 430
Leu Lys Met Tyr Gln Thr Glu Phe Gln Ala Ile Asn Ala Ala Leu Gln
435 440 445
Asn His Asn His Gln Gln Ile Ile Leu Asp Lys Gly Met Leu Val Ala
450 455 460
Ile Asp Glu Leu Met Gln Ser Leu Asn His Asn Gly Glu Thr Leu Arg
465 470 475 480
Gln Lys Pro Pro Val Gly Glu Ala Asp Pro Tyr Arg Val Lys Met Lys
485 490 495
Leu Cys Ile Leu Leu His Ala Phe Ser Thr Arg Val Val Thr Ile Asn
500 505 510
Arg Val Met Gly Tyr Leu Ser Ser Ala Gly Gly Gly Gly Ser Gly Gly
515 520 525
Gly Gly Ser Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys
530 535 540
Lys Cys Pro Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe
545 550 555 560
Pro Pro Lys Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val
565 570 575
Thr Cys Val Val Val Ala Val Ser Glu Asp Asp Pro Asp Val Gln Ile
580 585 590
Ser Trp Phe Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr
595 600 605
His Arg Glu Asp Tyr Gly Ser Thr Leu Arg Val Val Ser Ala Leu Pro
610 615 620
Ile Gln His Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val
625 630 635 640
Asn Asn Lys Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro
645 650 655
Lys Gly Ser Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu
660 665 670
Glu Glu Met Thr Lys Lys Gln Val Thr Leu Thr Cys Met Val Thr Asp
675 680 685
Phe Met Pro Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr
690 695 700
Glu Leu Asn Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser
705 710 715 720
Tyr Phe Met Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu
725 730 735
Arg Asn Ser Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His
740 745 750
His Thr Thr Lys Ser Phe Ser Arg Thr Pro Gly Gly Gly Gly Ser Gly
755 760 765
Gly Gly Gly Ser Gly Gly Gly Gly Ser Gln Val Gln Leu Gln Gln Ser
770 775 780
Gly Ala Glu Leu Ala Arg Pro Gly Ala Ser Val Asn Leu Ser Cys Lys
785 790 795 800
Ala Ser Gly Tyr Thr Phe Thr Asn Asn Gly Ile Asn Trp Leu Lys Gln
805 810 815
Arg Thr Gly Gln Gly Leu Glu Trp Ile Gly Glu Ile Tyr Pro Arg Ser
820 825 830
Thr Asn Thr Leu Tyr Asn Glu Lys Phe Lys Gly Lys Ala Thr Leu Thr
835 840 845
Ala Asp Arg Ser Ser Asn Thr Ala Tyr Met Glu Leu Arg Ser Leu Thr
850 855 860
Ser Glu Asp Ser Ala Val Tyr Phe Cys Ala Arg Thr Leu Thr Ala Pro
865 870 875 880
Phe Ala Phe Trp Gly Gln Gly Thr Leu Val Thr Val Ser Ala Gly Gly
885 890 895
Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly Gly Ser Gly Gly Gly
900 905 910
Gly Ser Gln Ile Val Leu Thr Gln Ser Pro Ala Ile Met Ser Ala Ser
915 920 925
Pro Gly Glu Lys Val Thr Met Thr Cys Ser Ala Ser Ser Gly Val Asn
930 935 940
Phe Met His Trp Tyr Gln Gln Lys Ser Gly Thr Ser Pro Lys Arg Trp
945 950 955 960
Ile Phe Asp Thr Ser Lys Leu Ala Ser Gly Val Pro Ala Arg Phe Ser
965 970 975
Gly Ser Gly Ser Gly Thr Ser Tyr Ser Leu Thr Ile Ser Ser Met Glu
980 985 990
Ala Glu Asp Ala Ala Thr Tyr Tyr Cys Gln Gln Trp Ser Phe Asn Pro
995 1000 1005
Pro Thr Phe Gly Gly Gly Thr Lys Leu Glu Ile Lys
1010 1015 1020
<210> 304
<211> 227
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> hu IgG1 Fc
<400> 304
Asp Lys Thr His Thr Cys Pro Pro Cys Pro Ala Pro Glu Leu Leu Gly
1 5 10 15
Gly Pro Ser Val Phe Leu Phe Pro Pro Lys Pro Lys Asp Thr Leu Met
20 25 30
Ile Ser Arg Thr Pro Glu Val Thr Cys Val Val Val Asp Val Ser His
35 40 45
Glu Asp Pro Glu Val Lys Phe Asn Trp Tyr Val Asp Gly Val Glu Val
50 55 60
His Asn Ala Lys Thr Lys Pro Arg Glu Glu Gln Tyr Asn Ser Thr Tyr
65 70 75 80
Arg Val Val Ser Val Leu Thr Val Leu His Gln Asp Trp Leu Asn Gly
85 90 95
Lys Glu Tyr Lys Cys Lys Val Ser Asn Lys Ala Leu Pro Ala Pro Ile
100 105 110
Glu Lys Thr Ile Ser Lys Ala Lys Gly Gln Pro Arg Glu Pro Gln Val
115 120 125
Tyr Thr Leu Pro Pro Ser Arg Asp Glu Leu Thr Lys Asn Gln Val Ser
130 135 140
Leu Thr Cys Leu Val Lys Gly Phe Tyr Pro Ser Asp Ile Ala Val Glu
145 150 155 160
Trp Glu Ser Asn Gly Gln Pro Glu Asn Asn Tyr Lys Thr Thr Pro Pro
165 170 175
Val Leu Asp Ser Asp Gly Ser Phe Phe Leu Tyr Ser Lys Leu Thr Val
180 185 190
Asp Lys Ser Arg Trp Gln Gln Gly Asn Val Phe Ser Cys Ser Val Met
195 200 205
His Glu Ala Leu His Asn His Tyr Thr Gln Lys Ser Leu Ser Leu Ser
210 215 220
Pro Gly Lys
225
<210> 305
<211> 233
<212> БЕЛОК
<213> Искусственная последовательность
<220>
<223> mu IgG2a Fc
<400> 305
Glu Pro Arg Gly Pro Thr Ile Lys Pro Cys Pro Pro Cys Lys Cys Pro
1 5 10 15
Ala Pro Asn Leu Leu Gly Gly Pro Ser Val Phe Ile Phe Pro Pro Lys
20 25 30
Ile Lys Asp Val Leu Met Ile Ser Leu Ser Pro Ile Val Thr Cys Val
35 40 45
Val Val Asp Val Ser Glu Asp Asp Pro Asp Val Gln Ile Ser Trp Phe
50 55 60
Val Asn Asn Val Glu Val His Thr Ala Gln Thr Gln Thr His Arg Glu
65 70 75 80
Asp Tyr Asn Ser Thr Leu Arg Val Val Ser Ala Leu Pro Ile Gln His
85 90 95
Gln Asp Trp Met Ser Gly Lys Glu Phe Lys Cys Lys Val Asn Asn Lys
100 105 110
Asp Leu Pro Ala Pro Ile Glu Arg Thr Ile Ser Lys Pro Lys Gly Ser
115 120 125
Val Arg Ala Pro Gln Val Tyr Val Leu Pro Pro Pro Glu Glu Glu Met
130 135 140
Thr Lys Lys Gln Val Thr Leu Thr Cys Met Val Thr Asp Phe Met Pro
145 150 155 160
Glu Asp Ile Tyr Val Glu Trp Thr Asn Asn Gly Lys Thr Glu Leu Asn
165 170 175
Tyr Lys Asn Thr Glu Pro Val Leu Asp Ser Asp Gly Ser Tyr Phe Met
180 185 190
Tyr Ser Lys Leu Arg Val Glu Lys Lys Asn Trp Val Glu Arg Asn Ser
195 200 205
Tyr Ser Cys Ser Val Val His Glu Gly Leu His Asn His His Thr Thr
210 215 220
Lys Ser Phe Ser Arg Thr Pro Gly Lys
225 230
<---
| название | год | авторы | номер документа |
|---|---|---|---|
| КОМПОЗИЦИЯ ДЛЯ ОБЛЕГЧЕНИЯ ИЛИ ЛЕЧЕНИЯ БОЛИ | 2017 |
|
RU2725830C1 |
| Биспецифическое антитело анти-HER2/анти-4-1BB и его применение | 2020 |
|
RU2831838C2 |
| АНТИ-LILRB1 АНТИТЕЛО И ЕГО ПРИМЕНЕНИЕ | 2020 |
|
RU2801535C1 |
| ФАРМАЦЕВТИЧЕСКАЯ КОМПОЗИЦИЯ, СОДЕРЖАЩАЯ АНТИТЕЛО, СПЕЦИФИЧНО СВЯЗЫВАЮЩЕЕСЯ С N-КОНЦОМ ЛИЗИЛ-тРНК-СИНТЕТАЗЫ, В КАЧЕСТВЕ ЭФФЕКТИВНОГО ИНГРЕДИЕНТА ДЛЯ ПРОФИЛАКТИКИ ИЛИ ЛЕЧЕНИЯ ЗАБОЛЕВАНИЯ, ОБУСЛОВЛЕННОГО МИГРАЦИЕЙ КЛЕТОК | 2018 |
|
RU2749591C1 |
| ВАРИАНТ АЛЬДОЛАЗЫ AROG И СПОСОБ ПОЛУЧЕНИЯ АМИНОКИСЛОТЫ С РАЗВЕТВЛЕННОЙ ЦЕПЬЮ С ЕГО ИСПОЛЬЗОВАНИЕМ | 2021 |
|
RU2826456C1 |
| СЛИТЫЙ БЕЛОК GDF15 ДЛИТЕЛЬНОГО ДЕЙСТВИЯ И СОДЕРЖАЩАЯ ЕГО ФАРМАЦЕВТИЧЕСКАЯ КОМПОЗИЦИЯ | 2020 |
|
RU2836280C1 |
| Новый вариант О-сукцинилгомосеринтрансферазы и способ получения О-сукцинилгомосерина с использованием этого варианта | 2018 |
|
RU2747493C1 |
| АНТИТЕЛА ПРОТИВ БЕЛКА-1 ЗАПРОГРАММИРОВАННОЙ КЛЕТОЧНОЙ СМЕРТИ (PD-1) И ИХ ПРИМЕНЕНИЕ | 2017 |
|
RU2725950C1 |
| БИСПЕЦИФИЧЕСКОЕ АНТИТЕЛО АНТИ-EGFR/АНТИ-4-1ВВ И ЕГО ПРИМЕНЕНИЕ | 2020 |
|
RU2831836C2 |
| КОМПОЗИЦИЯ ДЛЯ КУЛЬТИВИРОВАНИЯ РЕГУЛЯТОРНЫХ Т-КЛЕТОК И ЕЕ ПРИМЕНЕНИЕ | 2020 |
|
RU2807802C1 |


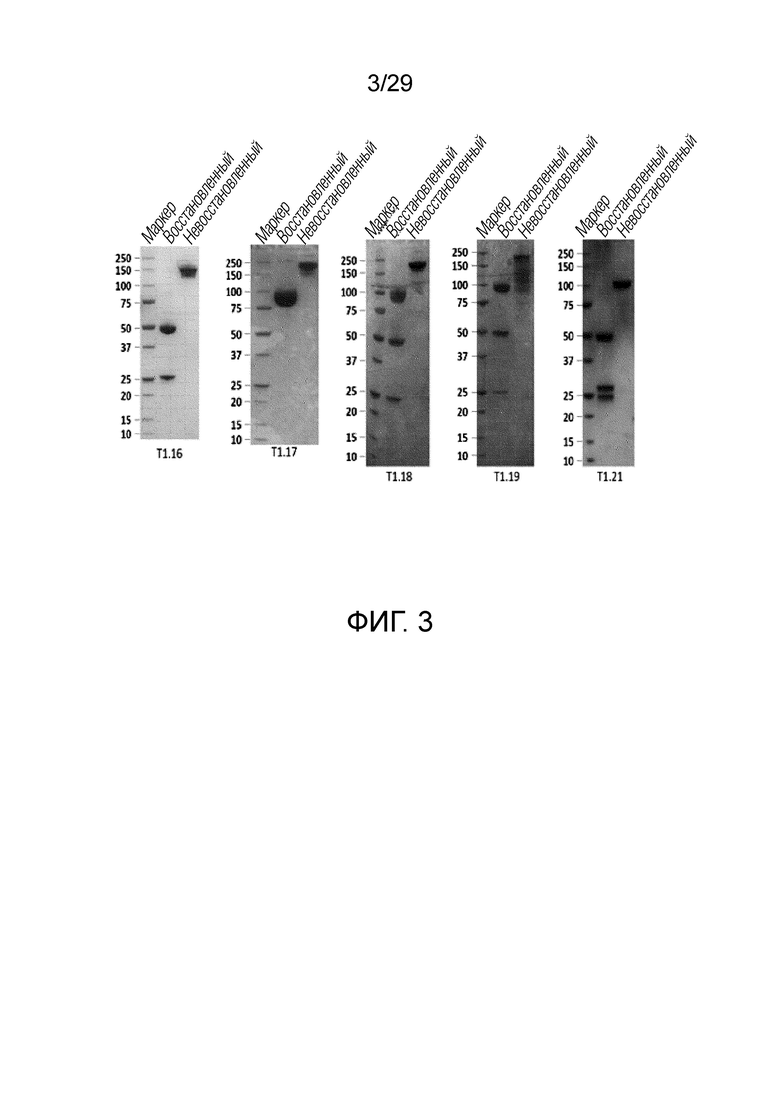
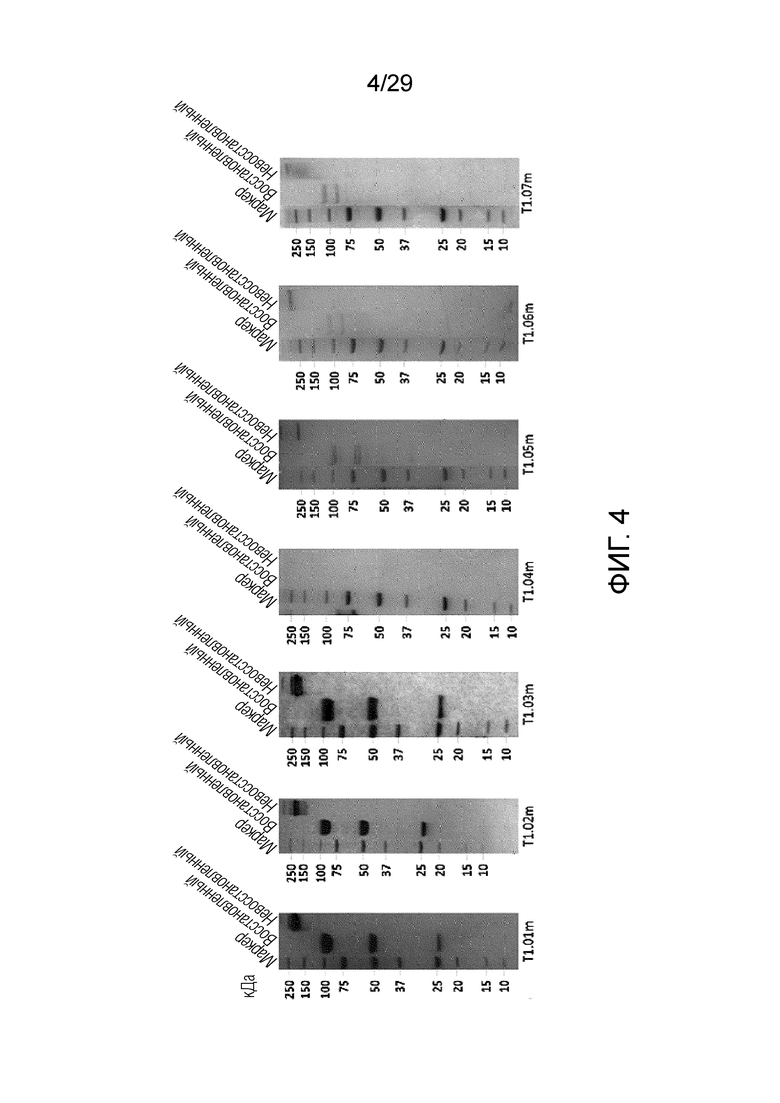

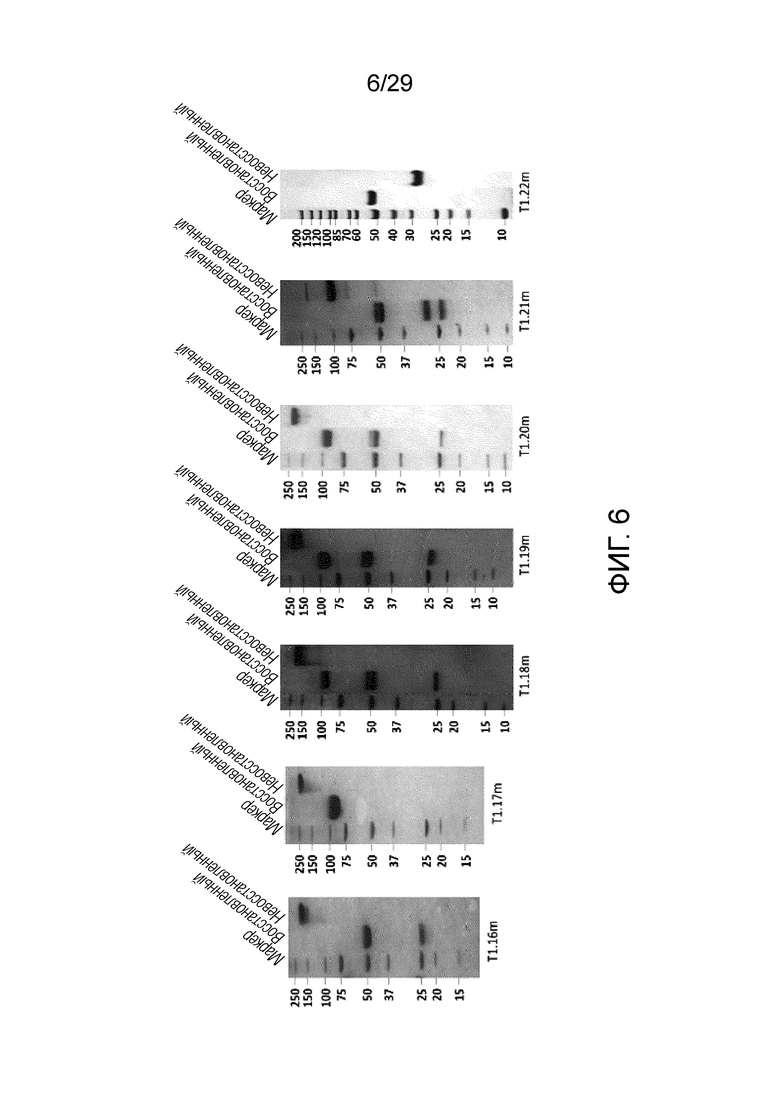
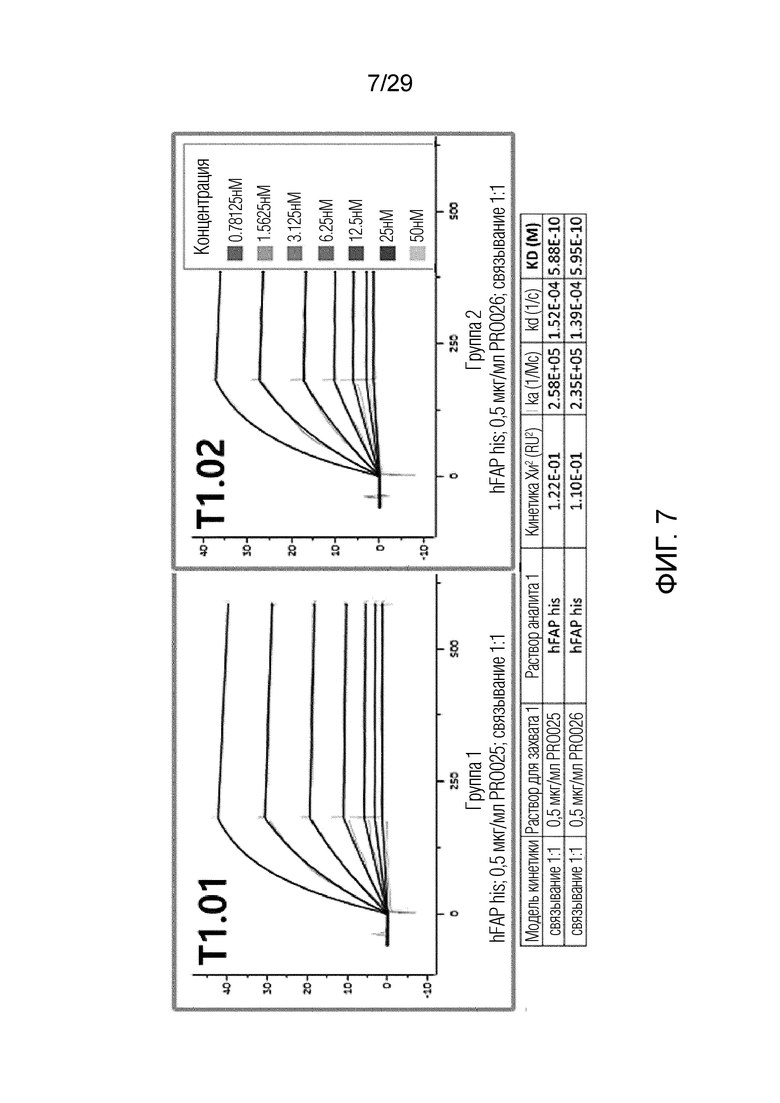
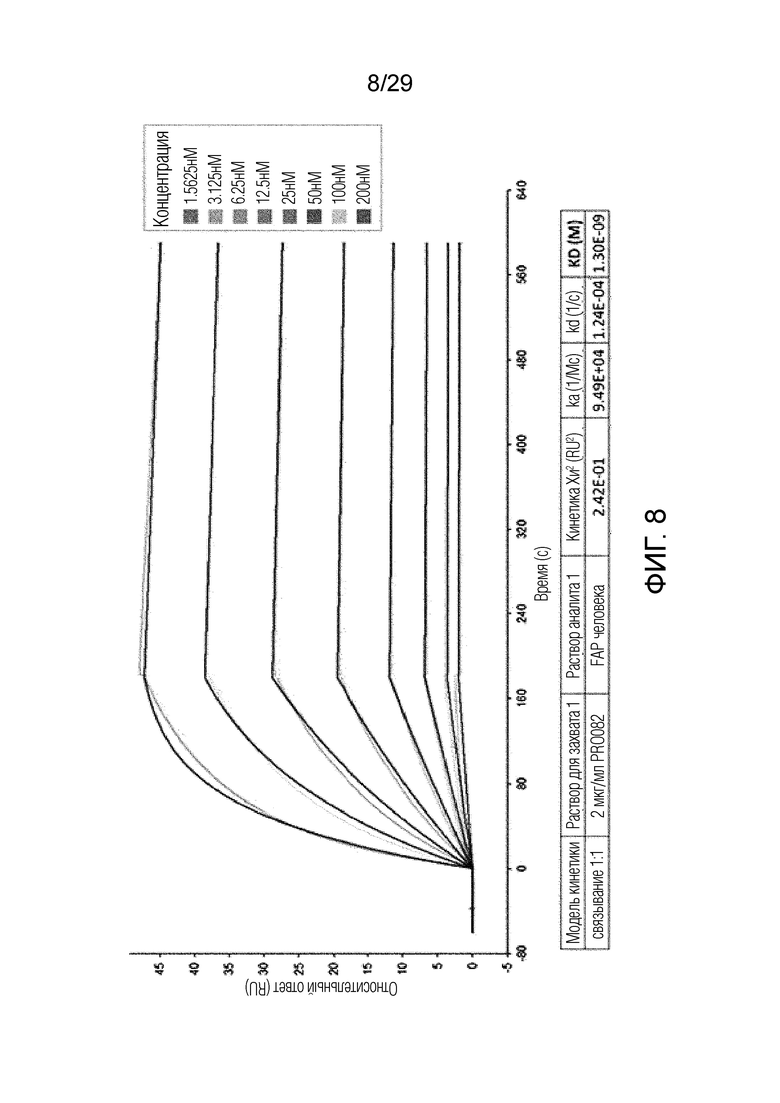
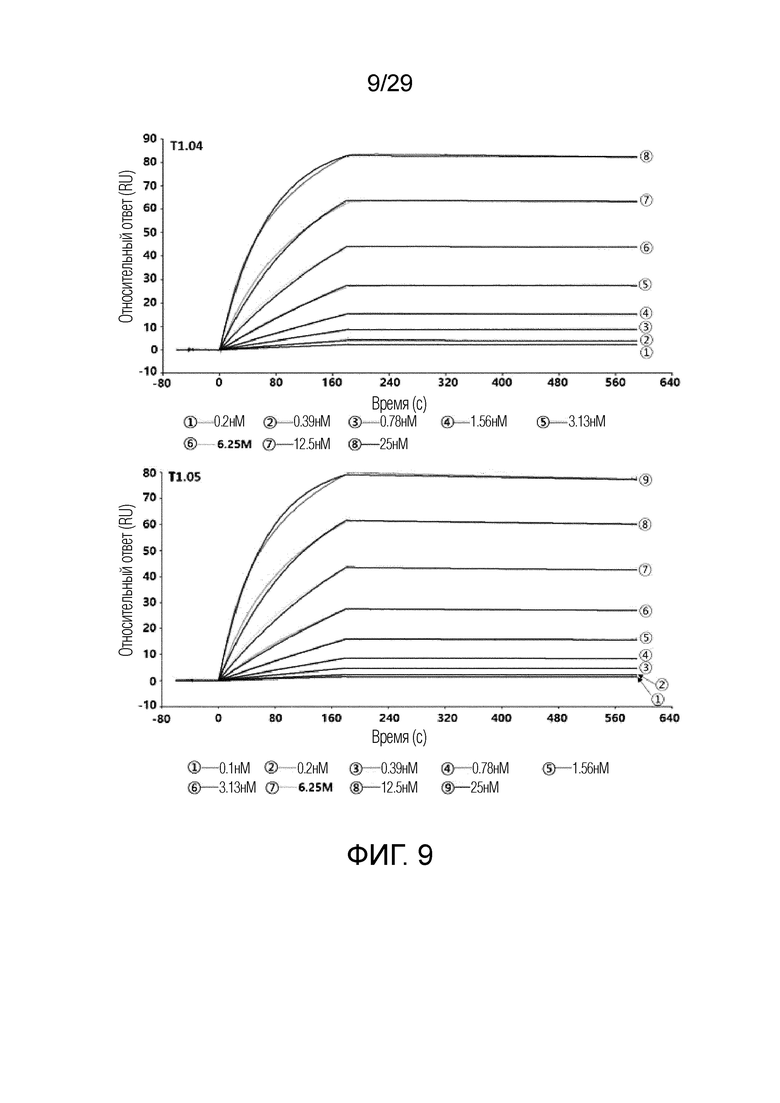
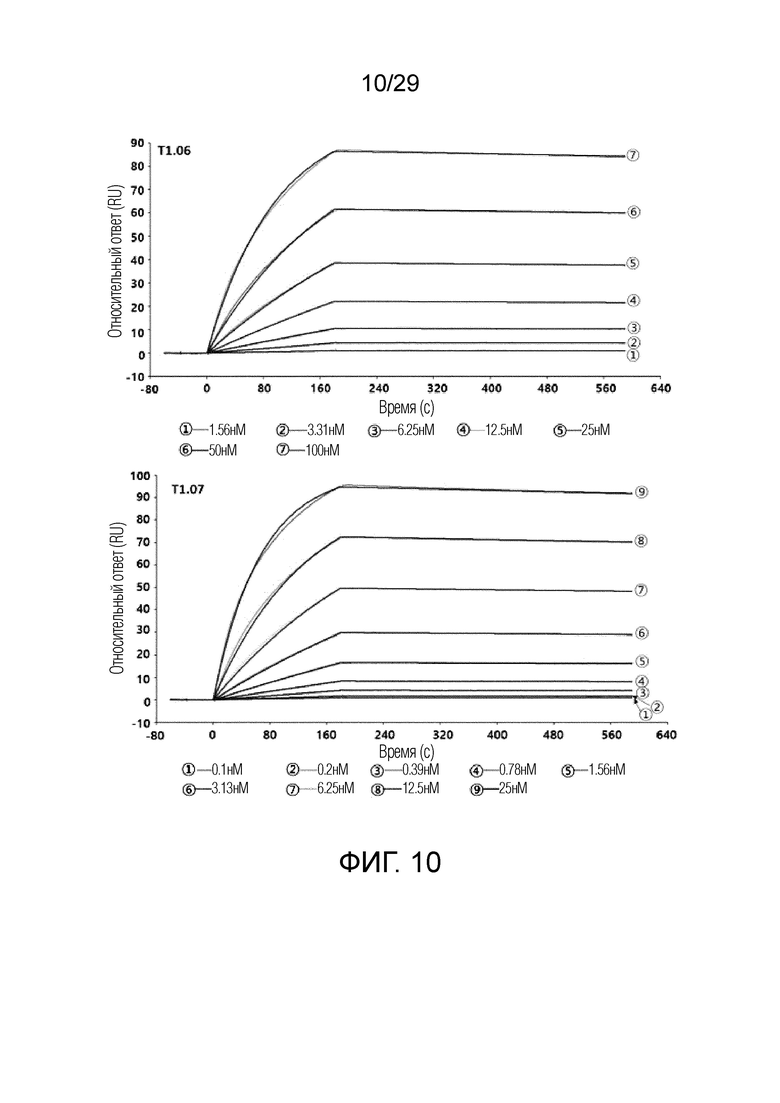
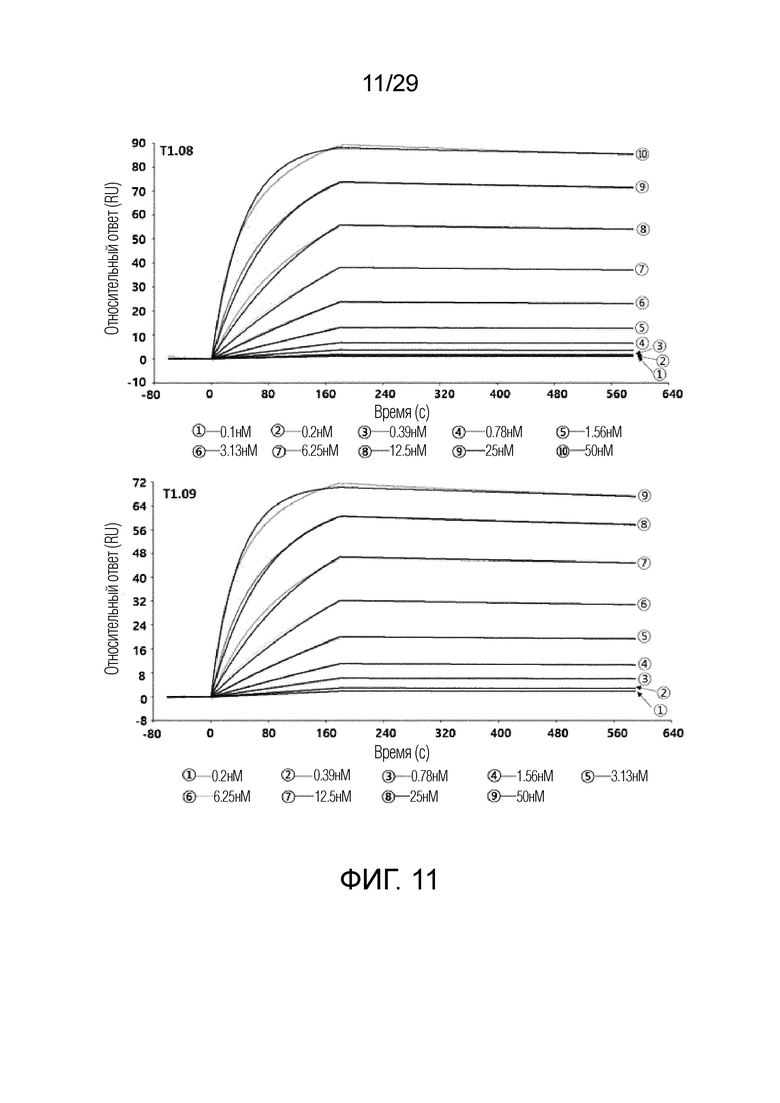
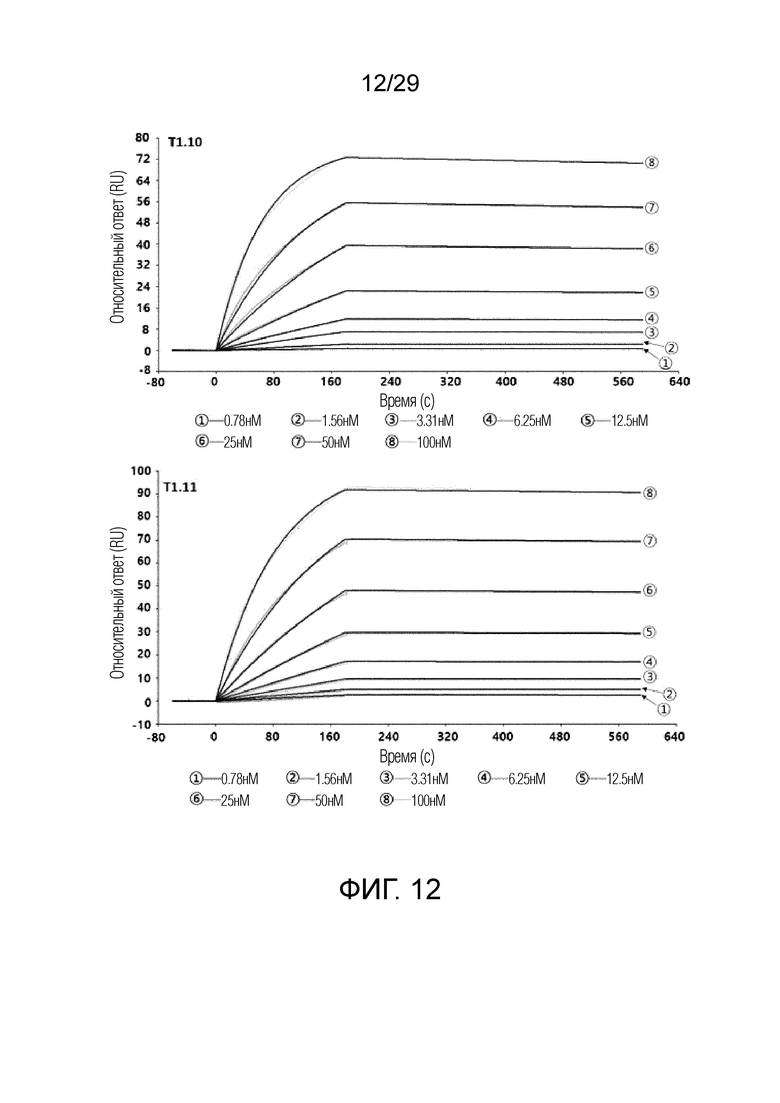
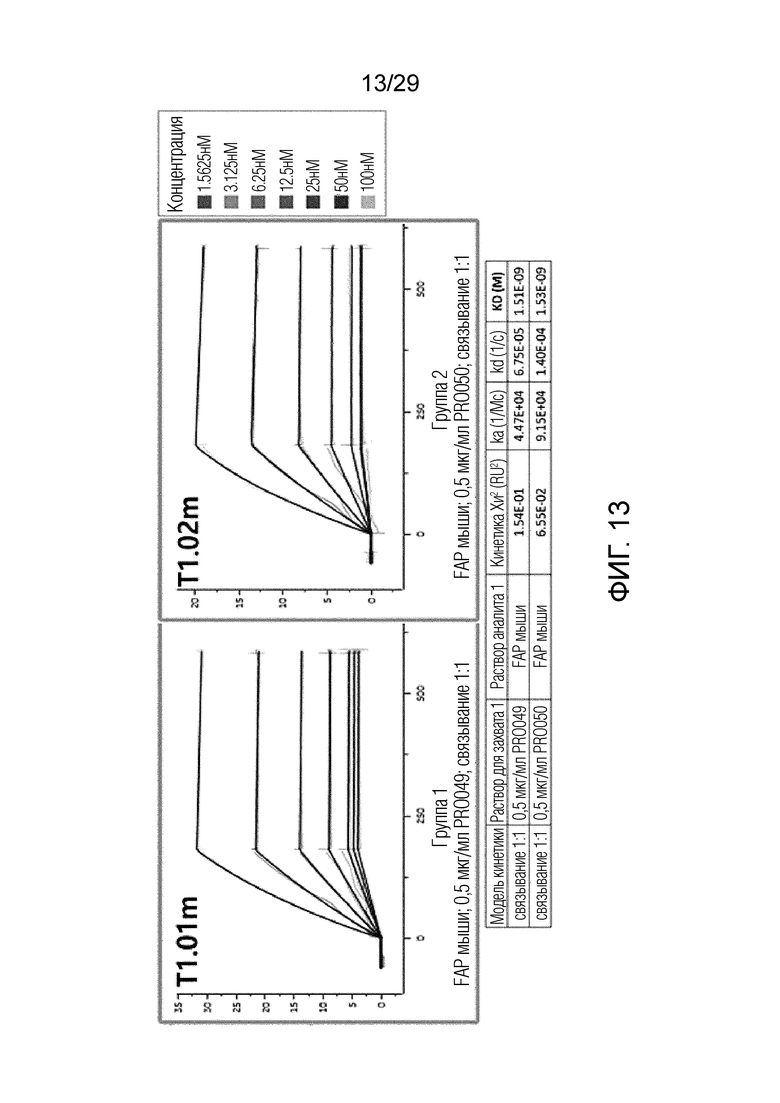
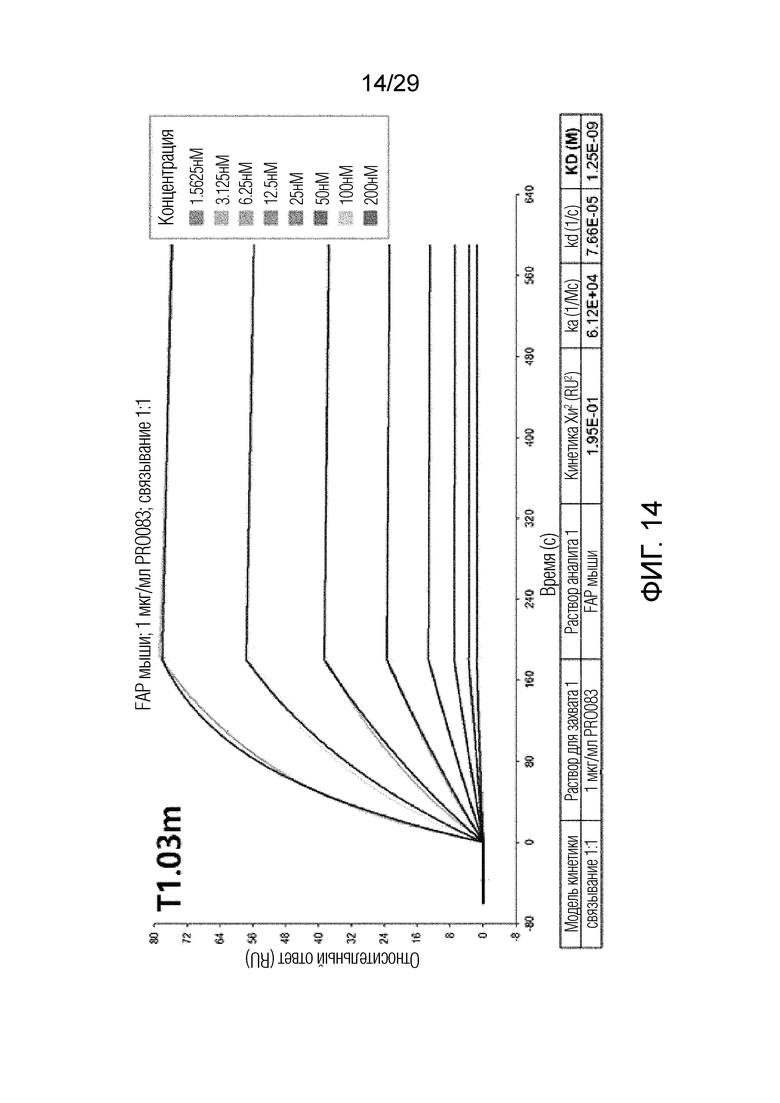
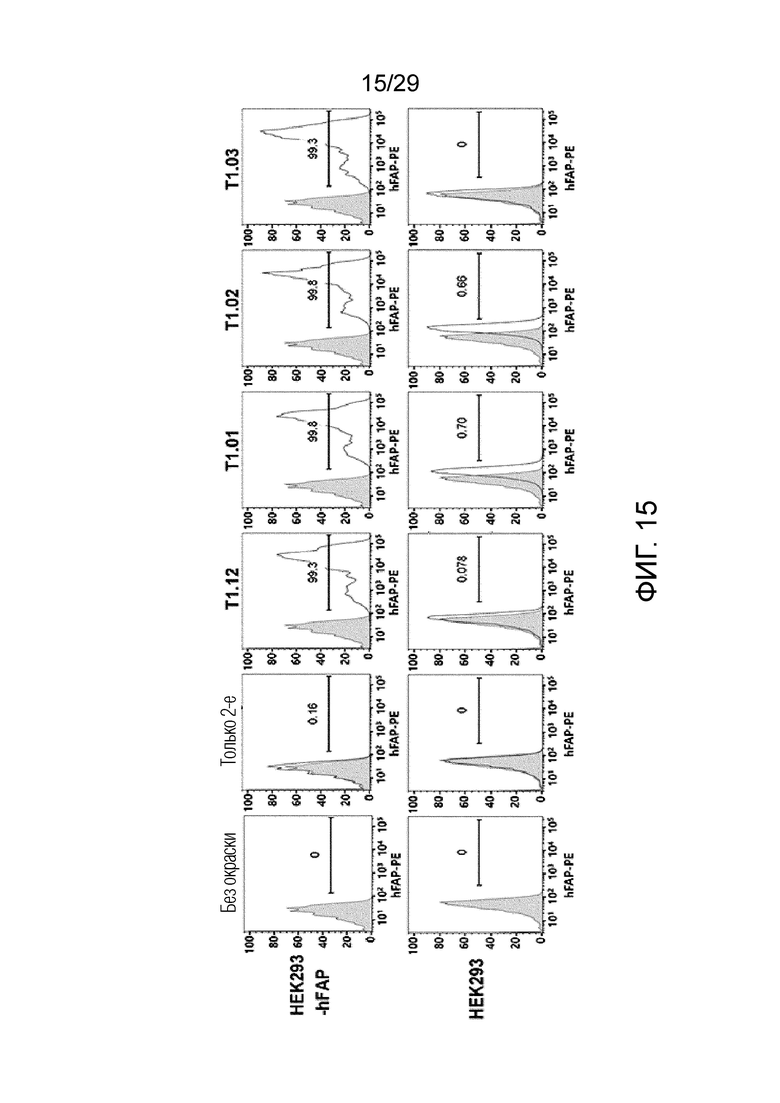
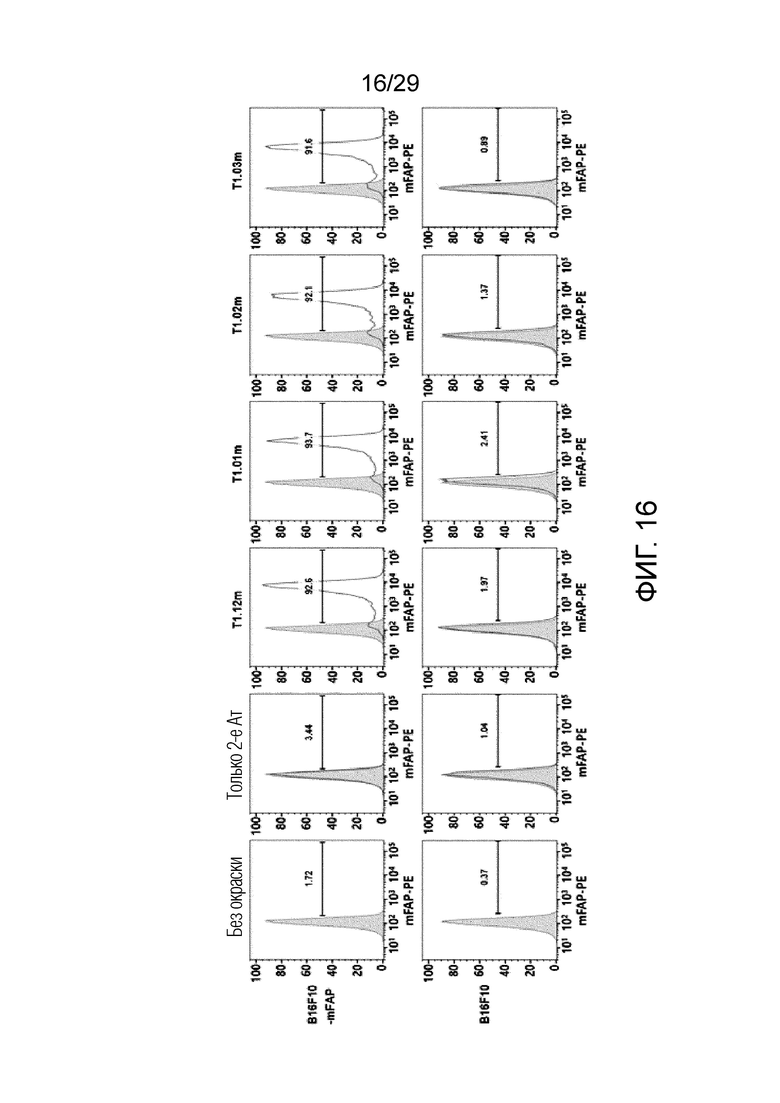
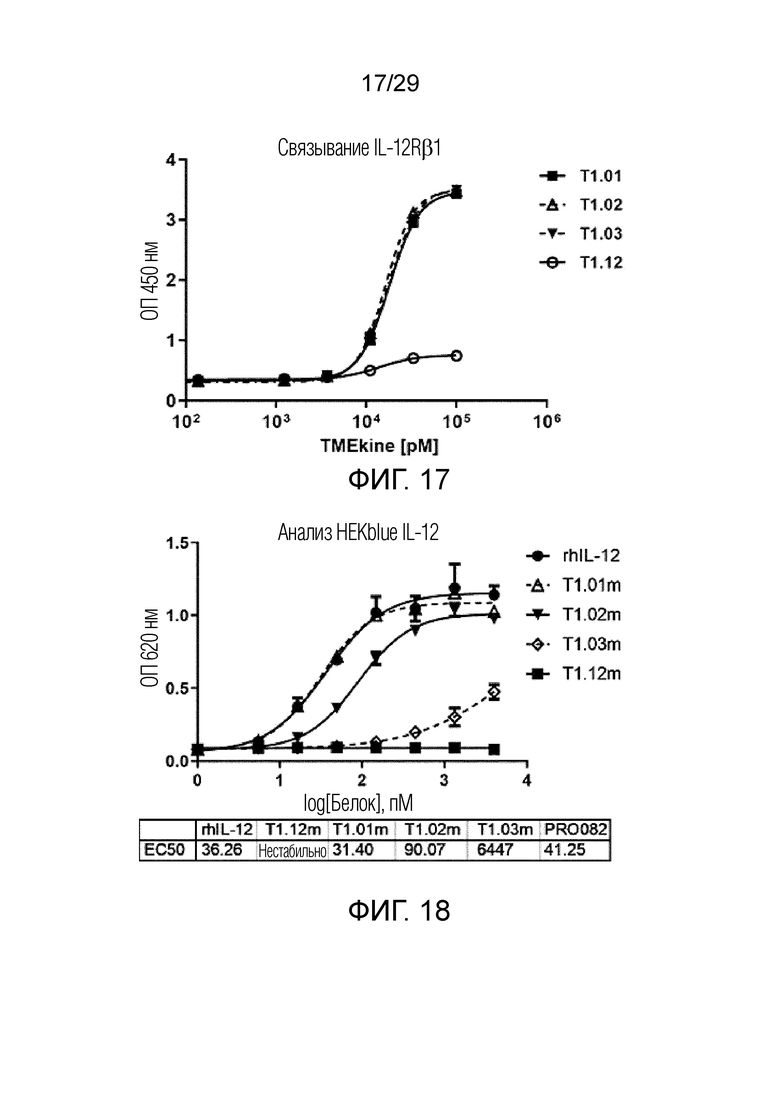
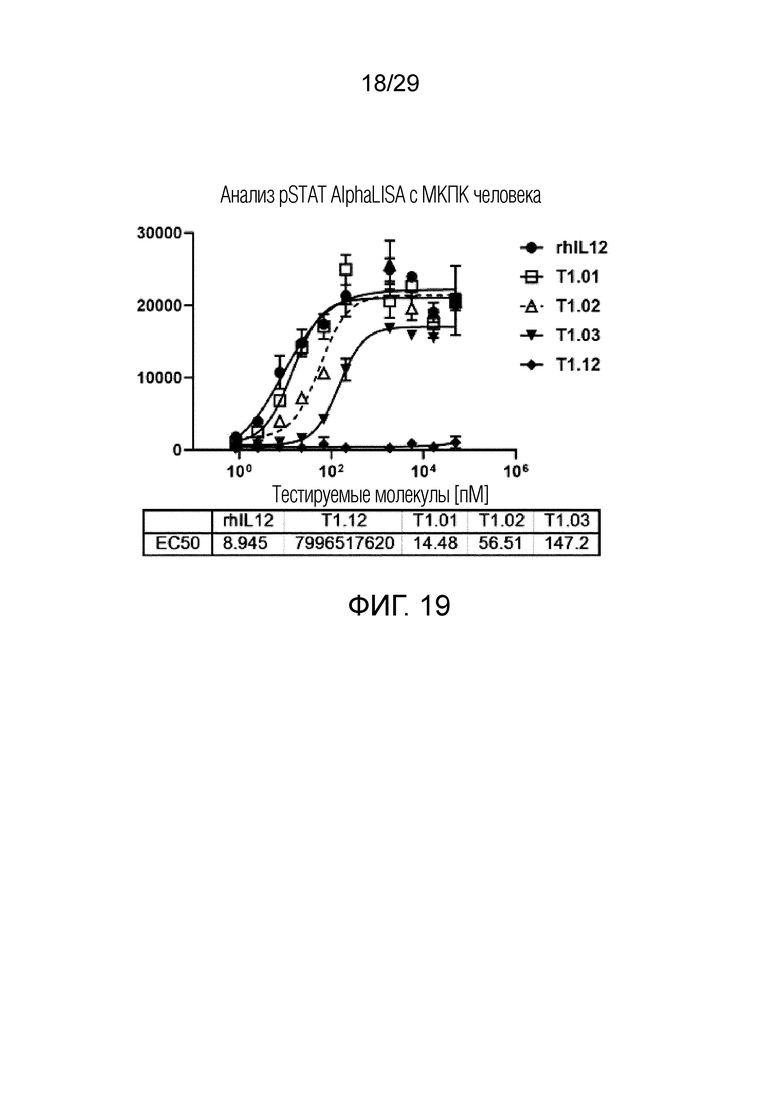
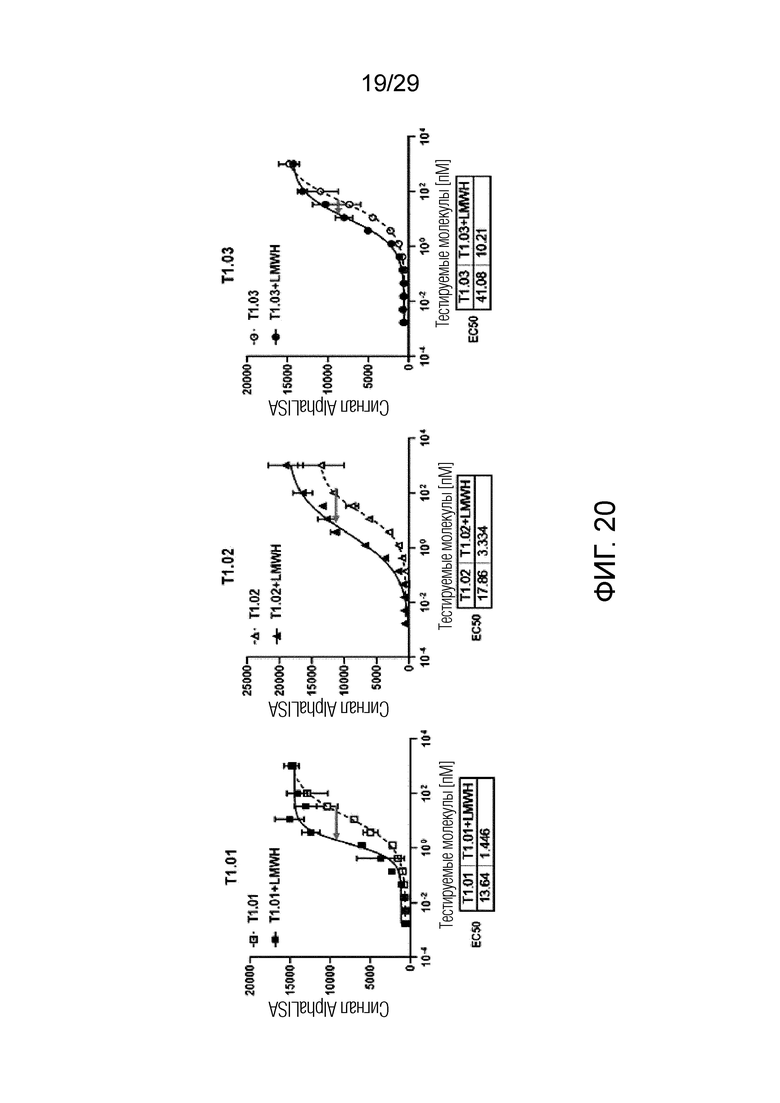
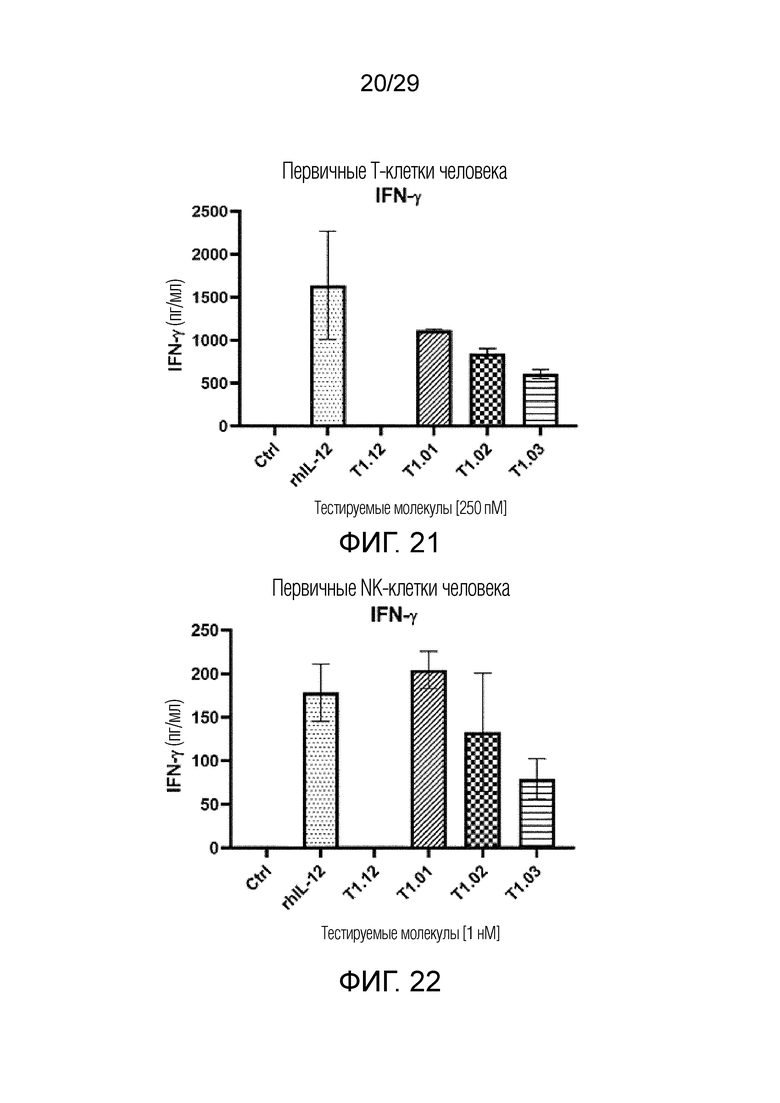
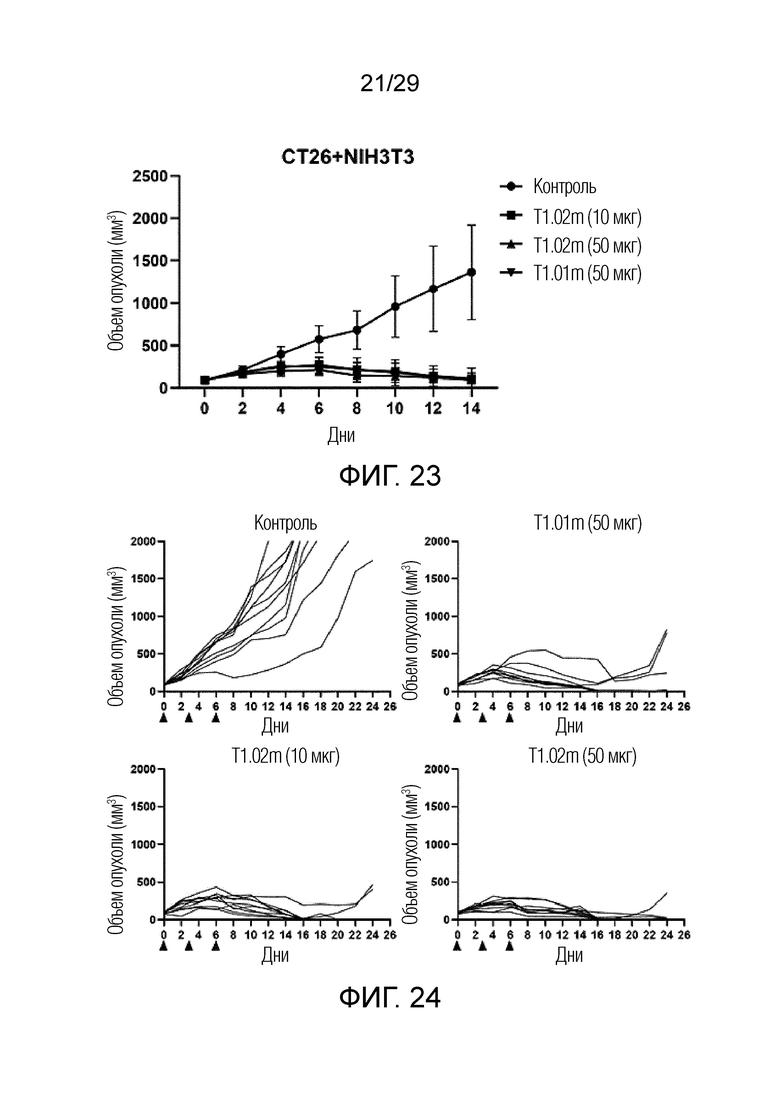
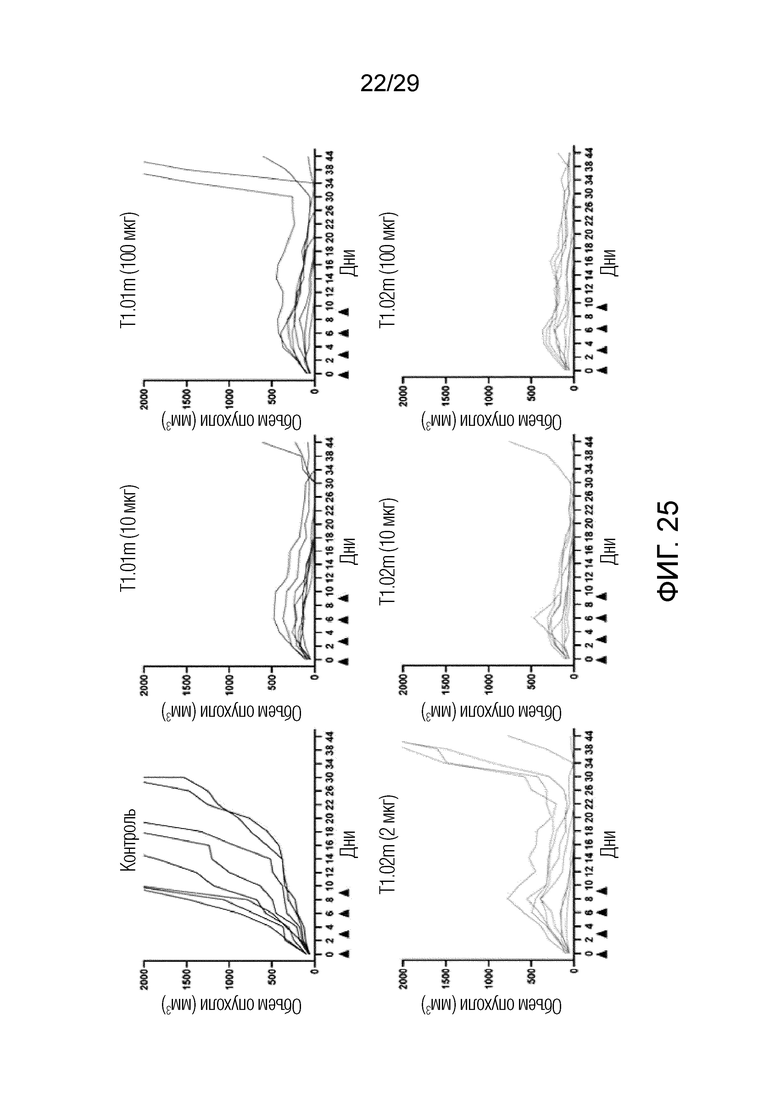
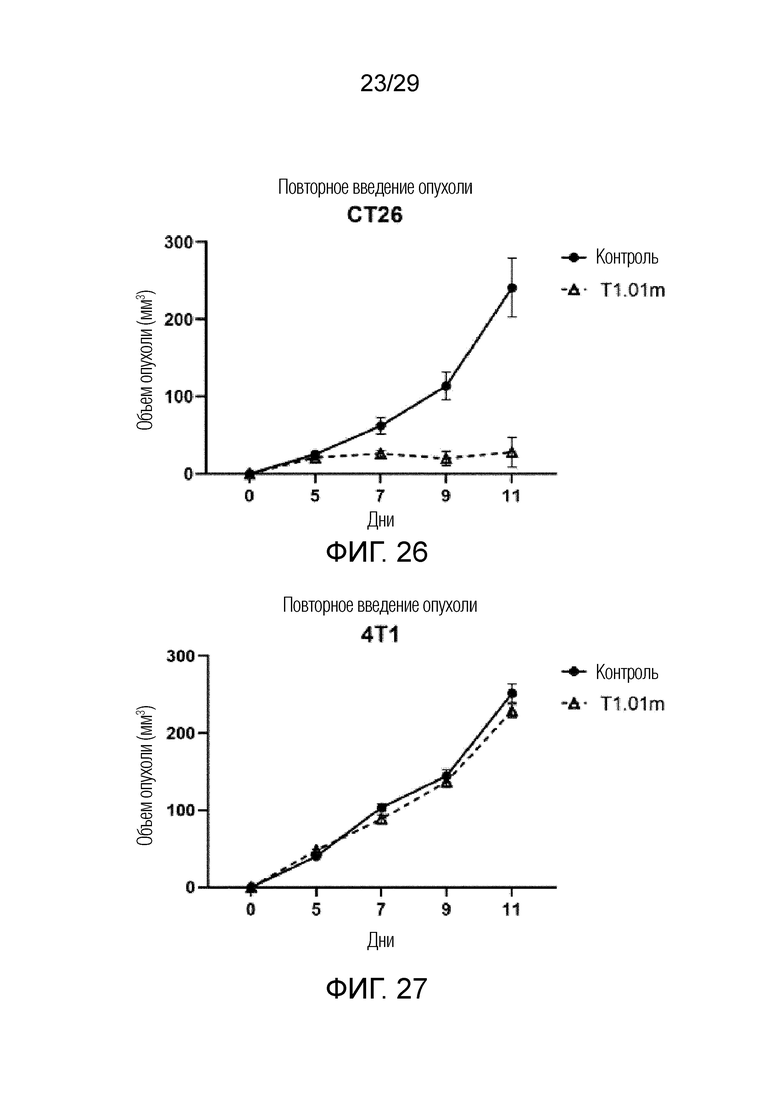
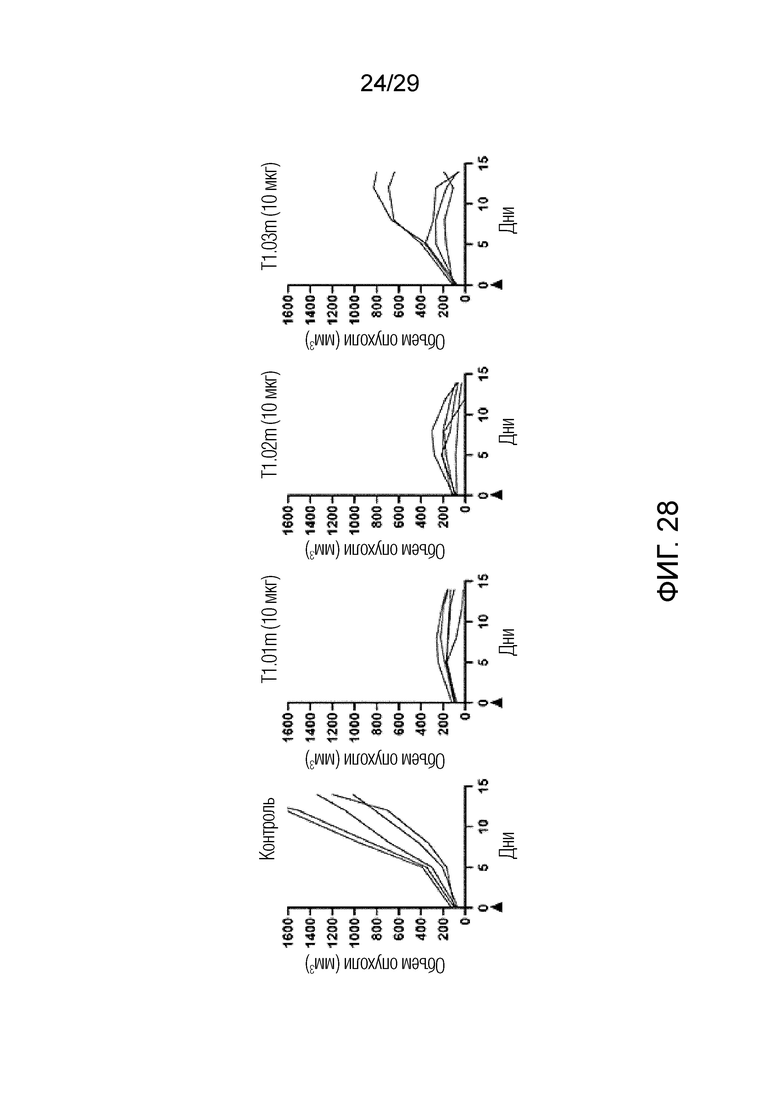
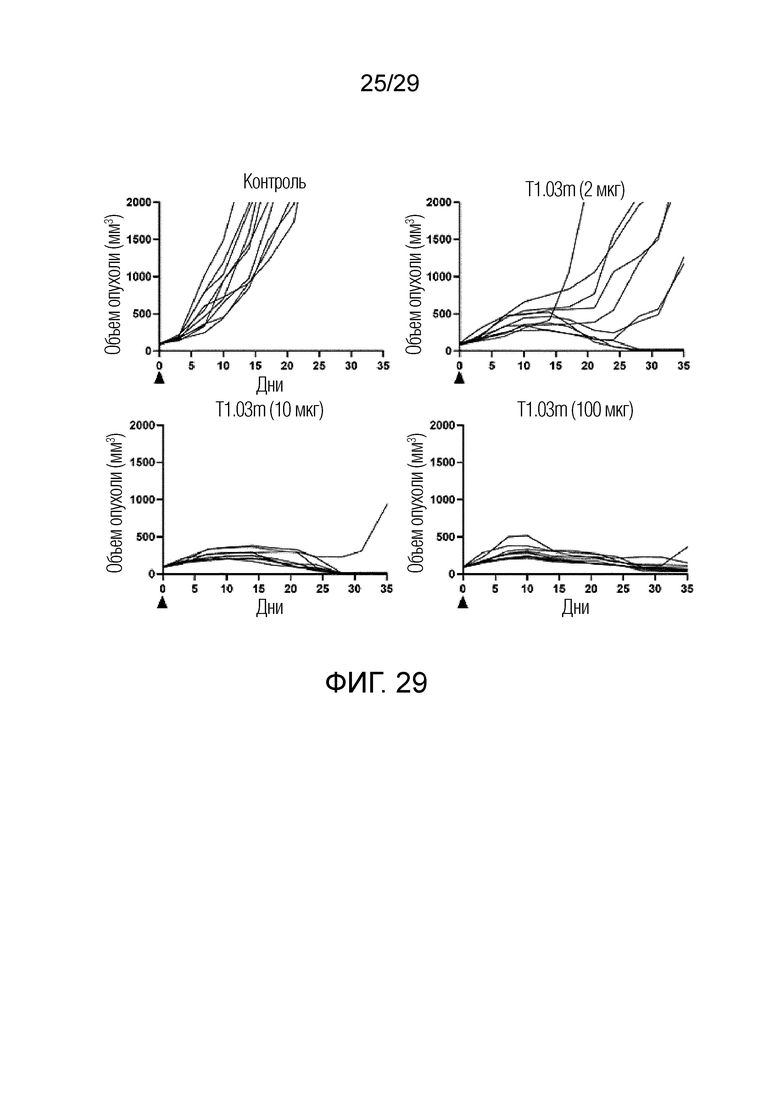
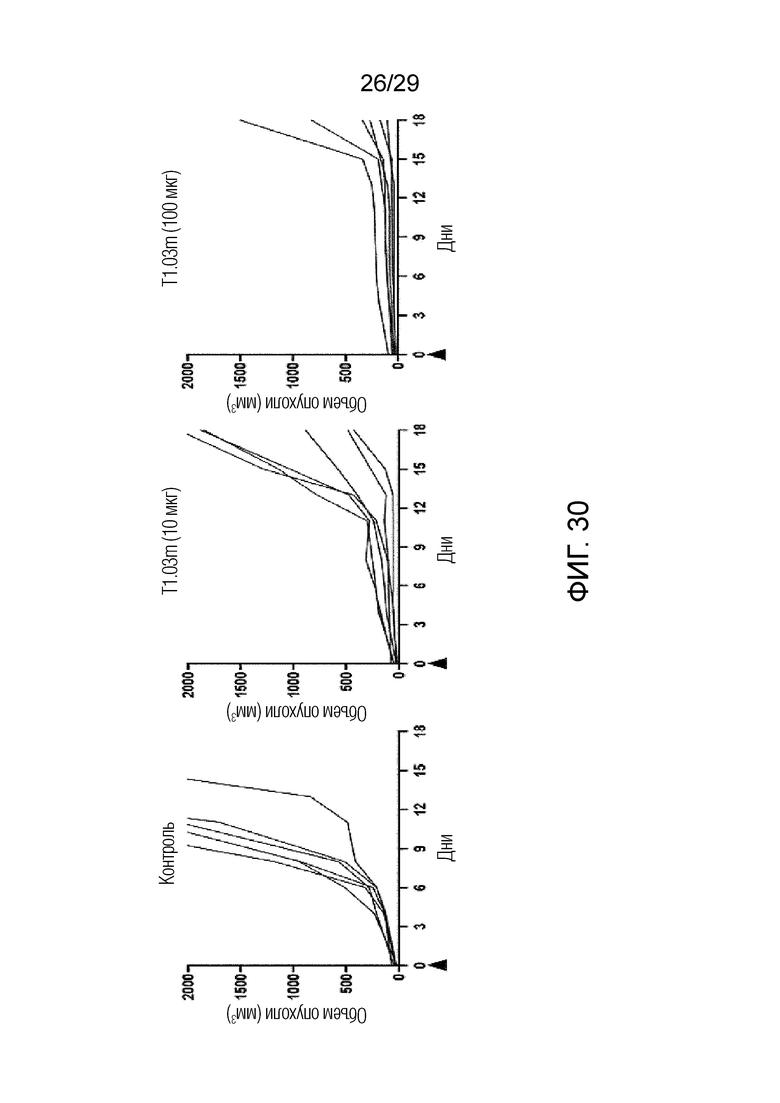
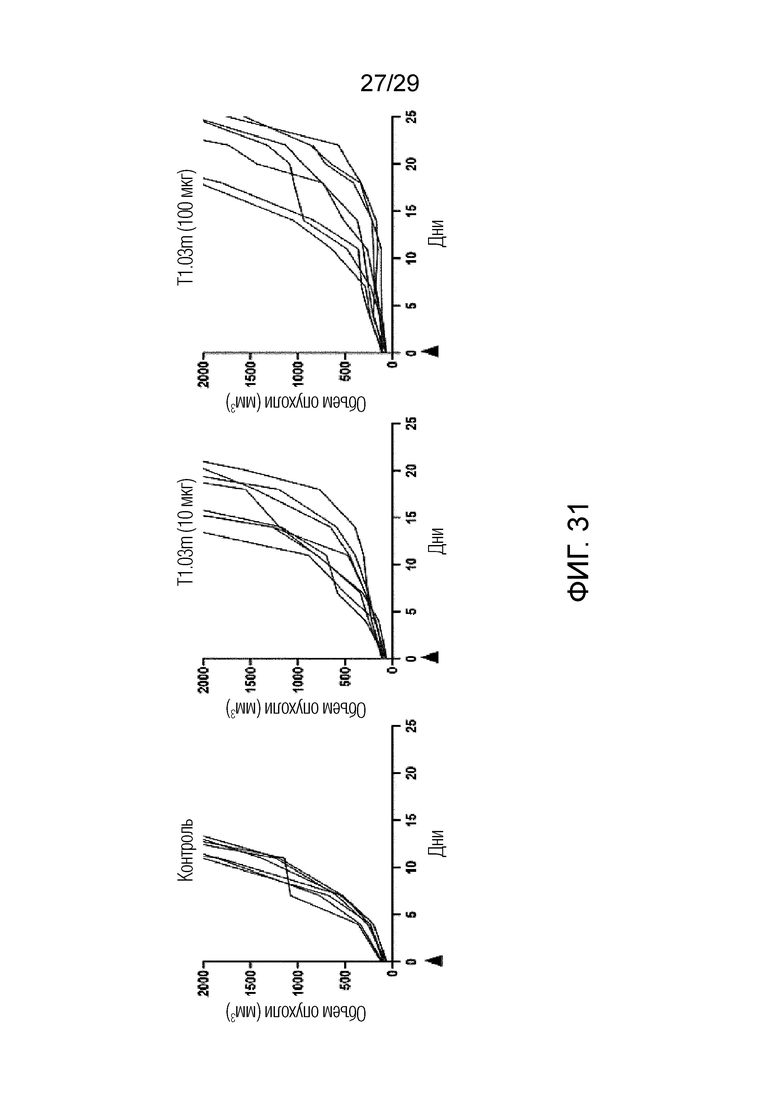
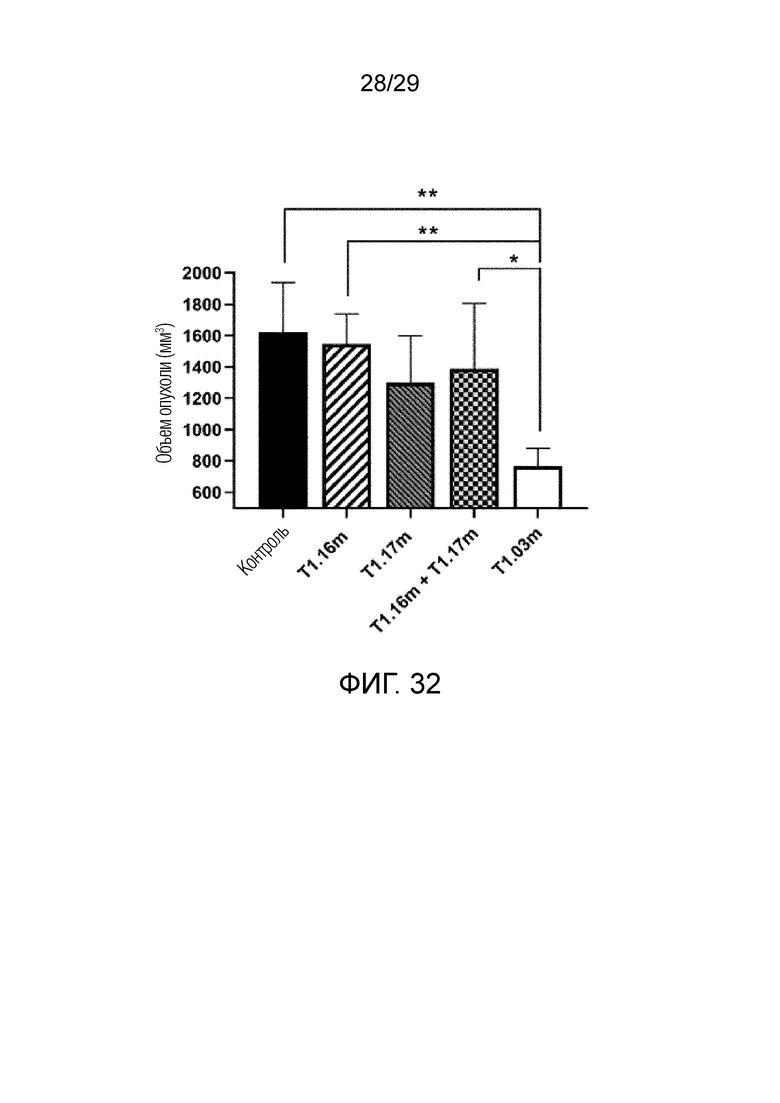
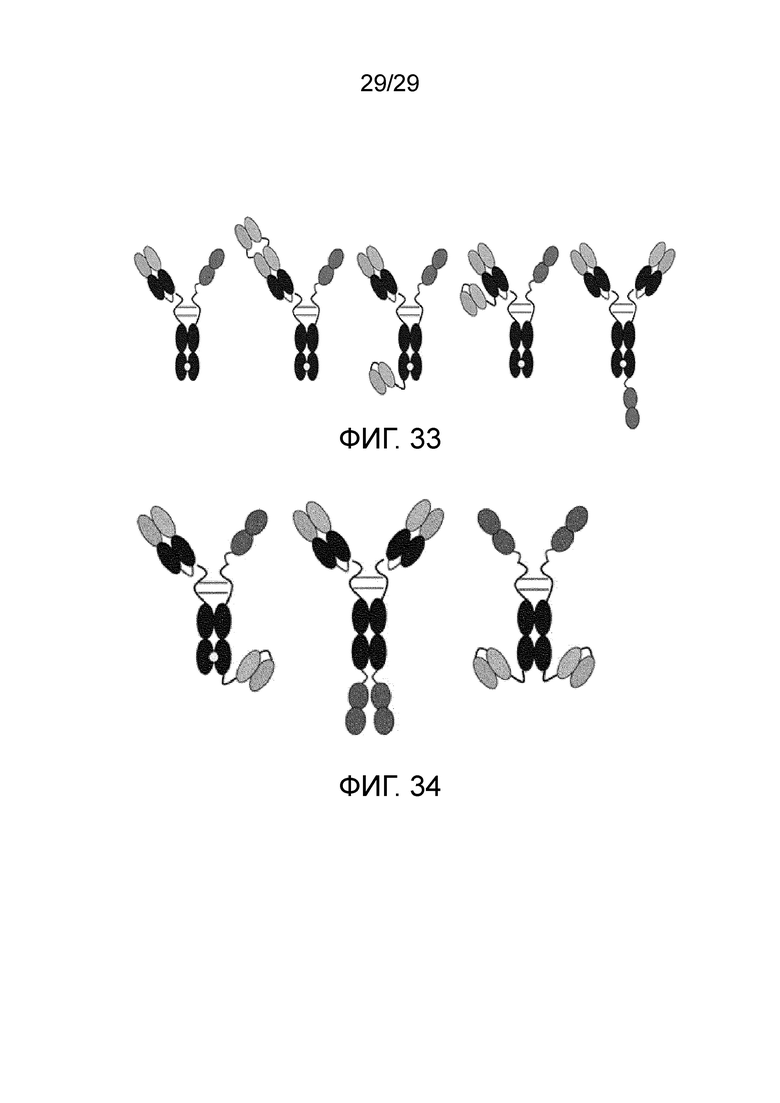
Изобретение относится к области биотехнологии. Предложены противораковый слитый белок и включающая его фармацевтическая композиция. Противораковый слитый белок содержит первый мономер, включающий вариант IL-12, и второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP. Также предложены полинуклеотиды, кодирующие слитый белок, векторы и трансформированные клетки для получения слитого белка. Слитый белок по изобретению обладает повышенной противоопухолевой активностью и может применяться для противоопухолевой терапии. 11 н. и 17 з.п. ф-лы, 34 ил., 12 табл., 6 пр.
1. Противораковый слитый белок, включающий:
первый мономер, включающий вариант IL-12; и
второй мономер, включающий антигенсвязывающий участок, который специфично связывается с FAP (белком активации фибробластов альфа),
где вариант IL-12 включает IL-12A (p35); и вариант IL-12B (p40), и
где вариант IL-12B (p40) содержит аминокислотную последовательность, включающую по меньшей мере одну замену, выбранную из группы, состоящей из K258A, K260A, K263A и K264A в аминокислотной последовательности SEQ ID NO: 74.
2. Слитый белок по п. 1, где вариант IL-12B (p40) включает аминокислотную последовательность, включающую замены K258A и K263A в аминокислотной последовательности SEQ ID NO: 74.
3. Слитый белок по п. 1, где вариант IL-12 включает следующую структурную формулу (I) или (II):
N'-Y-[линкер (1)]o-Z-C' (I),
N'-Z-[линкер (1)]o-Y-C' (II),
в структурных формулах (I) и (II)
N' представляет собой N-конец слитого белка,
C' представляет собой C-конец слитого белка,
Y представляет собой IL-12A,
Z представляет собой вариант IL-12B,
линкер (1) является пептидным линкером и
o равно 0 или 1.
4. Слитый белок по п. 1, где вариант IL-12B (p40) содержит аминокислотную последовательность, включающую замены K258A, K260A, K263A и K264A в аминокислотной последовательности SEQ ID NO: 74.
5. Слитый белок по п. 2, где вариант IL-12B (p40) содержит аминокислотную последовательность, включающую замены K258A и K263A и дополнительно включающую замену K260A или K264A в аминокислотной последовательности SEQ ID NO: 74.
6. Слитый белок по п. 1, где вариант IL-12B (p40) включает аминокислотную последовательность SEQ ID NO: 77 или SEQ ID NO: 79.
7. Слитый белок по п. 1, где IL-12A (p35) включает аминокислотную последовательность SEQ ID NO: 75 или SEQ ID NO: 87.
8. Слитый белок по п. 1, где вариант IL-12 включает аминокислотную последовательность SEQ ID NO: 76 или SEQ ID NO: 78.
9. Слитый белок по п. 1, где антигенсвязывающий участок, который специфично связывается с FAP, включает:
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 96, HCDR2 с SEQ ID NO: 97 и HCDR3 с SEQ ID NO: 98, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 99, LCDR2 с SEQ ID NO: 100 и LCDR3 с SEQ ID NO: 101;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 104, HCDR2 с SEQ ID NO: 105 и HCDR3 с SEQ ID NO: 106, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 107, LCDR2 с SEQ ID NO: 108 и LCDR3 с SEQ ID NO: 109;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 127, HCDR2 с SEQ ID NO: 128 и HCDR3 с SEQ ID NO: 129, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 130, LCDR2 с SEQ ID NO: 131 и LCDR3 с SEQ ID NO: 132;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 133, HCDR2 с SEQ ID NO: 134 и HCDR3 с SEQ ID NO: 135, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 136, LCDR2 с SEQ ID NO: 137 и LCDR3 с SEQ ID NO: 138;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 139, HCDR2 с SEQ ID NO: 140 и HCDR3 с SEQ ID NO: 141, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 142, LCDR2 с SEQ ID NO: 143 и LCDR3 с SEQ ID NO: 144;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 145, HCDR2 с SEQ ID NO: 146 и HCDR3 с SEQ ID NO: 147, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 148, LCDR2 с SEQ ID NO: 149 и LCDR3 с SEQ ID NO: 150;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 151, HCDR2 с SEQ ID NO: 152 и HCDR3 с SEQ ID NO: 153, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 154, LCDR2 с SEQ ID NO: 155 и LCDR3 с SEQ ID NO: 156;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 157, HCDR2 с SEQ ID NO: 158 и HCDR3 с SEQ ID NO: 159, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 160, LCDR2 с SEQ ID NO: 161 и LCDR3 с SEQ ID NO: 162;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 163, HCDR2 с SEQ ID NO: 164 и HCDR3 с SEQ ID NO: 165, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 166, LCDR2 с SEQ ID NO: 167 и LCDR3 с SEQ ID NO: 168;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 169, HCDR2 с SEQ ID NO: 170 и HCDR3 с SEQ ID NO: 171, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 172, LCDR2 с SEQ ID NO: 173 и LCDR3 с SEQ ID NO: 174;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 175, HCDR2 с SEQ ID NO: 176 и HCDR3 с SEQ ID NO: 177, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 178, LCDR2 с SEQ ID NO: 179 и LCDR3 с SEQ ID NO: 180;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 181, HCDR2 с SEQ ID NO: 182 и HCDR3 с SEQ ID NO: 183, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 184, LCDR2 с SEQ ID NO: 185 и LCDR3 с SEQ ID NO: 186;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 187, HCDR2 с SEQ ID NO: 188 и HCDR3 с SEQ ID NO: 189, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 190, LCDR2 с SEQ ID NO: 191 и LCDR3 с SEQ ID NO: 192;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 193, HCDR2 с SEQ ID NO: 194 и HCDR3 с SEQ ID NO: 195, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 196, LCDR2 с SEQ ID NO: 197 и LCDR3 с SEQ ID NO: 198;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 199, HCDR2 с SEQ ID NO: 200 и HCDR3 с SEQ ID NO: 201, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 202, LCDR2 с SEQ ID NO: 203 и LCDR3 с SEQ ID NO: 204;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 205, HCDR2 с SEQ ID NO: 206 и HCDR3 с SEQ ID NO: 207, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 208, LCDR2 с SEQ ID NO: 209 и LCDR3 с SEQ ID NO: 210;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 211, HCDR2 с SEQ ID NO: 212 и HCDR3 с SEQ ID NO: 213, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 214, LCDR2 с SEQ ID NO: 215 и LCDR3 с SEQ ID NO: 216;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 217, HCDR2 с SEQ ID NO: 218 и HCDR3 с SEQ ID NO: 219, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 220, LCDR2 с SEQ ID NO: 221 и LCDR3 с SEQ ID NO: 222;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 223, HCDR2 с SEQ ID NO: 224 и HCDR3 с SEQ ID NO: 225, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 226, LCDR2 с SEQ ID NO: 227 и LCDR3 с SEQ ID NO: 228;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 229, HCDR2 с SEQ ID NO: 230 и HCDR3 с SEQ ID NO: 231, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 232, LCDR2 с SEQ ID NO: 233 и LCDR3 с SEQ ID NO: 234;
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 235, HCDR2 с SEQ ID NO: 236 и HCDR3 с SEQ ID NO: 237, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 238, LCDR2 с SEQ ID NO: 239 и LCDR3 с SEQ ID NO: 240; или
вариабельную область тяжелой цепи, включающую HCDR1 с SEQ ID NO: 241, HCDR2 с SEQ ID NO: 242 и HCDR3 с SEQ ID NO: 243, и вариабельную область легкой цепи, включающую LCDR1 с SEQ ID NO: 244, LCDR2 с SEQ ID NO: 245 и LCDR3 с SEQ ID NO: 246.
10. Слитый белок по п. 1, где антигенсвязывающий участок, который специфично связывается с FAP, включает:
вариабельную область тяжелой цепи SEQ ID NO: 102 и вариабельную область легкой цепи SEQ ID NO: 103;
вариабельную область тяжелой цепи SEQ ID NO: 110 и вариабельную область легкой цепи SEQ ID NO: 111;
вариабельную область тяжелой цепи SEQ ID NO: 248 и вариабельную область легкой цепи SEQ ID NO: 249;
вариабельную область тяжелой цепи SEQ ID NO: 250 и вариабельную область легкой цепи SEQ ID NO: 251;
вариабельную область тяжелой цепи SEQ ID NO: 252 и вариабельную область легкой цепи SEQ ID NO: 253;
вариабельную область тяжелой цепи SEQ ID NO: 254 и вариабельную область легкой цепи SEQ ID NO: 255;
вариабельную область тяжелой цепи SEQ ID NO: 256 и вариабельную область легкой цепи SEQ ID NO: 257;
вариабельную область тяжелой цепи SEQ ID NO: 258 и вариабельную область легкой цепи SEQ ID NO: 259;
вариабельную область тяжелой цепи SEQ ID NO: 260 и вариабельную область легкой цепи SEQ ID NO: 261;
вариабельную область тяжелой цепи SEQ ID NO: 262 и вариабельную область легкой цепи SEQ ID NO: 263;
вариабельную область тяжелой цепи SEQ ID NO: 264 и вариабельную область легкой цепи SEQ ID NO: 265;
вариабельную область тяжелой цепи SEQ ID NO: 266 и вариабельную область легкой цепи SEQ ID NO: 267;
вариабельную область тяжелой цепи SEQ ID NO: 268 и вариабельную область легкой цепи SEQ ID NO: 269;
вариабельную область тяжелой цепи SEQ ID NO: 270 и вариабельную область легкой цепи SEQ ID NO: 271;
вариабельную область тяжелой цепи SEQ ID NO: 272 и вариабельную область легкой цепи SEQ ID NO: 273;
вариабельную область тяжелой цепи SEQ ID NO: 274 и вариабельную область легкой цепи SEQ ID NO: 275;
вариабельную область тяжелой цепи SEQ ID NO: 276 и вариабельную область легкой цепи SEQ ID NO: 277;
вариабельную область тяжелой цепи SEQ ID NO: 278 и вариабельную область легкой цепи SEQ ID NO: 279;
вариабельную область тяжелой цепи SEQ ID NO: 280 и вариабельную область легкой цепи SEQ ID NO: 281;
вариабельную область тяжелой цепи SEQ ID NO: 282 и вариабельную область легкой цепи SEQ ID NO: 283;
вариабельную область тяжелой цепи SEQ ID NO: 284 и вариабельную область легкой цепи SEQ ID NO: 285;
вариабельную область тяжелой цепи SEQ ID NO: 286 и вариабельную область легкой цепи SEQ ID NO: 287;
scFv SEQ ID NO: 72; или
scFv SEQ ID NO: 84.
11. Слитый белок по п. 3, где первый мономер дополнительно включает фрагмент Fc-области или его вариант.
12. Слитый белок по п. 3 или 11, где линкер включает линкер (G4S)n, где n является любым из целых чисел от 1 до 10.
13. Слитый белок по п. 11, где Fc-область первого мономера получена из IgG1 человека или IgG2a мыши.
14. Слитый белок по п. 11, где Fc первого мономера включает структуру выступа или структуру впадины.
15. Слитый белок по п. 1, где антигенсвязывающим участком, который специфично связывается с FAP, является Fab, scFv, Fv или их фрагмент.
16. Слитый белок по п. 1, где второй мономер включает тяжелую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 102, и легкую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 103; или тяжелую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 110, и легкую цепь, состоящую из аминокислотной последовательности SEQ ID NO: 111.
17. Слитый белок по п. 1, где Fc второго мономера включает структуру выступа или структуру впадины.
18. Фармацевтическая композиция для предупреждения или лечения рака, включающая слитый белок по любому из пп. 1-17 в качестве активного ингредиента.
19. Фармацевтическая композиция по п. 18, где рак является любым, выбранным из группы, состоящей из рака желудка, рака печени, рака легкого, рака толстой и прямой кишки, рака молочной железы, рака предстательной железы, рака кожи, рака кости, множественной миеломы, глиомы, рака яичника, рака поджелудочной железы, рака шейки матки, рака щитовидной железы, рака гортани, острого миелоидного лейкоза, хронического миелоидного лейкоза, острого лимфобластного лейкоза, хронического лимфобластного лейкоза, опухоли головного мозга, нейробластомы, ретинобластомы, рака головы и шеи, рака слюнных желез и лимфомы.
20. Полинуклеотид, кодирующий первый мономер, содержащий вариант IL-12,
где вариант IL-12 содержит IL-12A (p35); и вариант IL-12B (p40), и
при этом вариант IL-12B (p40) содержит аминокислотную последовательность, включающую по меньшей мере одну замену, выбранную из группы, состоящей из K258A, K260A, K263A и K264A в аминокислотной последовательности SEQ ID NO: 74.
21. Вектор для получения слитого белка по п. 1, включающий полинуклеотид по п. 20.
22. Полинуклеотид, кодирующий слитый белок по п. 1.
23. Вектор для получения слитого белка по п. 1, включающий полинуклеотид по п. 22.
24. Трансформированная клетка для получения слитого белка по п. 1, в которую был введен вектор по п. 23.
25. Способ получения слитого белка, включающий:
i) культивирование трансформированной клетки по п. 24; и
ii) выделение слитого белка по п. 1.
26. Способ лечения или предупреждения рака, включающий введение субъекту слитого белка по любому из пп. 1-17.
27. Применение слитого белка по любому из пп. 1-17 для лечения рака.
28. Применение слитого белка по любому из пп. 1-17 для производства лекарственного средства для лечения рака.
| P | |||
| MURER, NERI D., Antibody-cytokine fusion proteins: A novel class of biopharmaceuticals for the therapy of cancer and of chronic inflammation, New Biotechnology, 2019, Volume 52, pp.42-53 | |||
| ROLAND E | |||
| KONTERMANN, Antibody-cytokine fusion proteins, Archives of Biochemistry and Biophysics, 2012, Volume 526, Issue 2, Pages 194-205 | |||
| US 2012276125 A1, |
Авторы
Даты
2024-12-11—Публикация
2021-08-10—Подача